10x пространствен транскриптом на Genomics Visium
Предимства на услугата
1) Услугата на едно гише интегрира всички стъпки, базирани на опит и умения, включително крио-секция,HE оцветяване, тъканна оптимизация, пространствено баркодиране, подготовка на библиотека, секвениране и биоинформатика
2) Висококвалифицирана техническа група с опит в над 250 вида тъкани, 50+ вида, включително хора, мишки, бозайници, риби и растения
3) Актуализация в реално време на целия проект с пълен контрол върху експерименталния напредък
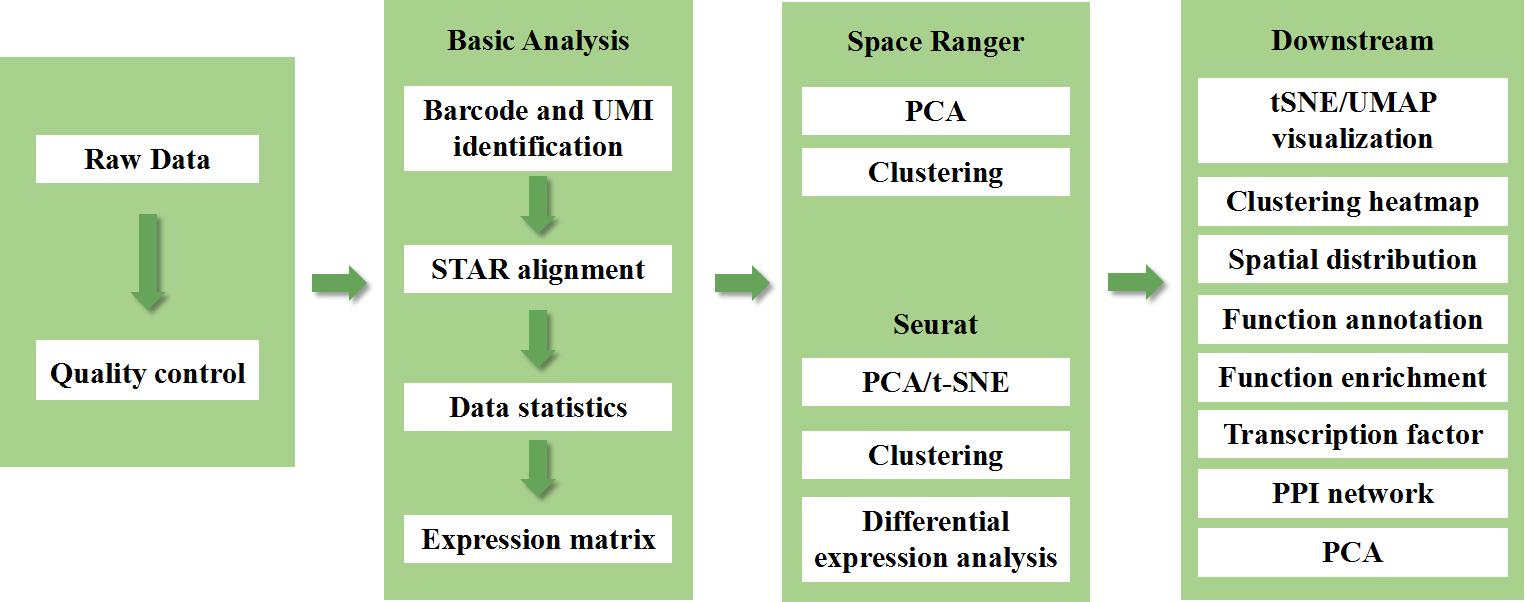
4) Изчерпателен стандартен биоинформатичен пакет с 29 анализа, 100+ висококачествени цифри
5) Персонализиран анализ на данни и визуализация, налични за различни заявки за изследванеs
Сервизни спецификации
| Библиотека | Стратегия за последователност | Препоръчителни данни | Примерни изисквания |
| 10X Visium cDNA библиотека | 10x Visium-Illumina PE150 | 60 Gb/проба | OCT вградени крио проби; FFPE проби (Оптимален диаметър: приблизително 6x6x6 mm3) |
За повече подробности относно насоките за подготовка на проби и работния процес на обслужване, моля, не се колебайте да говорите с aBMKGENE експерт
Работен поток на услугата

Дизайн на експеримента

Доставка на мостри

Предварителен експеримент
Пространствено баркодиране

Изграждане на библиотека

Секвениране

Анализ на данни

Следпродажбени услуги
1)Контрол на качеството на данните
Извеждане на данни и разпределение на резултата за качество
Откриване на ген на място
Покритие на тъканите
2)Анализ на вътрешна извадка
Откриване на ген
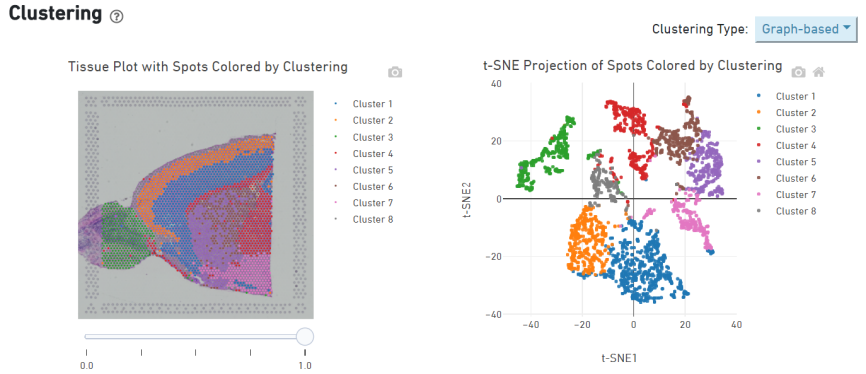
Групиране на място
Диференциален анализ между клъстери
3)Междугрупов анализ
Комбинация от данни
Точково групиране на съвместни данни
Диференциален анализ между групите
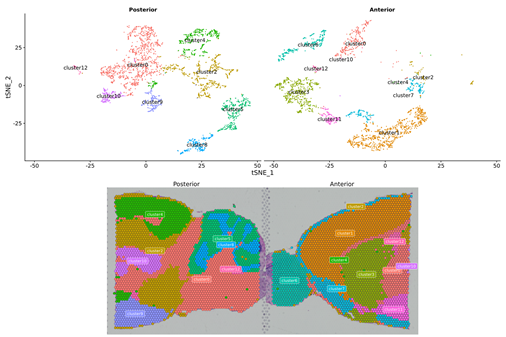
1.Клъстериране на място
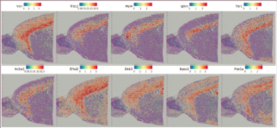
 2.Пространствено разпределениена маркерни гени
2.Пространствено разпределениена маркерни гени
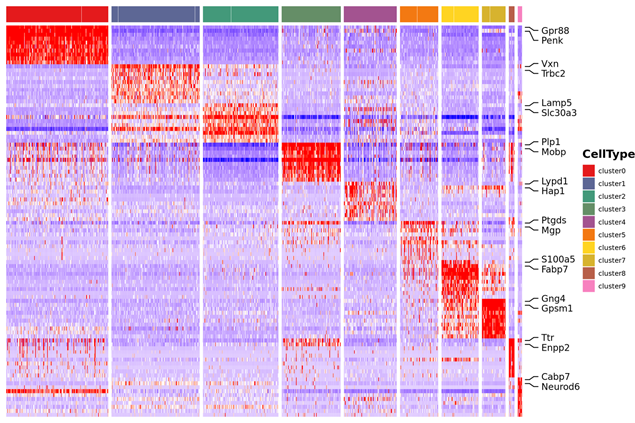
 3. Топлинна карта за клъстериране на изобилие на израз на маркер
3. Топлинна карта за клъстериране на изобилие на израз на маркер
 4. Анализ на данните между извадките
4. Анализ на данните между извадките