Секвениране на бисулфит с намалено представяне (RRBS)
Сервизни спецификации
Платформа: платформа NovaSeq, PE150
Тип библиотека: 200-400 bp вложка, третирана с бисулфит ДНК библиотека
Стратегия за секвениране: Paired-End 150 bp
Препоръчителен изход на данни: 10 Gb необработени данни/извадка
Примерни изисквания
Количество на ДНК: ≥ 2ug
ДНК концентрация:≥ 20ng/μl.
Чистота: OD260/280 = 1,8 до 2,0 без разграждане или замърсяване с РНК
Биоинформатичен анализ
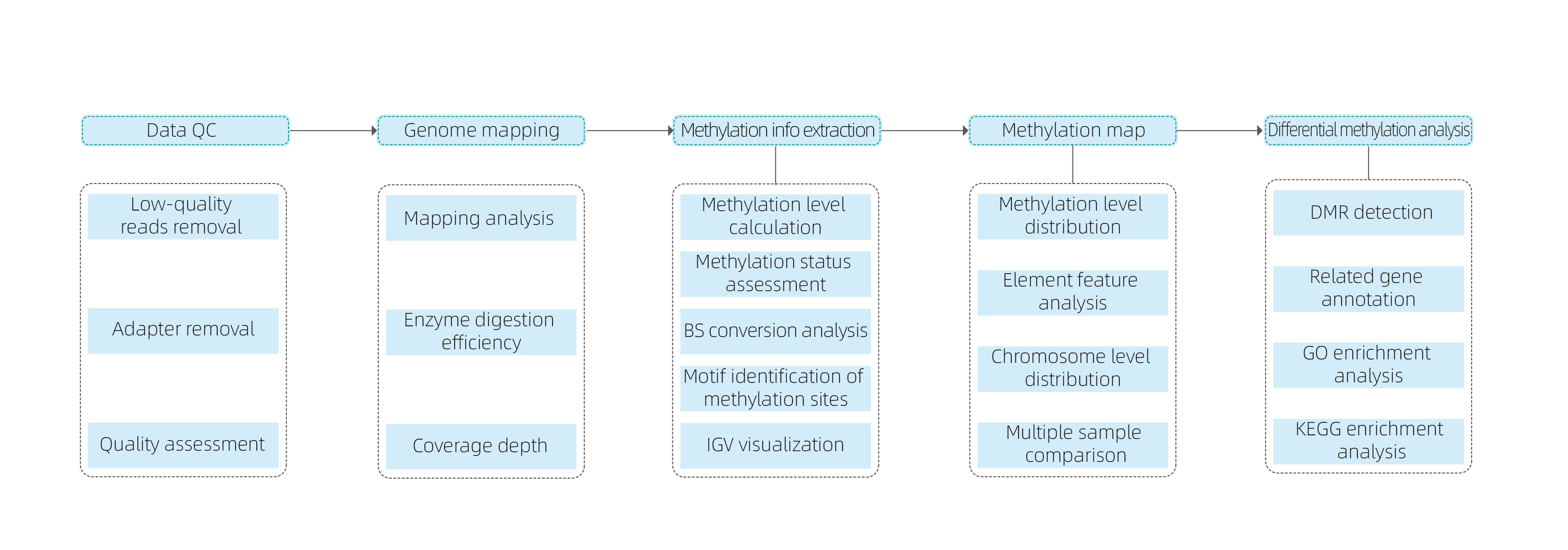
Работен поток на услугата

Доставка на мостри

Изграждане на библиотека

Секвениране

Анализ на данни
Следпродажбени услуги
a.Референтна статистика за подравняване на генома
Статистика на четенията на картографиране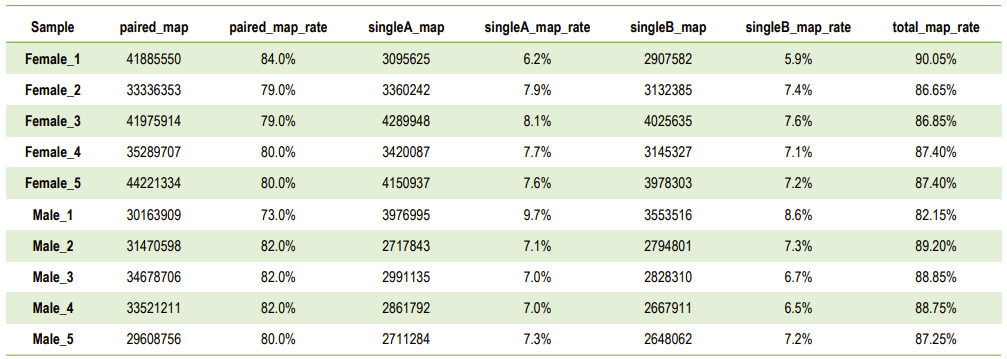
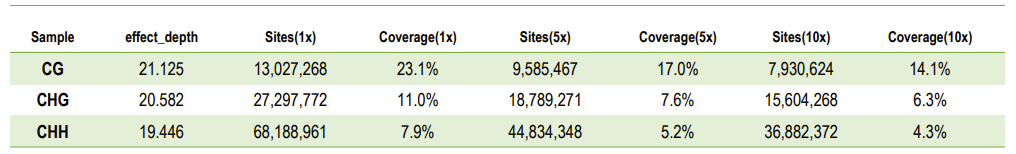
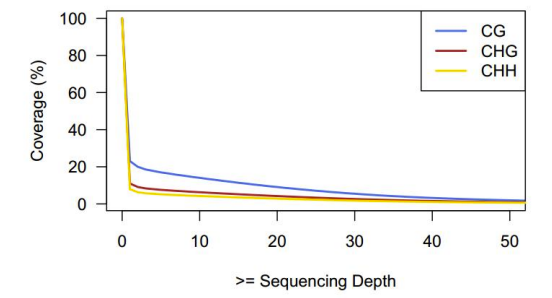
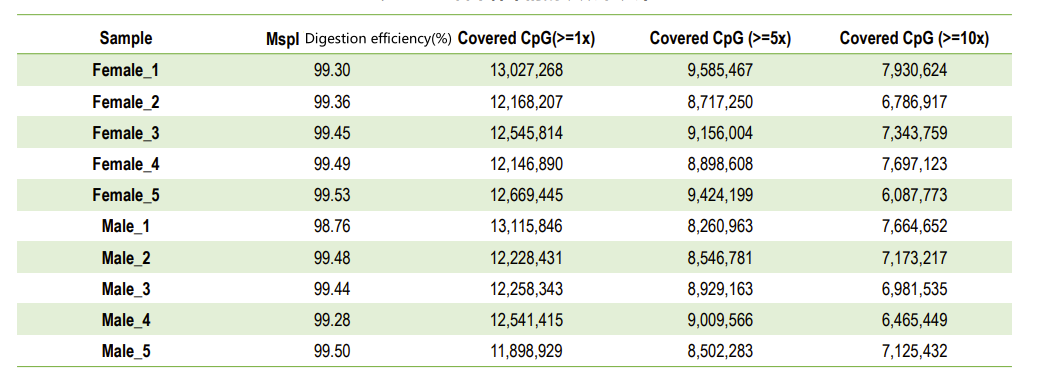
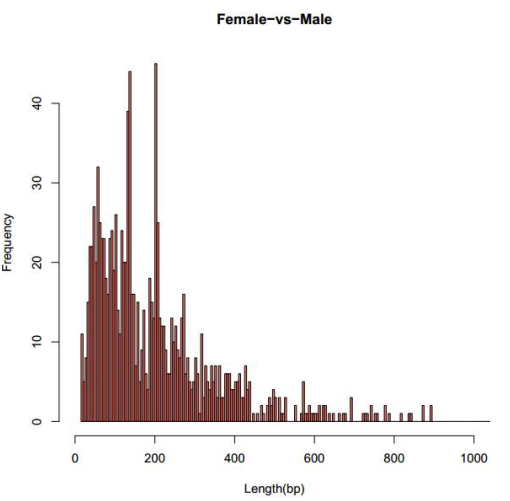
Sстатистика на дълбочината на секвениране и покритието на C сайта
Aнатрупано покритие
Dефективност на усвояване на всяка проба
b.Откриване на място на метилиране
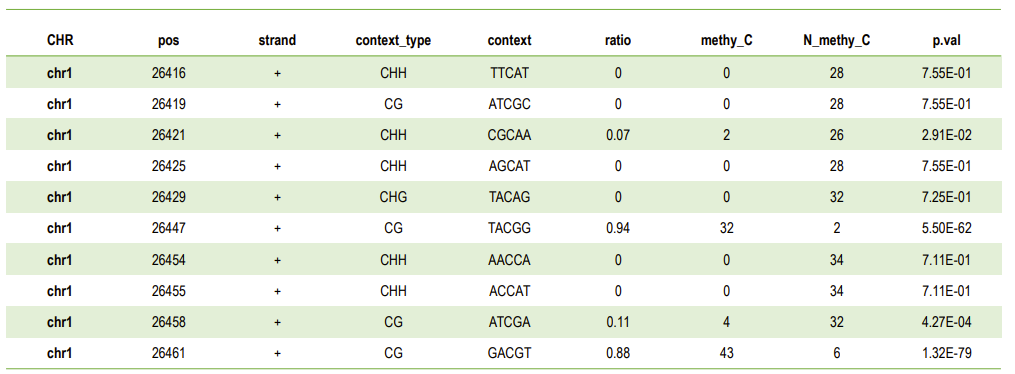
Списък на нивата на метилиране в С място
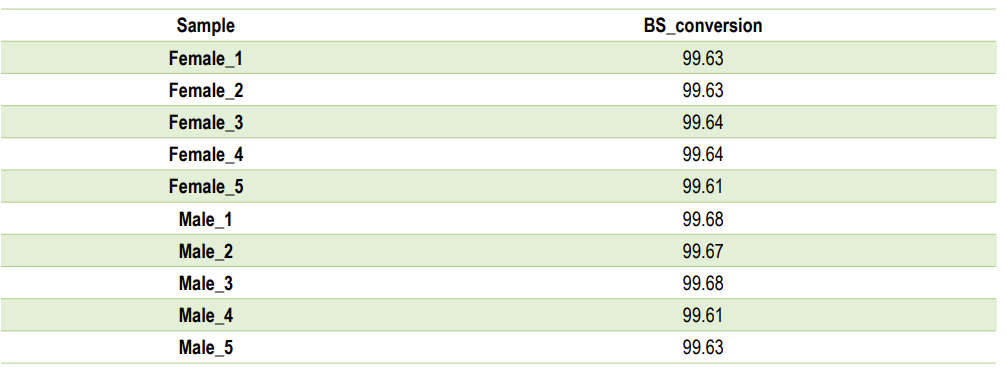
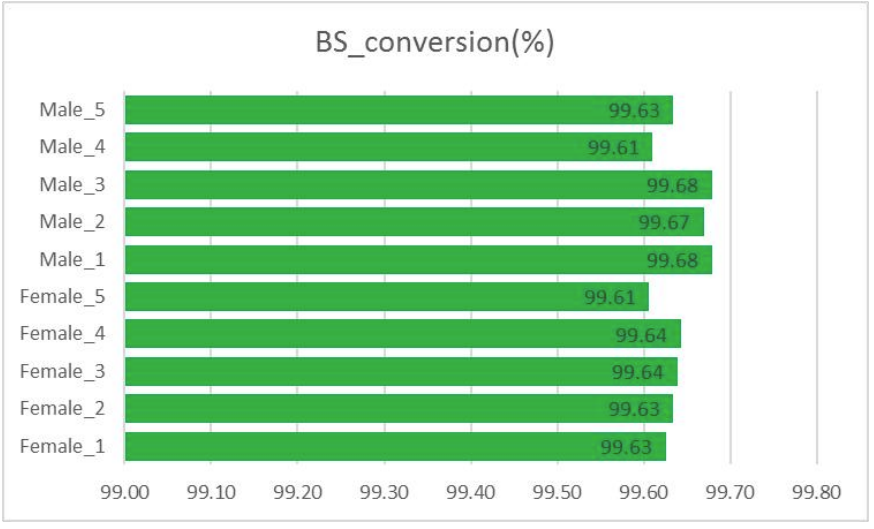
BS преобразуване
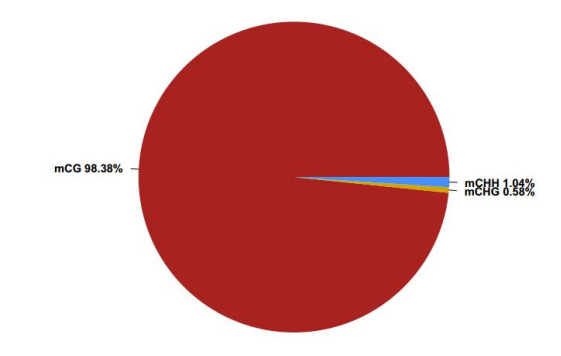
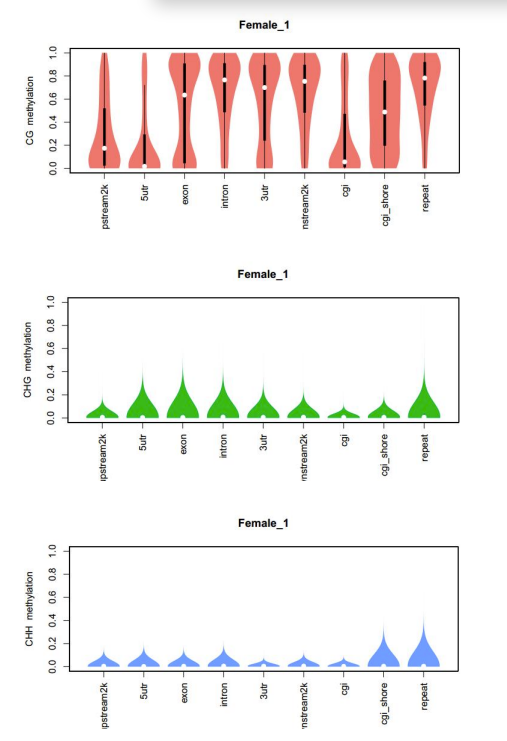
Разпределение на нивото на метилиране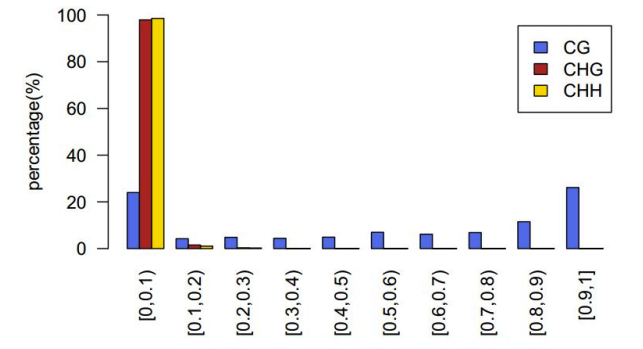
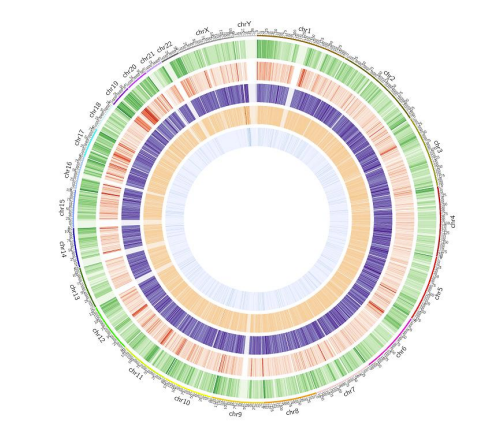
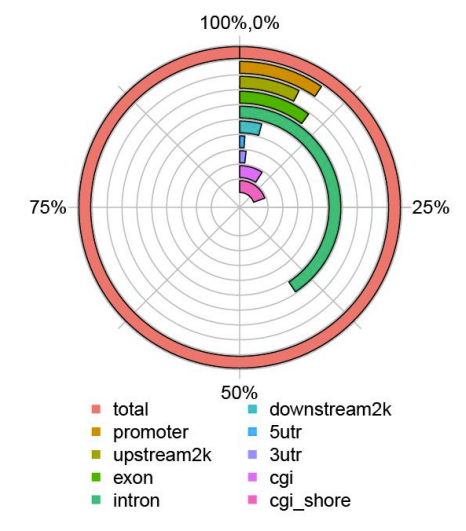
c.Карта на метилиране
Genome елемент
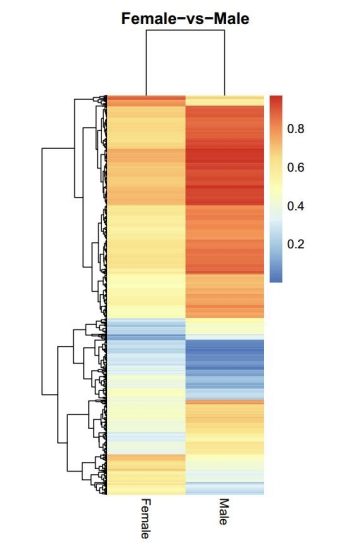
d.Сравнение на нивата на метилиране между пробите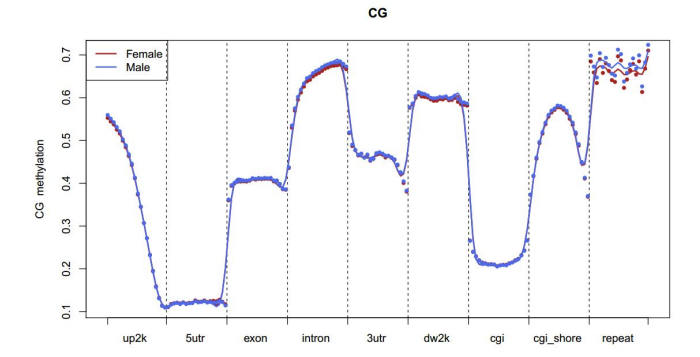
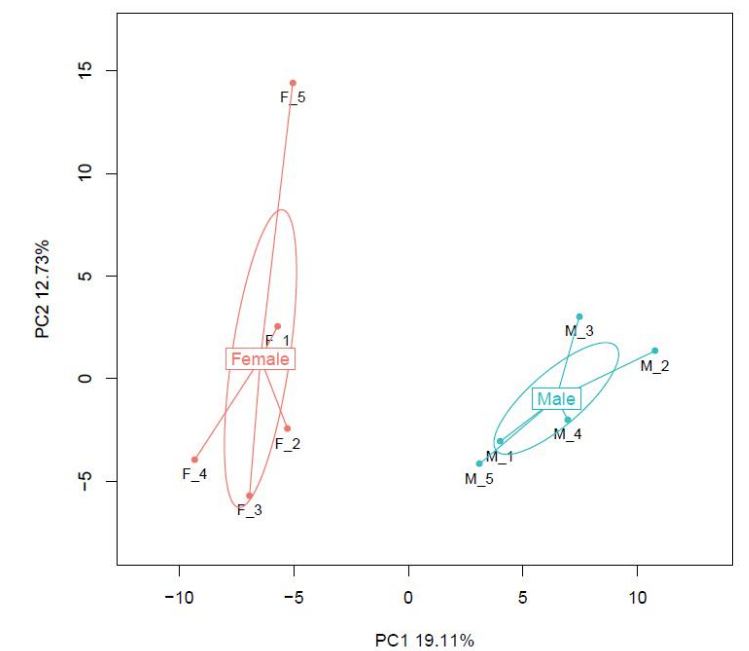
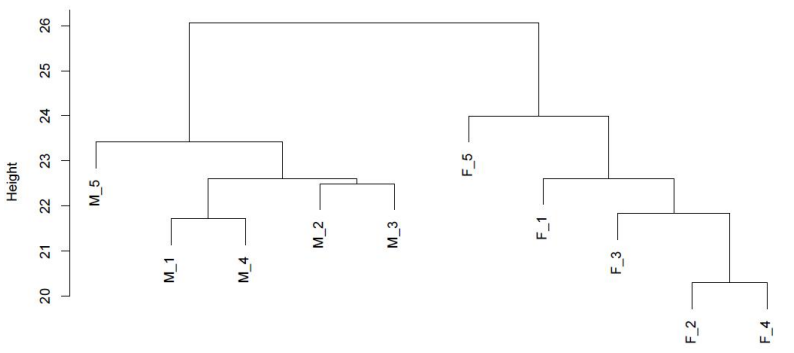
PAirwise Корелация на CG метилиране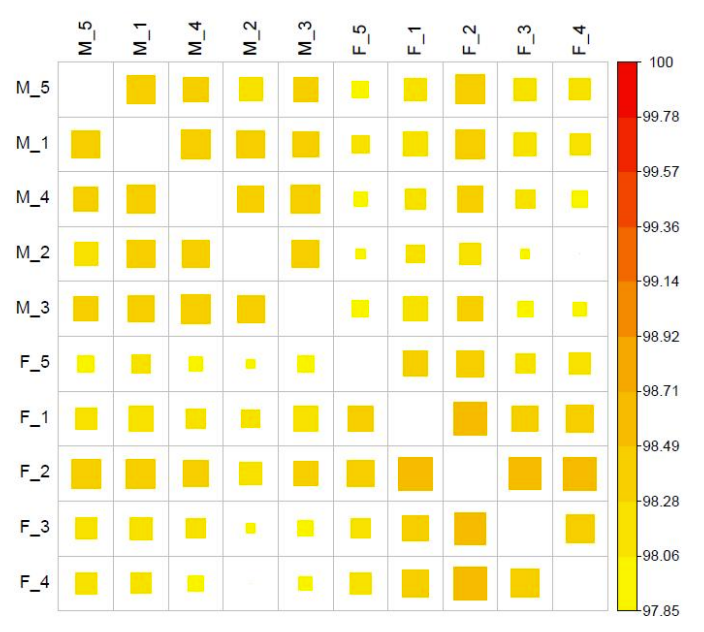
d.Диференциален анализ на метилиране
Sстатистика на DMR