Analisi di l'Associazione Genome-wide
1.Service Vantaghji
● Casi di Prughjettu Abundanti: dapoi u so stabilimentu in u 2009, BMKGENE hà cumpletu centinaie di prughjetti di spezie in a ricerca di a pupulazione GWAS, hà assistitu i ricercatori à publicà più di 100 articuli, è u fattore d'impattu cumulativu hà righjuntu 500.
● Analisti prufessiunali.
● Cortu ciclu di analisi.
● minazione di dati precisa.
2. Specificazioni di serviziu
| Tipu | Scala di pupulazione | Strategia di sequenza è prufundità |
| SLAF-GWAS | numeru di campionu ≥200 | Taglia di u genoma <400M, cù genoma ref, WGS hè cunsigliatu |
| Size Genome ≤ 1G, 100K Tags è 10X | ||
| 1G ≤ dimensione di u genoma ≤ 2G, 200K Tags è 10X | ||
| Size Genome> 2G, 300K Tags è 10X | ||
| WGS-GWAS | numeru di campionu ≥200 | 10X per ogni mostra |
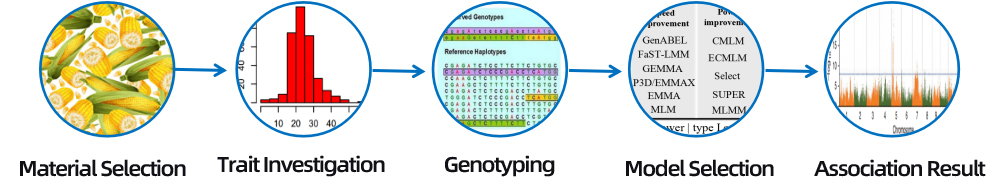
3. Selezzione di materiale



Diverse varietà, sottospecie, razze di terra / genebanks / famiglie miste / risorse salvatichi
Diversi variità, sottospecie, razze di terra
Famiglia mezza fratellanza / famiglia piena di frati / risorse salvatichi
4. Analisi Bioinformation
● Analisi di l'associu genomu
● Analisi è screening di SNP significativu
● Annotazione funzionale di u genu candidatu
5. Flussu di travagliu di serviziu

Prughjettu di cuncepimentu

Consegna di mostra

estrazione di RNA

Custruzzione di biblioteca

Sequencing

Analisi di dati

Servizi post-vendita
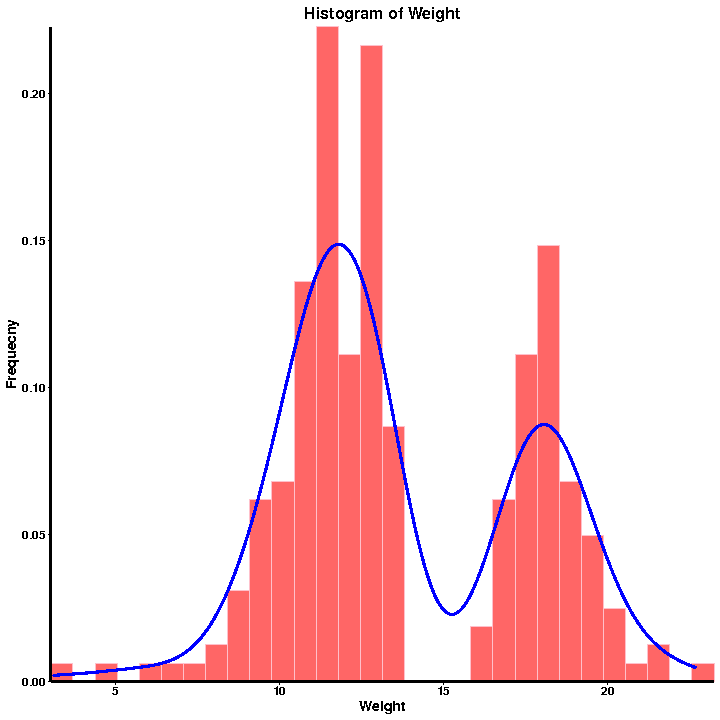
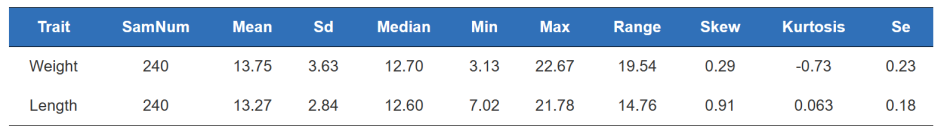
a.Fenotipu QC
Histogramma di distribuzione di freccia
statistiche di fenotipu
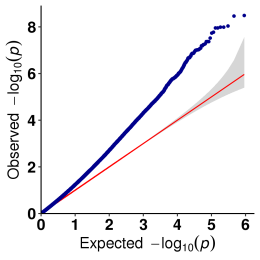
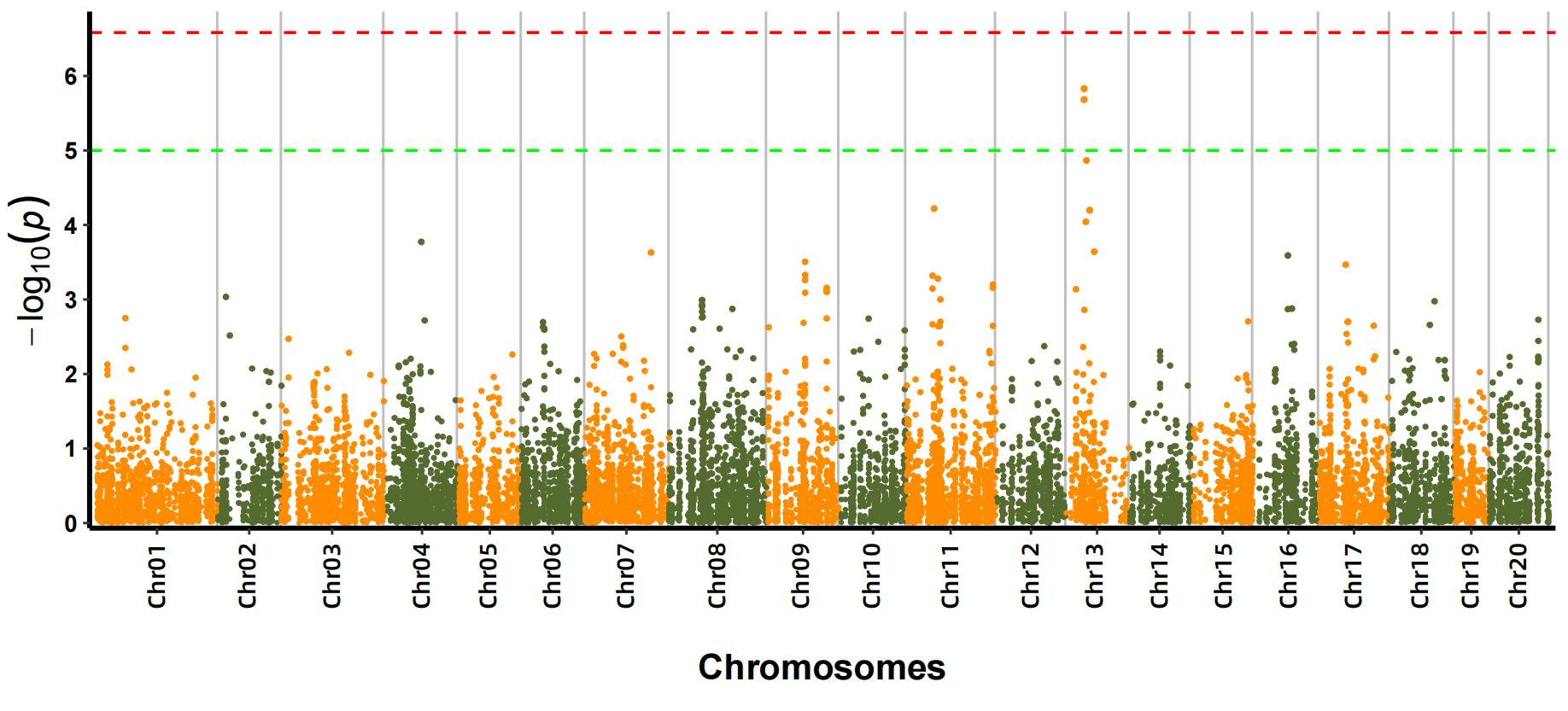
b.Analisi di l'associazione (Model: GEMMA, FaST-LMM, EMMAX)
Trama QQ
Trama di Manhattan
| Annu | Journal | IF | Titulu |
| 2022 | NC | 17.69 | Base génomique des giga-chromosomes et giga-génomes de la pivoine arborescente Paeonia ostii |
| 2015 | NP | 7.43 | L'impronte di domesticazione ancoranu e regioni genomiche d'impurtanza agronomica in a soia |
| 2018 | MP | 9.32 | A resequenza di u genoma sanu di una cullizzioni mundiale di accessioni di colza revela a basa genetica di a so divergenza di l'ecotipu |
| 2022 | HR | 7.29 | L'analisi di l'associazione di u genoma furnisce una visione moleculare di a variazione naturale di a dimensione di a semente di anguria |