
Sekvenování mRNA plné délky - PacBio
Výhody služby
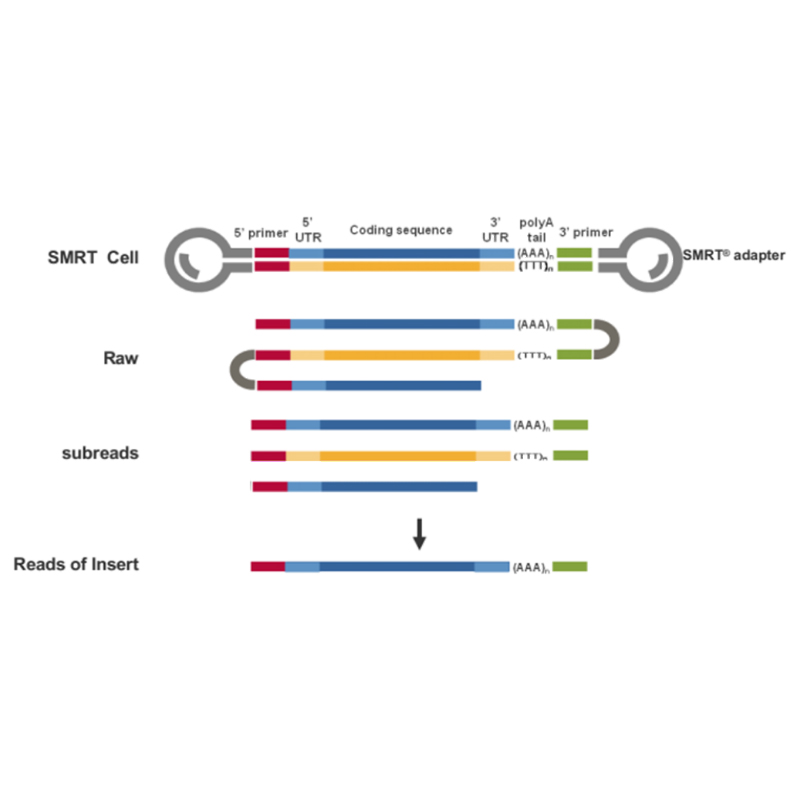
● Přímé čtení molekuly cDNA plné délky od 3'- konce k 5'- konci
● Rozlišení na úrovni isoformy ve struktuře sekvence
● Přepisy s vysokou přesností a integritou
● Vysoce kompatibilní s různými druhy
● Velká sekvenační kapacita se 4 vybavenými sekvenačními platformami PacBio Sequel II
● Zkušenosti s více než 700 projekty sekvenování RNA na bázi Pacbio
● Doručování výsledků na bázi BMKCloud: Na platformě je k dispozici přizpůsobené dolování dat.
● Poprodejní služby platné 3 měsíce po dokončení projektu
Specifikace služby
Platforma: PacBio Sequel II
Sekvenační knihovna: mRNA knihovna obohacená o Poly A
Doporučený datový výtěžek: 20 Gb/vzorek (v závislosti na druhu)
FLNC(%)): ≥75 %
*FLNC: Nechimérické transcipty plné délky
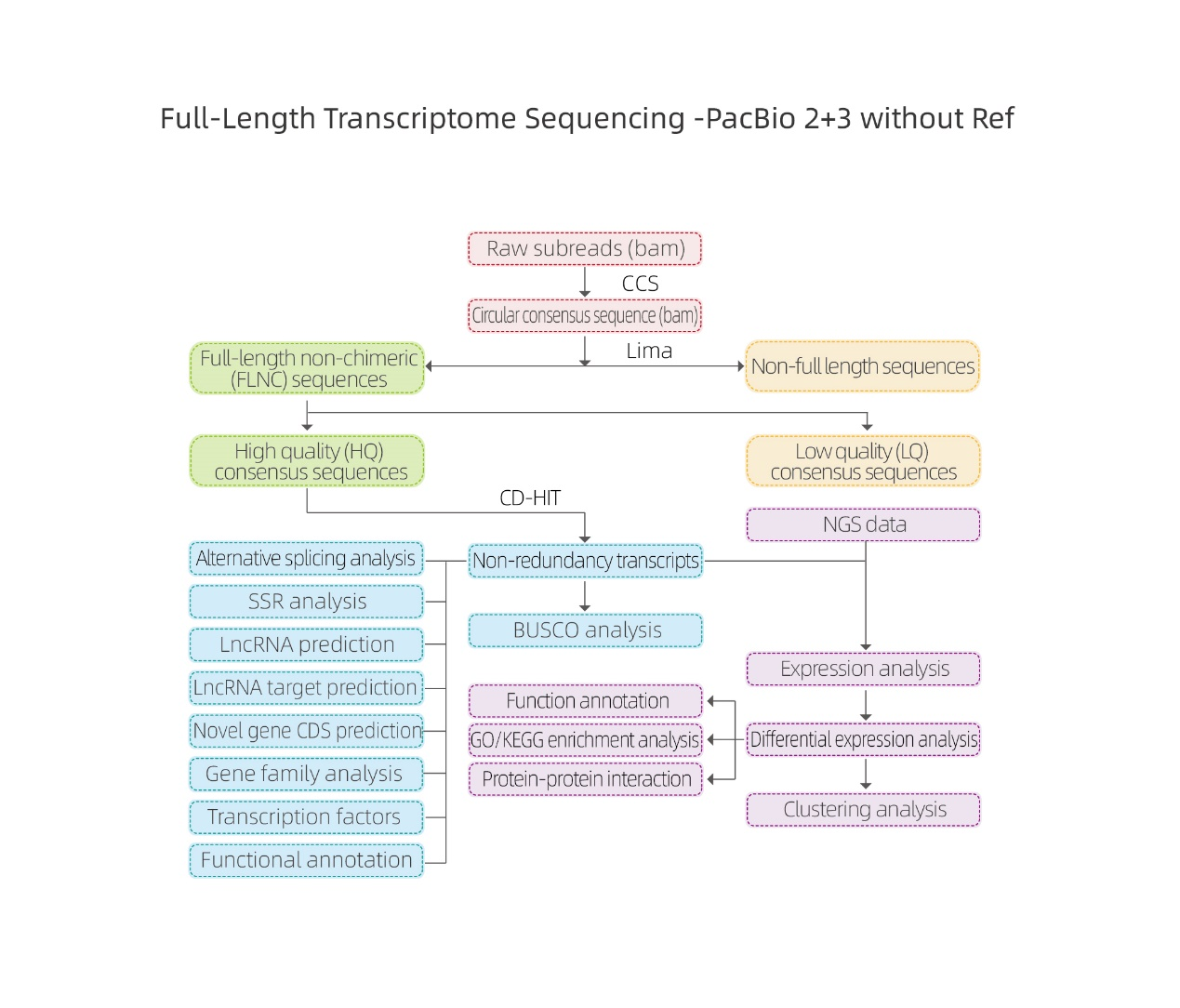
Bioinformatické analýzy
● Zpracování nezpracovaných dat
● Identifikace přepisu
● Struktura sekvence
● Kvantifikace výrazů
● Anotace funkce
Vzorové požadavky a dodání
Vzorové požadavky:
Nukleotidy:
| Konc. (ng/μl) | množství (μg) | Čistota | Integrita |
| ≥ 120 | ≥ 0,6 | OD260/280 = 1,7-2,5 OD260/230=0,5-2,5 Omezená nebo žádná kontaminace proteiny nebo DNA na gelu. | Pro rostliny: RIN≥7,5; Pro zvířata: RIN≥8,0; 5,0≥ 28S/18S≥1,0; omezená nebo žádná základní elevace |
Tkáň: Hmotnost (suchá):≥1 g
*Pro tkáň menší než 5 mg doporučujeme odeslat bleskově zmrazený (v tekutém dusíku) vzorek tkáně.
Buněčná suspenze:Počet buněk = 3×106- 1×107
*Doporučujeme zasílat zmrazený buněčný lyzát.V případě, že počet buněk je menší než 5×105, doporučuje se bleskově zmrazit v tekutém dusíku, což je vhodnější pro mikroextrakce.
Vzorky krve:Objem ≥1 ml
Mikroorganismus:Hmotnost ≥ 1 g
Doporučené doručení vzorku
Kontejner:
2 ml centrifugační zkumavka (nedoporučuje se cínová fólie)
Označení vzorků: Skupina+replikace např. A1, A2, A3;B1, B2, B3......
Náklad:
1. Suchý led: Vzorky je třeba zabalit do sáčků a zahrabat do suchého ledu.
2. Zkumavky RNAstable: Vzorky RNA lze sušit ve zkumavce pro stabilizaci RNA (např. RNAstable®) a přepravovat při pokojové teplotě.
Tok servisní práce

Návrh experimentu

Vzorová dodávka

Extrakce RNA

Stavba knihovny

Sekvenování

Analýza dat

Poprodejní služby
1.FLNC rozdělení délek
Délka nechimérického čtení o plné délce (FLNC) udává délku cDNA v konstrukci knihovny.Distribuce délek FLNC je klíčovým ukazatelem při hodnocení kvality výstavby knihovny.
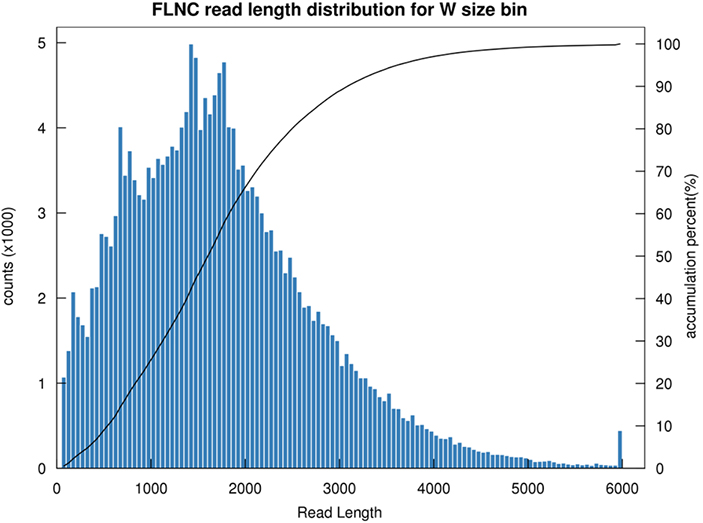
Distribuce délky čtení FLNC
2. Kompletní distribuce délky oblasti ORF
TransDecoder používáme k predikci oblastí kódujících protein a odpovídajících aminokyselinových sekvencí k vytvoření unigenových sad, které obsahují kompletní neredundantní transkriptové informace ve všech vzorcích.
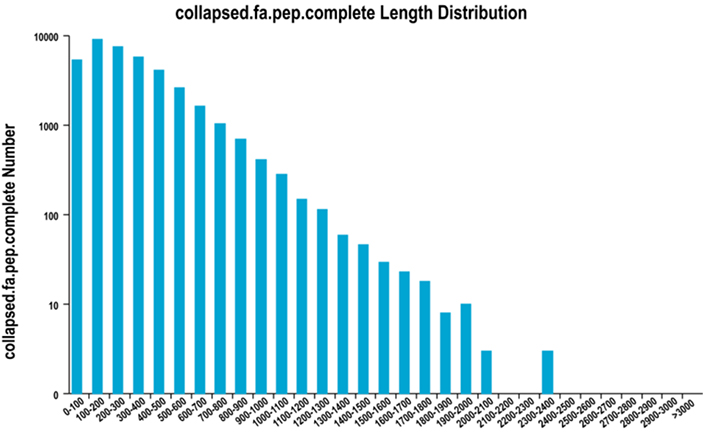
Kompletní distribuce délky oblasti ORF
3. Analýza obohacení KEGG dráhy
Diferenciálně exprimované transkripty (DET) mohou být identifikovány porovnáním dat sekvenování RNA na bázi NGS na souborech transkriptů plné délky generovaných daty sekvenování PacBio.Tyto DET lze dále zpracovat pro různé funkční analýzy, např. analýzu obohacení KEGG dráhy.
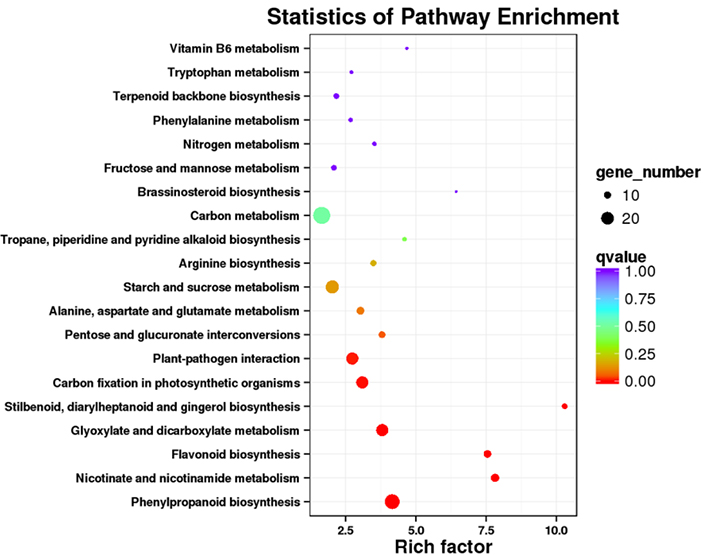
Obohacení dráhy DET KEGG -Dot plot
Pouzdro BMK
Vývojová dynamika transkriptomu kmene Populus
Publikováno: Plant Biotechnology Journal, 2019
Strategie sekvenování:
Kolekce vzorků:kmenové oblasti: vrchol, první internodium (IN1), druhé internodium (IN2), třetí internodium (IN3), internodium (IN4) a internodium (IN5) od Nanlin895
NGS sekvence:RNA 15 jedinců byla spojena jako jeden biologický vzorek.Tři biologické replikáty každého bodu byly zpracovány pro NGS sekvenci
Sekvence TGS:Kmenové oblasti byly rozděleny do tří oblastí, tj. apex, IN1-IN3 a IN4-IN5.Každá oblast byla zpracována pro sekvenování PacBio se čtyřmi typy knihoven: 0-1 kb, 1-2 kb, 2-3 kb a 3-10 kb.
Klíčové výsledky
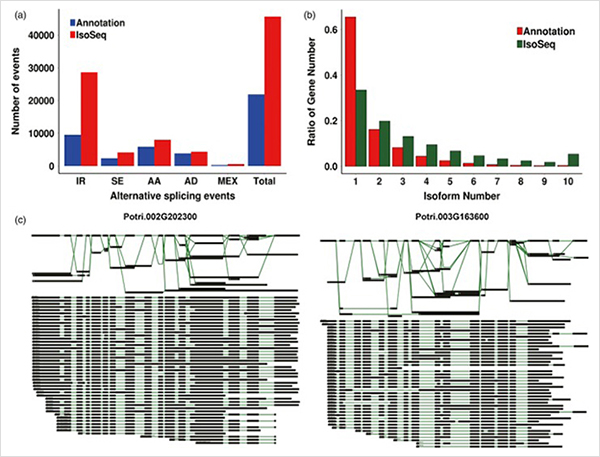
1. Celkem bylo identifikováno 87150 transkriptů plné délky, ve kterých bylo identifikováno 2081 nových isoforem a 62058 nových alternativních sestřižených isoforem.
Bylo identifikováno 2,1187 lncRNA a 356 fúzních genů.
3. Od primárního růstu k sekundárnímu růstu bylo identifikováno 15838 odlišně exprimovaných transkriptů z 995 odlišně exprimovaných genů.Ve všech DEG bylo 1216 transkripčních faktorů, z nichž většina dosud nebyla popsána.
4. Analýza obohacení GO odhalila význam buněčného dělení a oxidačně-redukčního procesu v primárním a sekundárním růstu.
Alternativní sestřihové události a různé izoformy
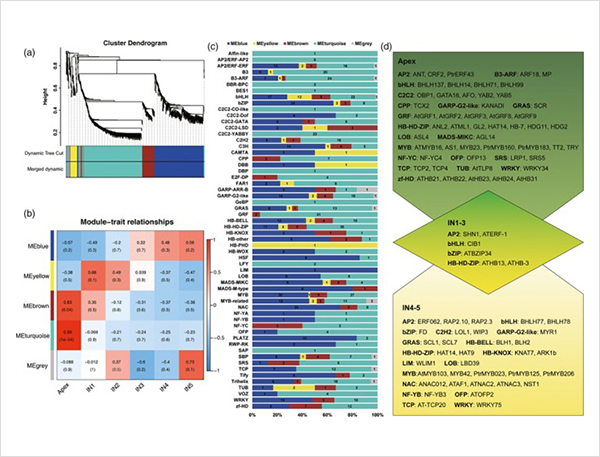
WGCNA analýza transkripčních faktorů
Odkaz
Chao Q, Gao ZF, Zhang D a kol.Vývojová dynamika transkriptomu kmene Populus.Plant Biotechnol J. 2019;17(1):206-219.doi:10.1111/pbi.12958











