Kleine RNA-Sequenzierung – Illumina
Merkmale
● Größenauswahl der RNA vor der Bibliotheksvorbereitung
● Bioinformatische Analyse mit Schwerpunkt auf der miRNA-Vorhersage und ihren Zielen
Servicevorteile
●Umfassende bioinformatische Analyse:Ermöglicht die Identifizierung bekannter und neuer miRNAs, die Identifizierung von miRNA-Zielen und die entsprechende funktionelle Annotation und Anreicherung mit mehreren Datenbanken (KEGG, GO)
●Strenge Qualitätskontrolle: Wir implementieren zentrale Kontrollpunkte in allen Phasen, von der Proben- und Bibliotheksvorbereitung bis hin zur Sequenzierung und Bioinformatik.Diese sorgfältige Überwachung gewährleistet die Lieferung gleichbleibend hochwertiger Ergebnisse.
●Post-Sales-Support: Unser Engagement geht über den Projektabschluss hinaus und umfasst einen 3-monatigen Kundendienstzeitraum.Während dieser Zeit bieten wir Projektnachverfolgung, Unterstützung bei der Fehlerbehebung und Frage-und-Antwort-Sitzungen an, um alle Fragen zu den Ergebnissen zu beantworten.
●Umfangreiches Fachwissen: Mit einer Erfolgsbilanz beim erfolgreichen Abschluss mehrerer sRNA-Projekte, die über 100 Arten in verschiedenen Forschungsbereichen abdecken, bringt unser Team einen großen Erfahrungsschatz in jedes Projekt ein.
Musteranforderungen und Lieferung
| Bibliothek | Plattform | Empfohlene Daten | Daten-QC |
| Größe ausgewählt | Illumina SE50 | 10–20 Mio. Lesungen | Q30≥85 % |
Probenanforderungen:
Nukleotide:
| Konz. (ng/μl) | Menge (μg) | Reinheit | Integrität |
| ≥ 80 | ≥ 0,5 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Begrenzte oder keine Protein- oder DNA-Kontamination auf dem Gel sichtbar. | RIN≥6,5; 5,0≥28S/18S≥1,0; begrenzte oder keine Grundlinienhöhe |
● Pflanzen:
Wurzel, Stamm oder Blütenblatt: 450 mg
Blatt oder Samen: 300 mg
Frucht: 1,2 g
● Tier:
Herz oder Darm: 450 mg
Eingeweide oder Gehirn: 240 mg
Muskel: 600 mg
Knochen, Haare oder Haut: 1,5 g
● Arthropoden:
Insekten: 9g
Krebstiere: 450 mg
● Vollblut: 2 Röhren
● Zellen: 106 Zellen
● Serum und Plasma:6 ml
Empfohlene Musterlieferung
Container:
2 ml Zentrifugenröhrchen (Alufolie wird nicht empfohlen)
Probenbeschriftung: Gruppe+Replikation, z. B. A1, A2, A3;B1, B2, B3... ...
Sendung:
1. Trockeneis: Proben müssen in Beutel verpackt und in Trockeneis vergraben werden.
2.RNAstable-Röhrchen: RNA-Proben können in RNA-Stabilisierungsröhrchen (z. B. RNAstable®) getrocknet und bei Raumtemperatur versendet werden.
Service-Workflow

Experimentdesign

Musterlieferung

RNA-Extraktion

Bibliotheksbau

Sequenzierung

Datenanalyse

Kundendienst
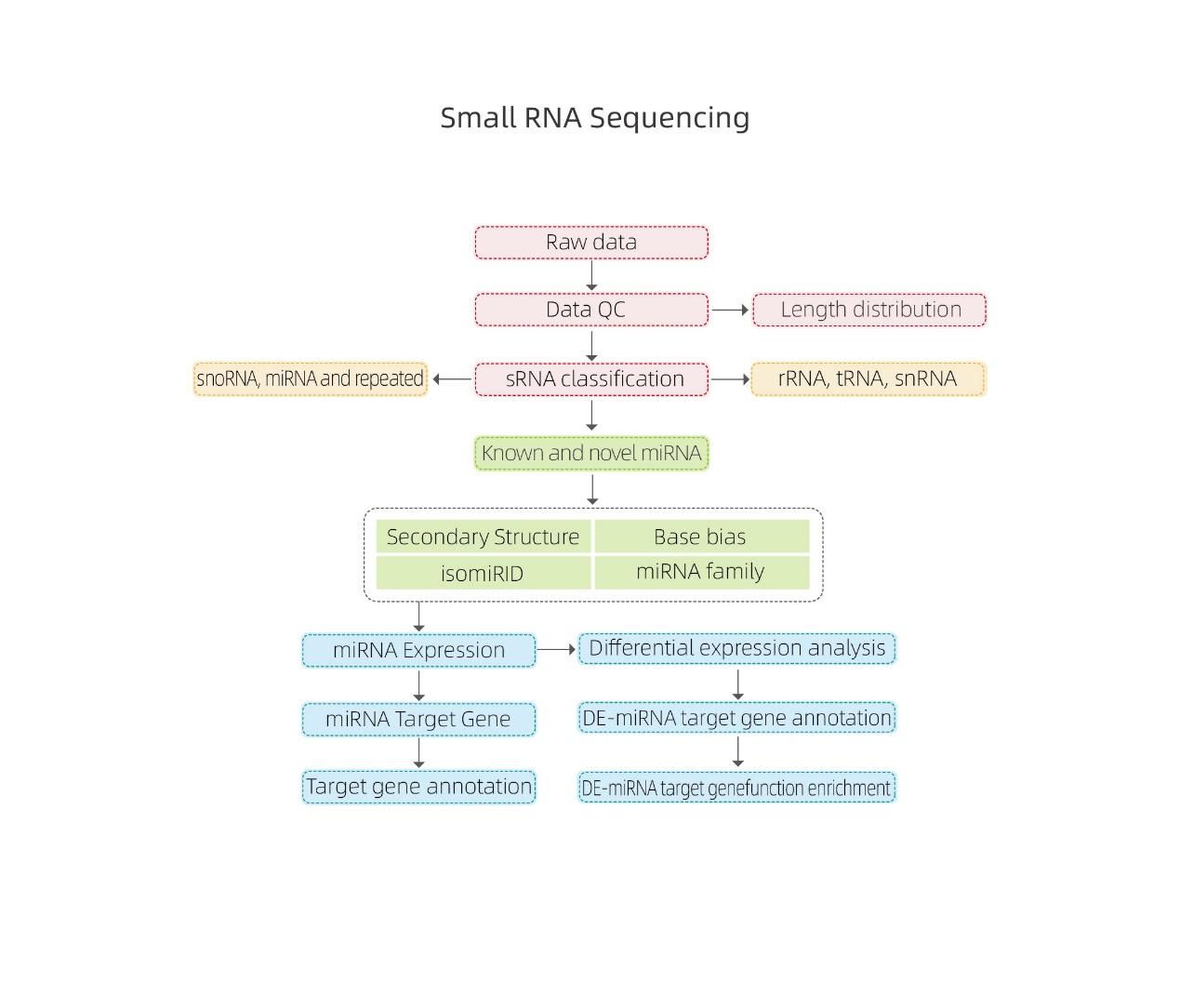
Bioinformatik
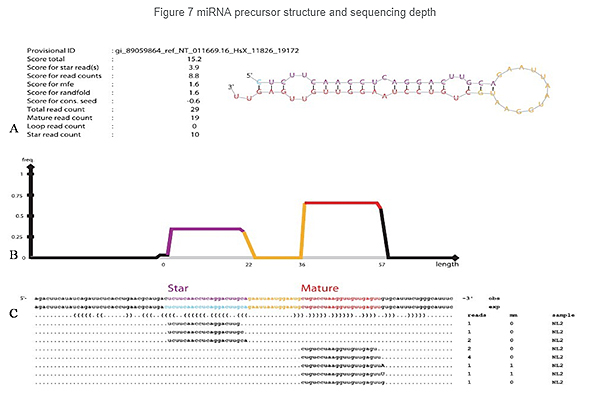
Identifizierung von miRNA: Struktur und Tiefe
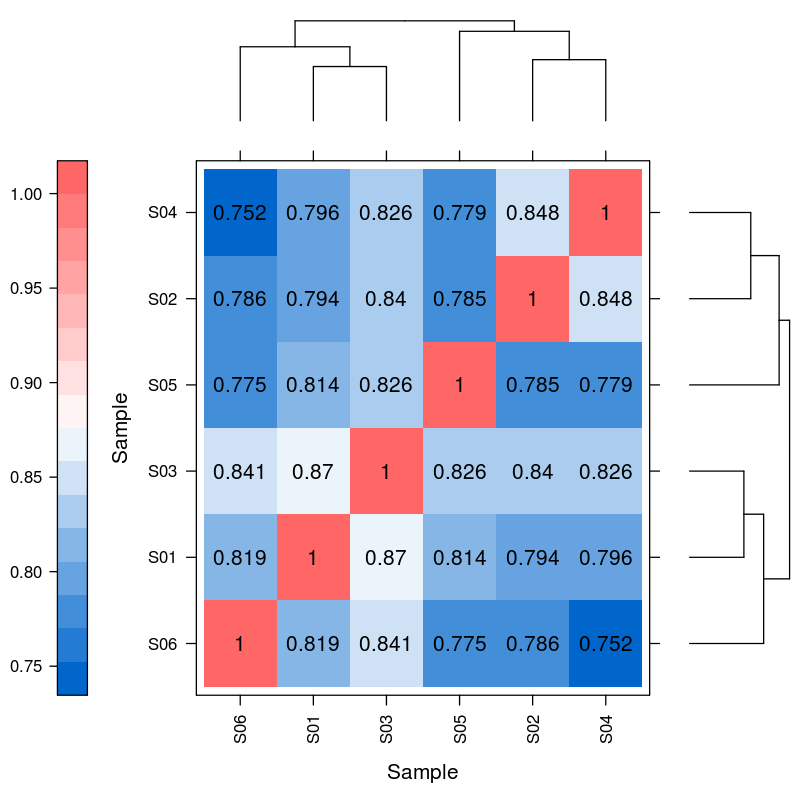
Differenzielle Expression von miRNA – hierarchisches Clustering
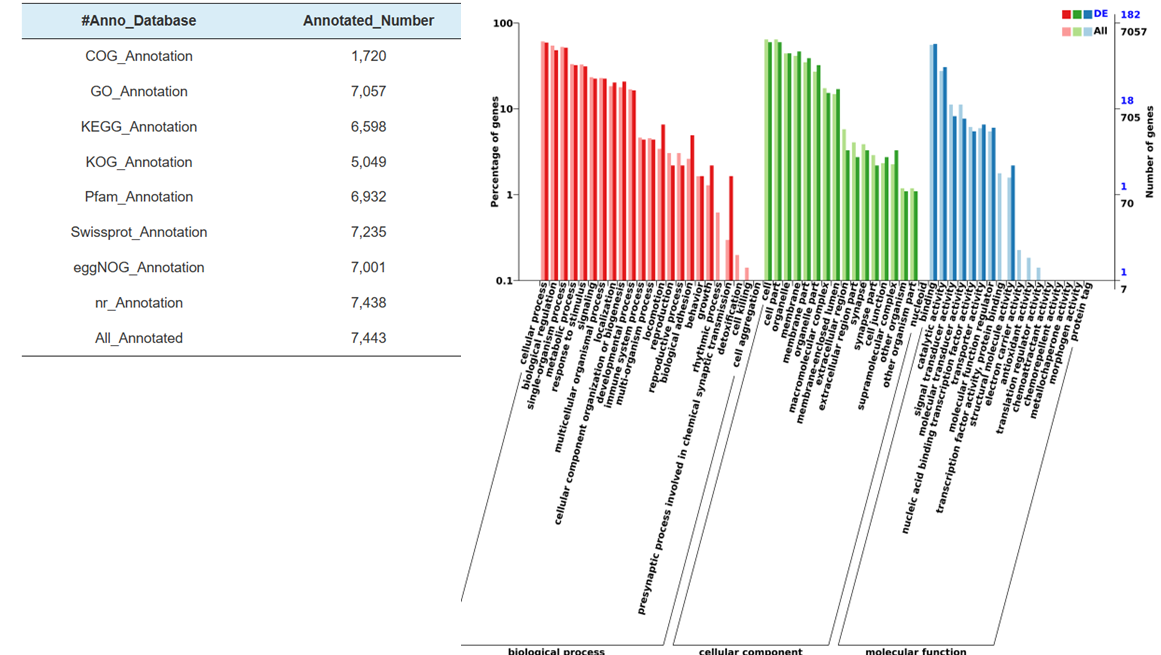
Funktionelle Annotation des Ziels unterschiedlich exprimierter miRNAs
Entdecken Sie die Forschungsfortschritte, die durch die sRNA-Sequenzierungsdienste von BMKGene ermöglicht werden, anhand einer kuratierten Sammlung von Veröffentlichungen.
Chen, H. et al.(2023) „Virusinfektionen hemmen die Saponinbiosynthese und Photosynthese in Panax notoginseng“, Plant Physiology and Biochemistry, 203, S.108038. doi: 10.1016/J.PLAPHY.2023.108038.
Li, H. et al.(2023) „Das pflanzliche FYVE-Domänen-enthaltende Protein FREE1 verbindet sich mit Mikroprozessorkomponenten, um die miRNA-Biogenese zu unterdrücken“, EMBO berichtet, 24(1).doi: 10.15252/EMBR.202255037/SUPPL_FILE/EMBR202255037-SUP-0004-SDATAFIG4.TIF.
Yu, J. et al.(2023) „Die MicroRNA Ame-Bantam-3p steuert die Larvenpuppenentwicklung, indem sie auf das Gen der multiplen epidermalen Wachstumsfaktor-ähnlichen Domänen 8 (megf8) in der Honigbiene Apis mellifera abzielt“, International Journal of Molecular Sciences, 24(6), S .5726. doi: 10.3390/IJMS24065726/S1.
Zhang, M. et al.(2018) „Integrierte Analyse von MiRNA und Genen im Zusammenhang mit der Fleischqualität zeigt, dass Gga-MiR-140-5p die intramuskuläre Fettablagerung bei Hühnern beeinflusst“, Cellular Physiology and Biochemistry, 46(6), S. 2421–2433.doi: 10.1159/000489649.