Planto/Besto Tuta Genaro Sekvencado
1.Servaj Avantaĝoj
Ampleksa sperto en genarsekvencado por pli ol 1000 specioj.
Pli ol 800 publikigitaj kazoj kun akumula efiko-faktoro de pli ol 4000.
Ampleksa bioinformatika analizo pri variavoko kaj funkcia analizo.
2. Servaj Specifoj
| Platformo | Biblioteko | Rekomendita seq-profundo | |
| Ilumino | PE 150 | Por SNP, InDel vokanta ≥ 10x Por SV, CNY vokado ≥ 30x
| |
| Nanoporo
| 8 kb | Por SV, CNY vokado ≥ 20x | |
| Pacbio | CCS | 15 kb | Por SNP, InDel, SV, CNY vokado ≥ 10x |
3. Specimenaj Postuloj
| Platformo | Konk.(ng/μL)
| Kvanto (ng)
| Pureco
| Agarose ĝelo
| ||
| OD260/280 | OD260/230 | 1. Klara ĉefa bando kun neniu aŭ limigitadegenero observita sur ĝelo. 2. Neniu aŭ limigita RNA aŭ proteina poluado
| ||||
| Ilumino | ≥1 | ≥30
| - | - | ||
| Nanoporo
| ≥30 | Dependas de la rendimento de datumoj 10μg/ĉelo | 1.7-2.2 | ≥1.5 | ||
| Pacbio | CCS | ≥50 | 1.7-2.2 | 1,8-2,5 | ||
4. Bioinforma Analizo
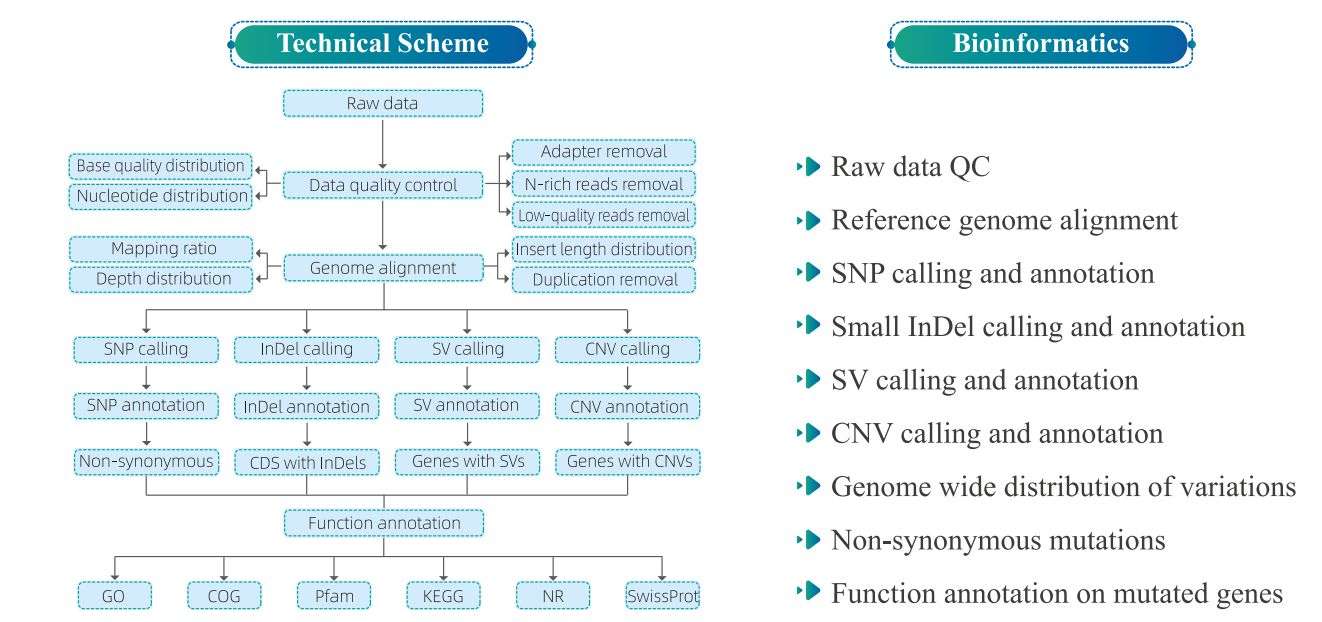
5. Serva Laborfluo

Specimena livero

DNA-eltiro

Bibliotekokonstruo

Sekvencado

Analizo de datumoj
Transdono de datumoj
1) Statistiko de Genoma Mapado
Tabelo 1 Statistiko de mapa rezulto
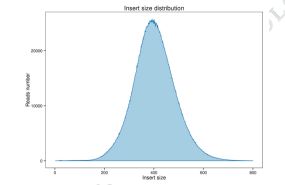
Figuro 1 Distribuado de enigaĵgrandeco kaj legas priraportado.
2) Varia Detektado
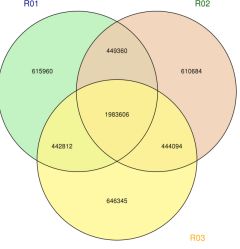
Figuro 2 Statistiko kaj komentario de SNP/INDEL/SV inter Specimenoj
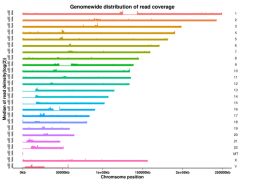
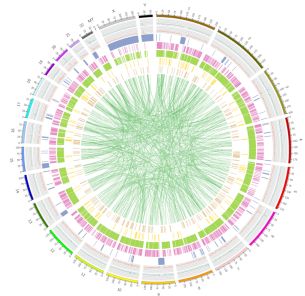
Figuro 3 Genaro-kovranta distribuado de vatiations
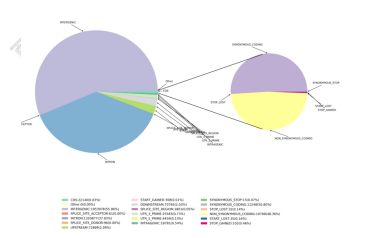
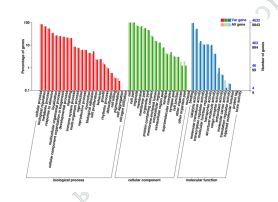
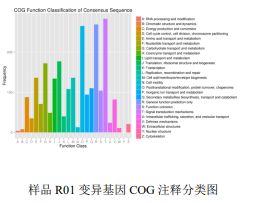
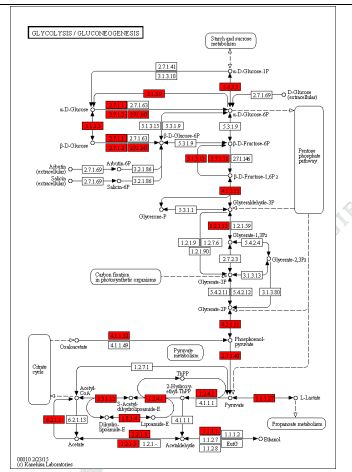
3) Funkcia komentario de variadoj
| 2019 | Naturkomunikadoj | Tutgenoma resekvencado rivelas originon de Brassica napus kaj genetikajn lokusojn implikitajn en ĝia plibonigo |
| 2020 | PNAS | La evolua origino kaj malsovaĝhistorio de orfiŝo ( Carassius auratus) |
| 2021 | Plant Biotechnology Journal | Referencogenaroj de la du kultivitaj jutospecioj |
| 2021 | Plant Biotechnology Journal | Genomaj signaturoj de legomo kaj oleosemo alopoliploida Brassicajuncea kaj genetikaj lokusoj kontrolantaj la amasiĝon de glukozinolatoj |
| 2019 | Molekula Planto | Tutgena resekvencado de tutmonda kolekto de kolzo-surtroniĝoj rivelas genetikan bazon de ilia ekotip-diverĝo. |
| 2022 | Hortikultura Esplorado | Genaro-kovranta asocia analizo disponigas molekulan sciojn pri la natura vario de akvomelona semgrandeco |
| 2021 | Ĵurnalo de Eksperimenta Botaniko | Genaro-kovranta asocio studo identigas variaĵojn de GhSAD1 transigante malvarman toleremon en kotono |
| 2021 | Ĵurnalo de Eksperimenta Botaniko | Genom-kovranta asocio-studo kaj transkriptomkomparo rivelas novajn QTL kaj kandidatojn kiuj kontrolas petalgrandecon en kolzo. |