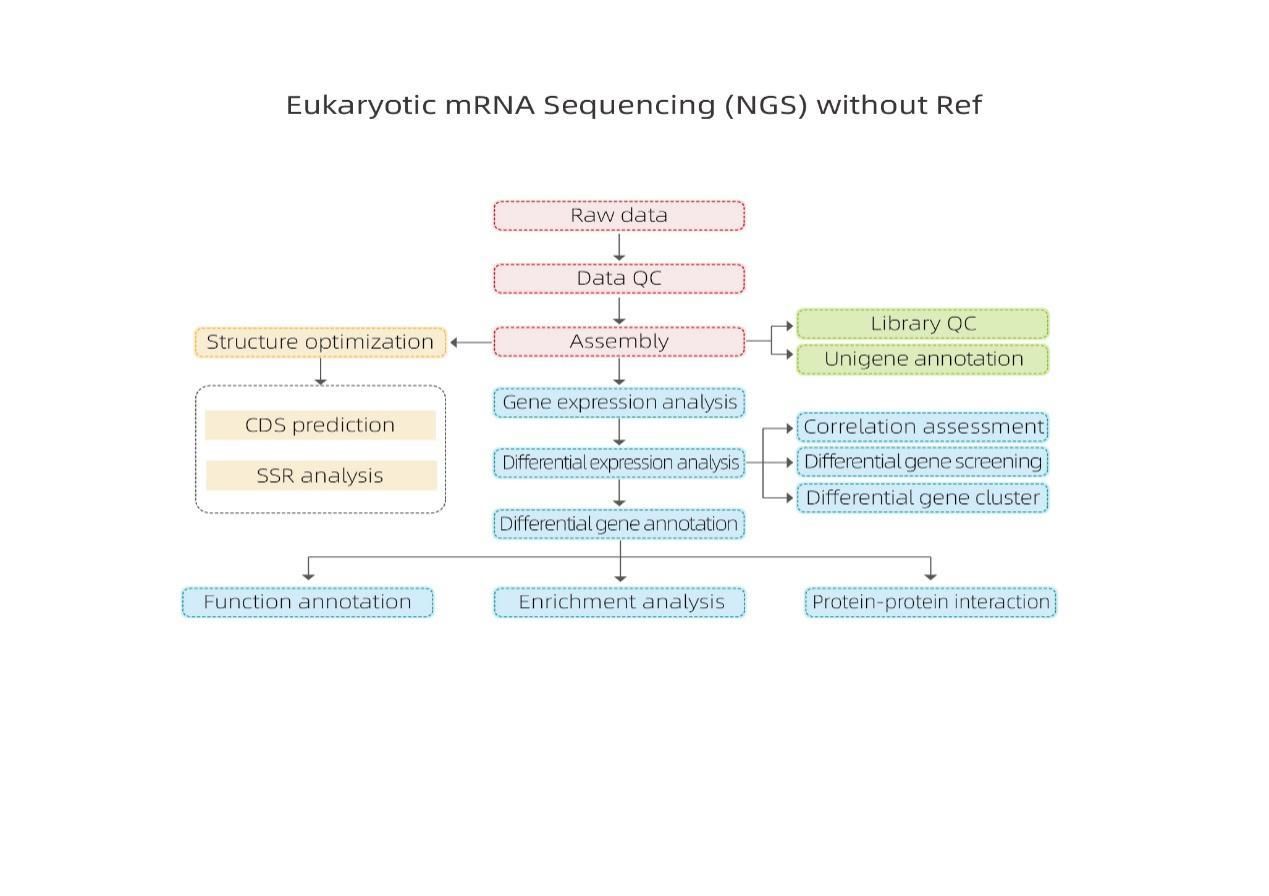
Secuenciación de ARNm sin referencia: Illumina
Características
● Independiente de cualquier genoma de referencia,
● Los datos podrían usarse para analizar la estructura y expresión de las transcripciones.
● Identificar sitios de recorte de variables
Ventajas del servicio
● Entrega de resultados basada en BMKCloud: los resultados se entregan como un archivo de datos y un informe interactivo a través de la plataforma BMKCloud, que permite una lectura fácil de usar de resultados de análisis complejos y una extracción de datos personalizada sobre la base de análisis bioinformáticos estándar.
● Servicios posventa: Servicios posventa válidos por 3 meses una vez finalizado el proyecto, incluido seguimiento de proyectos, resolución de problemas, preguntas y respuestas sobre resultados, etc.
Requisitos de muestra y entrega
Requisitos de muestra:
Nucleótidos:
| Conc.(ng/μl) | Cantidad (μg) | Pureza | Integridad |
| ≥ 20 | ≥ 0,5 | DO260/280=1,7-2,5 DO260/230=0,5-2,5 En el gel se muestra contaminación limitada o nula de proteínas o ADN. | Para plantas: RIN≥6,5; Para animales: RIN≥7,0; 5,0≥28S/18S≥1,0; elevación basal limitada o nula |
Tejido: Peso (seco): ≥1 g
*Para tejido de menos de 5 mg, recomendamos enviar una muestra de tejido congelada instantáneamente (en nitrógeno líquido).
Suspensión celular: Recuento de células = 3×107
*Recomendamos enviar lisado celular congelado.En caso de que la celda cuente menos de 5×105, se recomienda la congelación instantánea en nitrógeno líquido.
Muestras de sangre:
PA×genSangreARNTubo;
6 ml de TRIzol y 2 ml de sangre (TRIzol:Sangre=3:1)
Entrega de muestra recomendada
Envase:
Tubo de centrífuga de 2 ml (no se recomienda papel de aluminio)
Etiquetado de muestras: Grupo+réplica, por ejemplo, A1, A2, A3;B1, B2, B3... ...
Envío:
1. Hielo seco: las muestras deben empaquetarse en bolsas y enterrarse en hielo seco.
2.Tubos RNAstable: las muestras de ARN se pueden secar en un tubo de estabilización de ARN (por ejemplo, RNAstable®) y enviarse a temperatura ambiente.
Flujo de trabajo del servicio

Diseño de experimentos

Entrega de muestra

extracción de ARN

construcción de biblioteca

Secuenciación

Análisis de los datos

Servicios postventa
Bioinformática
1. Principio de ensamblaje del ARNm (denovo)
Mediante Trinity, las lecturas se fragmentan en partes más pequeñas, conocidas como K-mer.Estos K-mers luego se utilizan como semillas para extenderse a contigs y luego componentes basados en superposiciones de contigs.Finalmente, aquí se aplicó De Bruijn para reconocer transcripciones en los componentes.
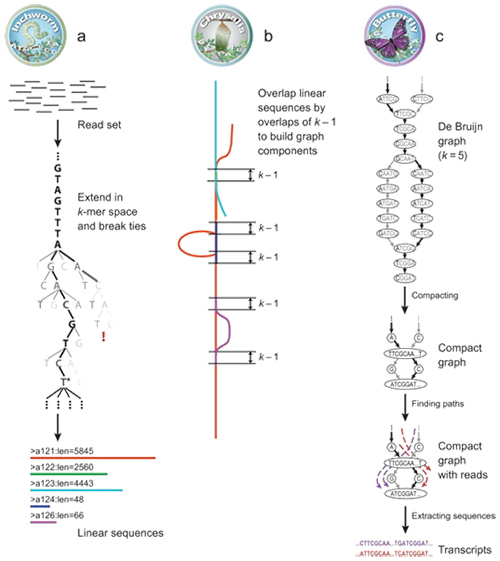
ARNm (de novo) Descripción general de Trinity
2. Distribución de ARNm (de novo) del nivel de expresión genética
RNA-Seq es capaz de lograr una estimación altamente sensible de la expresión genética.Normalmente, el rango detectable de expresión de transcripciones de FPKM oscila entre 10^-2 y 10^6.
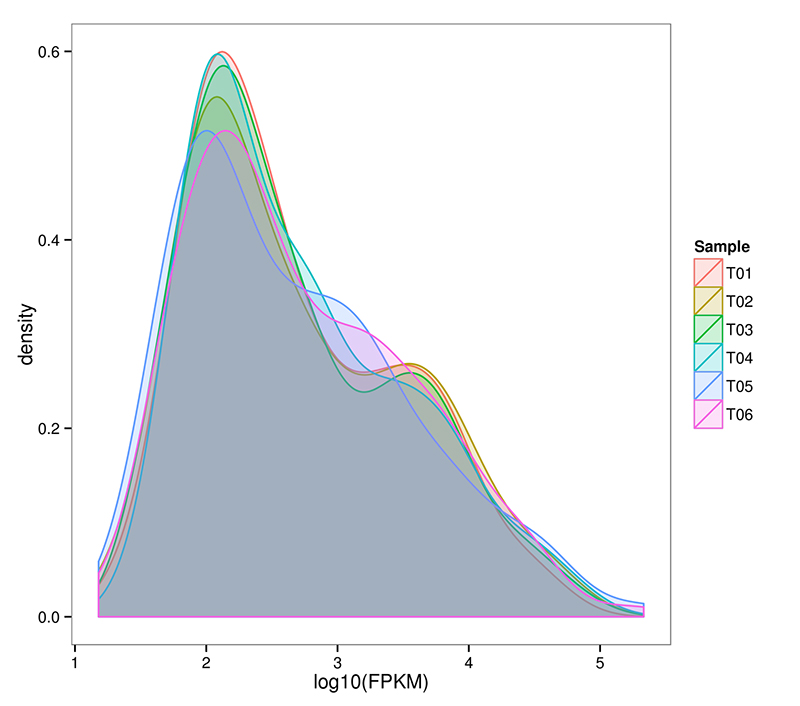
ARNm (De novo) Distribución de la densidad de FPKM en cada muestra.
3.Análisis de enriquecimiento GO de ARNm (de novo) de DEG
La base de datos GO (Gene Ontology) es un sistema estructurado de anotación biológica que contiene un vocabulario estándar de funciones de genes y productos genéticos.Contiene múltiples niveles, donde cuanto más bajo es el nivel, más específicas son las funciones.
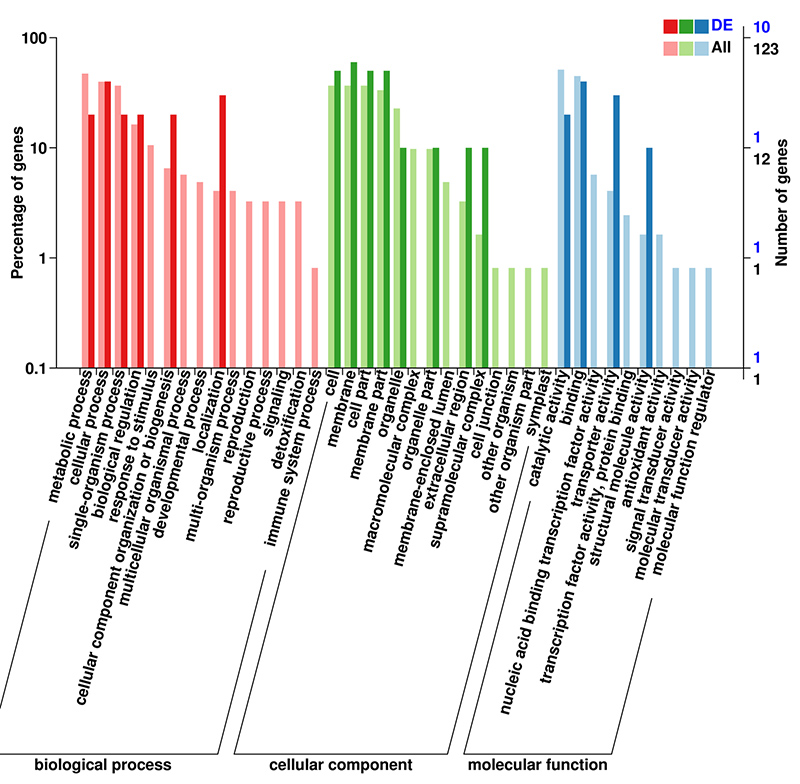
Clasificación GO de ARNm (de novo) de DEG en segundo nivel
Caso BMK
Análisis del transcriptoma del metabolismo de la sacarosa durante la hinchazón y el desarrollo del bulbo en cebolla (Allium cepa L.)
Publicado: fronteras en la ciencia de las plantas2016
Estrategia de secuenciación
Illumina HiSeq2500
Coleccion de muestra
En este estudio se utilizó el cultivar Utah Yellow Sweet Spain “Y1351”.El número de muestras recolectadas fue
15.º día después de la hinchazón (DAS) del bulbo (2 cm de diámetro y 3 a 4 g de peso), 30.º DAS (5 cm de diámetro y 100 a 110 g de peso) y ∼3 en el 40.º DAS (7 cm de diámetro y 100 a 110 g de peso). 260–300 gramos).
Resultados clave
1. En el diagrama de Venn, se detectaron un total de 146 DEG en los tres pares de etapas de desarrollo.
2. “Transporte y metabolismo de carbohidratos” estuvo representado por sólo 585 unigenes (es decir, el 7% del COG anotado).
3. Los Unigenes anotados con éxito en la base de datos GO se clasificaron en tres categorías principales para las tres etapas diferentes del desarrollo del bulbo.Los más representados en la categoría principal de “procesos biológicos” fueron los “procesos metabólicos”, seguidos por los “procesos celulares”.En la categoría principal de “función molecular”, las dos categorías más representadas fueron “unión” y “actividad catalítica”.
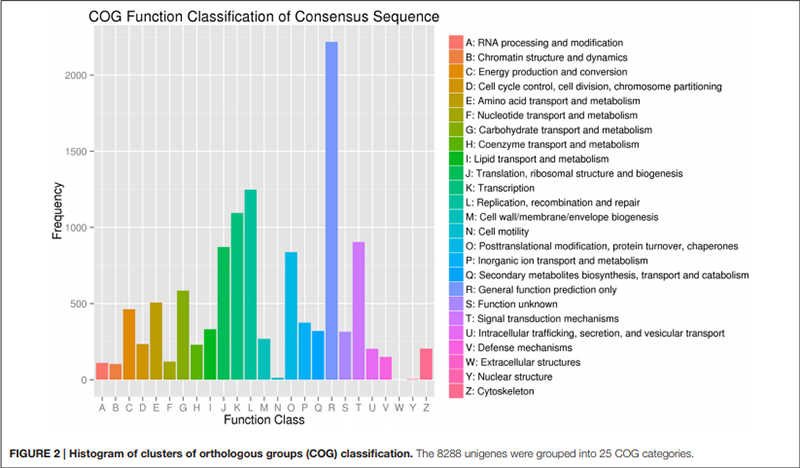 Histograma de clasificación de conglomerados de grupos ortólogos (COG) | 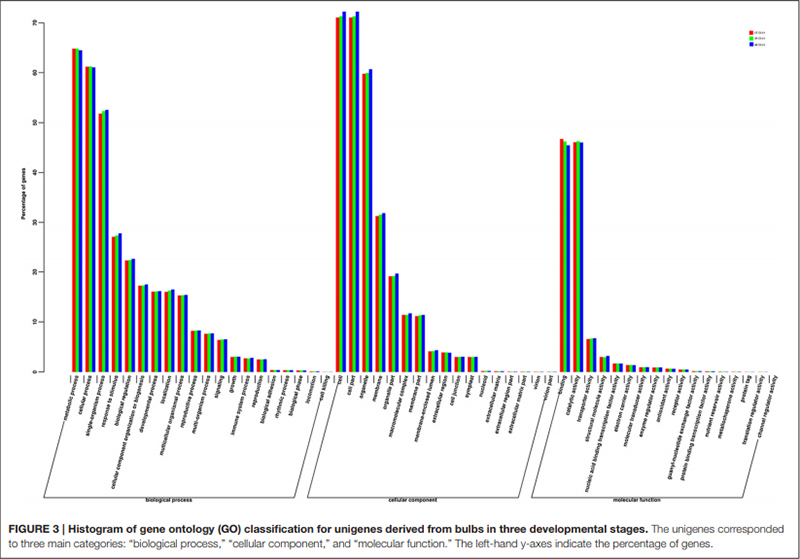 Histograma de clasificación de ontología genética (GO) para unigenes derivados de bulbos en tres etapas de desarrollo |
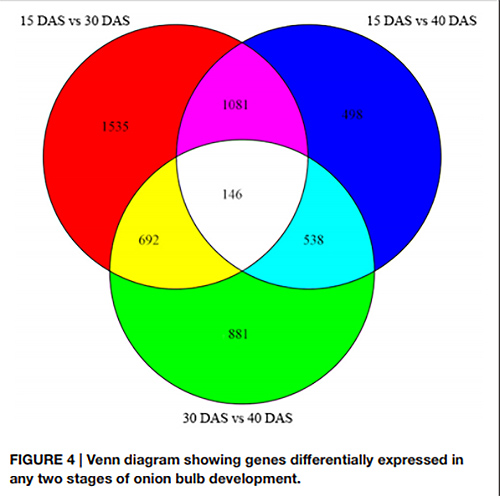 Diagrama de Venn que muestra genes expresados diferencialmente en dos etapas cualesquiera del desarrollo del bulbo de cebolla |
Referencia
Zhang C, Zhang H, Zhan Z, et al.Análisis del transcriptoma del metabolismo de la sacarosa durante la hinchazón y el desarrollo del bulbo en cebolla (Allium cepa L.) [J].Fronteras en la ciencia vegetal, 2016, 7:1425-.DOI: 10.3389/fpls.2016.01425