10x Genomics Visium Spatial Transcriptome
ominaisuudet
● Resoluutio: 100 µM
● Pistehalkaisija: 55 µM
● Kohteiden määrä: 4992
● Kuvausalue: 6,5 x 6,5 mm
● Jokainen viivakoodipiste on ladattu neljästä osasta koostuvilla pohjamaaleilla:
- poly(dT)-häntä mRNA-aloitusta ja cDNA-synteesiä varten
- Unique Molecular Identifier (UMI) vahvistaa vahvistusharhaa
- Tilaviivakoodi
- Osittain luetun 1 sekvensointialukkeen sitoutumissekvenssi
● Leikkeiden H&E-värjäys
Edut
●Yhden luukun palvelu: yhdistää kaikki kokemukseen ja taitoon perustuvat vaiheet, mukaan lukien kryoleikkaus, värjäys, kudosten optimointi, spatiaalinen viivakoodaus, kirjaston valmistelu, sekvensointi ja bioinformatiikka.
● Erittäin ammattitaitoinen tekninen tiimi: kokemusta yli 250 kudostyypistä ja yli 100 lajista, mukaan lukien ihminen, hiiri, nisäkäs, kala ja kasvi.
●Reaaliaikainen päivitys koko projektista: kokeen edistymisen täysi hallinta.
●Kattava standardi bioinformatiikka:Paketti sisältää 29 analyysiä ja yli 100 korkealaatuista lukua.
●Räätälöity data-analyysi ja visualisointi: saatavilla erilaisiin tutkimuspyyntöihin.
●Valinnainen yhteisanalyysi yksisoluisen mRNA-sekvensoinnin avulla
Tekniset tiedot
| Esimerkkivaatimukset | Kirjasto | Sekvensointistrategia | Tietoja suositellaan | Laadunvalvonta |
| OCT-upotetut kryonäytteet, FFPE-näytteet (Optimaalinen halkaisija: noin 6x6x6 mm3) 3 lohkoa per näyte | 10X Visiumin cDNA-kirjasto | Illumina PE150 | 50K PE-lukua kohdetta kohden (60Gb) | RIN>7 |
Saat lisätietoja näytteiden valmistelun ohjeista ja palvelun työnkulusta ottamalla yhteyttä aBMKGENE asiantuntija
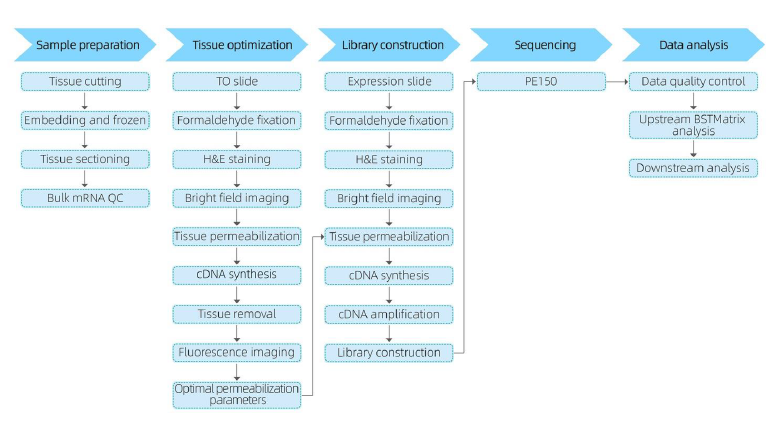
Palvelun työnkulku
Näytteen valmistusvaiheessa suoritetaan ensimmäinen bulkki-RNA:n uuttokoe, jotta voidaan varmistaa korkealaatuisen RNA:n saaminen.Kudosoptimointivaiheessa leikkeet värjätään ja visualisoidaan ja permeabilisaatioolosuhteet mRNA:n vapautumiselle kudoksesta optimoidaan.Optimoitua protokollaa sovelletaan sitten kirjaston rakentamisen aikana, minkä jälkeen suoritetaan sekvensointi ja data-analyysi.
Täydellinen palvelun työnkulku sisältää reaaliaikaiset päivitykset ja asiakasvahvistukset responsiivisen palautesilmukan ylläpitämiseksi, mikä varmistaa projektin sujuvan toteutuksen.
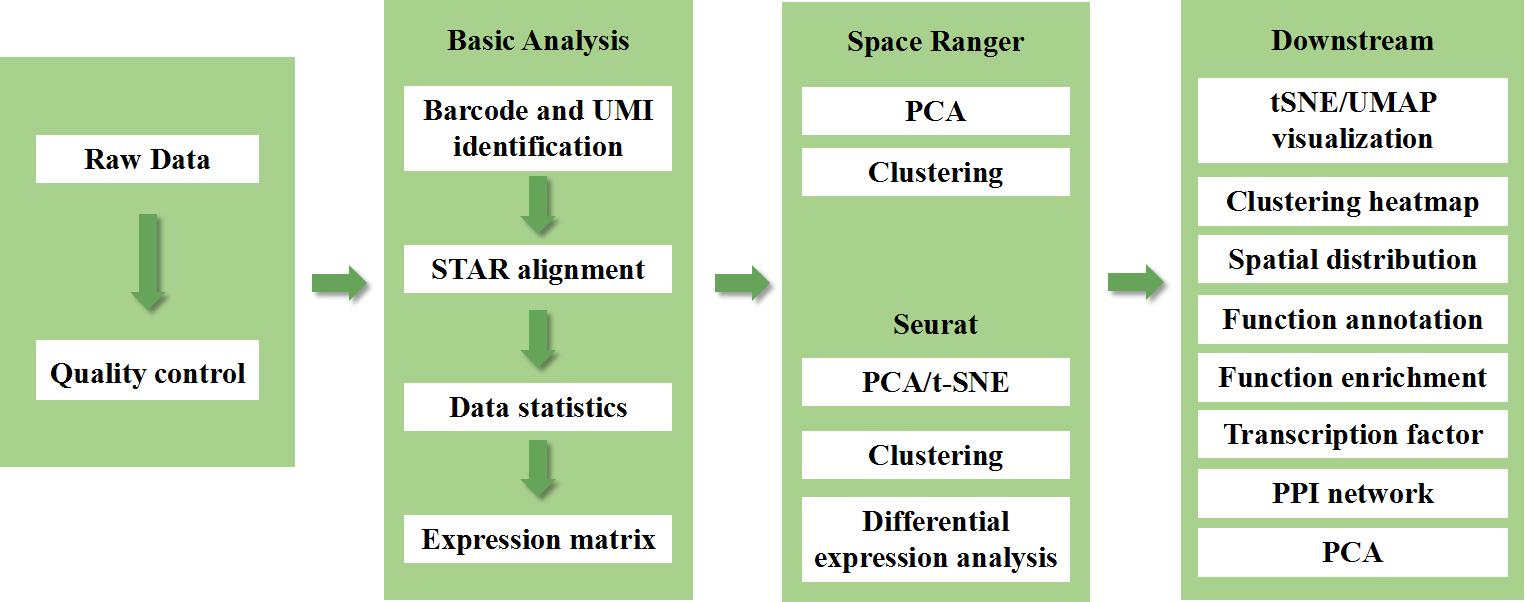
Sisältää seuraavan analyysin:
Tietojen laadunvalvonta:
o Tiedon tuotto ja laatupisteiden jakautuminen
o Geenien havaitseminen täplää kohti
o kudosten peitto
Sisäinen otosanalyysi:
o Geenirikkaus
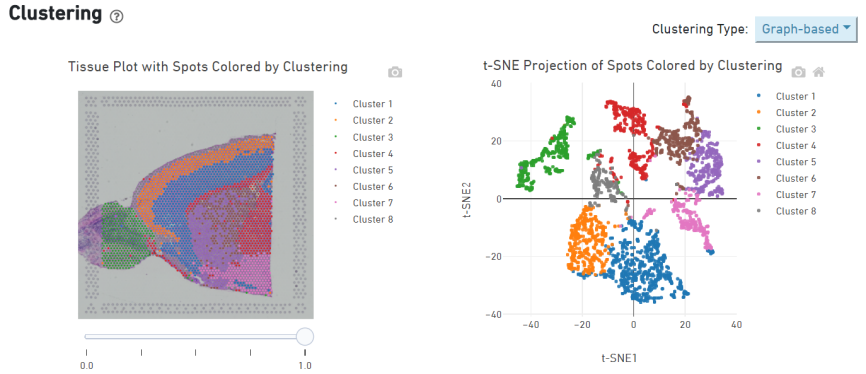
o Pisteklusterointi, mukaan lukien supistetun ulottuvuuden analyysi
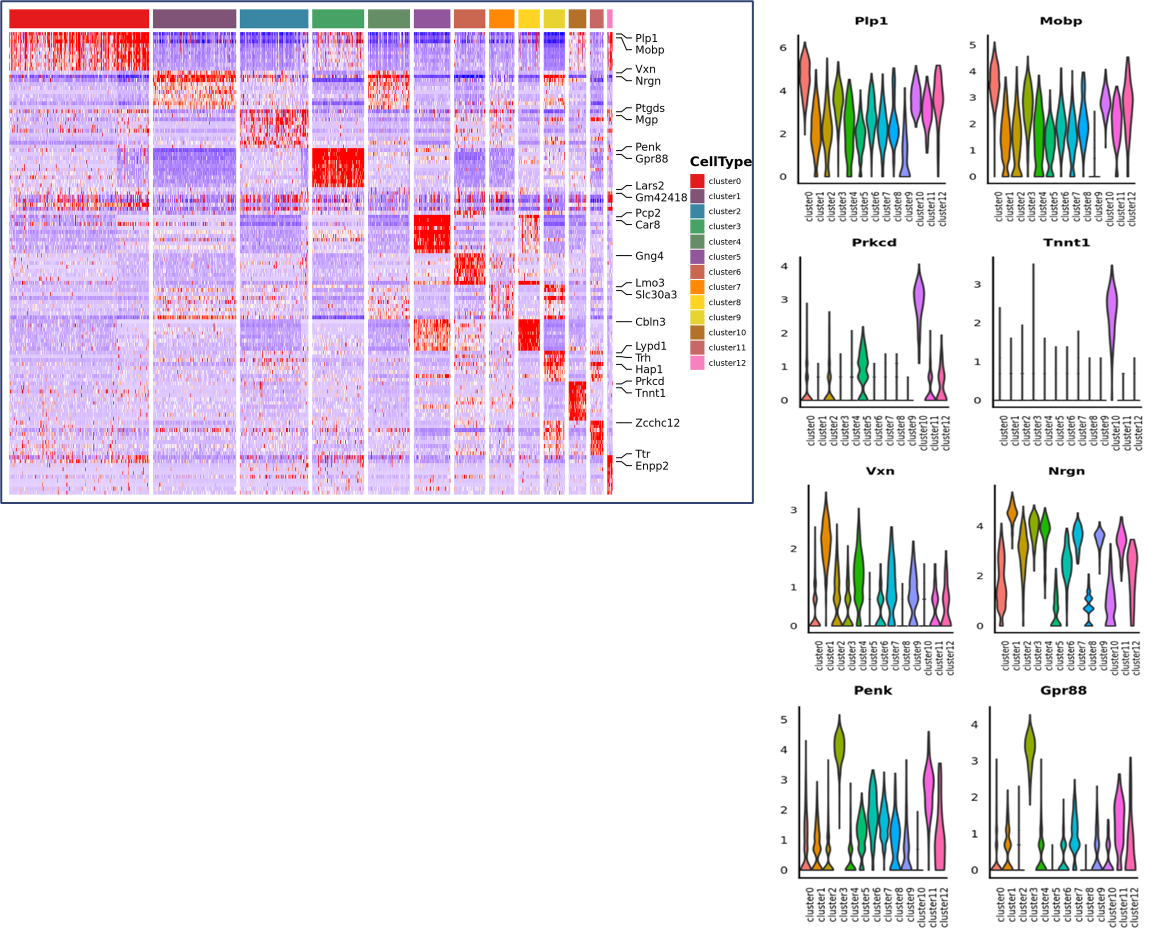
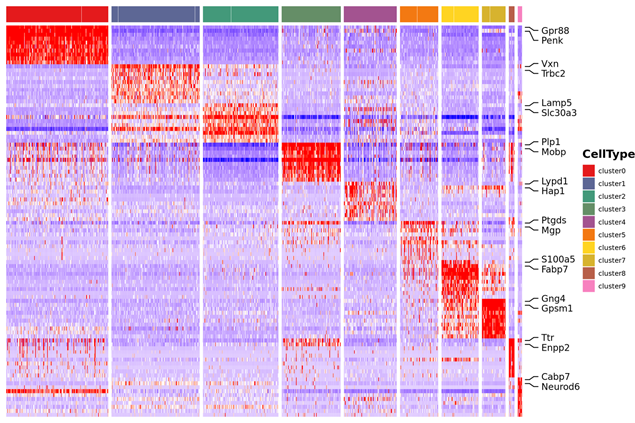
o Differentiaalinen ilmentymisanalyysi klustereiden välillä: markkerigeenien tunnistaminen
o Markkerigeenien toiminnallinen annotointi ja rikastaminen
Ryhmien välinen analyysi
o Molempien näytteiden (esim. sairaiden ja kontrollien) täplien yhdistäminen ja ryhmittyminen uudelleen
o Jokaisen klusterin markkerigeenien tunnistaminen
o Markkerigeenien toiminnallinen annotointi ja rikastaminen
o Saman klusterin differentiaalinen ilmaisu ryhmien välillä
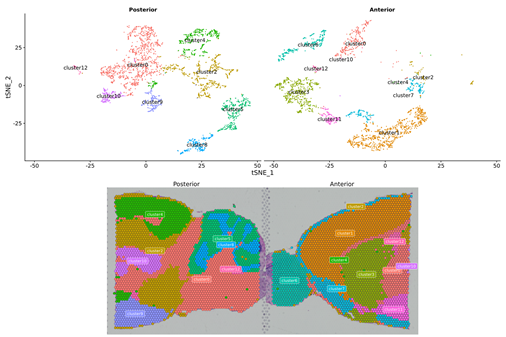
Sisäisen näytteen analyysi
Pisteklusterointi
Markkerigeenien tunnistus ja tilajakauma
Ryhmien välinen analyysi
Tietojen yhdistelmä molemmista ryhmistä ja uudelleenklusterista
Uusien klustereiden markkerigeenit
Tutustu 10X Visiumin BMKGenen spatiaalisen transkriptomiikan palvelun edistämiin edistysaskeliin näissä esitellyissä julkaisuissa:
Chen, D. et ai.(2023) "mthl1, nisäkkään adheesio-GPCR:iden mahdollinen Drosophila-homologi, osallistuu kasvainten vastaisiin reaktioihin injektoituihin onkogeenisiin soluihin kärpäsissä", Proceedings of the National Academy of Sciences of the United of America, 120(30), s.e2303462120.doi: /10.1073/pnas.2303462120
Chen, Y. et ai.(2023) "STEEL mahdollistaa spatiotemporaalisen transkriptomisen datan korkearesoluutioisen rajaamisen", Briefings in Bioinformatics, 24(2), s. 1–10.doi: 10.1093/BIB/BBAD068.
Liu, C. et ai.(2022) "Spatiotemporal atlas of organogenesis in the development of orkideakukkia", Nucleic Acids Research, 50(17), s. 9724–9737.doi: 10.1093/NAR/GKAC773.
Wang, J. et ai.(2023) "Integrating Spatial Transcriptomics and Single-nucleus RNA Sequencing Reveals the Potential Therapeutic Strategies for Uterine Leiomyooma", International Journal of Biological Sciences, 19(8), s. 2515–2530.doi: 10.7150/IJBS.83510.