Genom-szerte asszociációs elemzés
1. A szolgáltatás előnyei
● Bőséges projektesetek: 2009-es megalakulása óta a BMKGENE több száz fajprojektet hajtott végre a populációs GWAS-kutatásban, segítette a kutatókat több mint 100 cikk publikálásában, és a kumulatív impakt faktor elérte az 500-at.
● Profi elemzők.
● Rövid elemzési ciklus.
● Pontos adatbányászat.
2. Szolgáltatási specifikációk
| típus | Népességi skála | Szekvenálási stratégia és mélység |
| SLAF-GWAS | Mintaszám ≥200 | Genomméret < 400M, ref-genommal, WGS ajánlott |
| A genom mérete ≤ 1G, 100K címkék és 10X | ||
| 1G ≤ Genomméret ≤ 2G, 200K címkék és 10X | ||
| Genomméret > 2G, 300K címkék és 10X | ||
| WGS-GWAS | Mintaszám ≥200 | 10X minden minta esetében |
3. Anyagválasztás



Különböző fajták, alfajok, tájfajták/génbankok/vegyes családok/vad erőforrások
Különböző fajták, alfajok, tájfajták
Féltestvér család/teljes testvércsalád/vad erőforrások
4. Bioinformációs elemzés
● Genom-szerte asszociációs elemzés
● Szignifikáns SNP elemzése és szűrése
● A jelölt gén funkcionális annotációja
5. Szerviz munkafolyamat

Kísérleti tervezés

Mintaszállítás

RNS extrakció

Könyvtárépítés

Sorrendezés

Adatelemzés

Értékesítés utáni szolgáltatások
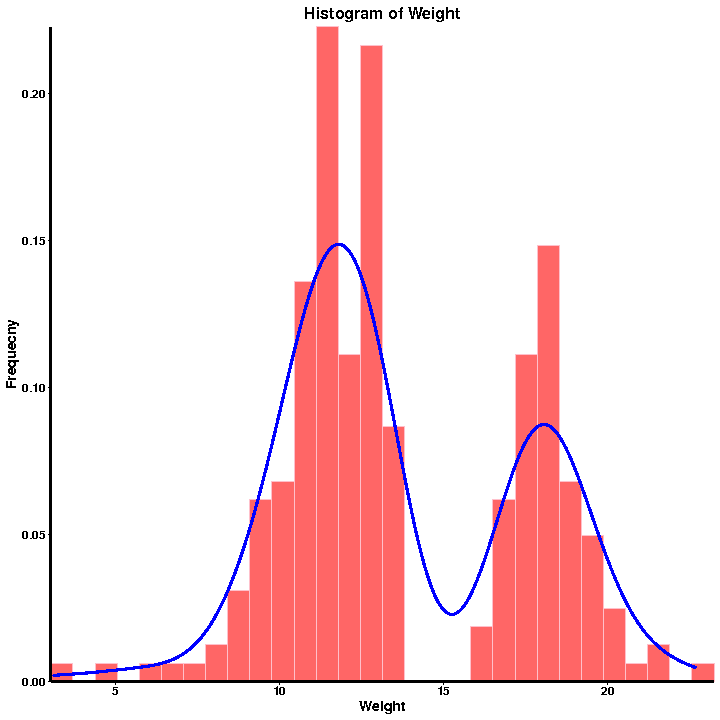
a.QC fenotípus
Frekvenciaeloszlás hisztogramja
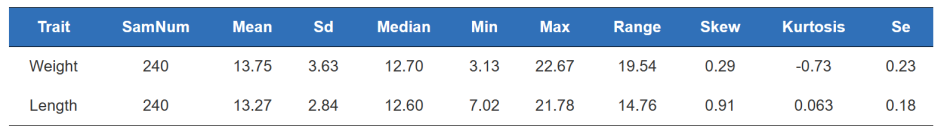
Fenotípus statisztika
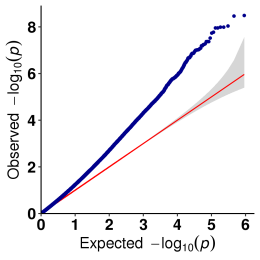
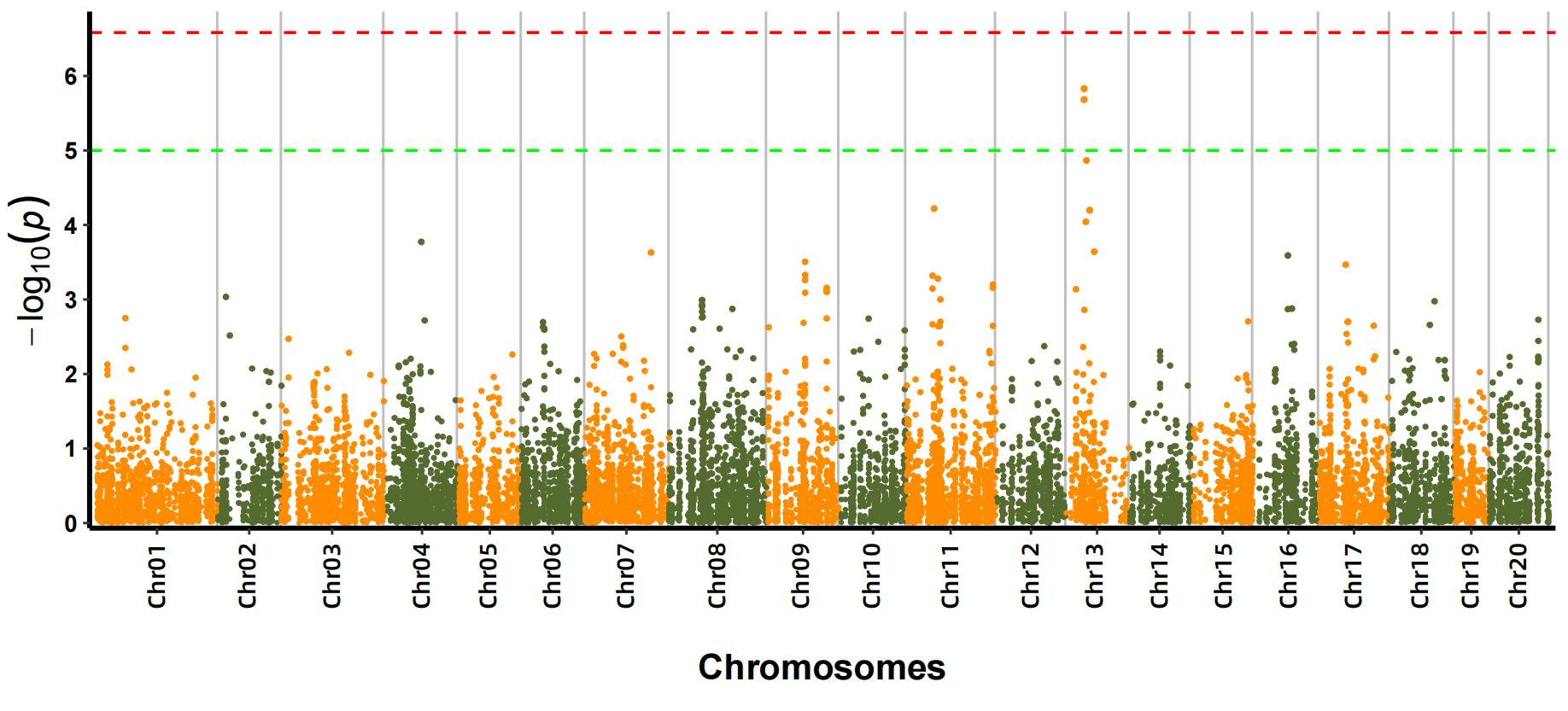
b.Asszociációs elemzés (Modell: GEMMA, FaST-LMM, EMMAX)
QQ telek
Manhattani cselekmény
| Év | Folyóirat | IF | Cím |
| 2022 | NC | 17.69 | A bazsarózsa Paeonia ostii giga-kromoszómáinak és giga-genomjának genomikai alapjai |
| 2015 | NP | 7.43 | A háziasítási lábnyomok agronómiai jelentőségű genomi régiókat rögzítenek a szójababban |
| 2018 | MP | 9.32 | A repcemagok világméretű gyűjteményének teljes genom újraszekvenálása feltárja ökotípus eltérésének genetikai alapját |
| 2022 | HR | 7.29 | A genomszintű asszociációs elemzés molekuláris betekintést nyújt a görögdinnye magméretének természetes változásaiba |