DNA/RNA シーケンシング – ナノポアシーケンサー
サービス詳細 特徴
| プラットホーム | ライブラリのサイズ | 理論上のデータ収量 (セルあたり) | 単一ベースの精度 | アプリケーション |
| ナノポア | 8Kb、10kb、20kb、超長鎖、cDNA-PCR | 70~90Gb/セル | 85~92% | SV コーリング、De novo、全長シーケンス、Iso-Seq、遺伝子アノテーション、DNA メチル化の検出 |
サービスのメリット
● PacBio シーケンシング プラットフォームにおける 5 年以上の経験。さまざまな生物種を対象とした数千のクローズド プロジェクトに携わる。
●BMKGENEはオックスフォードナノポアのオフィシャルパートナーであり、デュアルプラットフォームRNA/DNA認証を取得しています。
● シーケンサには、充実した装備と十分なシーケンス処理能力を備えた主流モデルがあります。
● Nanopore プラットフォームに基づいて、10 を超える動物および植物の Denovo 研究が国際的に有名な雑誌に掲載されています。
サンプル要件
| サンプルの種類 | 額 | 集中力(Qubit®) | 音量 | 純度 | その他 |
| ゲノムDNA | データ要件に応じて | ≧20ng/μl | 15μl以上 | OD260/280=1.7-2.2; OD260/230≧1.5; 260 nm の明確なピーク、汚染なし | 濃度は Qubit および Qubit/Nanopore ≤ 2 で測定する必要があります |
| 総RNA | 1.2μg以上 | ≧100μg/μl | 15μl以上 | OD260/280=1.7-2.5; OD260/230=0.5-2.5;汚染なし | RIN値≧7.5 |
サービスのワークフロー
サンプルの準備

図書館の建設

シーケンス

データ分析

プロジェクトの実施
DNA サンプルのデータ品質評価
表 1. クリーンデータの統計。
| BMKID | rawSeqNum | rawSumBase | cleanSeqNum | クリーンサムベース | クリーンN50レン | クリーンN90レン | クリーンミーンレン | クリーンマックスレン | クリーンミーンクアル |
| DNA_BMK01 | 1,218,239 | 26.37 | 1,121,736 | 25.90 | 28,014 | 15,764 | 23,090 | 143,181 | 9 |
RNA サンプルのデータ品質評価
表 1. クリーンデータの統計。
| ファイル名 | クライアントID | 読み取り番号 | BaseNum | N50 | 平均長さ | 最大長さ | 平均Qスコア |
| RNA_BMK001 | C2 | 8,947,708 | 4,047,230,083 | 398 | 452 | 129,227 | Q12 |
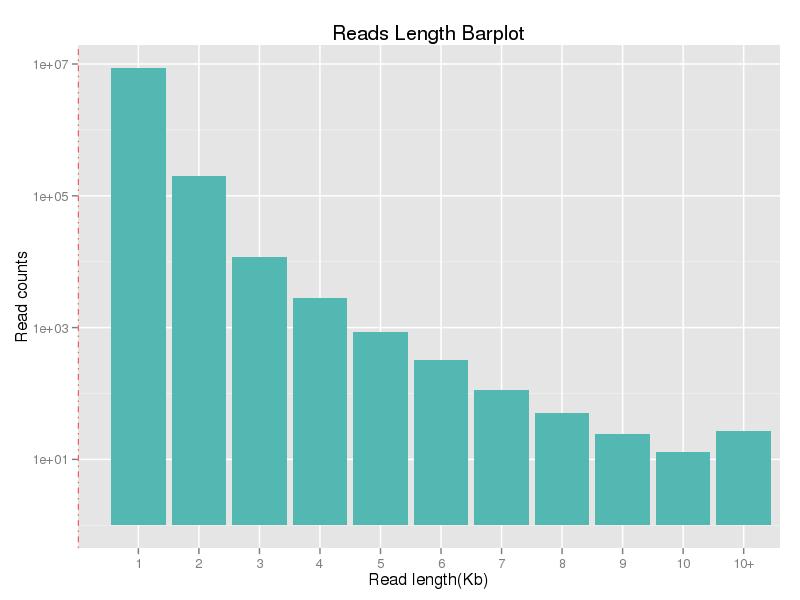
図 1. 読み取り長の分布
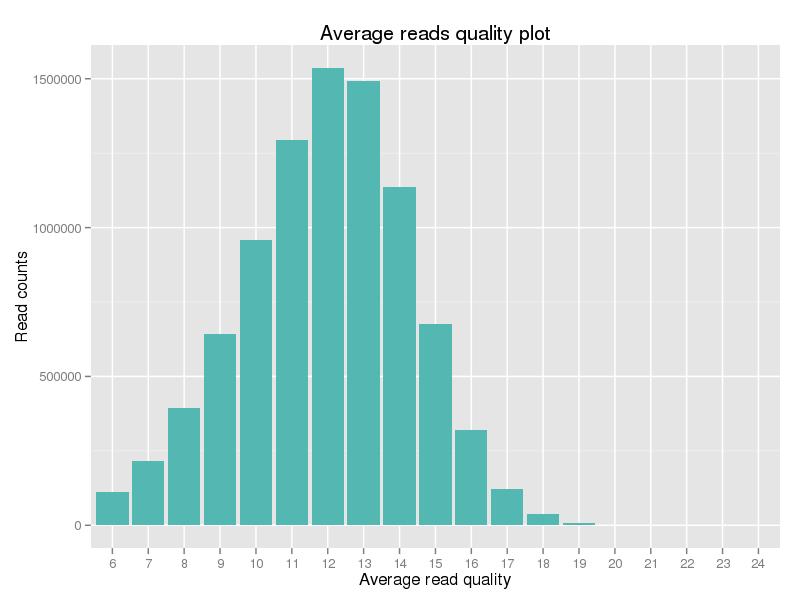
図 2. クリーン データの品質スコア分布
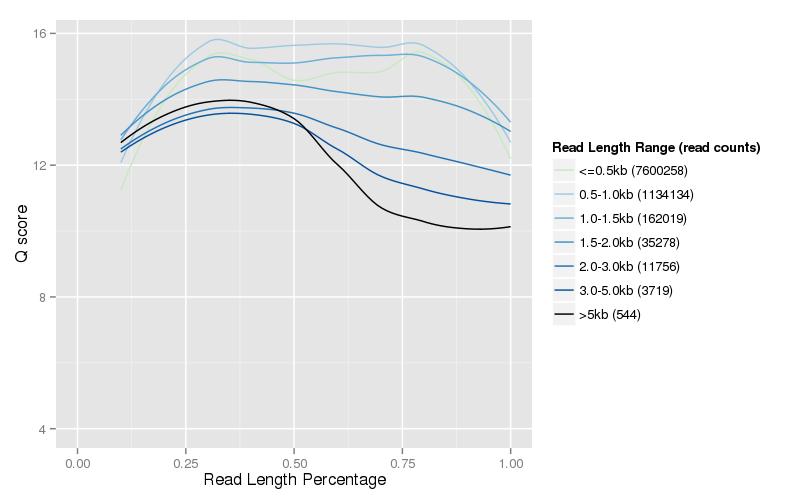
図 3. クリーン データの長さと品質スコアの分布