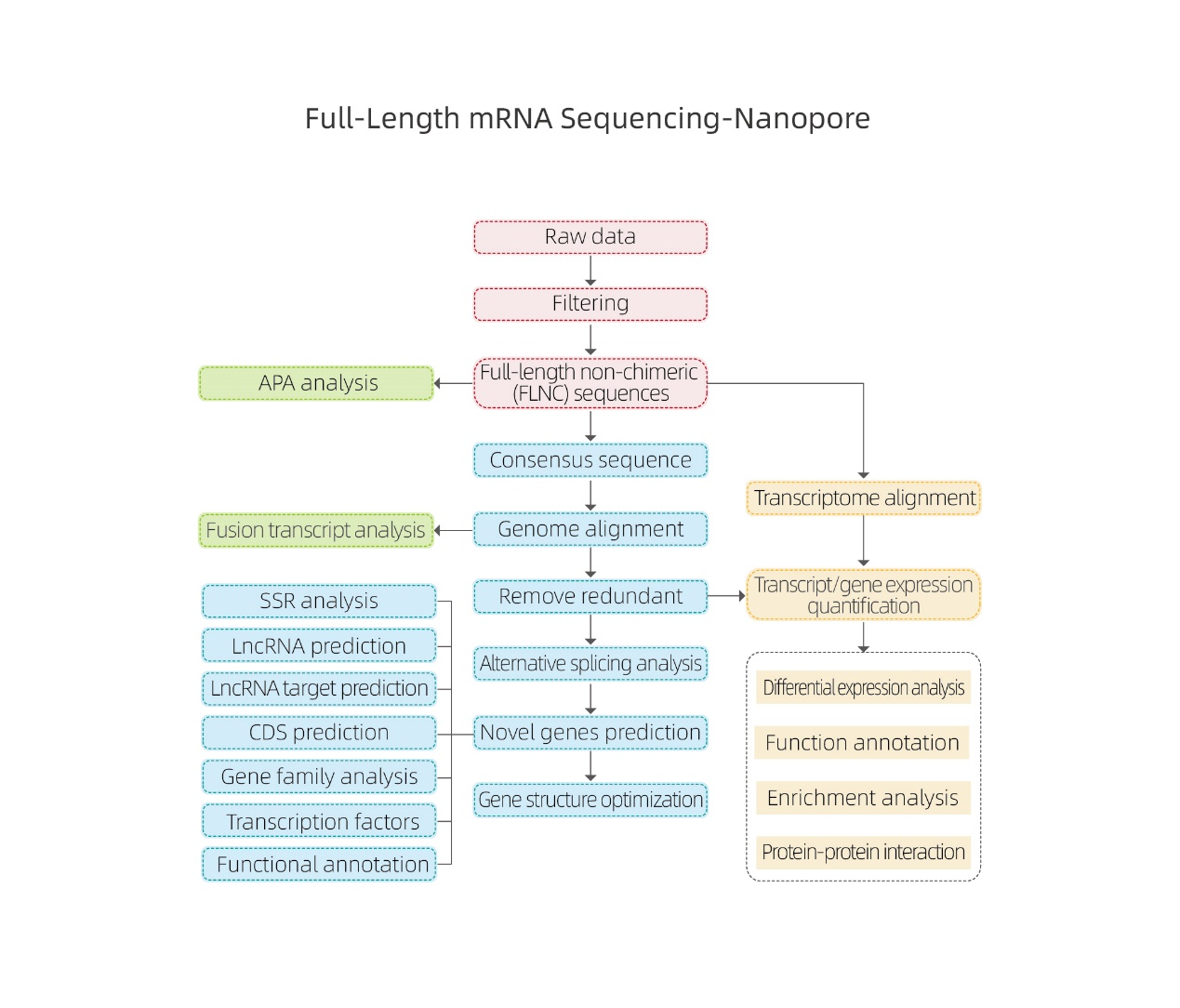
სრული სიგრძის mRNA თანმიმდევრობა-ნანოპური
სერვისის უპირატესობები
● დაბალი თანმიმდევრობის მიკერძოება
● სრული სიგრძის cDNA მოლეკულების გამოვლენა
● ნაკლები მონაცემებია საჭირო ტრანსკრიპტების იგივე რაოდენობის დასაფარად
● თითო გენზე მრავალი იზოფორმის იდენტიფიცირება
● გამოხატვის რაოდენობრივი განსაზღვრა იზოფორმის დონეზე
სერვისის სპეციფიკაციები
| ბიბლიოთეკა | Პლატფორმა | მონაცემთა რეკომენდებული გამოსავალი (გბ) | Ხარისხის კონტროლი |
| cDNA-PCR (პოლი-A გამდიდრებული) | Nanopore PromethION P48 | 6 გბ/ნიმუში (დამოკიდებულია სახეობაზე) | მთლიანი სიგრძის თანაფარდობა (70%) საშუალო ხარისხის ქულა: Q10
|
ბიოინფორმატიკის ანალიზები
●ნედლი მონაცემთა დამუშავება
● ტრანსკრიპტის იდენტიფიკაცია
● ალტერნატიული შერწყმა
● ექსპრესიის რაოდენობრივი განსაზღვრა გენის დონეზე და იზოფორმის დონეზე
● დიფერენციალური გამოხატვის ანალიზი
● ფუნქციის ანოტაცია და გამდიდრება (DEG და DET)
ნიმუშის მოთხოვნები და მიწოდება
ნიმუშის მოთხოვნები:
ნუკლეოტიდები:
| კონს.(ნგ/მკლ) | რაოდენობა (მკგ) | სიწმინდე | მთლიანობა |
| ≥ 100 | ≥ 0.6 | OD260/280=1.7-2.5 OD260/230=0.5-2.5 გელზე ნაჩვენებია შეზღუდული ცილის ან დნმ-ის დაბინძურება ან არა. | მცენარეებისთვის: RIN≥7.0; ცხოველებისთვის: RIN≥7.5; 5.0≥28S/18S≥1.0; შეზღუდული ან არ არის საბაზისო სიმაღლე |
ქსოვილი: წონა (მშრალი): ≥1 გ
*5 მგ-ზე ნაკლები ქსოვილისთვის, ჩვენ გირჩევთ გააგზავნოთ გაყინული (თხევადი აზოტით) ქსოვილის ნიმუში.
უჯრედის სუსპენზია: უჯრედების რაოდენობა = 3×106- 1×107
*ჩვენ გირჩევთ გაგზავნოთ გაყინული უჯრედის ლიზატი.თუ ეს უჯრედი ითვლის 5×10-ზე ნაკლები5რეკომენდირებულია თხევად აზოტში ფლეში გაყინული, რაც სასურველია მიკრო ექსტრაქციისთვის.
სისხლის ნიმუშები: მოცულობა≥1 მლ
რეკომენდებული ნიმუშის მიწოდება
კონტეინერი: 2 მლ ცენტრიფუგის მილაკი (თუნუქის ფოლგა არ არის რეკომენდებული)
ნიმუშის მარკირება: ჯგუფი+რეპლიკა, მაგ. A1, A2, A3;B1, B2, B3 ... ...
გადაზიდვა: 2, მშრალი ყინული: ნიმუშები უნდა იყოს შეფუთული ჩანთებში და დამარხული მშრალ ყინულში.
- რნმ სტაბილური მილები: რნმ-ის ნიმუშები შეიძლება გაშრეს რნმ-ის სტაბილიზაციის მილში (მაგ. RNAstable®) და გაიგზავნოს ოთახის ტემპერატურაზე.
სერვისის სამუშაო ნაკადი
ნუკლეოტიდები:

ნიმუშის მიწოდება

ბიბლიოთეკის მშენებლობა

თანმიმდევრობა

Მონაცემთა ანალიზი

გაყიდვის შემდგომი მომსახურება
სერვისის სამუშაო ნაკადი
ქსოვილი:

ექსპერიმენტის დიზაინი

ნიმუშის მიწოდება

რნმ-ის ექსტრაქცია

ბიბლიოთეკის მშენებლობა

თანმიმდევრობა

Მონაცემთა ანალიზი

გაყიდვის შემდგომი მომსახურება
1.დიფერენციალური გამოხატვის ანალიზი -ვულკანის ნაკვეთი
დიფერენციალური გამოხატვის ანალიზი შეიძლება დამუშავდეს როგორც გენის დონეზე დიფერენციალურად გამოხატული გენების (DEGs) იდენტიფიცირებისთვის, ასევე იზოფორმის დონეზე დიფერენციალური იდენტიფიკაციისთვის.
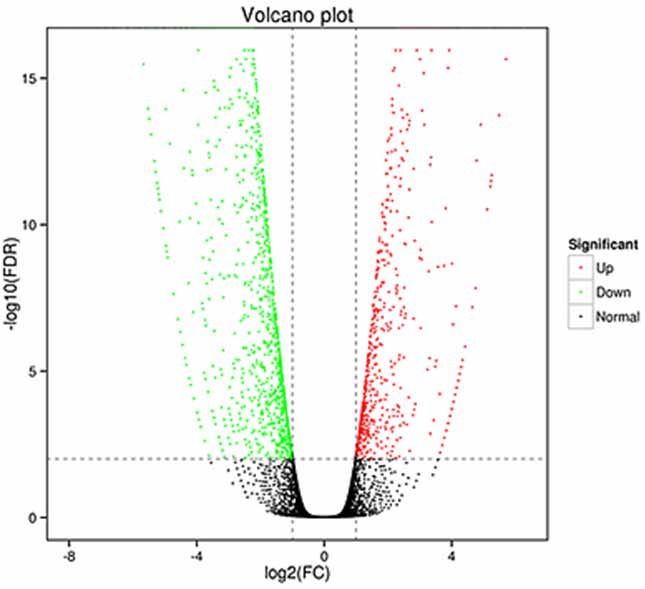
გამოხატული ტრანსკრიპტები (DETs)
2.იერარქიული კლასტერული სითბოს რუკა
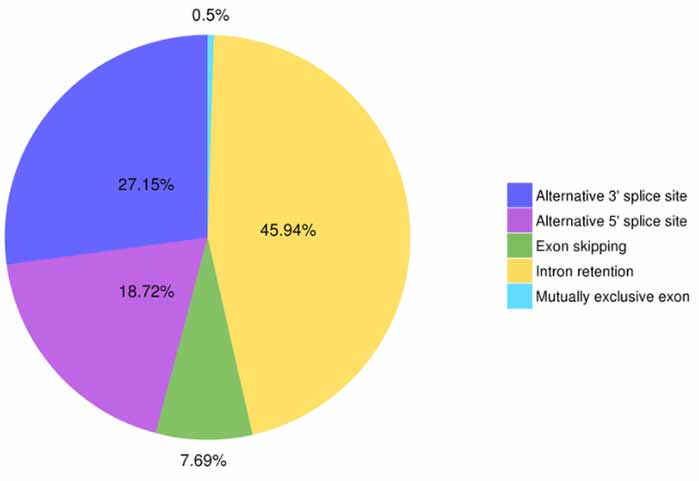
3. ალტერნატიული შეჯვარების იდენტიფიკაცია და კლასიფიკაცია
ალტერნატიული სპლაისინგის მოვლენების ხუთი ტიპის პროგნოზირება შესაძლებელია Astalavista-ს მიერ.
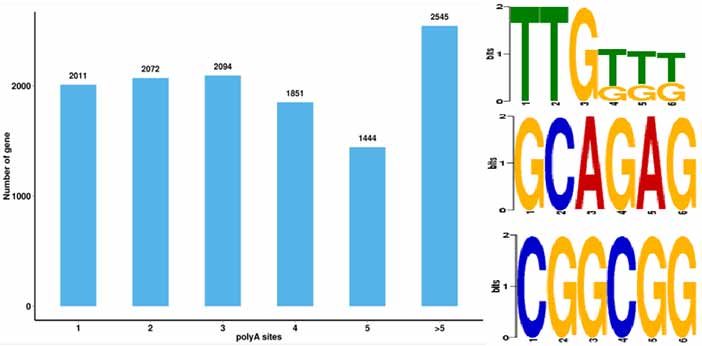
4.ალტერნატიული პოლი-ადენილაციის (APA) მოვლენების იდენტიფიკაცია და მოტივი 50 bp-ზე პოლი-A-ს ზემოთ
BMK საქმე
ალტერნატიული შეჯვარების იდენტიფიკაცია და იზოფორმის დონის რაოდენობრივი განსაზღვრა ნანოპური სრულმეტრაჟიანი ტრანსკრიპტომის თანმიმდევრობით
გამოქვეყნებულია:Nature Communications, 2020
თანმიმდევრობის სტრატეგია:
დაჯგუფება: 1. CLL-SF3B1(WT);2. CLL-SF3B1(K700E მუტაცია);3. ნორმალური B-უჯრედები
თანმიმდევრობის სტრატეგია: MinION 2D ბიბლიოთეკის თანმიმდევრობა, PromethION 1D ბიბლიოთეკის თანმიმდევრობა;მოკლედ წაკითხული მონაცემები იგივე ნიმუშებიდან
თანმიმდევრობის პლატფორმა: Nanopore MinION;Nanopore PromethION;
ძირითადი შედეგები
1.იზოფორმის დონის ალტერნატიული შეჯვარების იდენტიფიკაცია
დიდხანს წაკითხული თანმიმდევრობები აძლიერებს მუტანტის SF3B1 იდენტიფიკაციასK700Eშეცვლილი ადგილები იზოფორმის დონეზე.აღმოჩნდა, რომ 35 ალტერნატიული 3'SS და 10 ალტერნატიული 5'SSs მნიშვნელოვნად განსხვავებულად იყო შერწყმული SF3B1-ს შორისK700Eდა SF3B1WT.35 ცვლილებადან 33 ახლად იქნა აღმოჩენილი დიდი ხნის წაკითხული თანმიმდევრობით.
2.იზოფორმის დონის ალტერნატიული შერწყმის რაოდენობრივი განსაზღვრა
ინტრონის შეკავების (IR) იზოფორმების გამოხატვა SF3B1-შიK700Eდა SF3B1WTრაოდენობრივად შეფასდა ნანოპური თანმიმდევრობების საფუძველზე, რაც ავლენს IR იზოფორმების გლობალურ დაქვეითებას SF3B1-შიK700E.
მითითება
Tang AD, Soulette CM, Baren MJV და სხვ.ქრონიკული ლიმფოციტური ლეიკემიის დროს SF3B1 მუტაციის სრულმეტრაჟიანი ტრანსკრიპტის დახასიათება ავლენს შეკავებული ინტრონების დაქვეითებას [J].ბუნების კომუნიკაციები.