მცენარეთა/ცხოველთა მთელი გენომის თანმიმდევრობა
1.მომსახურების უპირატესობები
1000-ზე მეტი სახეობის გენომის თანმიმდევრობის დიდი გამოცდილება.
800-ზე მეტი გამოქვეყნებული შემთხვევა 4000-ზე მეტი დაგროვებითი ზემოქმედების ფაქტორით.
ყოვლისმომცველი ბიოინფორმატიკის ანალიზი ვარიაციის გამოძახებისა და ფუნქციის ანალიზის შესახებ.
2. სერვისის სპეციფიკაციები
| Პლატფორმა | ბიბლიოთეკა | რეკომენდებული მიმდევრობის სიღრმე | |
| ილუმინა | PE 150 | SNP-ისთვის, InDel-ის დარეკვა ≥ 10x SV-სთვის, CNY დარეკვა ≥ 30x
| |
| ნანოპორი
| 8 კბ | SV-სთვის, CNY დარეკვა ≥ 20x | |
| პაკბიო | CCS | 15 კბ | SNP, InDel, SV, CNY დარეკვისთვის ≥ 10x |
3. ნიმუშის მოთხოვნები
| Პლატფორმა | კონკ.(ng/μL)
| თანხა (ნგ)
| სიწმინდე
| აგაროზის გელი
| ||
| OD260/280 | OD260/230 | 1. გაწმინდეთ მთავარი ზოლი, გარეშე ან შეზღუდულიგელზე დაფიქსირებული დეგრადაცია. 2. არ არის ან შეზღუდულია რნმ ან ცილოვანი დაბინძურება
| ||||
| ილუმინა | ≥1 | ≥30
| - | - | ||
| ნანოპორი
| ≥30 | დამოკიდებულია მონაცემთა გამომუშავებაზე 10მკგ/უჯრედში | 1.7-2.2 | ≥1.5 | ||
| პაკბიო | CCS | ≥50 | 1.7-2.2 | 1.8-2.5 | ||
4. ბიოინფორმაციული ანალიზი
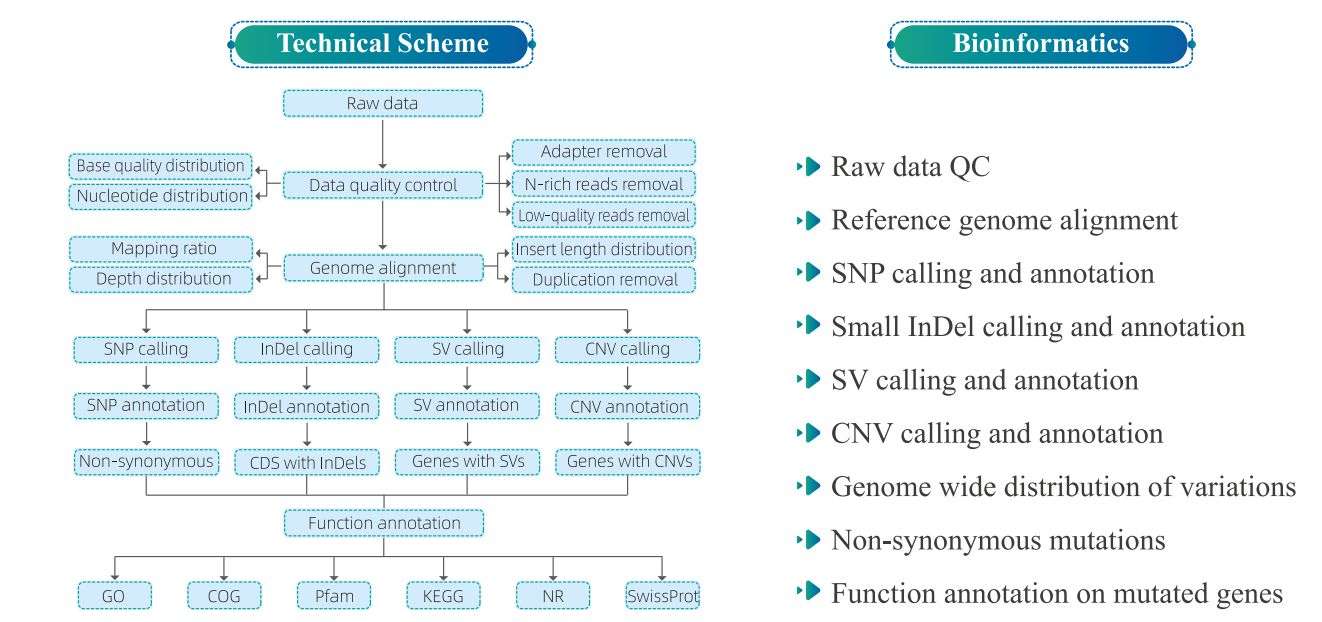
5. სერვისის სამუშაო ნაკადი

ნიმუშის მიწოდება

დნმ-ის ექსტრაქცია

ბიბლიოთეკის მშენებლობა

თანმიმდევრობა

Მონაცემთა ანალიზი
მონაცემთა მიწოდება
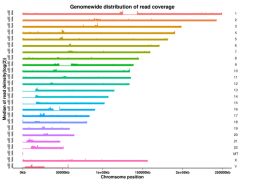
1) გენომის რუკების სტატისტიკა
ცხრილი 1 რუკების შედეგების სტატისტიკა
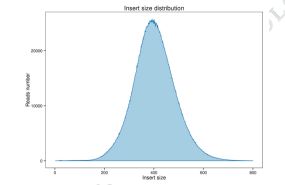
სურათი 1 ჩანართის ზომისა და წაკითხულის დაფარვის განაწილება.
2) Variate Detection
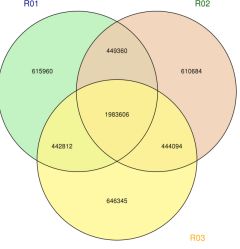
სურათი 2 SNP/INDEL/SV სტატისტიკა და ანოტაცია ნიმუშებს შორის
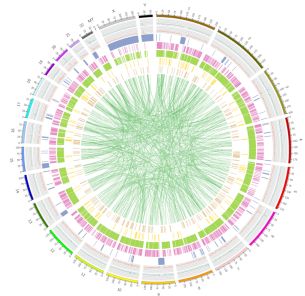
სურათი 3 ვატიაციების გენომის მასშტაბით განაწილება
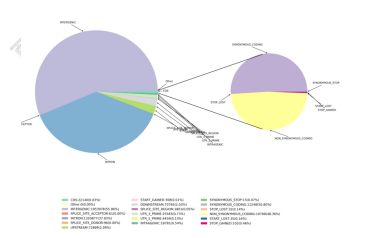
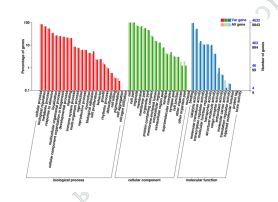
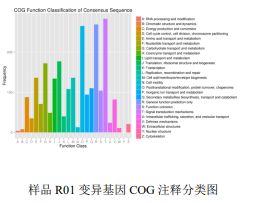
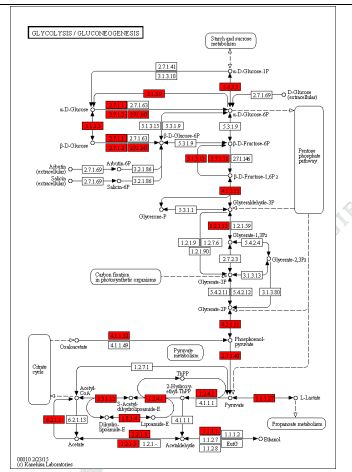
3) ვარიაციების ფუნქციური ანოტაცია
| 2019 წელი | ბუნების კომუნიკაციები | მთლიანი გენომის ხელახალი თანმიმდევრობა ავლენს Brassica napus-ის წარმოშობას და მის გაუმჯობესებაში მონაწილე გენეტიკურ ადგილს |
| 2020 წელი | PNAS | ოქროს თევზის ევოლუციური წარმოშობა და მოშინაურების ისტორია (Carassius auratus) |
| 2021 წელი | მცენარეთა ბიოტექნოლოგიის ჟურნალი | ორი კულტივირებული ჯუთის სახეობის საცნობარო გენომი |
| 2021 წელი | მცენარეთა ბიოტექნოლოგიის ჟურნალი | მცენარეული და ზეთოვანი ალოპოლიპლოიდის Brassicajuncea და გენეტიკური ლოკუსები, რომლებიც აკონტროლებენ გლუკოზინოლატების დაგროვებას |
| 2019 წელი | მოლეკულური მცენარე | რაფსის შეერთების მსოფლიო კოლექციის მთლიანი გენომის ხელახალი თანმიმდევრობა ავლენს მათი ეკოტიპური განსხვავების გენეტიკურ საფუძველს |
| 2022 წელი | მებაღეობის კვლევა | გენომის მასშტაბური ასოციაციის ანალიზი იძლევა მოლეკულურ შეხედულებებს საზამთროს თესლის ზომის ბუნებრივ ცვალებადობაზე |
| 2021 წელი | ჟურნალი ექსპერიმენტული ბოტანიკის | გენომის მასშტაბური ასოციაციის კვლევა გამოავლენს GhSAD1-ის ვარიანტებს, რომლებიც ანიჭებენ სიცივის ტოლერანტობას ბამბში |
| 2021 წელი | ჟურნალი ექსპერიმენტული ბოტანიკის | გენომის მასშტაბური ასოციაციის შესწავლა და ტრანსკრიპტომის შედარება გამოავლენს ახალ QTL და კანდიდატ გენებს, რომლებიც აკონტროლებენ ფურცლების ზომას რაფში |