
Viso ilgio mRNR sekos nustatymas - PacBio
Paslaugos privalumai
● Tiesioginis viso ilgio cDNR molekulės nuskaitymas nuo 3' galo iki 5' galo
● Izoformos lygio skiriamoji geba sekos struktūroje
● Didelio tikslumo ir vientisumo nuorašai
● Labai suderinama su vaiours rūšimis
● Didelė sekvenavimo talpa su 4 įrengtomis PacBio Sequel II sekos nustatymo platformomis
● Didelė patirtis dirbant su daugiau nei 700 Pacbio pagrindu sukurtų RNR sekos nustatymo projektų
● BMKCloud pagrįstas rezultatų pateikimas: platformoje pasiekiamas pritaikytas duomenų gavybos būdas.
● Užbaigus projektą galioja 3 mėn
Paslaugos specifikacijos
Platforma: PacBio Sequel II
Sekvenavimo biblioteka: poli A praturtinta mRNR biblioteka
Rekomenduojama duomenų išeiga: 20 Gb/pavyzdys (priklausomai nuo rūšies)
FLNC(%): ≥75%
*FLNC: viso ilgio nechimeriniai transkriptai
Bioinformatinės analizės
● Neapdorotų duomenų apdorojimas
● Nuorašo identifikavimas
● Sekos struktūra
● Išraiškos kiekybinis nustatymas
● Funkcijos anotacija
Pavyzdžių reikalavimai ir pristatymas
Pavyzdiniai reikalavimai:
Nukleotidai:
| Konc. (ng/μl) | Kiekis (μg) | Grynumas | Sąžiningumas |
| ≥ 120 | ≥ 0,6 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Ant gelio rodomas ribotas baltymų ar DNR užterštumas arba jo nėra. | Augalams: RIN≥7,5; Gyvūnams: RIN≥8,0; 5,0≥ 28S/18S≥1,0; ribotas arba jo nėra |
Audinys: Svoris (sausas):≥1 g
*Audiniams, kurių svoris mažesnis nei 5 mg, rekomenduojame siųsti greitai užšaldytą (skystame azotu) audinių mėginį.
Ląstelių suspensija:Ląstelių skaičius = 3×106- 1 × 107
*Rekomenduojame siųsti šaldytą ląstelių lizatą.Jei tų ląstelių skaičius mažesnis nei 5×105, rekomenduojamas greitas užšaldymas skystame azote, kuris geriau tinka mikro ekstrahavimui.
Kraujo mėginiai:Tūris ≥1 ml
Mikroorganizmas:Masė ≥ 1 g
Rekomenduojamas pavyzdžių pristatymas
Sudėtis:
2 ml centrifugos mėgintuvėlis (Alavo folija nerekomenduojama)
Mėginio ženklinimas: Grupė+pakartojimas pvz. A1, A2, A3;B1, B2, B3.....
Siuntimas:
1. Sausas ledas: mėginius reikia supakuoti į maišus ir palaidoti sausame lede.
2. RNR stabilūs mėgintuvėliai: RNR mėginius galima džiovinti RNR stabilizavimo mėgintuvėlyje (pvz., RNAstable®) ir gabenti kambario temperatūroje.
Aptarnavimo darbų eiga

Eksperimento dizainas

Mėginio pristatymas

RNR ekstrahavimas

Bibliotekos statyba

Sekos nustatymas

Duomenų analizė

Paslaugos po pardavimo
1.FLNC ilgio pasiskirstymas
Viso ilgio nechimerinio skaitymo (FLNC) ilgis rodo cDNR ilgį bibliotekos konstrukcijoje.FLNC ilgio pasiskirstymas yra esminis rodiklis vertinant bibliotekos statybos kokybę.
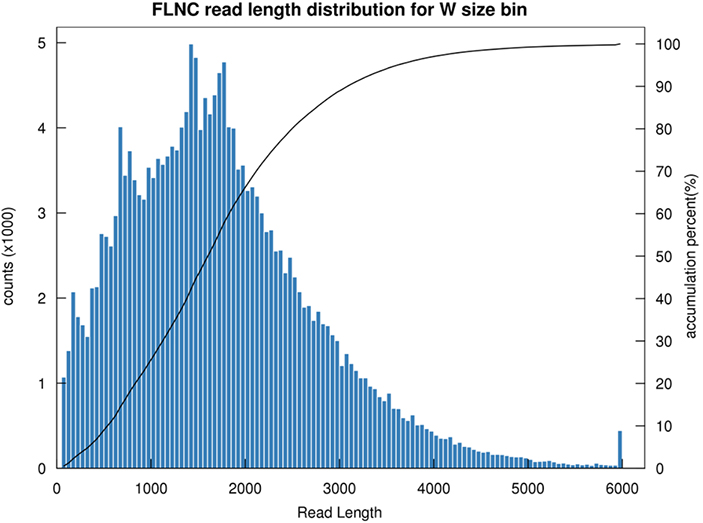
FLNC skaitymo ilgio pasiskirstymas
2. Pilnas ORF regiono ilgio pasiskirstymas
Mes naudojame „TransDecoder“, kad prognozuotume baltymus koduojančius regionus ir atitinkamas aminorūgščių sekas, kad sukurtume unigeninius rinkinius, kuriuose yra visa nereikalinga transkripto informacija visuose mėginiuose.
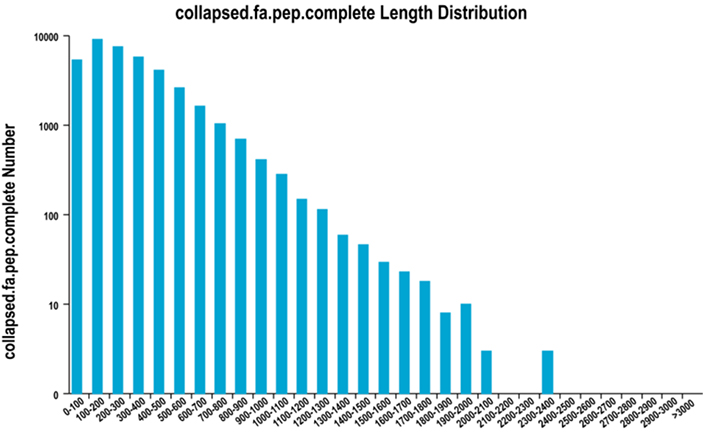
Pilnas ORF regiono ilgio pasiskirstymas
3.KEGG kelio sodrinimo analizė
Skirtingai išreikštus nuorašus (DET) galima nustatyti suderinus NGS pagrįstus RNR sekos duomenis su viso ilgio nuorašų rinkiniais, sugeneruotais naudojant PacBio sekos duomenis.Šiuos DET galima toliau apdoroti įvairiai funkcinei analizei, pvz., KEGG kelio sodrinimo analizei.
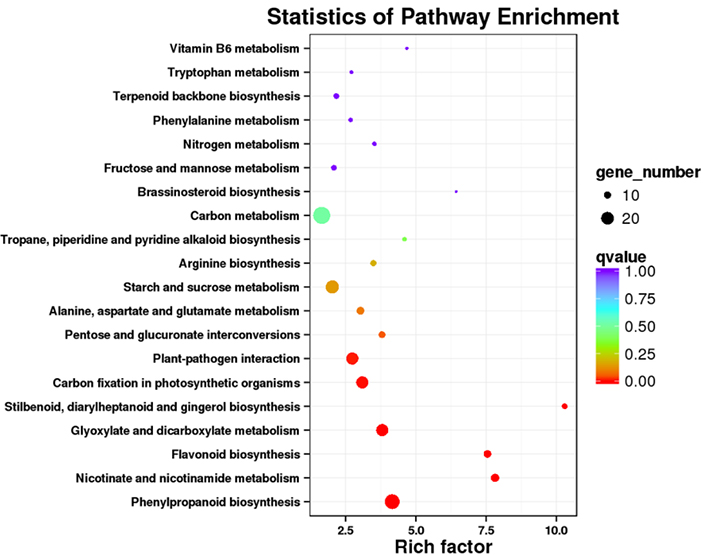
DET KEGG kelio praturtinimas - Taškinis sklypas
BMK dėklas
Populus kamieno transkripto vystymosi dinamika
Paskelbta: Augalų biotechnologijos žurnalas, 2019 m
Sekos nustatymo strategija:
Pavyzdžių rinkinys:kamieno sritys: viršūnė, pirmasis mazgas (IN1), antrasis tarpmazgas (IN2), trečiasis tarpmazgas (IN3), tarpmazgas (IN4) ir tarpmazgas (IN5) iš Nanlin895
NGS seka:15 asmenų RNR buvo sujungta kaip vienas biologinis mėginys.NGS sekai buvo apdoroti trys kiekvieno taško biologiniai pakartojimai
TGS seka:Stiebo regionai buvo suskirstyti į tris sritis, ty viršūnę, IN1-IN3 ir IN4-IN5.Kiekvienas regionas buvo apdorotas PacBio sekos nustatymui naudojant keturių tipų bibliotekas: 0-1 kb, 1-2 kb, 2-3 kb ir 3-10 kb.
Pagrindiniai rezultatai
1. Iš viso nustatyta 87150 pilno ilgio nuorašų, kuriuose identifikuota 2081 nauja izoforma ir 62058 naujos alternatyvios sujungtos izoformos.
Nustatyti 2,1187 lncRNR ir 356 sulieti genai.
3. Nuo pirminio augimo iki antrinio augimo buvo nustatyti 15838 skirtingai išreikšti transkriptai iš 995 skirtingai išreikštų genų.Visuose DEG 1216 buvo transkripcijos faktoriai, apie kuriuos dar nebuvo pranešta.
4.GO sodrinimo analizė atskleidė ląstelių dalijimosi ir oksidacijos-redukcijos proceso svarbą pirminiame ir antriniame augime.
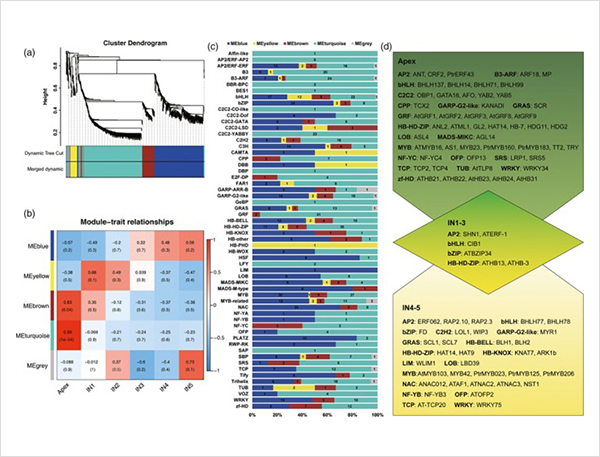
Alternatyvūs sujungimo įvykiai ir skirtingos izoformos
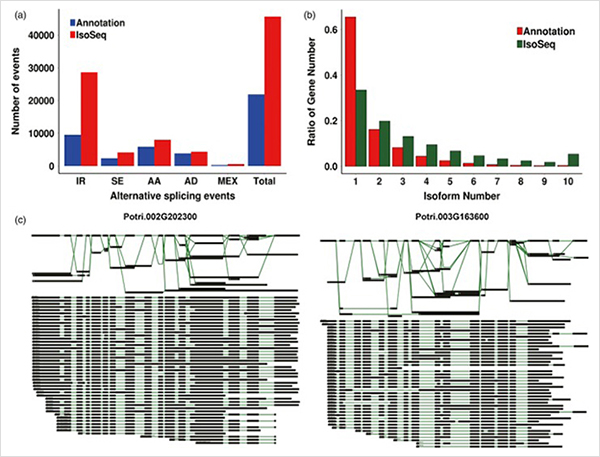
WGCNA transkripcijos faktorių analizė
Nuoroda
Chao Q, Gao ZF, Zhang D ir kt.Populus kamieno transkripto vystymosi dinamika.Plant Biotechnol J. 2019;17(1):206-219.doi:10.1111/pbi.12958











