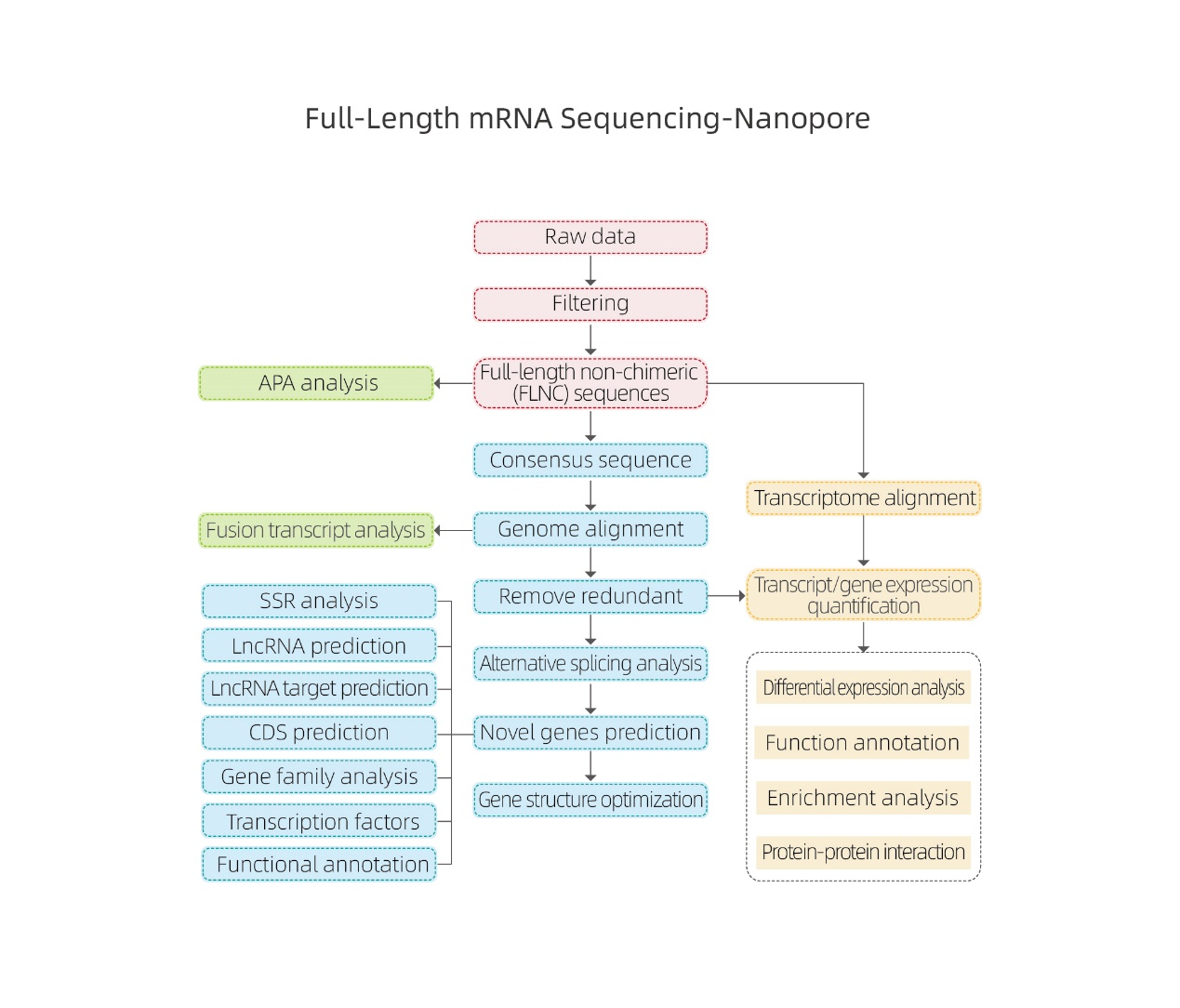
Viso ilgio mRNR sekos nustatymas-nanoporas
Paslaugos privalumai
● Mažas sekos poslinkis
● Atskleidžiančios viso ilgio cDNR molekules
● Tam pačiam nuorašų skaičiui padengti reikia mažiau duomenų
● Kelių izoformų vieno geno identifikavimas
● Išraiškos kiekybinis įvertinimas izoformų lygiu
Paslaugos specifikacijos
| biblioteka | Platforma | Rekomenduojamas duomenų kiekis (Gb) | Kokybės kontrolė |
| cDNR-PCR (praturtintas poli-A) | Nanopore PromethION P48 | 6 Gb/pavyzdys (priklausomai nuo rūšies) | Viso ilgio santykis> 70 % Vidutinis kokybės balas: Q10
|
Bioinformatinės analizės
●Neapdorotų duomenų apdorojimas
● Nuorašo identifikavimas
● Alternatyvus sujungimas
● Išraiškos kiekybinis įvertinimas genų lygiu ir izoformų lygiu
● Diferencinė išraiškų analizė
● Funkcijų anotacija ir praturtinimas (DEG ir DET)
Pavyzdžių reikalavimai ir pristatymas
Pavyzdiniai reikalavimai:
Nukleotidai:
| Konc. (ng/μl) | Kiekis (μg) | Grynumas | Sąžiningumas |
| ≥ 100 | ≥ 0,6 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Ant gelio rodomas ribotas baltymų ar DNR užterštumas arba jo nėra. | Augalams: RIN≥7,0; Gyvūnams: RIN≥7,5; 5,0≥28S/18S≥1,0; ribotas arba jo nėra |
Audinys: Svoris (sausas): ≥1 g
*Audiniams, kurių svoris mažesnis nei 5 mg, rekomenduojame siųsti greitai užšaldytą (skystame azotu) audinių mėginį.
Ląstelių suspensija: ląstelių skaičius = 3 × 106- 1 × 107
*Rekomenduojame siųsti šaldytą ląstelių lizatą.Jei tų ląstelių skaičius mažesnis nei 5×105, rekomenduojamas greitas užšaldymas skystame azote, kuris geriau tinka mikro ekstrahavimui.
Kraujo mėginiai: Tūris≥1 ml
Rekomenduojamas pavyzdžių pristatymas
Talpykla: 2 ml centrifugos mėgintuvėlis (Alavo folija nerekomenduojama)
Mėginio ženklinimas: Grupė+pakartojimas pvz. A1, A2, A3;B1, B2, B3.....
Siuntimas: 2, sausas ledas: mėginiai turi būti supakuoti į maišus ir palaidoti sausame lede.
- RNR stabilūs mėgintuvėliai: RNR mėginius galima džiovinti RNR stabilizavimo mėgintuvėlyje (pvz., RNAstable®) ir gabenti kambario temperatūroje.
Aptarnavimo darbų eiga
Nukleotidai:

Mėginio pristatymas

Bibliotekos statyba

Sekos nustatymas

Duomenų analizė

Paslaugos po pardavimo
Aptarnavimo darbų eiga
Audinys:

Eksperimento dizainas

Mėginio pristatymas

RNR ekstrahavimas

Bibliotekos statyba

Sekos nustatymas

Duomenų analizė

Paslaugos po pardavimo
1.Diferencialinės išraiškos analizė -Vulkano sklypas
Diferencinė ekspresijos analizė gali būti apdorojama tiek genų lygiu, kad būtų galima identifikuoti skirtingai išreikštus genus (DEG), tiek izoformų lygiu, kad būtų galima identifikuoti skirtingai.
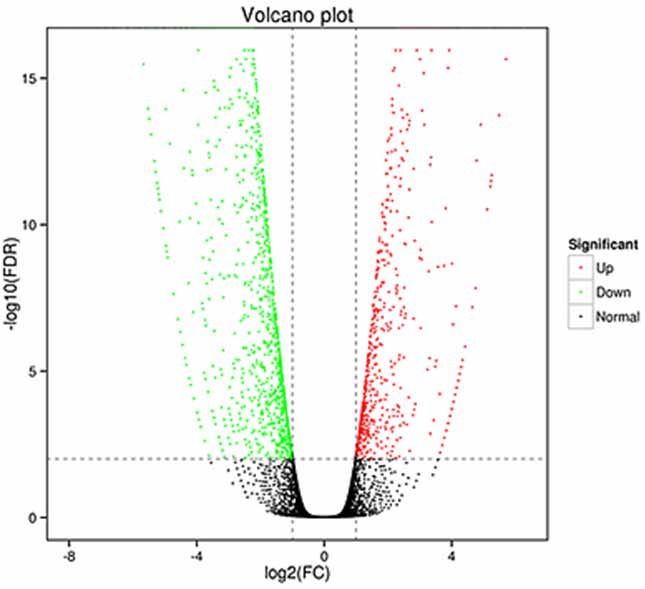
išreikšti nuorašai (DET)
2.Hierarchinis klasterizacijos šilumos žemėlapis
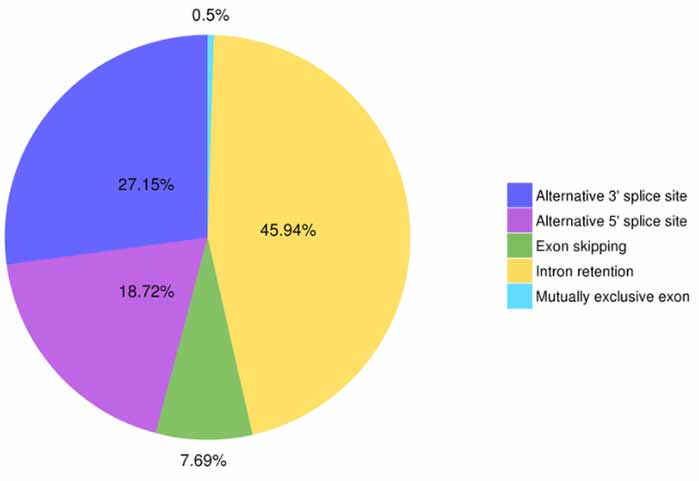
3. Alternatyvus sandūrų identifikavimas ir klasifikavimas
„Astalavista“ gali numatyti penkis alternatyvių sujungimo įvykių tipus.
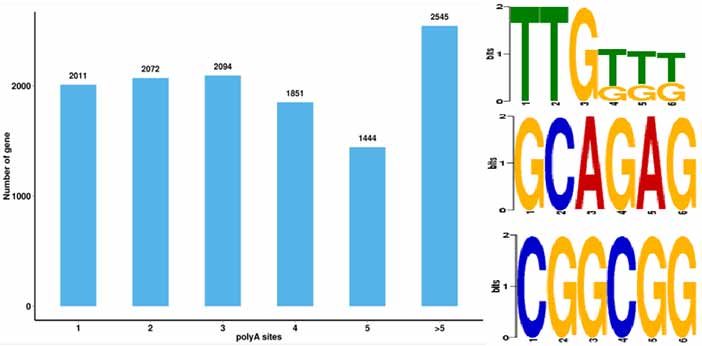
4.Alternatyvių poliadenilinimo (APA) įvykių identifikavimas ir motyvas 50 bp prieš poli-A
BMK dėklas
Alternatyvus sujungimo identifikavimas ir izoformos lygio kiekybinis nustatymas naudojant nanoporų viso ilgio transkripto seką
Paskelbta:Gamtos komunikacijos, 2020 m
Sekos nustatymo strategija:
Grupavimas: 1. CLL-SF3B1(WT);2. CLL-SF3B1 (K700E mutacija);3. Normalios B ląstelės
Sekos nustatymo strategija: MinION 2D bibliotekos sekos nustatymas, PromethION 1D bibliotekos sekos nustatymas;trumpai nuskaityti duomenys iš tų pačių pavyzdžių
Sekos nustatymo platforma: Nanopore MinION;Nanopore PromethION;
Pagrindiniai rezultatai
1. Izoformos lygio alternatyvaus sujungimo identifikavimas
Ilgai skaitytos sekos leidžia identifikuoti mutantą SF3B1K700E- pakeistos sujungimo vietos izoformos lygiu.Nustatyta, kad 35 alternatyvios 3′SS ir 10 alternatyvių 5′SS yra labai skirtingai sujungtos tarp SF3B1K700Eir SF3B1WT.33 iš 35 pakeitimų buvo naujai aptikti ilgai skaitytomis sekomis.
2. Izoformos lygio alternatyvaus sujungimo kiekybinis įvertinimas
Intronų sulaikymo (IR) izoformų raiška SF3B1K700Eir SF3B1WTbuvo kiekybiškai įvertinti remiantis nanoporų sekomis, atskleidžiant visuotinį IR izoformų reguliavimą SF3B1K700E.
Nuoroda
Tang AD, Soulette CM, Baren MJV ir kt.Lėtinės limfocitinės leukemijos SF3B1 mutacijos viso ilgio nuorašo apibūdinimas atskleidžia sumažėjusį sulaikytų intronų reguliavimą [J].Gamtos komunikacijos.