cirRNS sekvencēšana-Illumina
Iespējas
● rRNS izsīkšana, kam seko virziena bibliotēkas sagatavošana, ļaujot sekvencēt datus, kas ir specifiski virknei.
● Bioinformātiskā darbplūsma nodrošina cirRNS prognozēšanu un ekspresijas kvantitatīvo noteikšanu
Pakalpojuma priekšrocības
●Plašākas RNS bibliotēkas:mēs izmantojam rRNS samazināšanos, nevis lineāro RNS samazināšanos mūsu pirmsbibliotēkas sagatavošanā, nodrošinot, ka sekvencēšanas dati ietver ne tikai cirRNS, bet arī mRNS un lncRNS, ļaujot veikt šo datu kopu kopīgu analīzi.
●Izvēles konkurētspējīgu endogēno RNS (ceRNA) tīklu analīze: sniedzot dziļāku ieskatu šūnu regulēšanas mehānismos
●Plaša ekspertīze: ar vairāk nekā 20 000 paraugu apstrādi BMK, kas aptver dažādus paraugu veidus un lncRNA projektus, mūsu komanda katrā projektā ienes bagātīgu pieredzi.
●Stingra kvalitātes kontrole: mēs ieviešam galvenos kontroles punktus visos posmos, sākot no paraugu un bibliotēkas sagatavošanas līdz sekvencēšanai un bioinformātikai.Šī rūpīgā uzraudzība nodrošina nemainīgi augstas kvalitātes rezultātu piegādi.
● Pēcpārdošanas atbalsts: Mūsu saistības sniedzas tālāk par projekta pabeigšanu ar 3 mēnešu pēcpārdošanas servisa periodu.Šajā laikā mēs piedāvājam projekta pārraudzību, problēmu novēršanas palīdzību un jautājumu un atbilžu sesijas, lai risinātu visus ar rezultātiem saistītus vaicājumus.
Prasību paraugs un piegāde
| Bibliotēka | Platforma | Ieteicamie dati | Datu kvalitātes kontrole |
| Poly A bagātināts | Illumina PE150 | 16-20 Gb | Q30≥85% |
Prasību paraugs:
Nukleotīdi:
| Konc. (ng/μl) | Daudzums (μg) | Tīrība | Integritāte |
| ≥ 100 | ≥ 0,5 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Uz gēla parādīts ierobežots proteīnu vai DNS piesārņojums vai tā nav. | Augiem: RIN≥6,5; Dzīvniekiem: RIN≥7,0; 5,0≥28S/18S≥1,0; ierobežots vai vispār nav bāzes līmeņa pacēluma |
● Augi:
Sakne, stublājs vai ziedlapa: 450 mg
Lapa vai sēklas: 300 mg
Augļi: 1,2 g
● Dzīvnieks:
Sirds vai zarnas: 450 mg
Iekšējie orgāni vai smadzenes: 240 mg
Muskuļi: 600 mg
Kauli, mati vai āda: 1,5 g
● Posmkāji:
Kukaiņi: 9g
Vēžveidīgie: 450 mg
● Pilnas asinis:2 caurules
● Šūnas: 106 šūnas
● Serums un plazma: 6 ml
Ieteicamā paraugu piegāde
Tvertne: 2 ml centrifūgas caurule (skārda folija nav ieteicama)
Marķējuma paraugs: grupa + atkārtojums, piemēram, A1, A2, A3;B1, B2, B3......
Sūtījums:
1. Sausais ledus: paraugi jāiepako maisos un jāierok sausajā ledū.
2. RNAstable caurules: RNS paraugus var žāvēt RNS stabilizācijas mēģenē (piemēram, RNAstable®) un nosūtīt istabas temperatūrā.
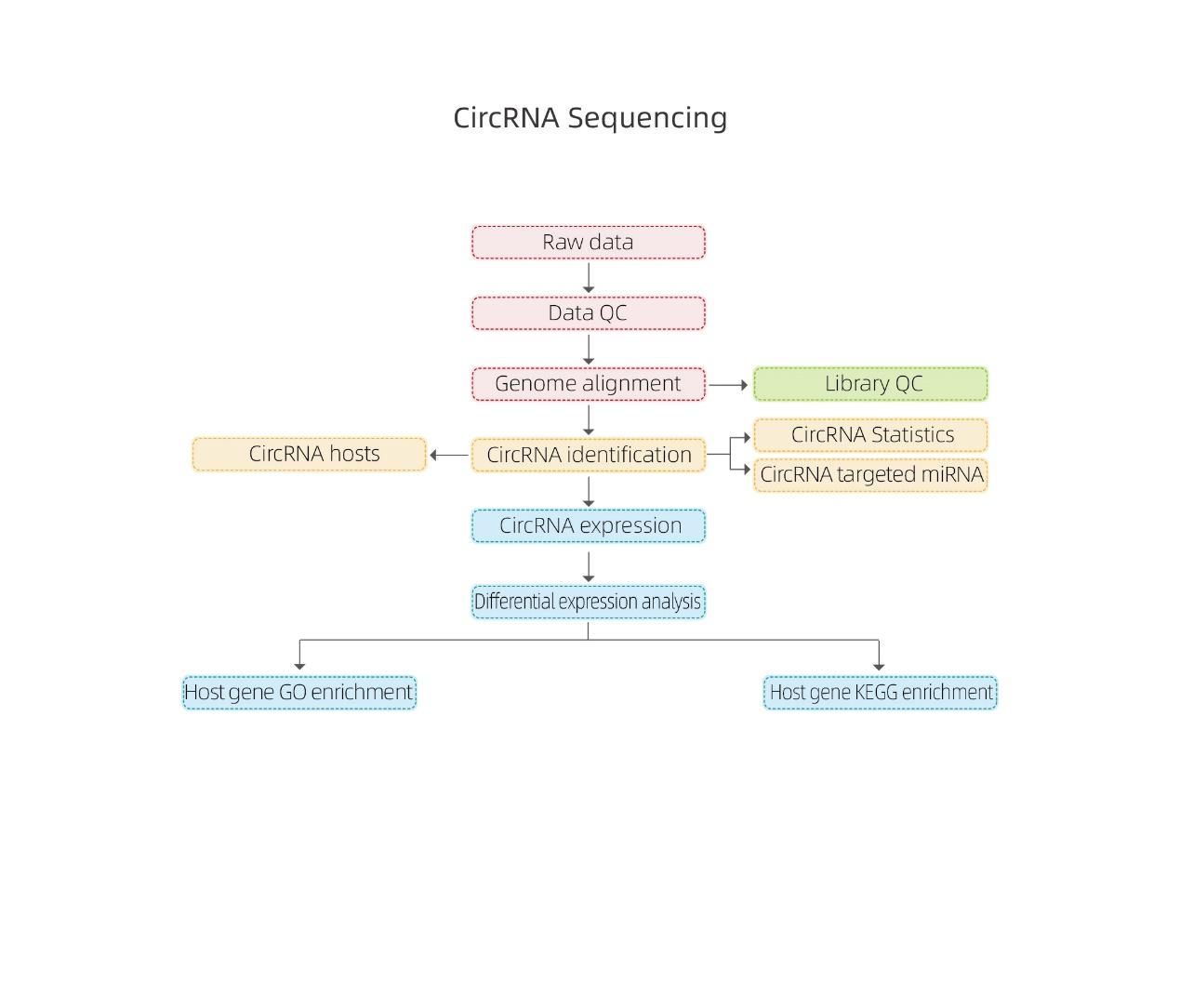
Pakalpojuma darba plūsma

Eksperimenta dizains

Paraugu piegāde

RNS ekstrakcija

Bibliotēkas celtniecība

Secība

Datu analīze

Pēcpārdošanas pakalpojumi
Bioinformātika
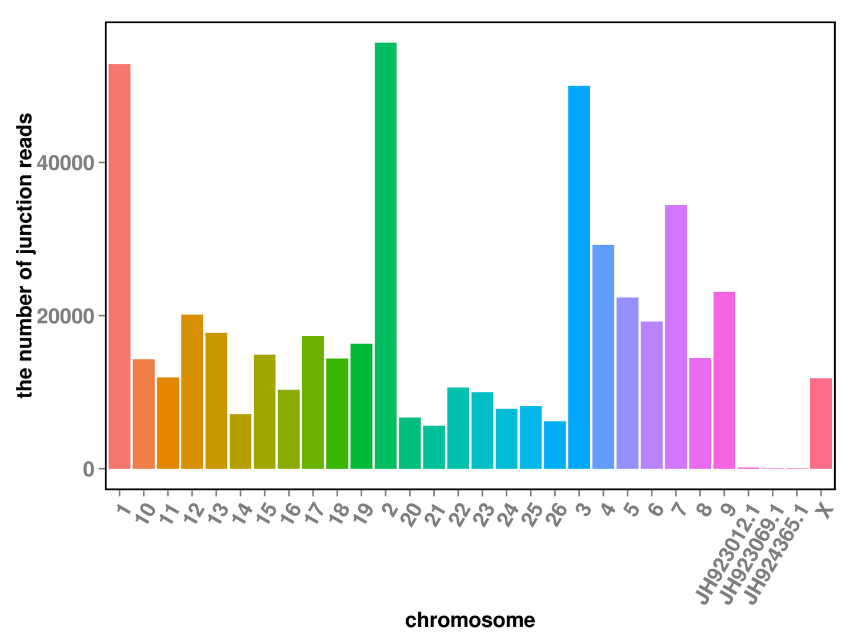
cirRNS prognozēšana: hromosomu sadalījums
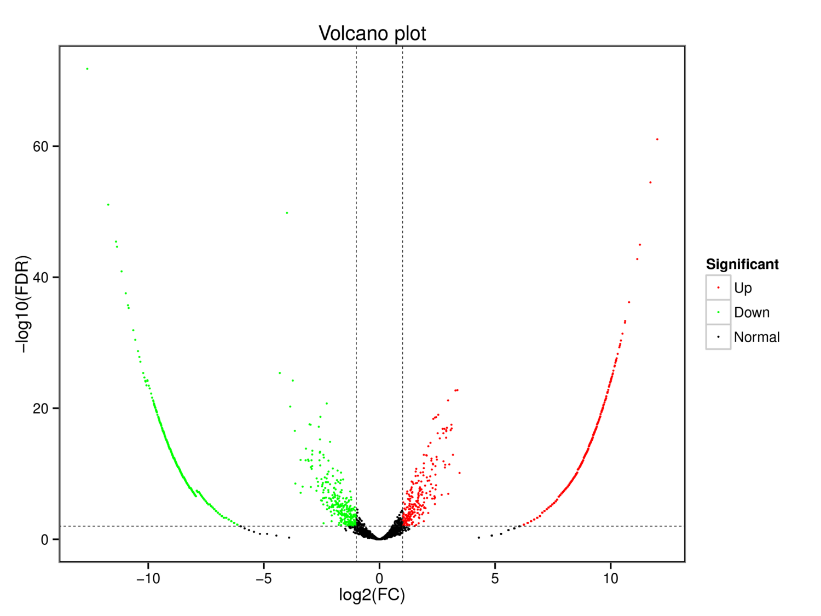
Diferenciāli izteiktas cirRNS – vulkāna grafiks
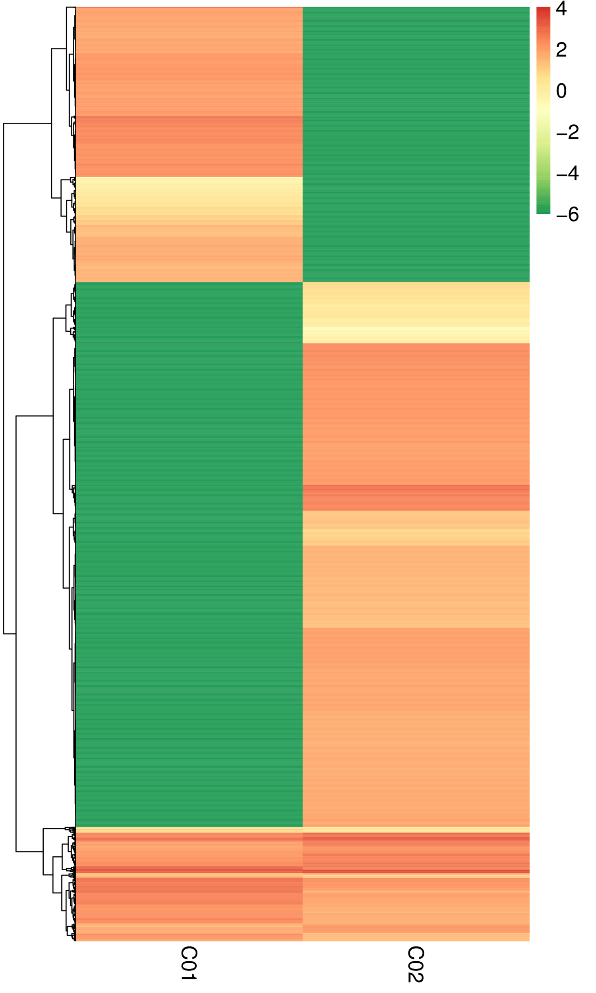
Diferenciāli izteiktas cirRNS – hierarhiska klasterizācija
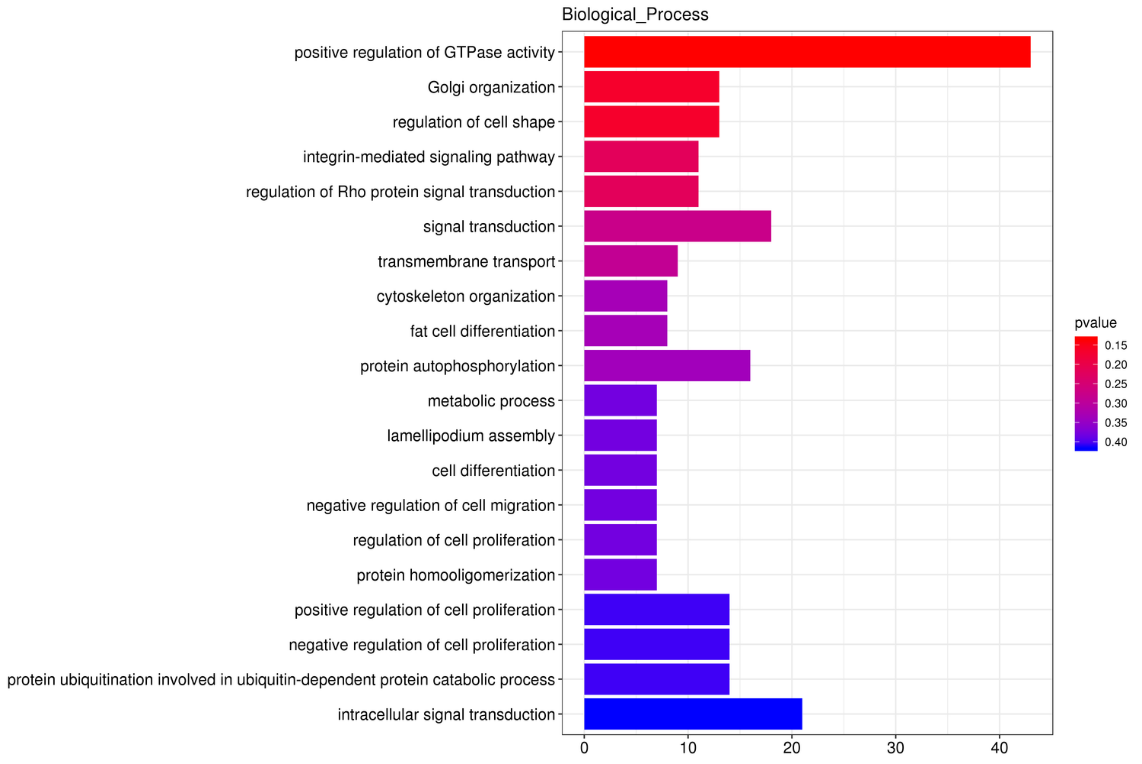
CirRNS saimniekgēnu funkcionālā bagātināšana
Izpētiet pētniecības sasniegumus, ko veicina BMKGene cirRNS sekvencēšanas pakalpojumi, izmantojot apkopotu publikāciju kolekciju.
Wang, X. et al.(2021) “CPSF4 regulē cirRNS veidošanos un mikroRNS mediētu gēnu klusēšanu hepatocelulārā karcinomas gadījumā”, Oncogene 2021, 40:25, 40(25), 4338.–4351. lpp.doi: 10.1038/s41388-021-01867-6.
Xia, K. et al.(2023) “X oo-reaģējošais transkripts atklāj cirkulārās RNS133 lomu slimību rezistencē, regulējot OsARAB ekspresiju rīsos”, Phytopathology Research, 5(1), 1.–14. lpp.doi: 10.1186/S42483-023-00188-8/FIGURES/6.
Y, H. et al.(2023) “CPSF3 modulē cirkulāro un lineāro transkriptu līdzsvaru hepatocelulārā karcinomas gadījumā”.doi: 10.21203/RS.3.RS-2418311/V1.
Džans, Y. et al.(2023) “Visaptverošs cirRNS novērtējums cirozes kardiomiopātijas gadījumā pirms un pēc aknu transplantācijas”, International Immunopharmacology, 114, 1. lpp.109495. doi: 10.1016/J.INTIMP.2022.109495.