
Pilna garuma mRNS sekvencēšana - PacBio
Pakalpojuma priekšrocības
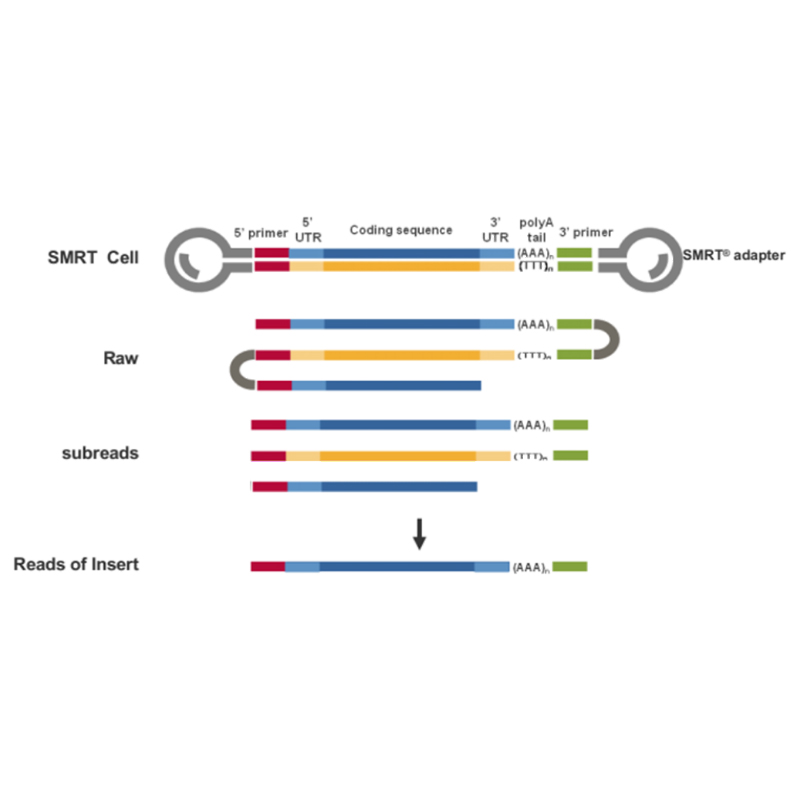
● Tieša pilna garuma cDNS molekulas nolasīšana no 3'-gala līdz 5'-galam
● Izoformas līmeņa izšķirtspēja secības struktūrā
● Atšifrējumi ar augstu precizitāti un integritāti
● Ļoti saderīgs ar vaiours sugām
● Liela sekvencēšanas jauda ar 4 aprīkotām PacBio Sequel II sekvencēšanas platformām
● Liela pieredze darbā ar vairāk nekā 700 RNS sekvencēšanas projektiem, kuru pamatā ir Pacbio
● Uz BMKCloud balstīta rezultātu piegāde: platformā pieejama pielāgota datu ieguve.
● Pēcpārdošanas pakalpojumi spēkā 3 mēnešus pēc projekta pabeigšanas
Pakalpojuma specifikācijas
Platforma: PacBio Sequel II
Sekvencēšanas bibliotēka: ar poli A bagātināta mRNS bibliotēka
Ieteicamais datu apjoms: 20 Gb/paraugs (atkarībā no sugas)
FLNC(%): ≥75%
*FLNC: pilna garuma nehimēriskas transkripcijas
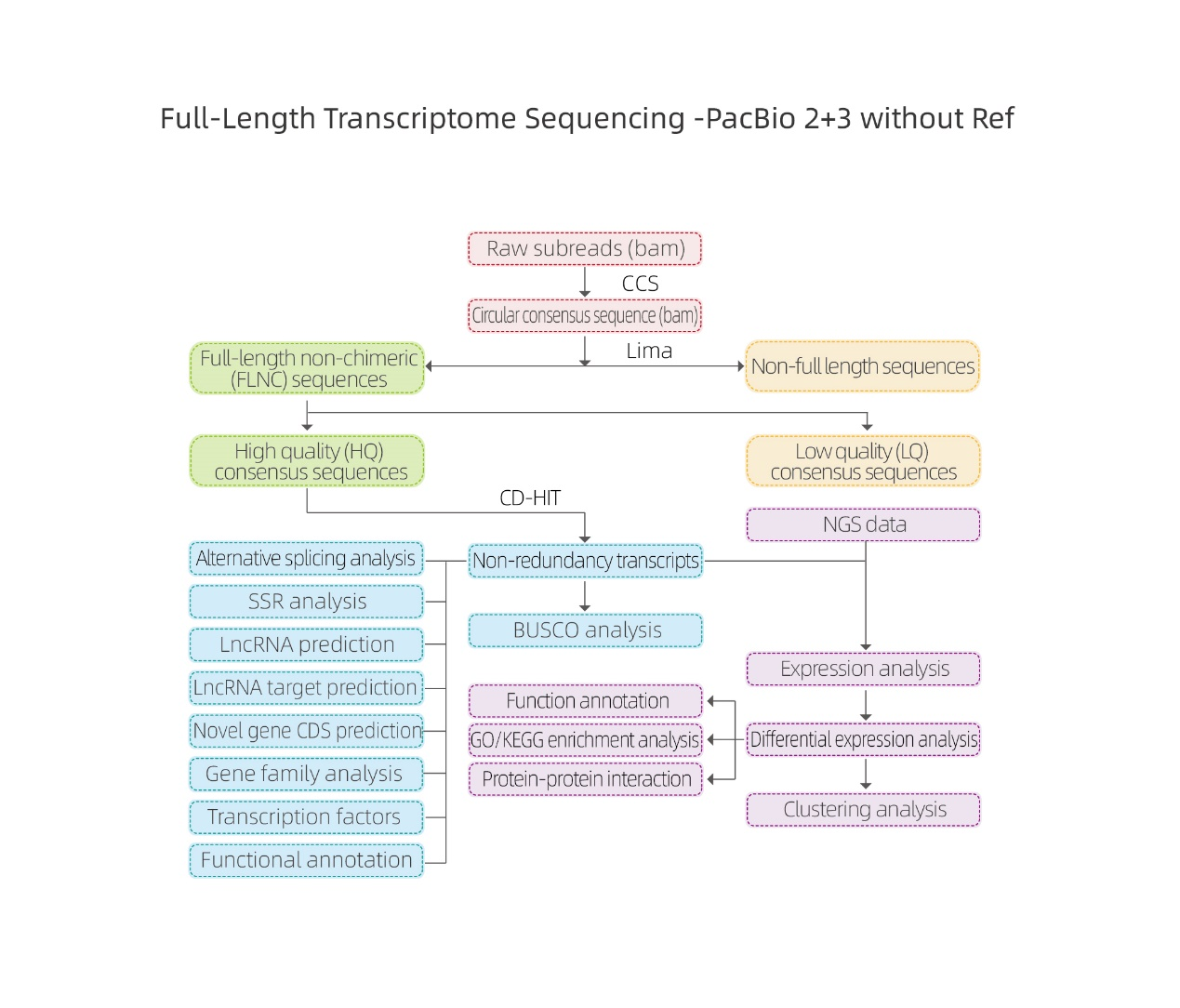
Bioinformātikas analīzes
● Neapstrādātu datu apstrāde
● Atšifrējuma identifikācija
● Secības struktūra
● Izteiksmes kvantifikācija
● Funkciju anotācija
Prasību paraugs un piegāde
Prasību paraugs:
Nukleotīdi:
| Konc. (ng/μl) | Daudzums (μg) | Tīrība | Integritāte |
| ≥ 120 | ≥ 0,6 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Uz gēla parādīts ierobežots proteīnu vai DNS piesārņojums vai tā nav. | Augiem: RIN≥7,5; Dzīvniekiem: RIN≥8,0; 5,0≥ 28S/18S≥1,0; ierobežots vai vispār nav bāzes līmeņa pacēluma |
Audi: svars (sauss):≥1 g
*Audiem, kas ir mazāki par 5 mg, iesakām nosūtīt ātri sasaldētu (šķidrā slāpeklī) audu paraugu.
Šūnu suspensija:Šūnu skaits = 3 × 106- 1 × 107
* Mēs iesakām nosūtīt saldētu šūnu lizātu.Gadījumā, ja šūnu skaits ir mazāks par 5 × 105, ieteicams ātri sasaldēt šķidrā slāpeklī, kas ir vēlams mikro ekstrakcijai.
Asins paraugi:Tilpums ≥1 ml
Mikroorganisms:Masa ≥ 1 g
Ieteicamā paraugu piegāde
Konteiners:
2 ml centrifūgas caurule (skārda folija nav ieteicama)
Marķējuma paraugs: grupa + atkārtojums, piemēram, A1, A2, A3;B1, B2, B3......
Sūtījums:
1. Sausais ledus: paraugi jāiepako maisos un jāierok sausajā ledū.
2. RNAstable caurules: RNS paraugus var žāvēt RNS stabilizācijas mēģenē (piemēram, RNAstable®) un nosūtīt istabas temperatūrā.
Pakalpojuma darba plūsma

Eksperimenta dizains

Paraugu piegāde

RNS ekstrakcija

Bibliotēkas celtniecība

Secība

Datu analīze

Pēcpārdošanas pakalpojumi
1.FLNC garuma sadalījums
Pilna garuma nehimēriskās lasīšanas (FLNC) garums norāda cDNS garumu bibliotēkas konstrukcijā.FLNC garuma sadalījums ir būtisks rādītājs, novērtējot bibliotēkas būvniecības kvalitāti.
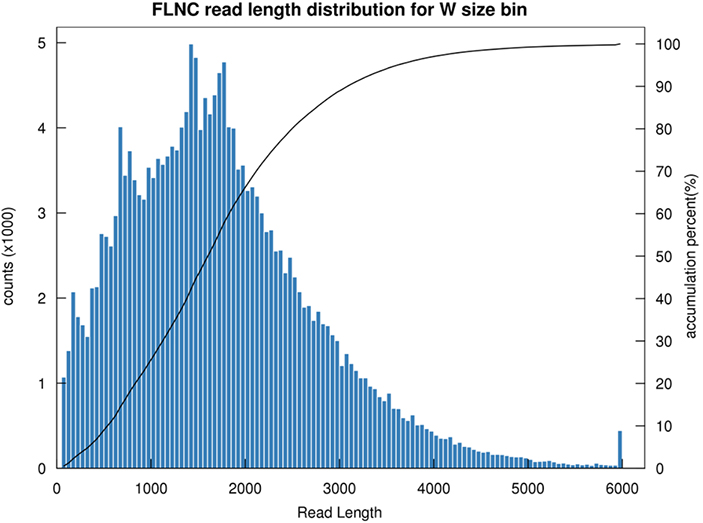
FLNC lasīšanas garuma sadalījums
2. Pilnīgs ORF reģiona garuma sadalījums
Mēs izmantojam TransDecoder, lai prognozētu proteīnu kodēšanas reģionus un atbilstošās aminoskābju sekvences, lai ģenerētu unigēnas kopas, kas visos paraugos satur pilnīgu nelieku transkripta informāciju.
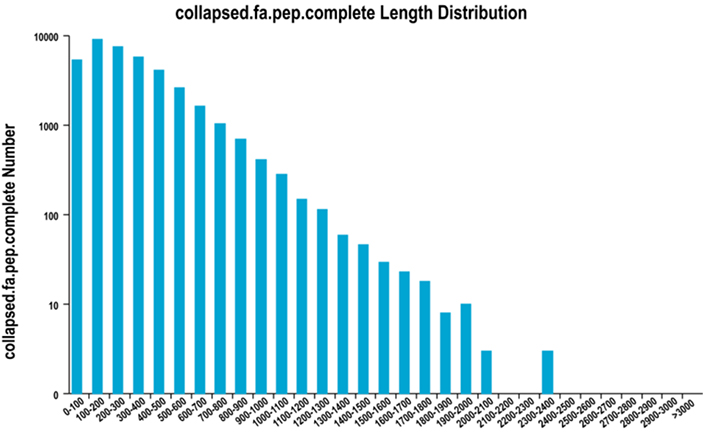
Pilnīgs ORF reģiona garuma sadalījums
3.KEGG ceļa bagātināšanas analīze
Atšķirīgi izteiktus transkriptus (DET) var identificēt, saskaņojot uz NGS balstītus RNS sekvencēšanas datus pilna garuma transkriptu kopām, ko ģenerē PacBio sekvencēšanas dati.Šos DET var tālāk apstrādāt dažādām funkcionālām analīzēm, piemēram, KEGG ceļa bagātināšanas analīzei.
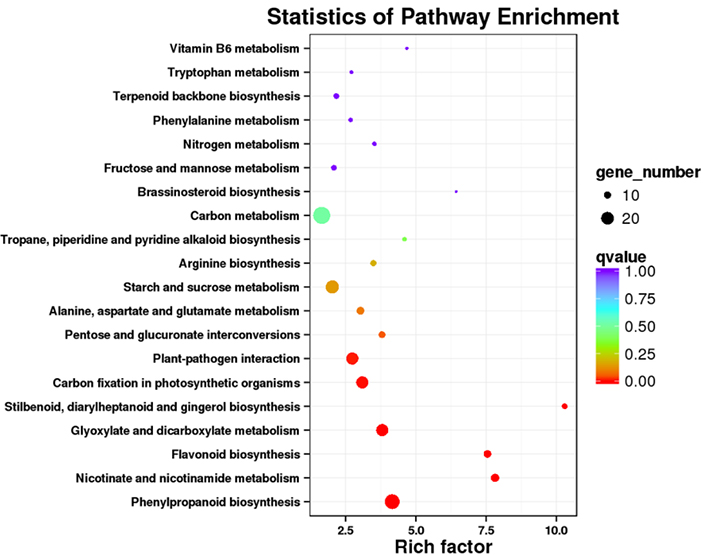
DET KEGG ceļa bagātināšana - Punktu diagramma
BMK lieta
Populus stumbra transkripta attīstības dinamika
Publicēts: Augu biotehnoloģijas žurnāls, 2019. gads
Secības noteikšanas stratēģija:
Paraugu kolekcija:cilmes reģioni: virsotne, pirmais starpmezgls (IN1), otrais starpmezgls (IN2), trešais starpmezgls (IN3), starpmezgls (IN4) un starpmezgls (IN5) no Nanlin895
NGS secība:15 indivīdu RNS tika apvienotas kā viens bioloģiskais paraugs.NGS secībai tika apstrādāti trīs katra punkta bioloģiskie atkārtojumi
TGS secība:Stumbra reģioni tika sadalīti trīs reģionos, ti, virsotnē, IN1-IN3 un IN4-IN5.Katrs reģions tika apstrādāts PacBio sekvencēšanai ar četru veidu bibliotēkām: 0-1 kb, 1-2 kb, 2-3 kb un 3-10 kb.
Galvenie rezultāti
1.Kopā tika identificēti 87150 pilna garuma transkripti, kuros identificēta 2081 jauna izoforma un 62058 jaunas alternatīvas savienotās izoformas.
Tika identificēti 2,1187 lncRNS un 356 saplūšanas gēni.
3. No primārās augšanas līdz sekundārajai augšanai tika identificēti 15838 atšķirīgi izteikti transkripti no 995 atšķirīgi ekspresētiem gēniem.Visos DEG 1216 bija transkripcijas faktori, no kuriem lielākā daļa vēl nav ziņots.
4.GO bagātināšanas analīze atklāja šūnu dalīšanās un oksidācijas-reducēšanās procesa nozīmi primārajā un sekundārajā augšanā.
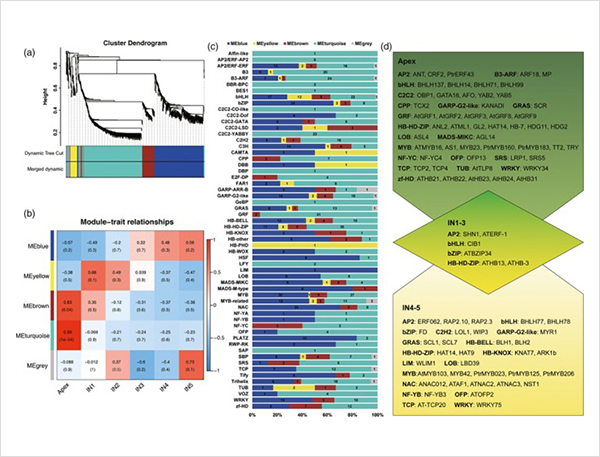
Alternatīvi splicēšanas notikumi un dažādas izoformas
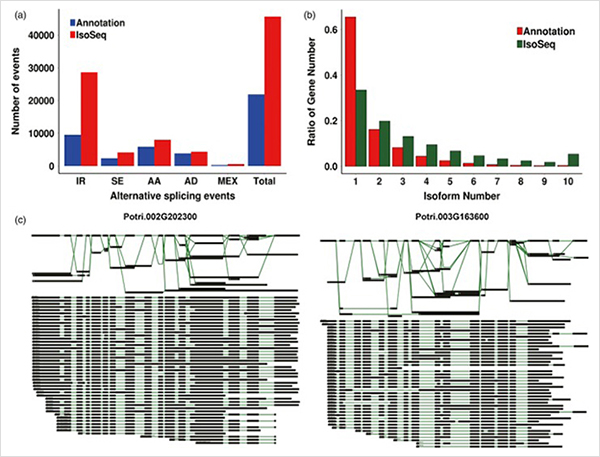
WGCNA analīze par transkripcijas faktoriem
Atsauce
Chao Q, Gao ZF, Zhang D u.c.Populus stumbra transkripta attīstības dinamika.Plant Biotechnol J. 2019;17(1):206-219.doi:10.1111/pbi.12958











