
Evolūcijas ģenētika
Pakalpojuma priekšrocības
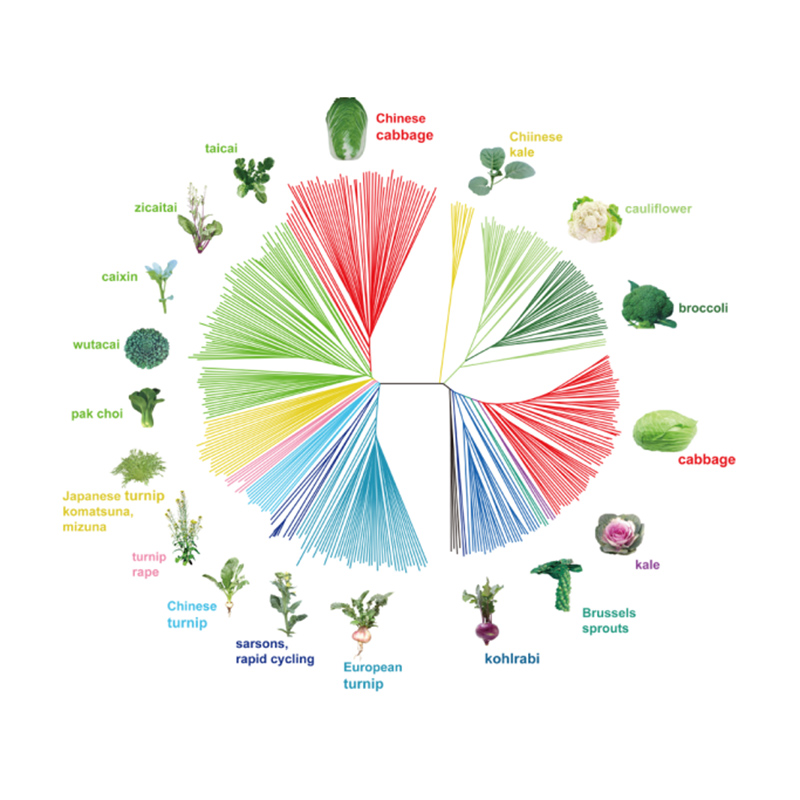
Takagi et al.,Augu žurnāls, 2013. gads
● sugu atšķirības laika un ātruma novērtēšana, pamatojoties uz variācijām nukleotīdu un aminoskābju līmenī
● uzticamākas filoģenētiskās attiecības atklāšana starp sugām ar minimālu konverģentas evolūcijas un paralēlās evolūcijas ietekmi
● Saikņu veidošana starp ģenētiskajām izmaiņām un fenotipiem, lai atklātu ar pazīmēm saistītus gēnus
● ģenētiskās daudzveidības novērtēšana, kas atspoguļo sugu evolūcijas potenciālu
● Ātrāks izpildes laiks
● Plaša pieredze: BMK ir uzkrājusi milzīgu pieredzi ar populāciju un evolūciju saistītos projektos vairāk nekā 12 gadu garumā, aptverot simtiem sugu utt., un ir piedalījusies vairāk nekā 80 augsta līmeņa projektos, kas publicēti Nature Communications, Molecular Plants, Plant Biotechnology Journal u.c.
Pakalpojuma specifikācijas
Materiāli:
Parasti ir ieteicamas vismaz trīs apakšpopulācijas (piemēram, pasugas vai celmi).Katrā apakšpopulācijā jābūt ne mazāk kā 10 īpatņiem (augi >15, var samazināt retām sugām).
Secības noteikšanas stratēģija:
* WGS var izmantot sugām ar augstas kvalitātes atsauces genomu, savukārt SLAF-Seq ir piemērojams sugām ar vai bez atsauces genoma vai sliktas kvalitātes atsauces genoma.
| Attiecas uz genoma izmēru | WGS | SLAF-birkas (×10 000) |
| ≤ 500 Mb | 10×/individuāli | WGS ir vairāk ieteicama |
| 500 Mb - 1 Gb | 10 | |
| 1 Gb - 2 Gb | 20 | |
| ≥2 Gb | 30 |
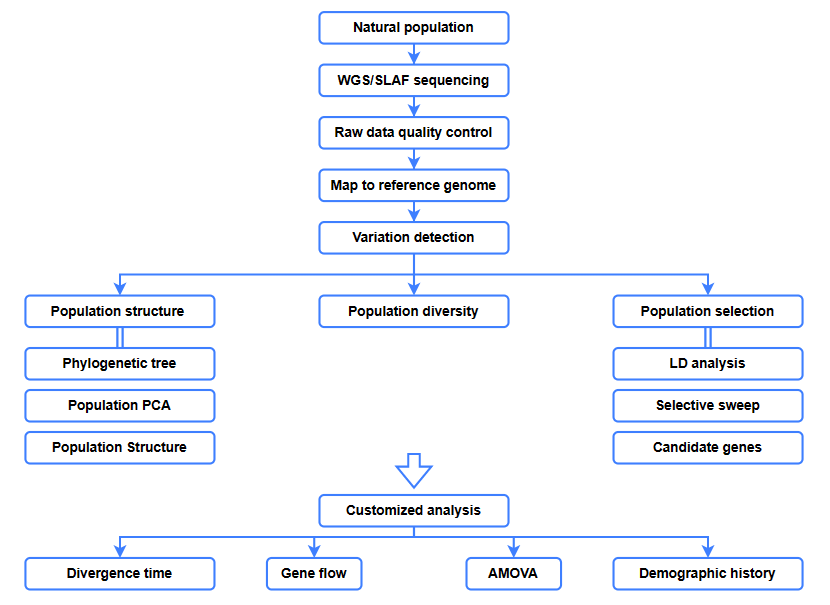
Bioinformātikas analīzes
● Evolūcijas analīze
● Selektīva slaucīšana
● Gēnu plūsma
● Demogrāfiskā vēsture
● Diverģences laiks
Prasību paraugs un piegāde
Prasību paraugs:
| Sugas | Audu | WGS-NGS | SLAF |
| Dzīvnieks
| Viscerālie audi |
0,5-1 g
|
0,5 g
|
| Muskuļu audi | |||
| Zīdītāju asinis | 1,5 ml
| 1,5 ml
| |
| Mājputnu/zivju asinis | |||
| Augu
| Svaiga Lapa | 1-2 g | 0,5-1 g |
| Ziedlapa/Stumbrs | |||
| Sakne/Sēkla | |||
| Šūnas | Kultivēta šūna |
| gDNS | Koncentrēšanās | Summa (ug) | OD260/OD280 |
| SLAF | ≥35 | ≥1,6 | 1,6-2,5 |
| WGS-NGS | ≥1 | ≥0,1 | - |
Pakalpojuma darba plūsma

Eksperimenta dizains

Paraugu piegāde

Bibliotēkas celtniecība

Secība

Datu analīze

Pēcpārdošanas pakalpojumi
*Šeit parādītie demonstrācijas rezultāti ir no genomiem, kas publicēti ar BMKGENE
1.Evolūcijas analīze ietver filoģenētiskā koka uzbūvi, populācijas struktūru un PCA, pamatojoties uz ģenētiskajām variācijām.
Filoģenētiskais koks atspoguļo taksonomiskās un evolūcijas attiecības starp sugām, kurām ir kopīgs sencis.
PCA mērķis ir vizualizēt tuvumu starp apakšpopulācijām.
Populācijas struktūra parāda ģenētiski atšķirīgu apakšpopulāciju klātbūtni alēļu biežuma izteiksmē.
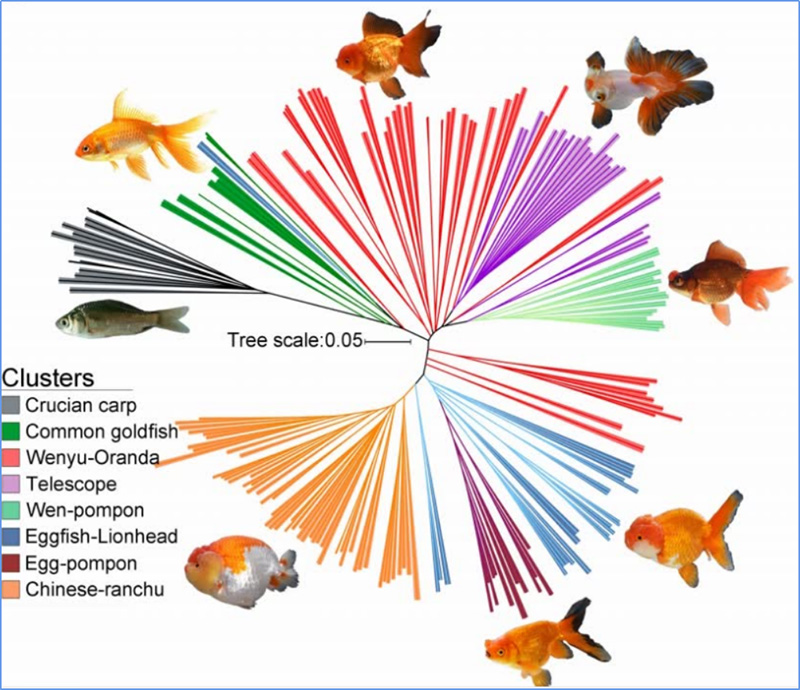
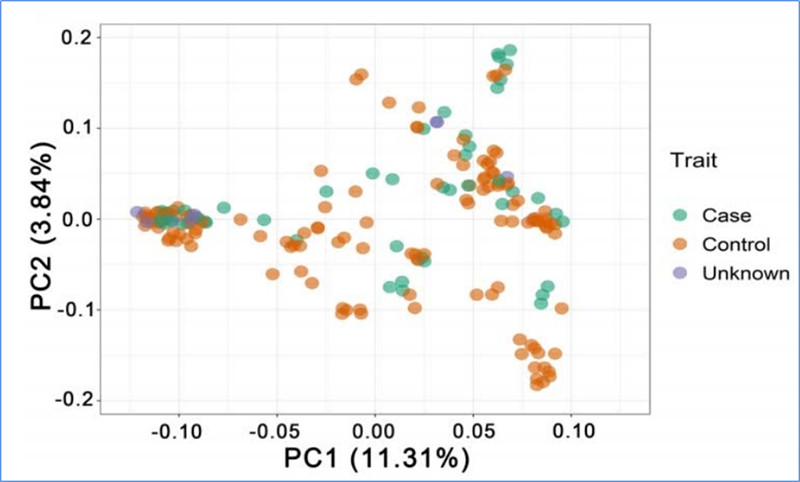
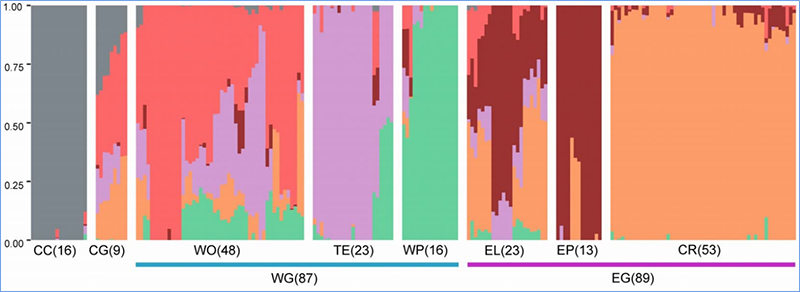
Čens u.c.al.,PNAS, 2020. gads
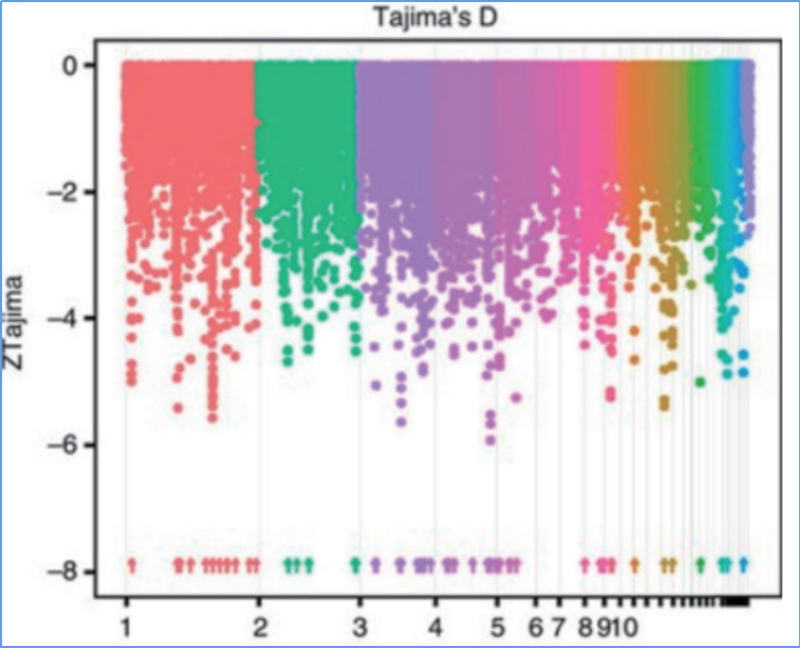
2.Selektīva slaucīšana
Selektīvā slaucīšana attiecas uz procesu, kurā tiek izvēlēta izdevīga vietne un palielināts saistīto neitrālo vietņu biežums un samazināts nesaistīto vietņu biežums, kā rezultātā samazinās reģionālais.
Genoma mēroga noteikšana selektīvos slaucīšanas reģionos tiek apstrādāta, aprēķinot visu SNP populācijas ģenētisko indeksu (π,Fst, Tajima's D) bīdāmā logā (100 Kb) noteiktā solī (10 Kb).
Nukleotīdu daudzveidība (π)
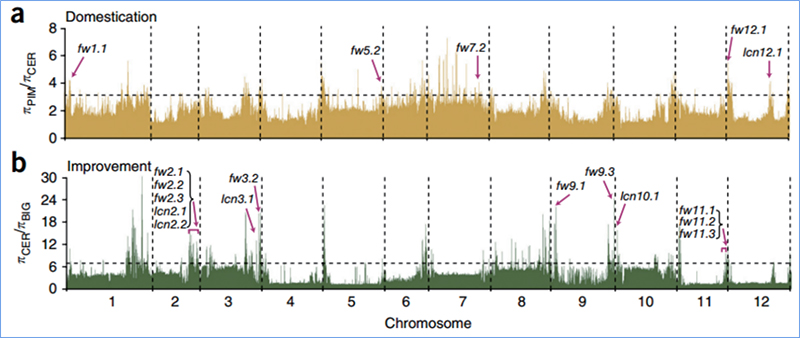
Tadžima D
Fiksācijas indekss (Fst)
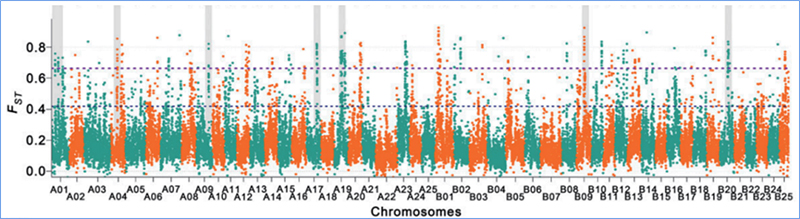
Wu u.c.al.,Molekulārais augs, 2018. gads
3.Gēnu plūsma
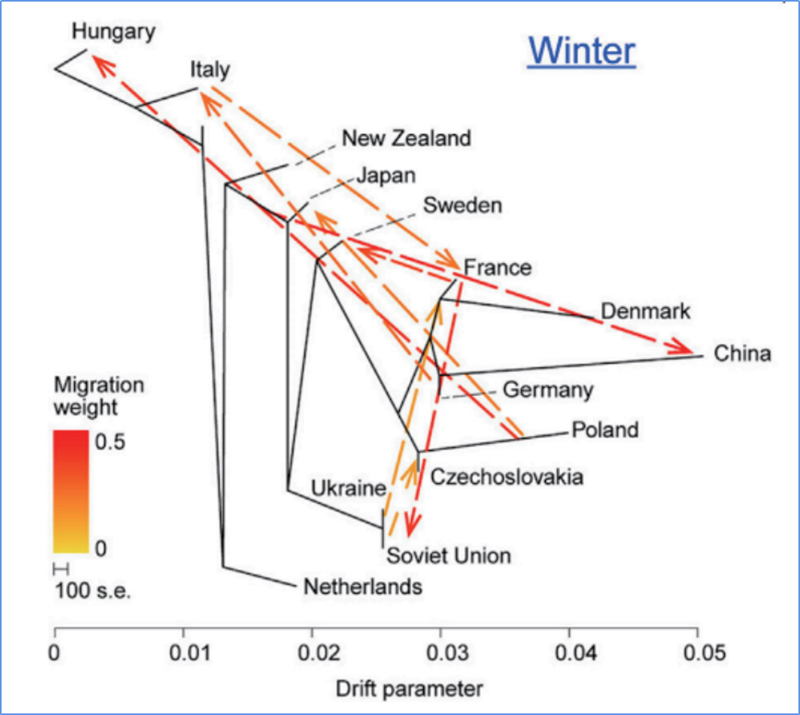
Wu u.c.al.,Molekulārais augs, 2018. gads
4.Demogrāfiskā vēsture
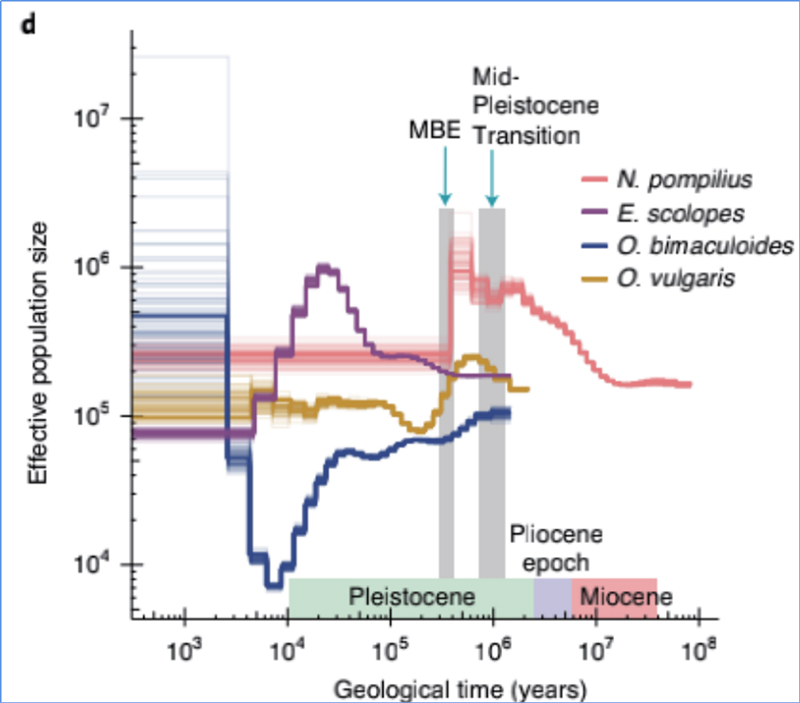
Džans u.c.al.,Dabas ekoloģija un evolūcija, 2021. gads
5.Diverģences laiks
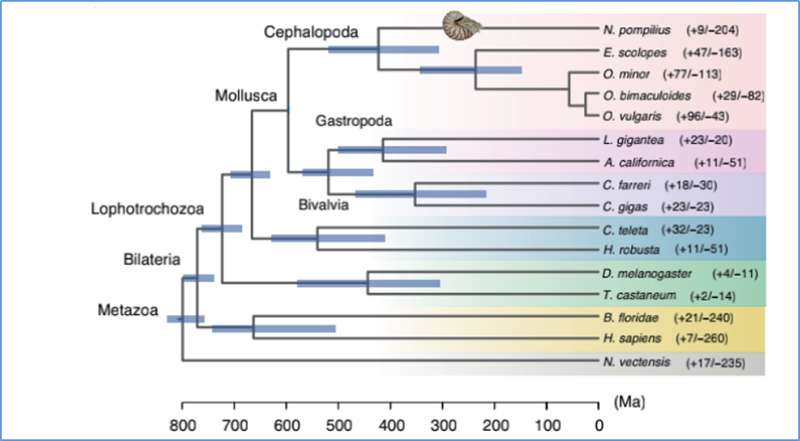
Džans u.c.al.,Dabas ekoloģija un evolūcija, 2021. gads
BMK lieta
Genomisko variāciju karte sniedz ieskatu pavasara Ķīnas kāpostu (Brassica rapa ssp. Pekinensis) selekcijas ģenētiskajā pamatā.
Publicēts: Molekulārais augs, 2018. gads
Secības noteikšanas stratēģija:
Atkārtota secība: secības dziļums: 10×
Galvenie rezultāti
Šajā pētījumā 194 Ķīnas kāposti tika apstrādāti atkārtotai sekvencēšanai ar vidējo dziļumu 10 ×, kas deva 1 208 499 SNP un 416 070 InDels.Šo 194 līniju filoģenētiskā analīze parādīja, ka šīs līnijas var iedalīt trīs ekotipos - pavasarī, vasarā un rudenī.Turklāt populācijas struktūra un PCA analīze liecināja, ka pavasara Ķīnas kāposti tika iegūti no rudens kāpostiem Shandong, Ķīnā.Pēc tam tos ieveda Korejā un Japānā, krustoja ar vietējām līnijām, un dažas to vēlīnās šķirnes tika ievestas atpakaļ Ķīnā un beidzot kļuva par pavasara Ķīnas kāpostiem.
Pavasara Ķīnas kāpostu un rudens kāpostu selekcijas genoma mēroga skenēšana atklāja 23 genoma lokusus, kuriem tika veikta spēcīga atlase, no kuriem divi pārklājās ar skrūvēšanas laika kontroles reģionu, pamatojoties uz QTL kartēšanu.Tika konstatēts, ka šajos divos reģionos ir galvenie gēni, kas regulē ziedēšanu, BrVIN3.1 un BrFLC1.Šie divi gēni tika apstiprināti, ka tie ir iesaistīti skrūvēšanas laikā, izmantojot transkripta pētījumu un transgēnu eksperimentus.
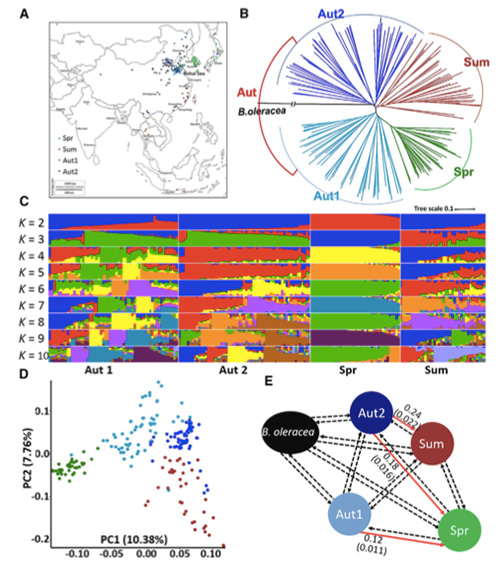 Pekinas kāpostu populācijas struktūras analīze | 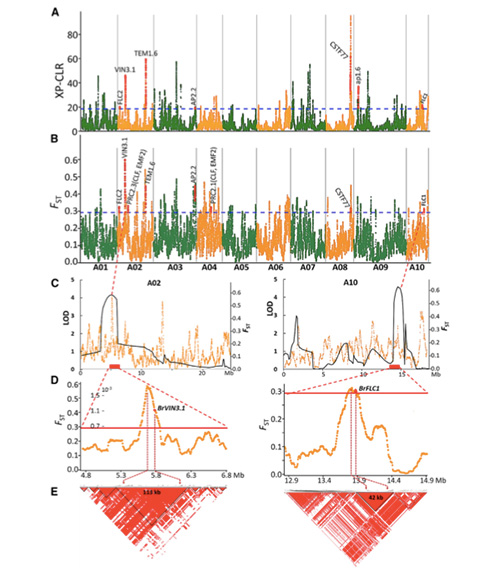 Ģenētiskā informācija par Ķīnas kāpostu izvēli |
Tongbings u.c."Genomisko variāciju karte sniedz ieskatu pavasara Ķīnas kāpostu (Brassica rapa ssp.pekinensis) selekcijas ģenētiskajā pamatā."Molekulārie augi,11(2018): 1360-1376.















