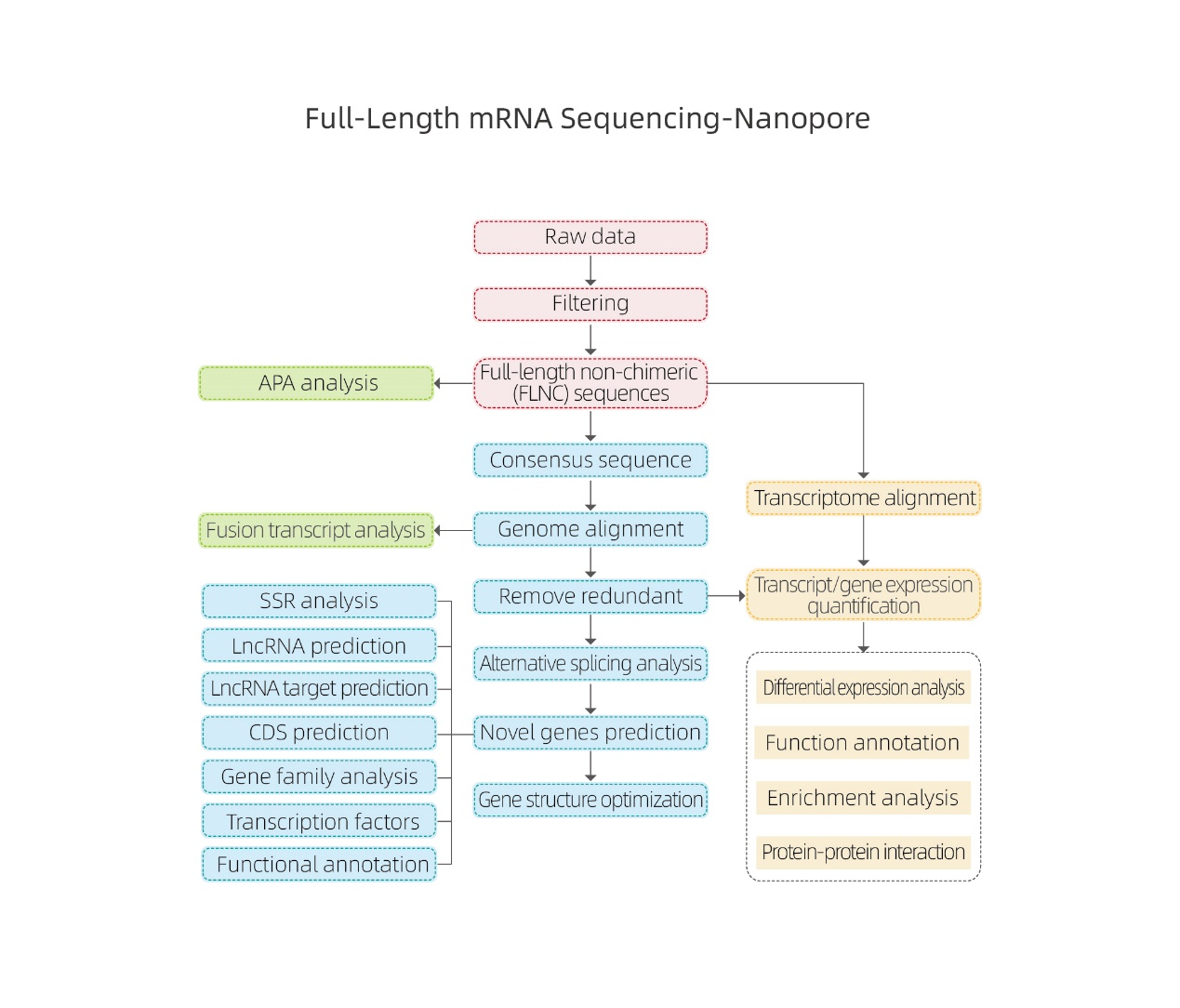
Pilna garuma mRNS sekvencēšana-nanopore
Pakalpojuma priekšrocības
● Zema secības novirze
● Pilna garuma cDNS molekulu atklāšana
● Nepieciešams mazāk datu, lai aptvertu tādu pašu atšifrējumu skaitu
● Vairāku izoformu identificēšana vienā gēnā
● Izteiksmes kvantitatīva noteikšana izoformu līmenī
Pakalpojuma specifikācijas
| Bibliotēka | Platforma | Ieteicamais datu apjoms (Gb) | Kvalitātes kontrole |
| cDNS-PCR (bagātināts ar poli-A) | Nanopore PromethION P48 | 6 Gb/paraugs (atkarībā no sugas) | Pilna garuma attiecība>70% Vidējais kvalitātes rādītājs: Q10
|
Bioinformātikas analīzes
●Neapstrādātu datu apstrāde
● Atšifrējuma identifikācija
● Alternatīva savienošana
● Ekspresijas kvantitatīva noteikšana gēnu līmenī un izoformu līmenī
● Diferenciālās izteiksmes analīze
● Funkciju anotācija un bagātināšana (DEG un DET)
Prasību paraugs un piegāde
Prasību paraugs:
Nukleotīdi:
| Konc. (ng/μl) | Daudzums (μg) | Tīrība | Integritāte |
| ≥ 100 | ≥ 0,6 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Uz gēla parādīts ierobežots proteīnu vai DNS piesārņojums vai tā nav. | Augiem: RIN≥7,0; Dzīvniekiem: RIN≥7,5; 5,0≥28S/18S≥1,0; ierobežots vai vispār nav bāzes līmeņa pacēluma |
Audi: svars (sauss): ≥1 g
*Audiem, kas ir mazāki par 5 mg, iesakām nosūtīt ātri sasaldētu (šķidrā slāpeklī) audu paraugu.
Šūnu suspensija: Šūnu skaits = 3 × 106- 1 × 107
* Mēs iesakām nosūtīt saldētu šūnu lizātu.Gadījumā, ja šūnu skaits ir mazāks par 5 × 105, ieteicams ātri sasaldēt šķidrā slāpeklī, kas ir vēlams mikro ekstrakcijai.
Asins paraugi: Tilpums≥1 ml
Ieteicamā paraugu piegāde
Tvertne: 2 ml centrifūgas caurule (skārda folija nav ieteicama)
Marķējuma paraugs: grupa + atkārtojums, piemēram, A1, A2, A3;B1, B2, B3......
Sūtījums: 2. Sausais ledus: Paraugi jāiepako maisos un jāierok sausajā ledū.
- RNS stabilas caurules: RNS paraugus var žāvēt RNS stabilizācijas mēģenē (piemēram, RNAstable®) un nosūtīt istabas temperatūrā.
Pakalpojuma darba plūsma
Nukleotīdi:

Paraugu piegāde

Bibliotēkas celtniecība

Secība

Datu analīze

Pēcpārdošanas pakalpojumi
Pakalpojuma darba plūsma
Audi:

Eksperimenta dizains

Paraugu piegāde

RNS ekstrakcija

Bibliotēkas celtniecība

Secība

Datu analīze

Pēcpārdošanas pakalpojumi
1.Diferenciālās izteiksmes analīze - Vulkāna gabals
Diferenciālās ekspresijas analīzi var apstrādāt gan gēnu līmenī, lai identificētu diferencēti ekspresētus gēnus (DEG), gan izoformas līmenī, lai identificētu atšķirīgi
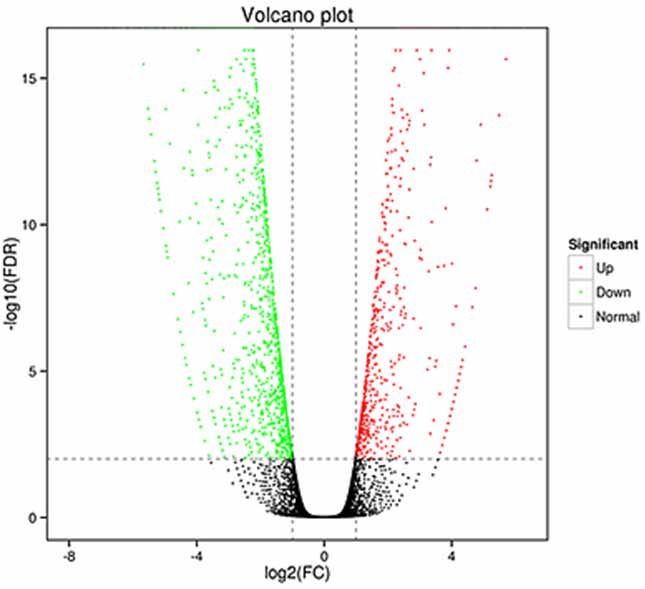
izteiktie atšifrējumi (DET)
2.Hierarhiskā klasteru siltuma karte
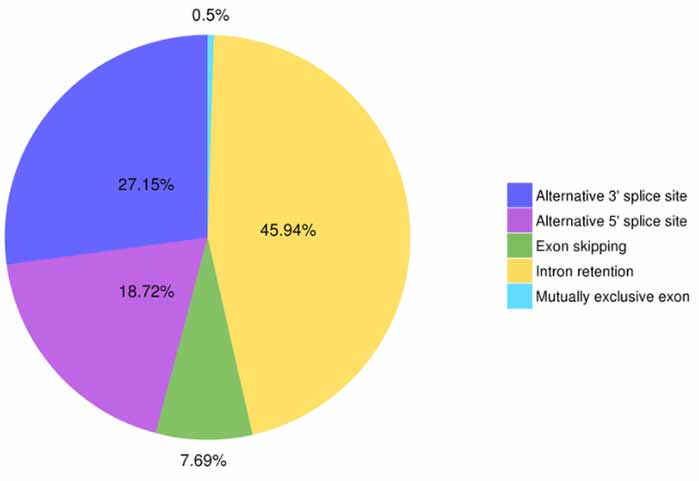
3. Alternatīvā savienojuma identifikācija un klasifikācija
Astalavista var paredzēt piecus alternatīvu savienošanas notikumu veidus.
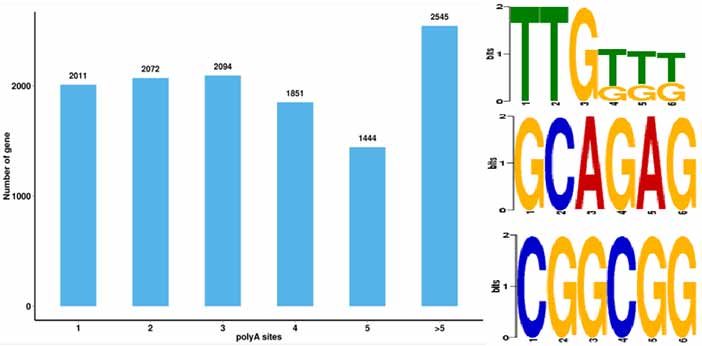
4.Alternatīvu poliadenilācijas (APA) notikumu identifikācija un motīvs 50 bp augšpus poli-A
BMK lieta
Alternatīva savienojuma identifikācija un izoformas līmeņa kvantitatīva noteikšana ar nanoporu pilna garuma transkripta sekvencēšanu
Publicēts:Dabas sakari, 2020
Secības noteikšanas stratēģija:
Grupēšana: 1. CLL-SF3B1(WT);2. CLL-SF3B1 (K700E mutācija);3. Normālas B-šūnas
Sekvencēšanas stratēģija: MinION 2D bibliotēkas sekvencēšana, PromethION 1D bibliotēkas sekvencēšana;īsi nolasīti dati no tiem pašiem paraugiem
Sekvencēšanas platforma: Nanopore MinION;Nanopore PromethION;
Galvenie rezultāti
1. Izoformas līmeņa alternatīvās savienošanas identifikācija
Ilgi lasītas sekvences ļauj identificēt mutantu SF3B1K700E-izmainītas savienojuma vietas izoformas līmenī.Tika konstatēts, ka 35 alternatīvas 3′SS un 10 alternatīvas 5′SS ir ievērojami atšķirīgi savienotas starp SF3B1K700Eun SF3B1WT.33 no 35 izmaiņām tika jaunatklātas ar ilgi lasītām sekvencēm.
2. Izoformas līmeņa alternatīvās savienošanas kvantitatīva noteikšana
Intronu aiztures (IR) izoformu ekspresija SF3B1K700Eun SF3B1WTtika kvantificēti, pamatojoties uz nanoporu sekvencēm, atklājot globālu infrasarkano izoformu pazemināšanos SF3B1K700E.
Atsauce
Tang AD, Soulette CM, Baren MJV u.c.SF3B1 mutācijas pilna garuma transkripta raksturojums hroniskas limfoleikozes gadījumā atklāj saglabāto intronu [J] pazemināšanos.Dabas sakari.