Genoma mēroga asociācijas analīze
1. Pakalpojuma priekšrocības
● Daudzas projektu lietas: kopš tās dibināšanas 2009. gadā BMKGENE ir pabeidzis simtiem sugu projektu populācijas GWAS izpētē, palīdzējis pētniekiem publicēt vairāk nekā 100 rakstus, un kumulatīvā ietekmes faktors sasniedza 500.
● Profesionāli analītiķi.
● Īss analīzes cikls.
● Precīza datu ieguve.
2. Pakalpojuma specifikācijas
| Tips | Iedzīvotāju skala | Sekvences stratēģija un dziļums |
| SLAF-GWAS | Parauga numurs ≥200 | Genoma izmērs < 400 M, ar ref-genomu ieteicams izmantot WGS |
| Genoma lielums ≤ 1G, 100K tagi un 10X | ||
| 1 G ≤ Genoma izmērs ≤ 2 G, 200 000 tagu un 10 X | ||
| Genoma izmērs > 2G, 300K tagi un 10X | ||
| WGS-GWAS | Parauga numurs ≥200 | 10X katram paraugam |
3. Materiālu izvēle



Dažādas šķirnes, pasugas, zemes rases/gēnu bankas/jauktas ģimenes/savvaļas resursi
Dažādas šķirnes, pasugas, zemes rases
Pusmāšu ģimene/pilna brāļa ģimene/savvaļas resursi
4. Bioinformācijas analīze
● Genoma mēroga asociācijas analīze
● Nozīmīgu SNP analīze un skrīnings
● Kandidāta gēna funkcionālā anotācija
5. Servisa darba plūsma

Eksperimenta dizains

Paraugu piegāde

RNS ekstrakcija

Bibliotēkas celtniecība

Secība

Datu analīze

Pēcpārdošanas pakalpojumi
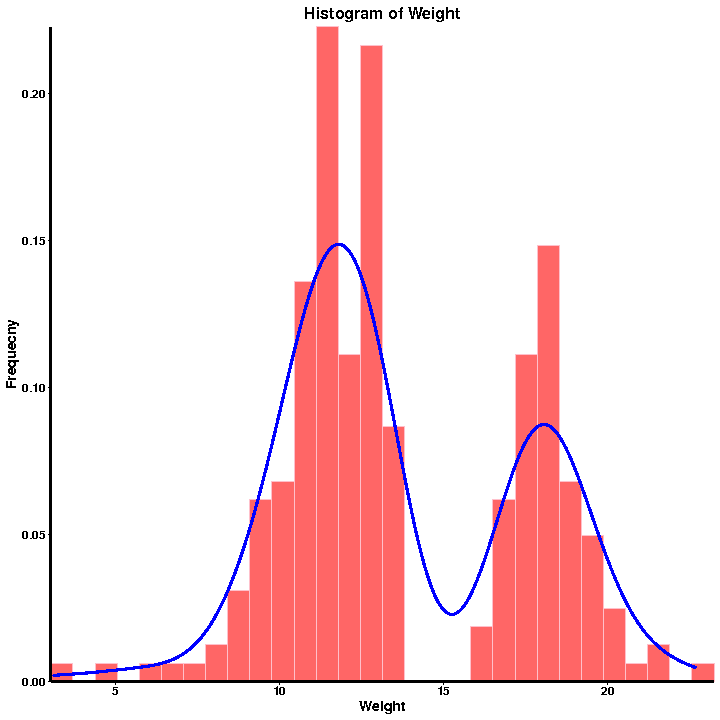
a.QC fenotips
Frekvences sadalījuma histogramma
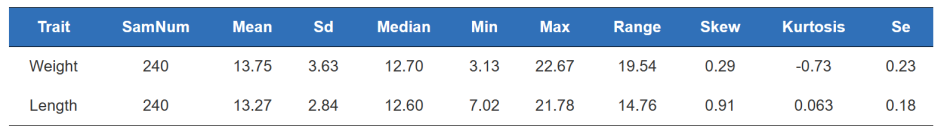
Fenotipu statistika
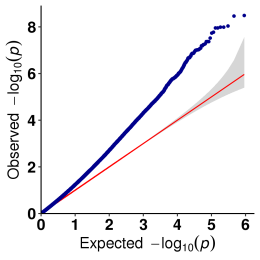
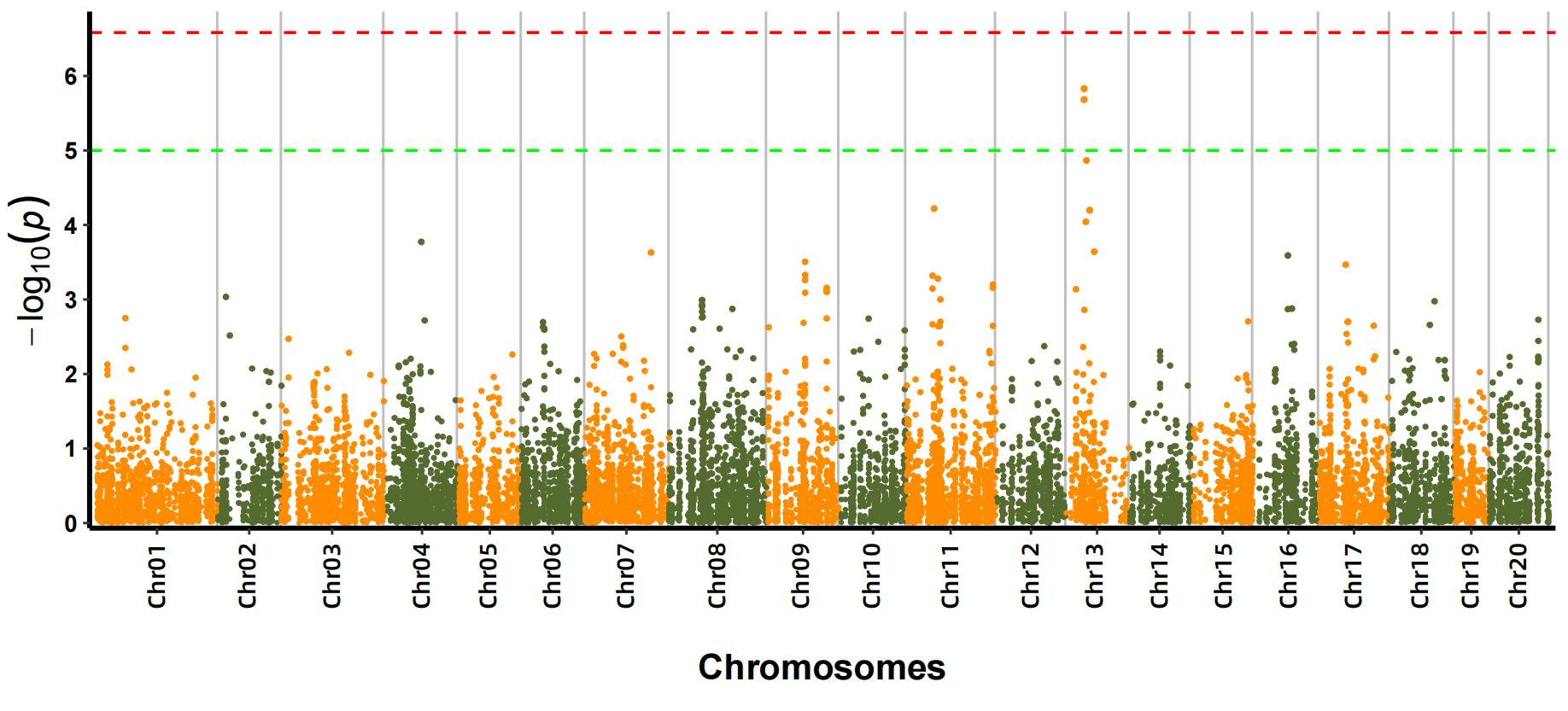
b.Asociācijas analīze (modelis: GEMMA, FaST-LMM, EMMAX)
QQ sižets
Manhetenas sižets
| gads | Žurnāls | IF | Nosaukums |
| 2022. gads | NC | 17.69 | Koku peonijas Paeonia ostii giga-hromosomu un giga-genoma genomiskais pamats |
| 2015. gads | NP | 7.43 | Domestācijas pēdas noenkuro agronomiski nozīmīgus genoma reģionus sojas pupās |
| 2018. gads | MP | 9.32 | Visa genoma atkārtota sekvencēšana pasaules mēroga rapša pievienošanās kolekcijai atklāj to ekotipa atšķirības ģenētisko pamatu |
| 2022. gads | HR | 7.29 | Genoma mēroga asociācijas analīze sniedz molekulāru ieskatu arbūzu sēklu lieluma dabiskajās variācijās |