
Hi-C balstīta genoma montāža
Pakalpojuma priekšrocības
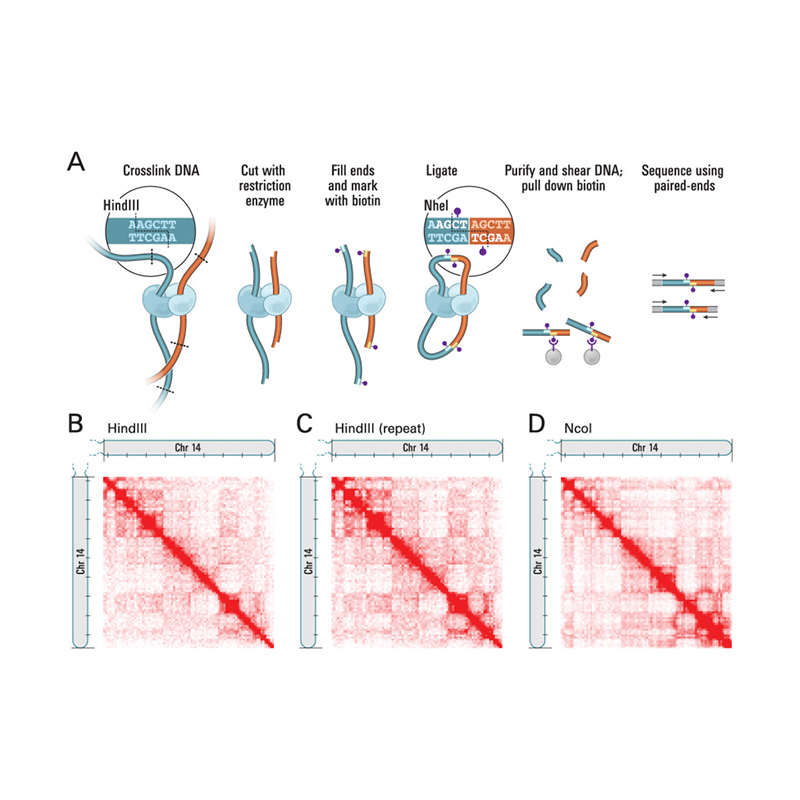
Pārskats par Hi-C
(Lībermans-Eidens E et al.,Zinātne, 2009)
● Nav nepieciešams izveidot ģenētisko populāciju kontig noenkurošanai;
● Lielāks marķiera blīvums, kas nodrošina lielāku kontigciju noenkurošanas koeficientu virs 90%;
● Nodrošina esošo genomu komplektu novērtēšanu un korekcijas;
● Īsāks darbības laiks ar augstāku genoma montāžas precizitāti;
● Bagātīga pieredze ar vairāk nekā 1000 Hi-C bibliotēkām, kas izveidotas vairāk nekā 500 sugām;
● Vairāk nekā 100 veiksmīgu gadījumu ar uzkrāto publicēto ietekmes koeficientu virs 760;
● Hi-C bāzes genoma montāža poliploīdam genomam, 100% noenkurošanās ātrums tika sasniegts iepriekšējā projektā;
● Iekšējie patenti un programmatūras autortiesības Hi-C eksperimentiem un datu analīzei;
● Pašu izstrādāta vizualizētu datu regulēšanas programmatūra, kas nodrošina manuālu bloku pārvietošanu, apgriešanu, atsaukšanu un atkārtotu darbību.
Pakalpojuma specifikācijas
|
Bibliotēkas veids
|
Platforma | Lasīšanas garums | Ieteikt stratēģiju |
| Sveiki, C! | Illumina NovaSeq | PE150 | ≥ 100X |
Bioinformātikas analīzes
● Neapstrādātu datu kvalitātes kontrole
● Hi-C bibliotēkas kvalitātes kontrole
● Hi-C balstīta genoma montāža
● Pēcmontāžas novērtējums
Prasību paraugs un piegāde
Prasību paraugs:
| Dzīvnieks | Sēnīte | Augi
|
| Saldēti audi: 1-2g vienā bibliotēkā Šūnas: 1 x 10^7 šūnas vienā bibliotēkā | Saldēti audi: 1 g vienā bibliotēkā | Saldēti audi: 1-2g vienā bibliotēkā
|
| *Mēs ļoti iesakām Hi-C eksperimentam nosūtīt vismaz 2 alikvotas daļas (katra 1 g). | ||
Ieteicamā paraugu piegāde
Tvertne: 2 ml centrifūgas caurule (skārda folija nav ieteicama)
Lielākajai daļai paraugu mēs iesakām neglabāt etanolā.
Paraugu marķējums: paraugiem jābūt skaidri marķētiem un identiskiem ar iesniegto parauga informācijas veidlapu.
Sūtījums: Sausais ledus: Paraugi vispirms jāiepako maisos un jāierok sausajā ledū.
Pakalpojuma darba plūsma

Eksperimenta dizains

Paraugu piegāde

DNS ekstrakcija

Bibliotēkas celtniecība

Secība

Datu analīze

Pēcpārdošanas pakalpojumi
*Šeit parādītie demonstrācijas rezultāti ir no genomiem, kas publicēti ar Biomarker Technologies
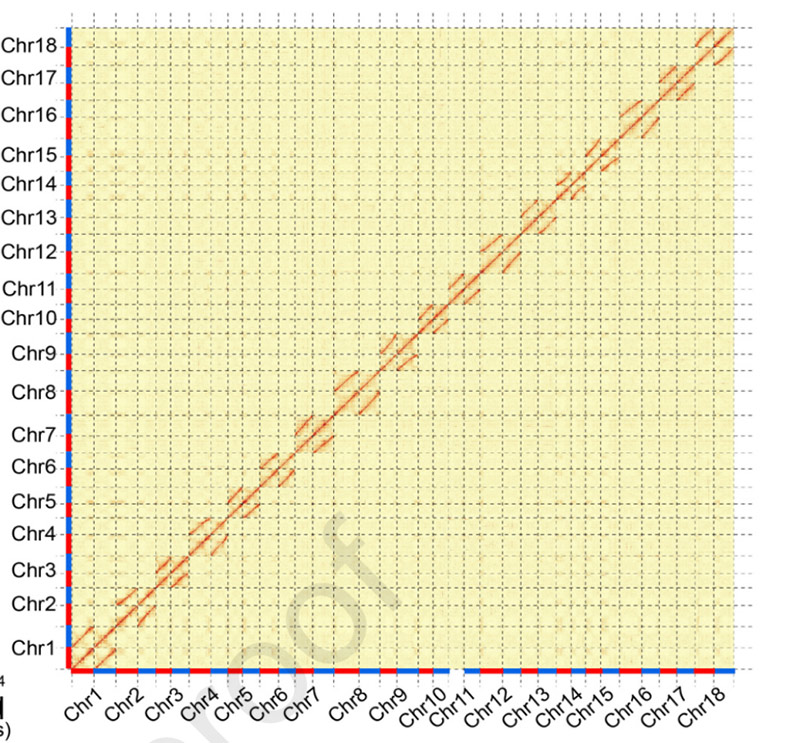
1.Hi-C mijiedarbības siltuma karteCamptotheca acuminatagenoms.Kā parādīts kartē, mijiedarbības intensitāte ir negatīvi korelēta ar lineāro attālumu, kas norāda uz ļoti precīzu hromosomu līmeņa montāžu.(enkurošanas koeficients: 96,03%)
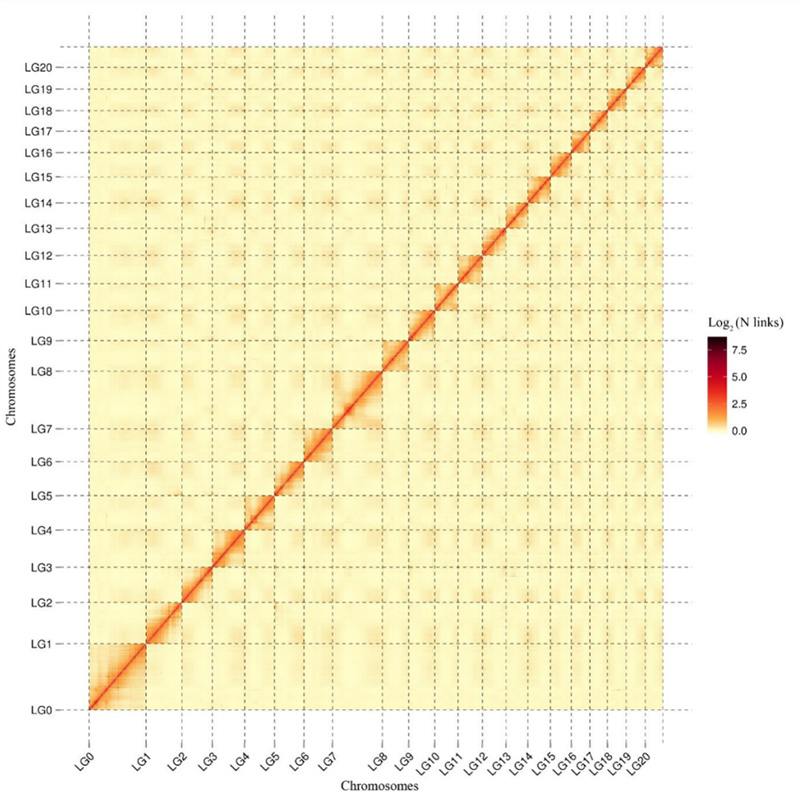
Kang M et al.,Dabas sakari, 2021. gads
2.Hi-C veicināja inversiju validāciju starpGossypium hirsutumL. TM-1 A06 unG. arboreumChr06
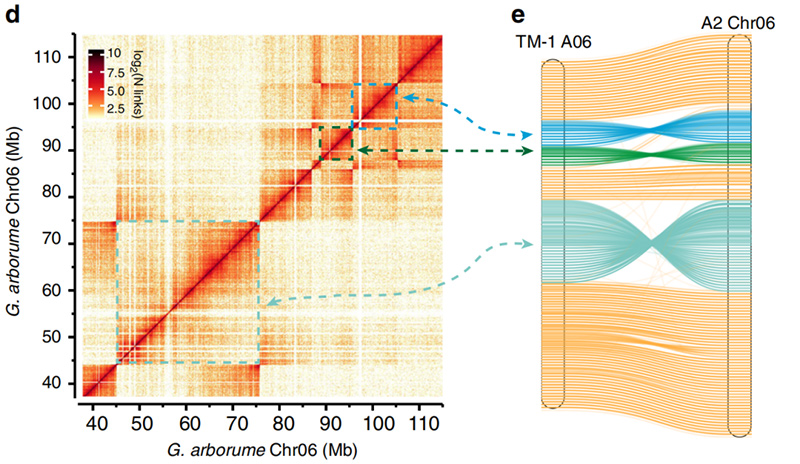
Yang Z et al.,Dabas sakari, 2019
3. Manokas genoma SC205 montāža un bialēliskā diferenciācija.Hi-C siltuma kartē parādīts skaidrs sadalījums homologās hromosomās.
Hu W et al.,Molekulārais augs, 2021. gads
4. Hi-C siltuma karte divu Ficus sugu genoma komplektā:F.microcarpa(enkurošanas koeficients: 99,3%) unF.hispida (enkurošanas attiecība: 99,7%)
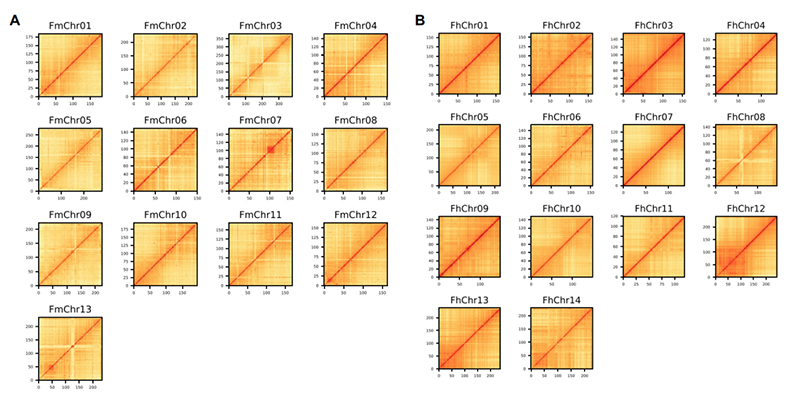
Zhang X et al.,Šūna, 2020. gads
BMK lieta
Banjankoka un apputeksnētājlapsenes genomi sniedz ieskatu vīģu-lapseņu koevolūcijā
Publicēts: Šūna, 2020. gads
Secības noteikšanas stratēģija:
F. microcarpa genoms: apm.84 X PacBio RSII (36,87 Gb) + Hi-C (44 Gb)
F. hispidagenoms: apm.97 X PacBio RSII (36,12 Gb) + Hi-C (60 Gb)
Eupristina verticillatagenoms: apm.170 X PacBio RSII (65 Gb)
Galvenie rezultāti
1. Izmantojot PacBio sekvencēšanu, Hi-C un saišu karti, tika izveidoti divi banāna koka genomi un viens apputeksnētāja lapsenes genoms.
(1)F. microcarpagenoms: tika izveidots 426 Mb (97,7% no aplēstā genoma lieluma) komplekts ar 908 Kb kontig N50, BUSCO punktu skaits 95,6%.Kopumā Hi-C pie 13 hromosomām noenkuroja 423 Mb sekvences.Genoma anotācija radīja 29 416 proteīnus kodējošus gēnus.
(2)F. Hispidagenoms: 360 Mb (97,3% no aplēstā genoma lieluma) komplekta ieguva ar kontig N50 492 Kb un BUSCO punktu skaitu 97,4%.Kopā 359 Mb sekvences tika noenkurotas 14 hromosomās ar Hi-C un ļoti identiskas augsta blīvuma saišu kartei.
(3)Eupristina verticillatagenoms: tika izveidots 387 Mb komplekts (paredzētais genoma izmērs: 382 Mb) ar kontig N50 3,1 Mb un BUSCO punktu skaitu 97,7%.
2. Salīdzinošā genomikas analīze atklāja lielu skaitu struktūras variāciju starp divāmFicusgenomi, kas nodrošināja nenovērtējamu ģenētisko resursu adaptīvās evolūcijas pētījumiem.Šis pētījums pirmo reizi sniedza ieskatu vīģu-lapseņu koevolūcijā genoma līmenī.
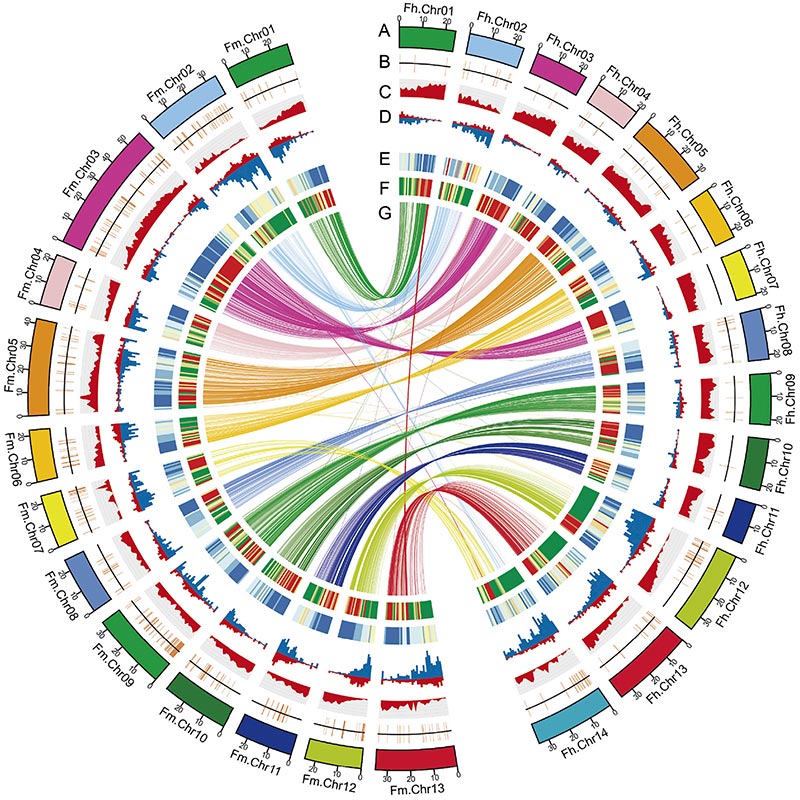 Circos diagramma par divu genomu iezīmēmFicusgenomi, tostarp hromosomas, segmentālās dublēšanās (SD), transpozoni (LTR, TE, DNS TE), gēnu ekspresija un sintēnija | 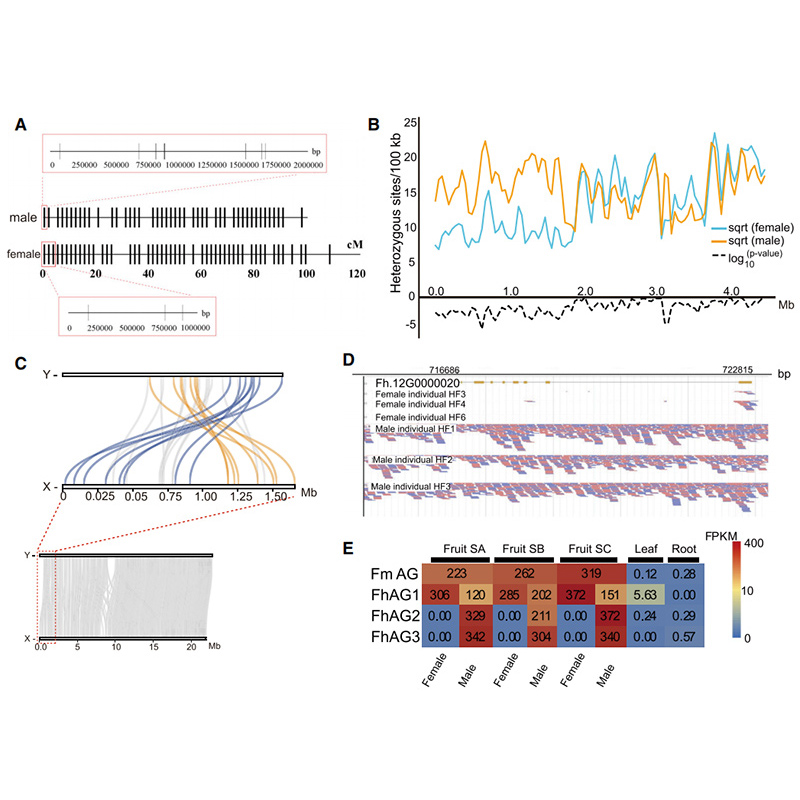 Y hromosomas un dzimuma noteikšanas kandidāta gēna identifikācija |
Džans, X. u.c."Banjankoka un apputeksnētājlapseņu genomi sniedz ieskatu vīģu-lapseņu koevolūcijā."Šūna 183.4 (2020).














