Visa cilvēka eksoma sekvencēšana
Pakalpojuma priekšrocības
● Mērķtiecīgs proteīnu kodēšanas reģions: notverot un sekvenējot proteīnu kodēšanas reģionu, hWES tiek izmantots, lai atklātu ar proteīna struktūru saistītus variantus;
● Augsta precizitāte: ar augstu secības dziļumu hWES atvieglo izplatītu variantu un retu variantu noteikšanu ar frekvencēm, kas zemākas par 1%;
● Rentabls: hWES rada aptuveni 85% cilvēku slimību mutāciju no 1% cilvēka genoma;
● Piecas stingras kvalitātes kontroles procedūras, kas aptver visu procesu ar Q30> 85% garantētu.
Parauga specifikācijas
| Platforma
| Bibliotēka
| Exon uztveršanas stratēģija
| Ieteikt secības noteikšanas stratēģiju
|
|
Illumina NovaSeq platforma
| PE150 | Agilent SureSelect Human All Exon V6 IDT xGen Exome Hyb panelis V2 | 5 Gb 10 Gb |
Prasību paraugs
| Parauga veids
| Summa(Qubit®)
| Skaļums
| Koncentrēšanās
| Tīrība (NanoDrop™) |
|
Genomiskā DNS
| ≥ 300 ng | ≥ 15 μL | ≥ 20 ng/μL | OD260/280=1,8-2,0 nav degradācijas, nav piesārņojuma
|
Ieteicamais secības dziļums
Mendeļa traucējumiem/retām slimībām: efektīvais secības dziļums virs 50×
Audzēju paraugiem: efektīvais sekvencēšanas dziļums virs 100 ×
Bioinformātika
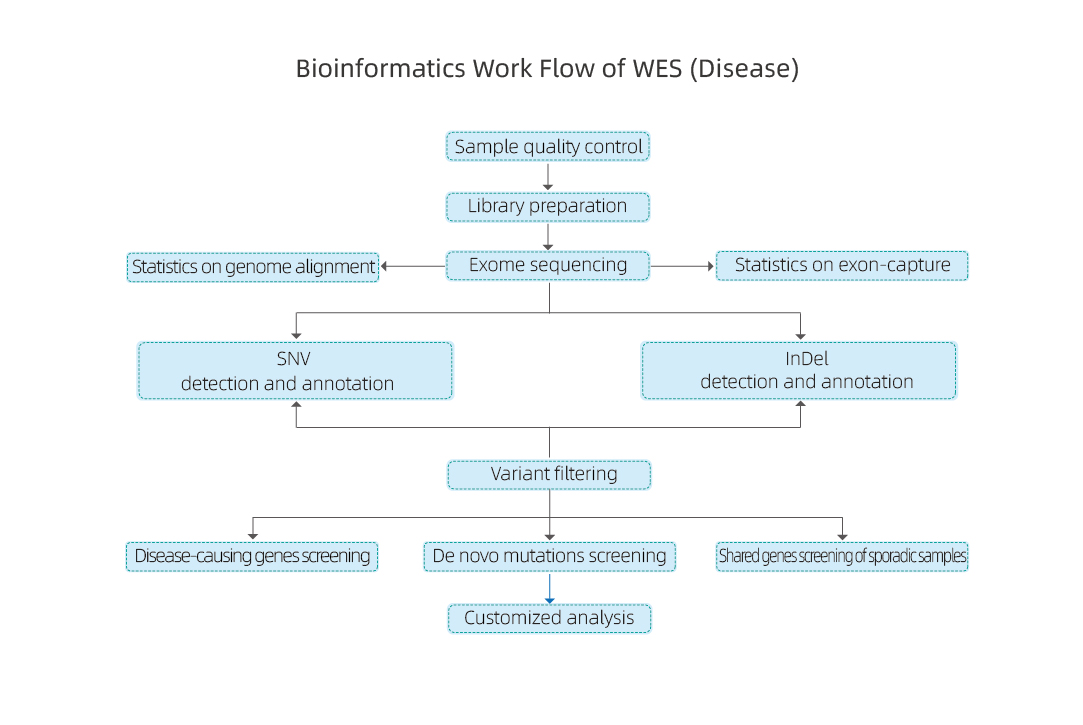
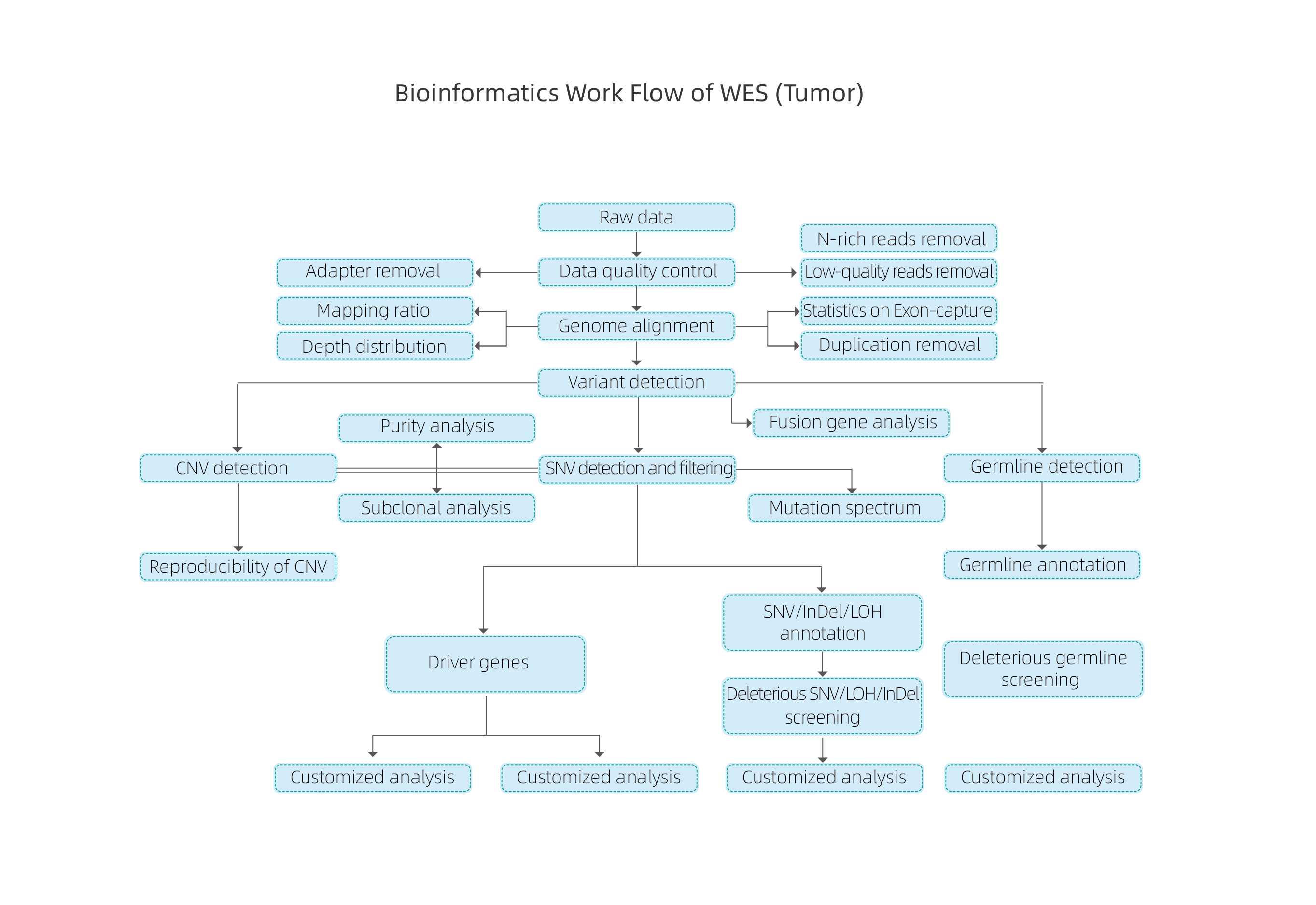
Pakalpojuma darba plūsma
Paraugu piegāde

DNS ekstrakcija

Bibliotēkas celtniecība

Secība

Datu analīze
Datu piegāde

Pēcpārdošanas pakalpojumi
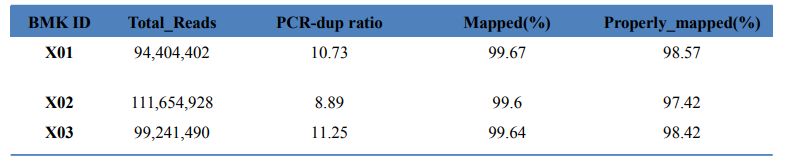
1.Līdzināšanas statistika
1. tabula Kartes rezultātu statistika
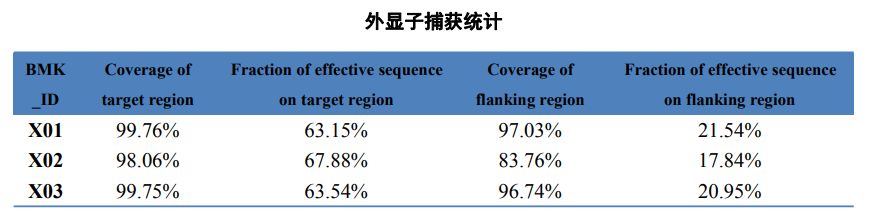
2. tabula Eksome uztveršanas statistika
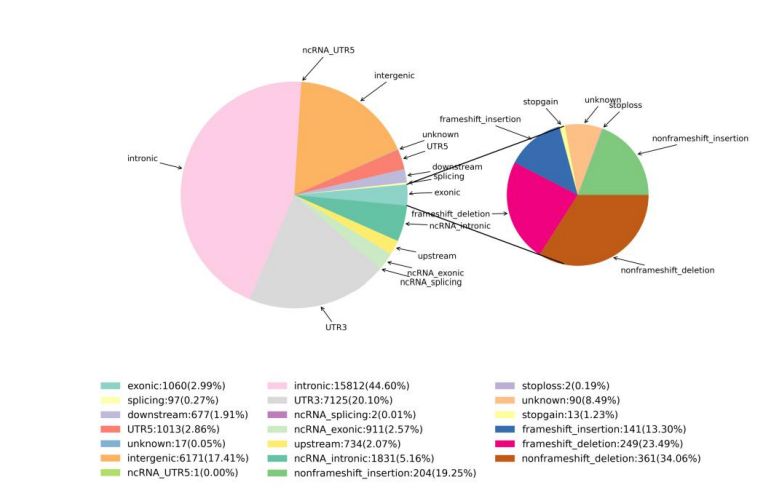
2. Variāciju noteikšana
1. attēls SNV un InDel statistika
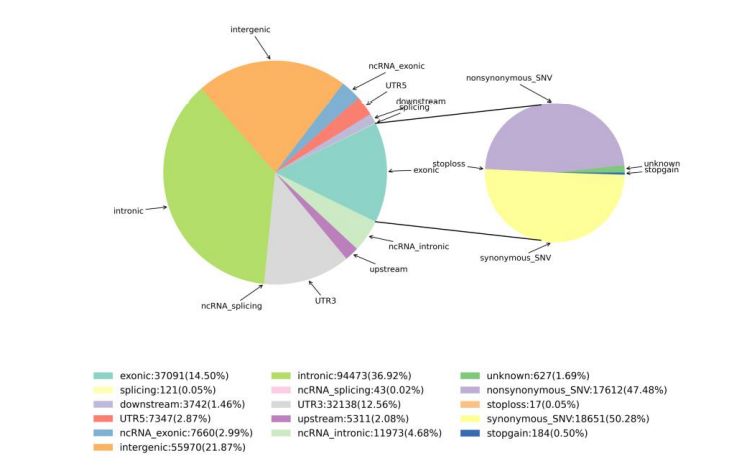
3. Papildu analīze
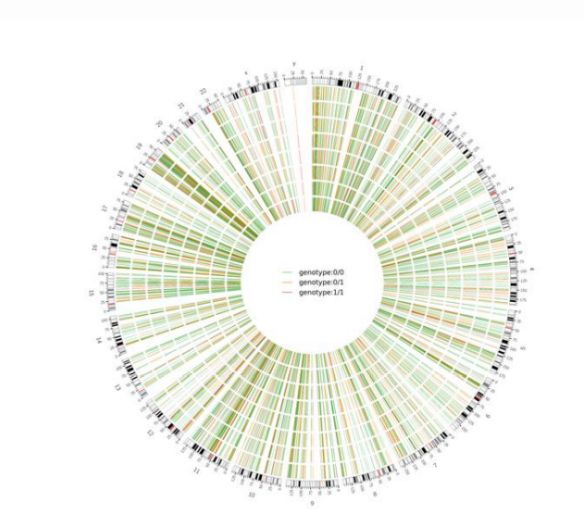
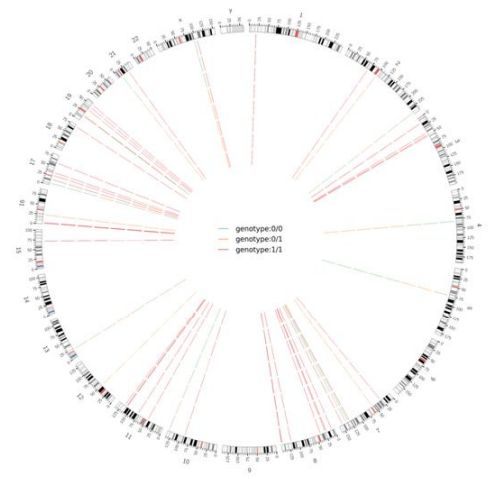
2. attēls Genoma mēroga kaitīgo SNV un InDel cirku diagramma
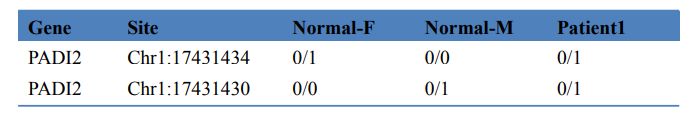
3. tabula Slimību izraisošo gēnu skrīnings