Metagenomiskā sekvencēšana-nanopora
Pakalpojuma priekšrocības
● Augstas kvalitātes montāža — uzlabo sugu identifikācijas un funkcionālo gēnu prognozēšanas precizitāti
● Slēgta baktēriju genoma izolācija
● Jaudīgāks un uzticamāks pielietojums dažādās jomās, piemēram, patogēnu mikroorganismu vai antibiotiku rezistenci saistītu gēnu noteikšana
● Salīdzinošā metagenomu analīze
Pakalpojuma specifikācijas
| Platforma | Secība | Ieteicamie dati | Apgrozījuma laiks |
| Nanopore | ONT | 6 G/10 G | 65 darba dienas |
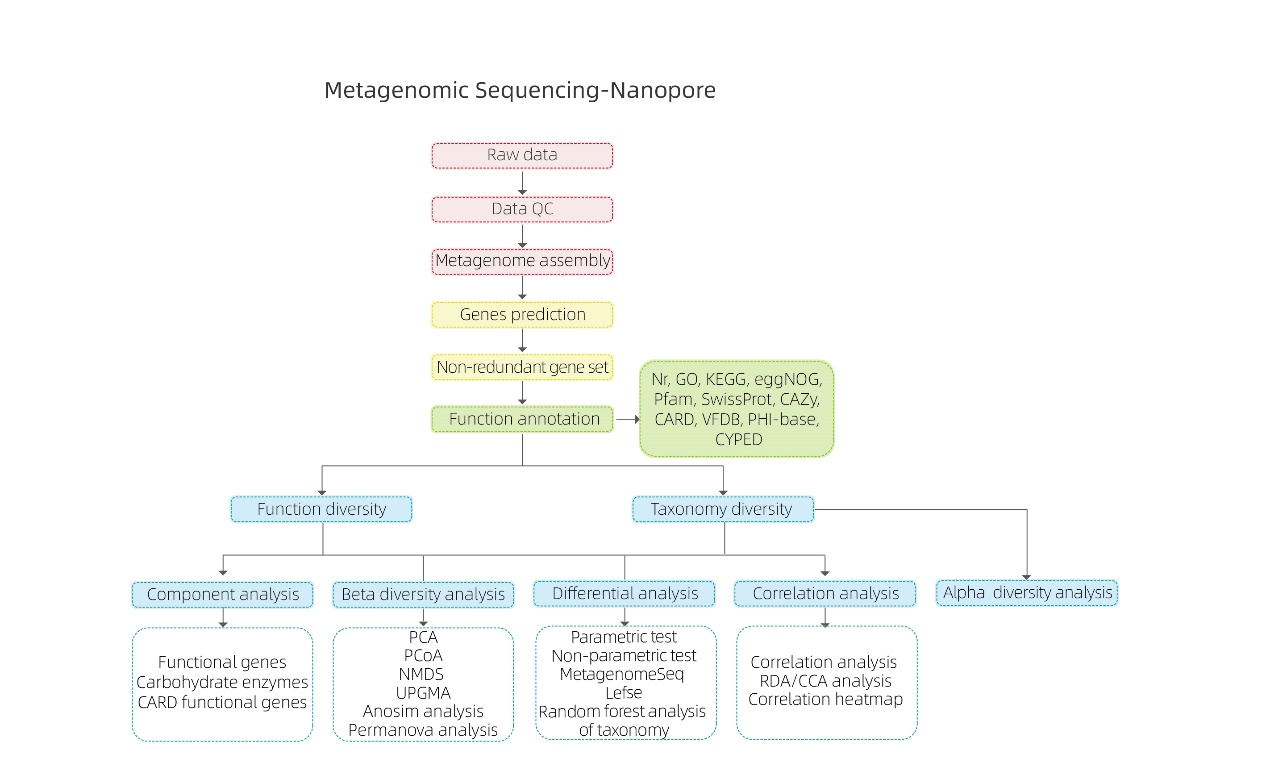
Bioinformātikas analīzes
● Neapstrādātu datu kvalitātes kontrole
● Metagenomu montāža
● Nelieka gēnu kopa un anotācija
● Sugu daudzveidības analīze
● Ģenētisko funkciju daudzveidības analīze
● Starpgrupu analīze
● Asociāciju analīze pret eksperimentāliem faktoriem
Prasību paraugs un piegāde
Parauga prasības un piegāde
Prasību paraugs:
PriekšDNS ekstrakti:
| Parauga veids | Summa | Koncentrēšanās | Tīrība |
| DNS ekstrakti | 1-1,5 μg | > 20 ng/μl | OD260/280= 1,6-2,5 |
Vides paraugiem:
| Parauga veids | Ieteicamā paraugu ņemšanas procedūra |
| Augsne | Paraugu ņemšanas apjoms: apm.5 g;Atlikušo nokaltušo vielu nepieciešams noņemt no virsmas;Sasmalcina lielus gabalus un izlaiž cauri 2 mm filtram;Paraugu alikvotā daļa rezervēšanai sterilā EP mēģenē vai cirotūbiņā. |
| Izkārnījumi | Paraugu ņemšanas apjoms: apm.5 g;Savākt un alikvot paraugus sterilā EP mēģenē vai kriomēģenē rezervēšanai. |
| Zarnu saturs | Paraugi jāapstrādā aseptiskos apstākļos.Nomazgājiet savāktos audus ar PBS;Centrifugējiet PBS un savāciet nogulsnes EP mēģenēs. |
| Dūņas | Paraugu ņemšanas apjoms: apm.5 g;Savāc un alikvotā dūņu paraugu sadala sterilā EP mēģenē vai kriomēģenē rezervēšanai |
| Ūdenstilpne | Paraugam ar ierobežotu mikrobu daudzumu, piemēram, krāna ūdeni, akas ūdeni utt., Savākt vismaz 1 l ūdens un izlaist cauri 0,22 μm filtram, lai bagātinātu membrānas mikroorganismus.Uzglabājiet membrānu sterilā mēģenē. |
| Āda | Uzmanīgi nokasiet ādas virsmu ar sterilu vates tamponu vai ķirurģisko asmeni un ievietojiet to sterilā mēģenē. |
Ieteicamā paraugu piegāde
Sasaldējiet paraugus šķidrā slāpeklī 3-4 stundas un uzglabājiet šķidrā slāpeklī vai -80 grādos līdz ilgstošai rezervēšanai.Nepieciešama paraugu piegāde ar sauso ledu.
Pakalpojuma darba plūsma

Paraugu piegāde

Bibliotēkas celtniecība

Secība

Datu analīze

Pēcpārdošanas pakalpojumi
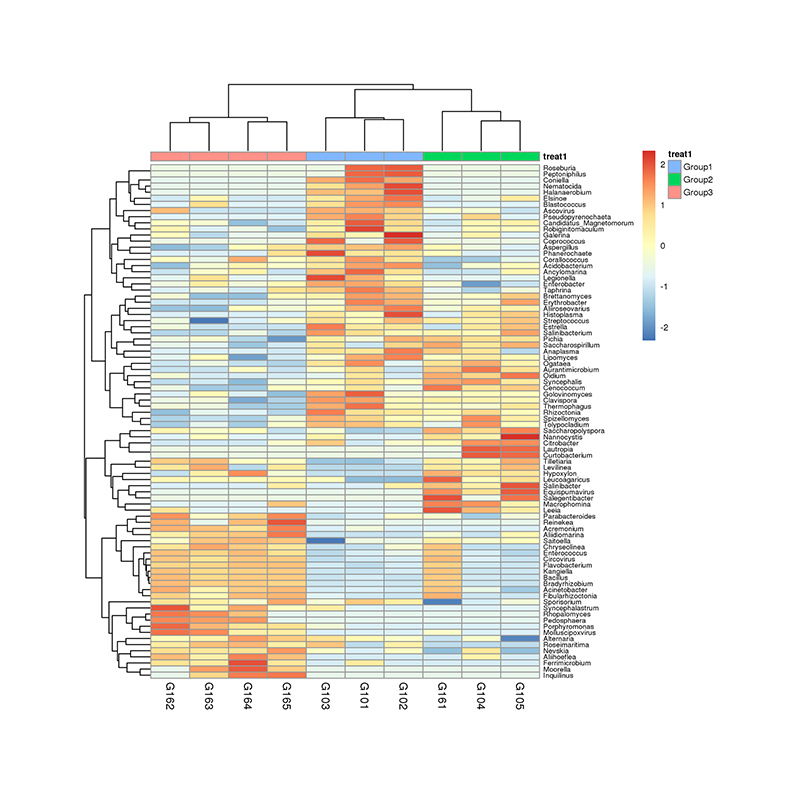
1. Siltuma karte: sugu bagātības klasterizācija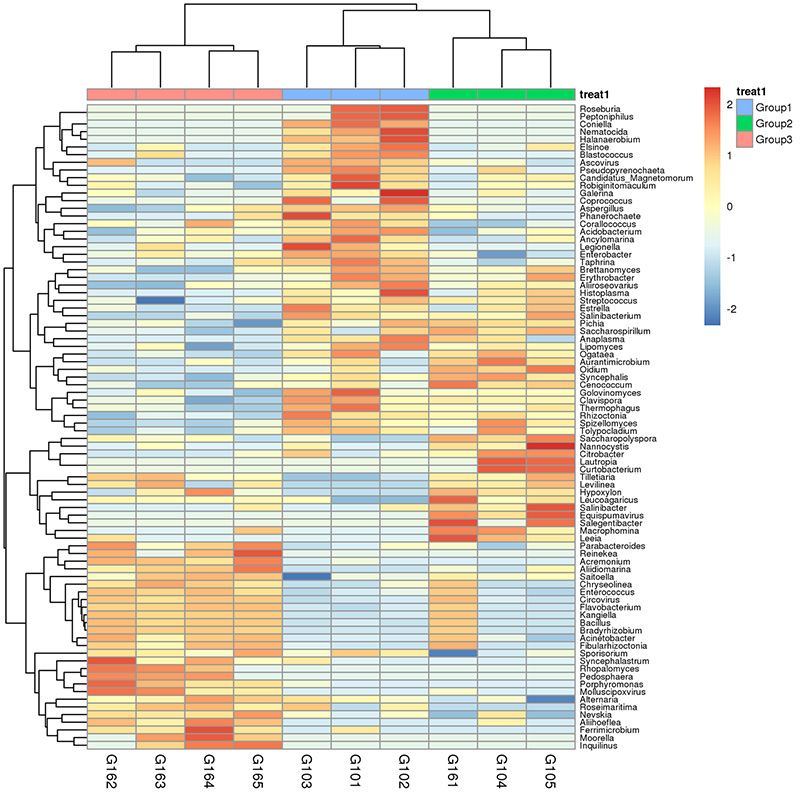 2. Funkcionālie gēni, kas anotēti uz KEGG vielmaiņas ceļiem
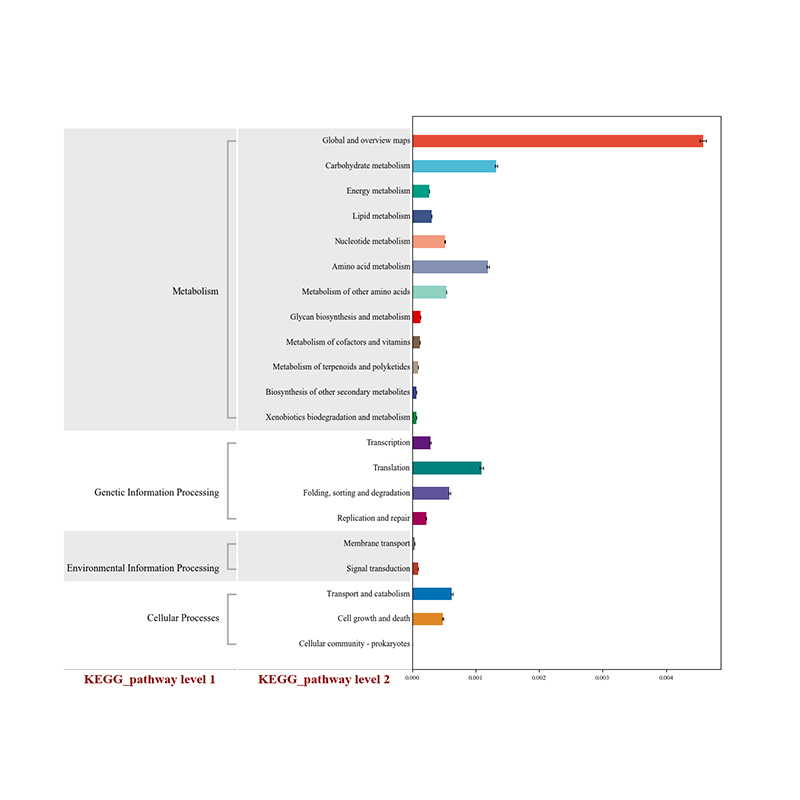
2. Funkcionālie gēni, kas anotēti uz KEGG vielmaiņas ceļiem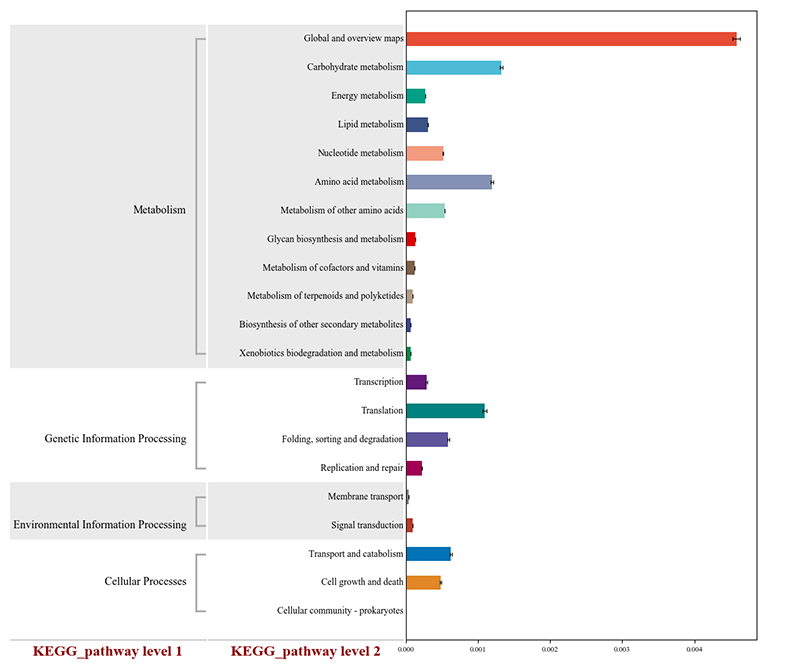 3.Sugu korelācijas tīkls
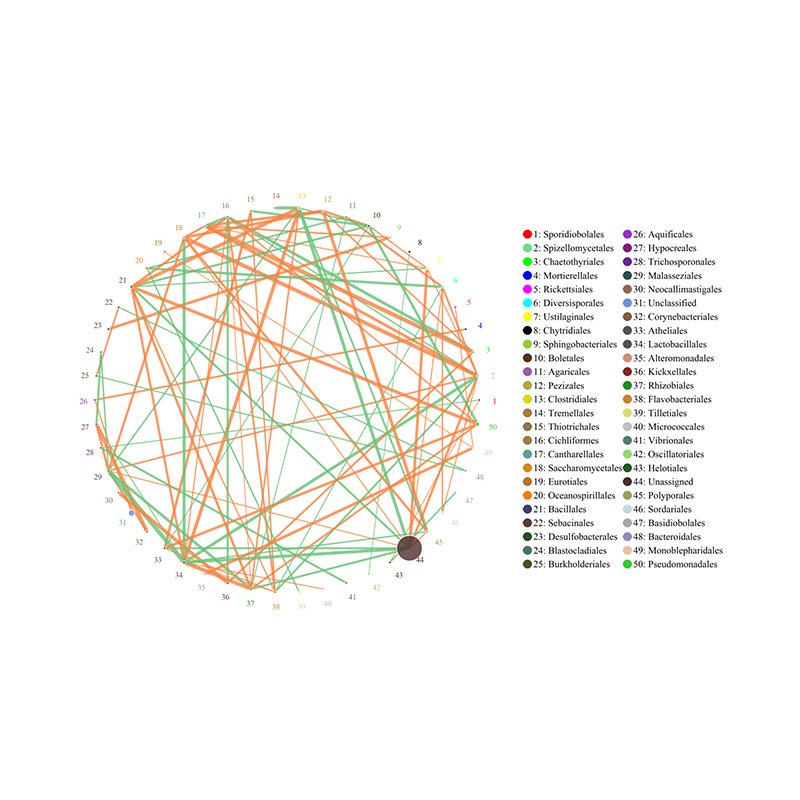
3.Sugu korelācijas tīkls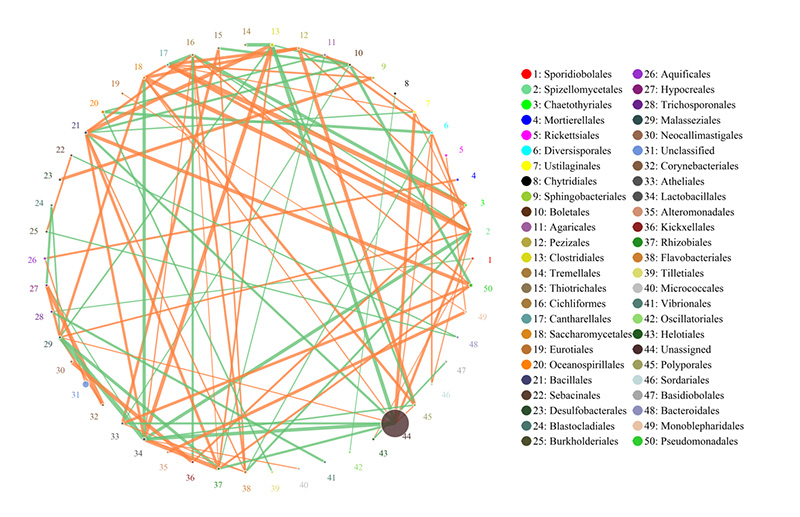 4. CARD antibiotiku rezistences gēnu cirki
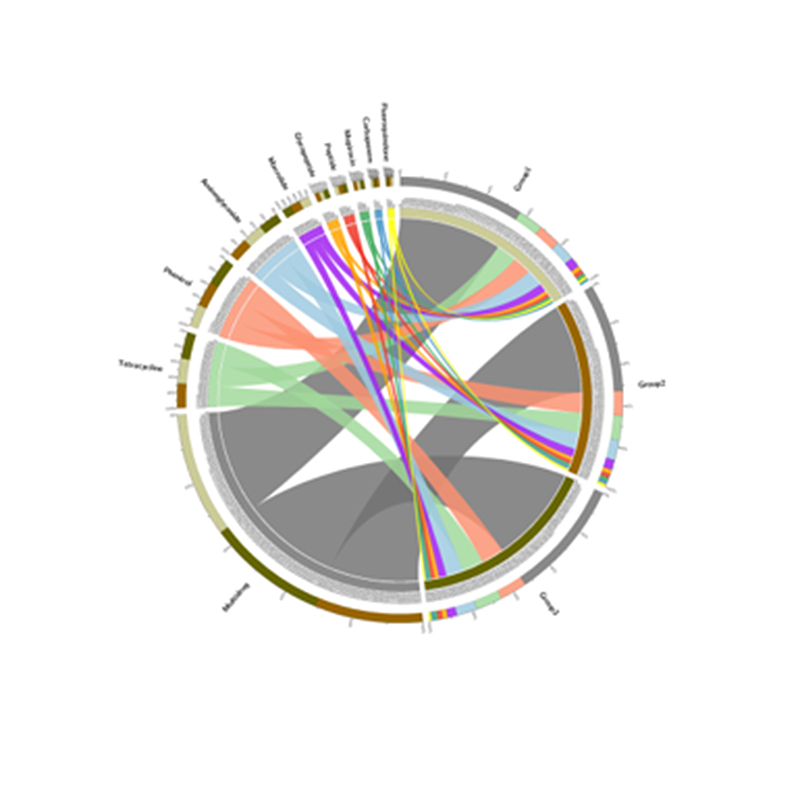
4. CARD antibiotiku rezistences gēnu cirki
BMK lieta
Nanoporu metagenomika ļauj ātri klīniski diagnosticēt apakšējo elpceļu bakteriālu infekciju
Publicēts:Dabas biotehnoloģija, 2019
Tehniskie akcenti
Secība: Nanopore MinION
Klīniskā metagenomikas bioinformātika: saimnieka DNS izsīkšana, WIMP un ARMA analīze
Ātra noteikšana: 6 stundas
Augsta jutība: 96,6%
Galvenie rezultāti
2006. gadā apakšējo elpceļu infekcija (LR) izraisīja 3 miljonu cilvēku nāvi visā pasaulē.Tipiskā LR1 patogēna noteikšanas metode ir kultivēšana, kurai ir vāja jutība, ilgs darbības laiks un trūkst norādījumu agrīnai antibiotiku terapijai.Ātra un precīza mikrobu diagnoze jau sen ir bijusi steidzama nepieciešamība.Dr Džastins no Austrumanglijas universitātes un viņa partneri veiksmīgi izstrādāja uz nanoporu balstītu metagenomisko metodi patogēnu noteikšanai.Saskaņā ar viņu darbplūsmu 99,99% saimnieka DNS var būt noplicināti.Patogēnu un antibiotiku rezistentu gēnu noteikšanu var pabeigt 6 stundu laikā.
Atsauce
Charalampous, T., Kay, GL, Richardson, H., Aydin, A. un O'Grady, J. .(2019).Nanoporu metagenomika ļauj ātri klīniski diagnosticēt apakšējo elpceļu bakteriālu infekciju.Nature Biotechnology, 37(7), 1.