Visa transkripta sekvencēšana – Illumina
Iespējas
● Dubultā bibliotēka, lai secinātu visu transkriptu: rRNS izsīkšana, kam seko PE150 bibliotēkas sagatavošana un lieluma izvēle, kam seko SE50 bibliotēkas sagatavošana
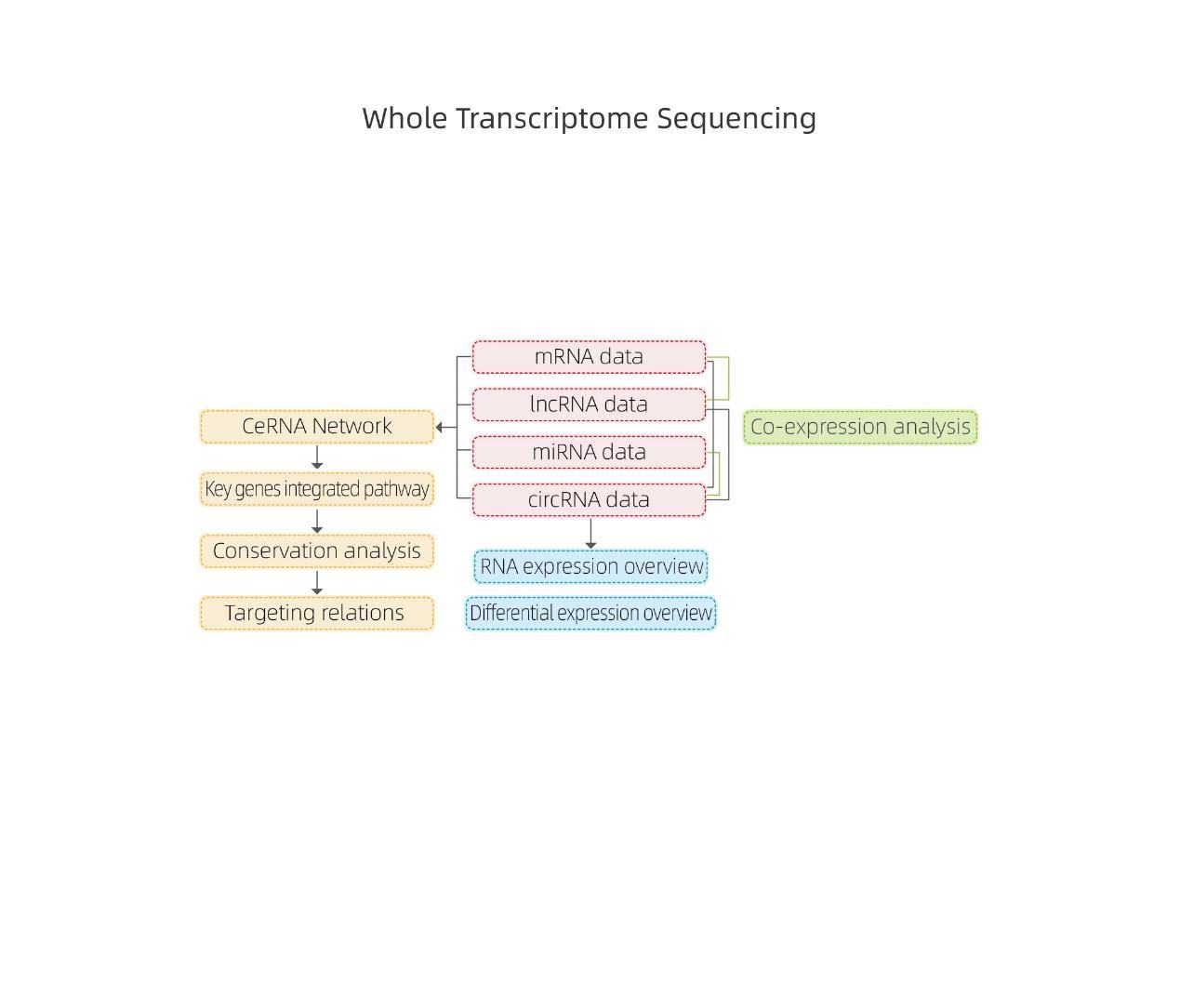
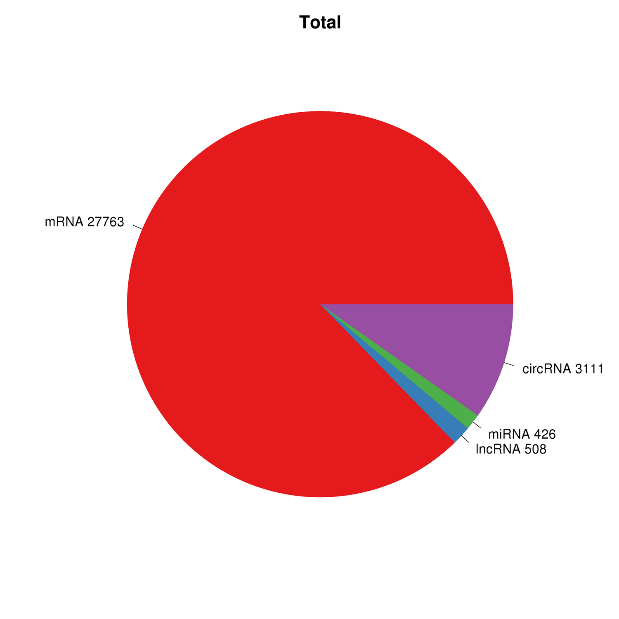
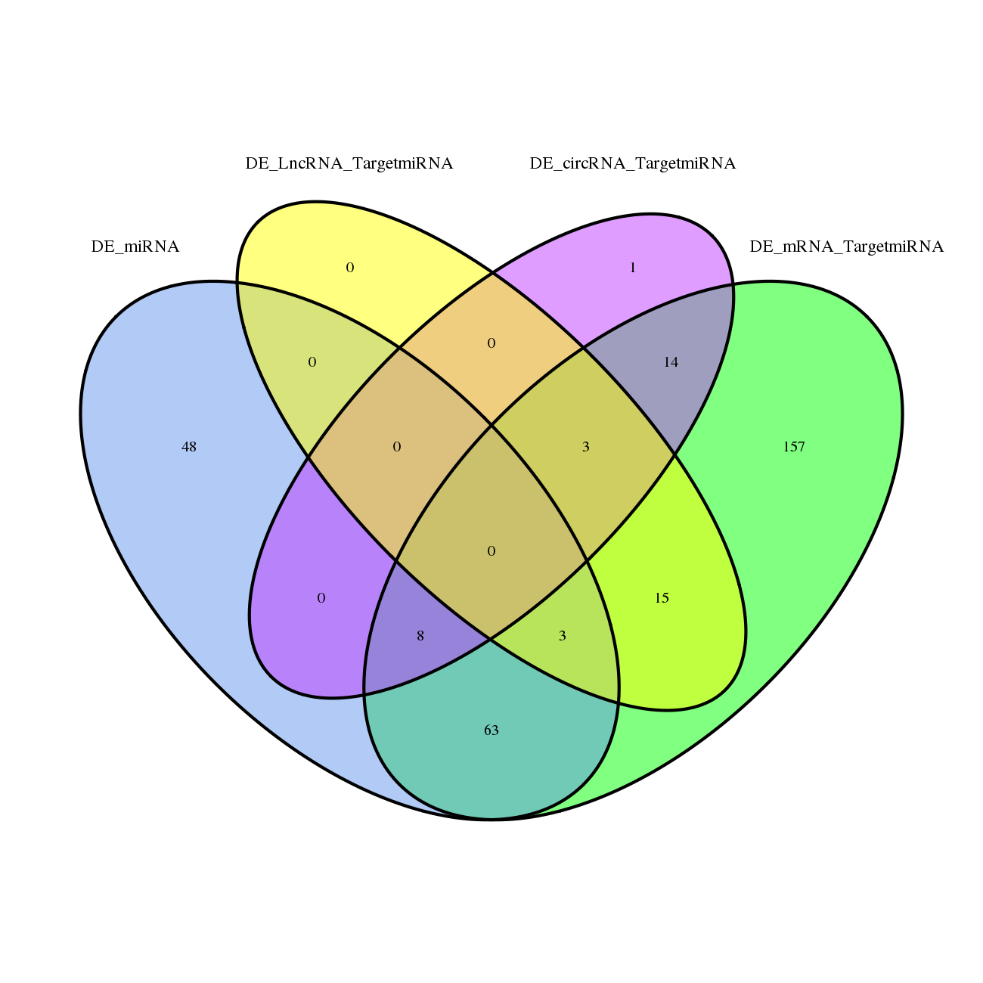
● Pilnīga mRNS, lncRNS, cirRNS un miRNS bioinformātikas analīze atsevišķos bioinformātikas pārskatos
● Kopīga visas RNS ekspresijas analīze kombinētajā ziņojumā, ieskaitot ceRNS tīklu analīzi.
Pakalpojuma priekšrocības
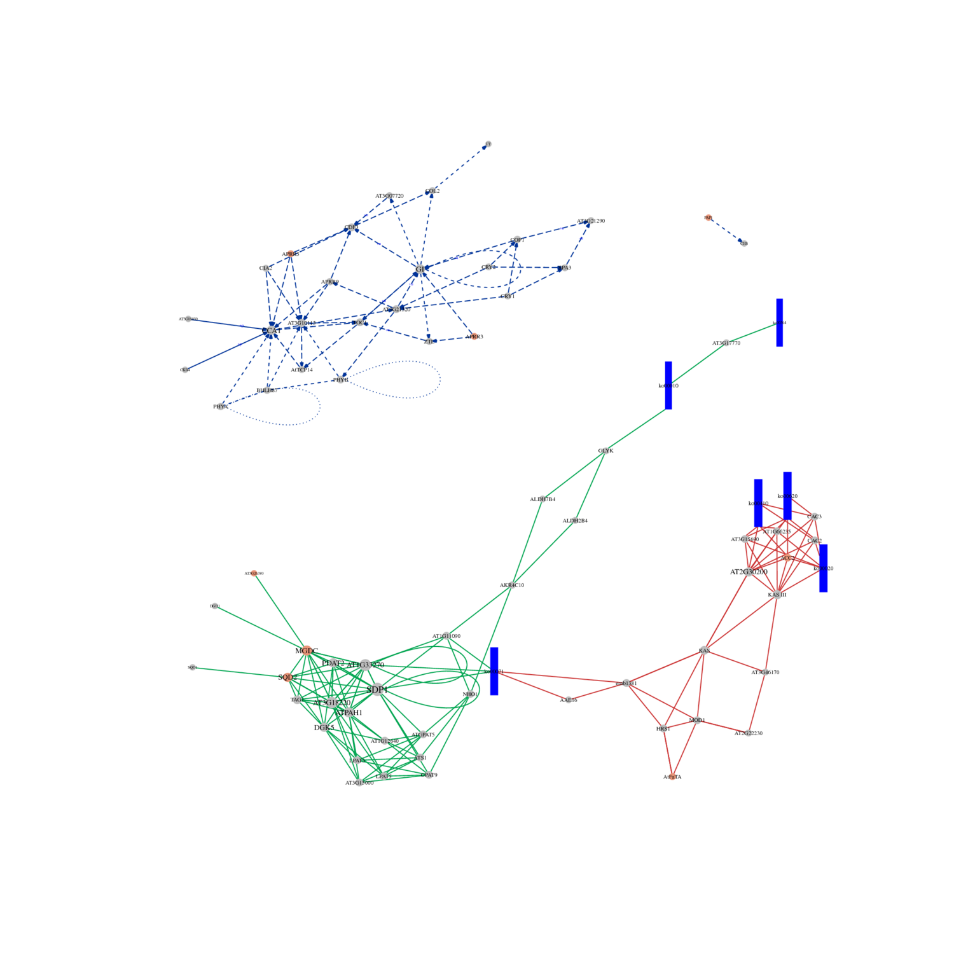
●Regulēšanas tīklu padziļināta analīze: ceRNS tīkla analīzi nodrošina kopīga mRNS, lncRNS, cirRNS un miRNS sekvencēšana un izsmeļoša bioinformātiskā darbplūsma.
●Visaptveroša anotācija: mēs izmantojam vairākas datu bāzes, lai funkcionāli anotētu diferencēti izteiktus gēnus (DEG) un veiktu atbilstošo bagātināšanas analīzi, sniedzot ieskatu par šūnu un molekulārajiem procesiem, kas ir transkripta reakcijas pamatā.
●Plaša ekspertīze: ar panākumiem sekmīgi noslēdzot vairāk nekā 2000 visu transkripta projektu dažādās pētniecības jomās, mūsu komanda sniedz bagātīgu pieredzi katrā projektā.
●Stingra kvalitātes kontrole: mēs ieviešam galvenos kontroles punktus visos posmos, sākot no paraugu un bibliotēkas sagatavošanas līdz sekvencēšanai un bioinformātikai.Šī rūpīgā uzraudzība nodrošina nemainīgi augstas kvalitātes rezultātu piegādi.
● Visaptveroša anotācija: mēs izmantojam vairākas datu bāzes, lai funkcionāli anotētu diferencēti izteiktus gēnus (DEG) un veiktu atbilstošo bagātināšanas analīzi, sniedzot ieskatu par šūnu un molekulārajiem procesiem, kas ir transkripta reakcijas pamatā.
●Pēcpārdošanas atbalsts: Mūsu saistības sniedzas tālāk par projekta pabeigšanu ar 3 mēnešu pēcpārdošanas servisa periodu.Šajā laikā mēs piedāvājam projekta pārraudzību, problēmu novēršanas palīdzību un jautājumu un atbilžu sesijas, lai risinātu visus ar rezultātiem saistītus jautājumus.
Prasību paraugs un piegāde
| Bibliotēka | Sekvences stratēģija | Ieteicamie dati | Kvalitātes kontrole |
| rRNS noplicināts | Illumina PE150 | 16 Gb | Q30≥85% |
| Izmērs izvēlēts | Illumina SE50 | 10-20 miljoni nolasījumu |
Prasību paraugs:
Nukleotīdi:
| Konc. (ng/μl) | Daudzums (μg) | Tīrība | Integritāte |
| ≥ 100 | ≥ 1 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Uz gēla parādīts ierobežots proteīnu vai DNS piesārņojums vai tā nav. | Augi: RIN≥6,5 Dzīvnieks: RIN≥7,0 5,0≥28S/18S≥1,0; ierobežots vai vispār nav bāzes līmeņa pacēluma |
Ieteicamā paraugu piegāde
Konteiners:
2 ml centrifūgas caurule (skārda folija nav ieteicama)
Marķējuma paraugs: grupa + atkārtojums, piemēram, A1, A2, A3;B1, B2, B3......
Sūtījums:
1. Sausais ledus: paraugi jāiepako maisos un jāierok sausajā ledū.
2.RNAstable caurules: RNS paraugus var žāvēt RNS stabilizācijas mēģenē (piemēram, RNAstable®) un nosūtīt istabas temperatūrā.
Pakalpojuma darba plūsma

Eksperimenta dizains

Paraugu piegāde

RNS ekstrakcija

Bibliotēkas celtniecība

Secība

Datu analīze

Pēcpārdošanas pakalpojumi
Bioinformātika
RNS ekspresijas pārskats
Atšķirīgi izteikti gēni
ceRNS analīze
Izpētiet pētniecības sasniegumus, ko veicina visi BMKGene transkriptu sekvencēšanas pakalpojumi, izmantojot apkopotu publikāciju kolekciju.
Dai, Y. et al.(2022) “Visaptveroši mRNS, lncRNS un miRNS ekspresijas profili Kašina-Beka slimībā, kas identificēta ar RNS sekvencēšanu”, Molecular Omics, 18(2), 154.–166. lpp.doi: 10.1039/D1MO00370D.
Liu, N. nan et al.(2022) “Apis cerana aukstumizturības pilna garuma transkriptu analīze Čangbai kalnā ziemošanas periodā.”, Gene, 830, 146503.–146503. lpp.doi: 10.1016/J.GENE.2022.146503.
Wang, XJ et al.(2022) “Uz vairāku omiku integrāciju balstīta prioritāšu noteikšana konkurējošiem endogēnās RNS regulēšanas tīkliem sīkšūnu plaušu vēža gadījumā: molekulārās īpašības un zāļu kandidāti”, Frontiers in Oncology, 12. lpp.904865. doi: 10.3389/FONC.2022.904865/BIBTEX.
Xu, P. et al.(2022) "Integrētā lncRNS/cirRNS-miRNS-mRNS ekspresijas profilu analīze atklāj jaunus ieskatus potenciālajos mehānismos, reaģējot uz sakņu nematodēm zemesriekstos", BMC Genomics, 23(1), 1.–12. lpp.doi: 10.1186/S12864-022-08470-3/FIGURES/7.
Yan, Z. et al.(2022) “Visas transkripta RNS sekvencēšana izceļ molekulāros mehānismus, kas saistīti ar brokoļu kvalitātes saglabāšanu pēc novākšanas, izmantojot sarkano LED apstarošanu”, Postharvest Biology and Technology, 188. lpp.111878. doi: 10.1016/J.POSTHARVBIO.2022.111878.