
Full-lengde mRNA-sekvensering -PacBio
Tjenestefordeler
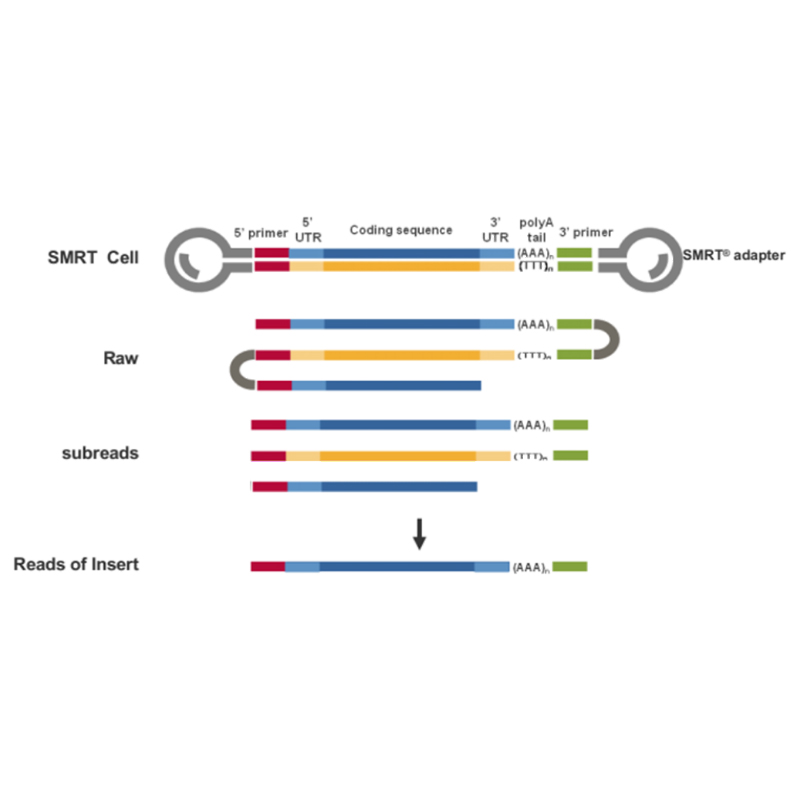
● Direkte avlesning av cDNA-molekyl i full lengde fra 3'-ende til 5'-ende
● Iso-formnivåoppløsning i sekvensstruktur
● Transkripsjoner med høy nøyaktighet og integritet
● Svært kompatibel med vaiours arter
● Stor sekvenseringskapasitet med 4 PacBio Sequel II sekvenseringsplattformer utstyrt
● Svært erfaren med over 700 Pacbio-baserte RNA-sekvenseringsprosjekter
● BMKCloud-basert resultatlevering: Tilpasset datautvinning tilgjengelig på plattformen.
● Ettersalgstjenester gyldig i 3 måneder etter ferdigstillelse av prosjektet
Tjenestespesifikasjoner
Plattform: PacBio Sequel II
Sekvenseringsbibliotek: Poly A-anriket mRNA-bibliotek
Anbefalt datautbytte: 20 Gb/prøve (avhengig av art)
FLNC(%): ≥75%
*FLNC: Ikke-kimeriske transsipter i full lengde
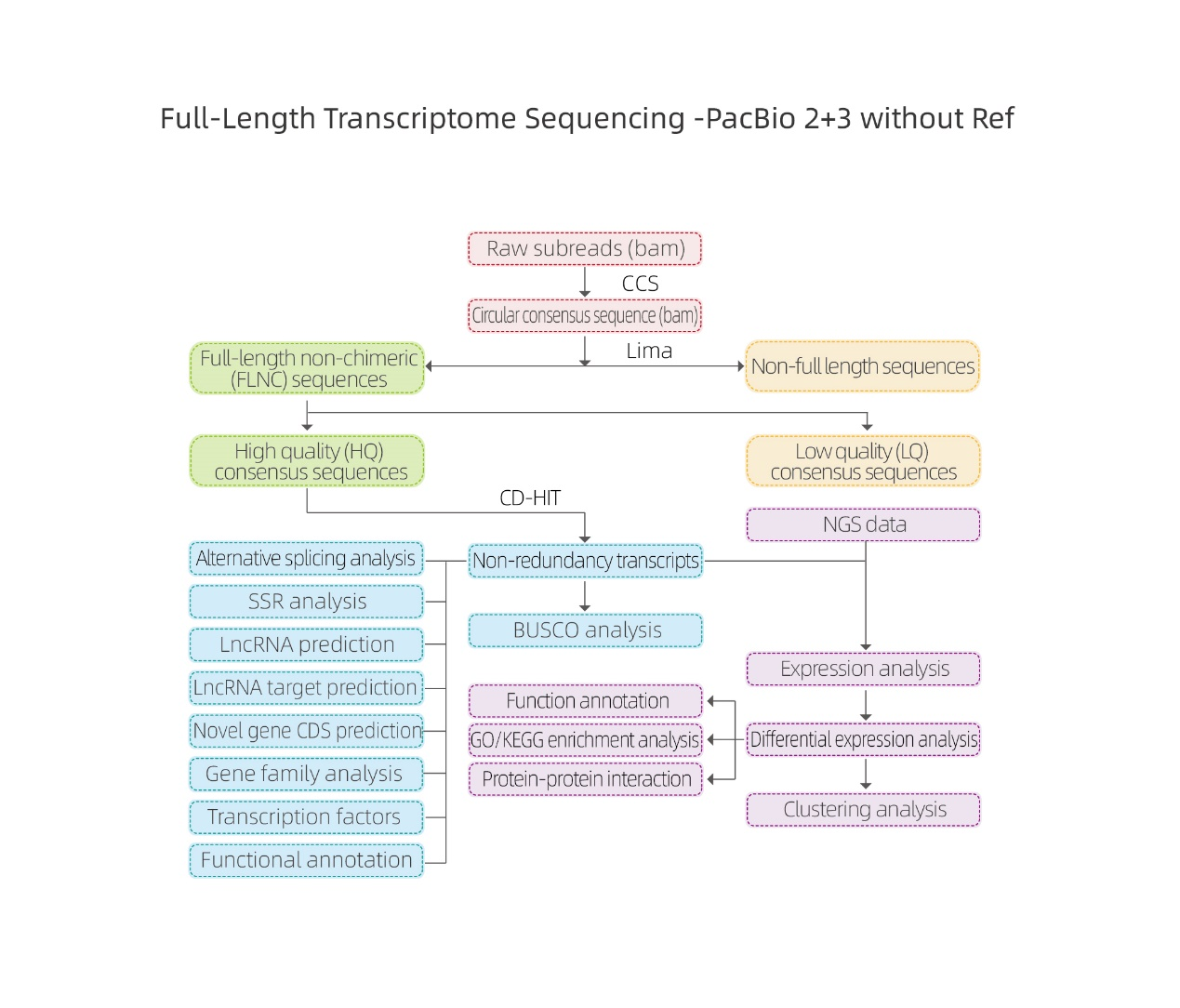
Bioinformatikkanalyser
● Behandling av rådata
● Transkripsjonsidentifikasjon
● Sekvensstruktur
● Kvantifisering av uttrykk
● Funksjonsanmerkning
Prøvekrav og levering
Eksempelkrav:
Nukleotider:
| Kons.(ng/μl) | Mengde (μg) | Renhet | Integritet |
| ≥ 120 | ≥ 0,6 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Begrenset eller ingen protein- eller DNA-kontaminering vist på gel. | For planter: RIN≥7,5; For dyr: RIN≥8,0; 5,0≥ 28S/18S≥1,0; begrenset eller ingen grunnlinjehøyde |
Vev: Vekt (tørr):≥1 g
*For vev mindre enn 5 mg anbefaler vi å sende hurtigfrosset (i flytende nitrogen) vevsprøve.
Cellesuspensjon:Celletall = 3×106- 1×107
*Vi anbefaler å sende frosset cellelysat.I tilfelle den cellen teller mindre enn 5×105, anbefales hurtigfryst i flytende nitrogen, som er å foretrekke for mikroekstraksjon.
Blodprøver:Volum ≥1 mL
Mikroorganisme:Masse ≥ 1 g
Anbefalt prøvelevering
Container:
2 ml sentrifugerør (tinnfolie anbefales ikke)
Prøvemerking: Gruppe+replikat f.eks. A1, A2, A3;B1, B2, B3... ...
Forsendelse:
1. Tørris: Prøver må pakkes i poser og begraves i tørris.
2. RNAstabile rør: RNA-prøver kan tørkes i RNA-stabiliseringsrør (f.eks. RNAstable®) og sendes i romtemperatur.
Servicearbeidsflyt

Eksperimentdesign

Prøvelevering

RNA-ekstraksjon

Bygging av bibliotek

Sekvensering

Dataanalyse

Ettersalgstjenester
1.FLNC lengdefordeling
Lengden på ikke-kimerisk lesing i full lengde (FLNC) indikerer lengden på cDNA i bibliotekkonstruksjon.FLNC-lengdefordeling er en avgjørende indikator for å evaluere kvaliteten på bibliotekkonstruksjonen.
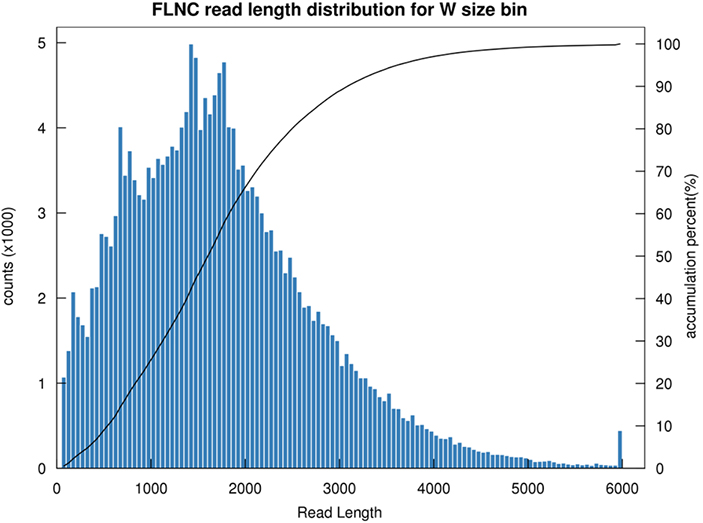
FLNC leselengdefordeling
2.Fullfør ORF-regionlengdefordeling
Vi bruker TransDecoder for å forutsi proteinkodende regioner og tilsvarende aminosyresekvenser for å generere unigen sett, som inneholder fullstendig ikke-redundant transkripsjonsinformasjon i alle prøver.
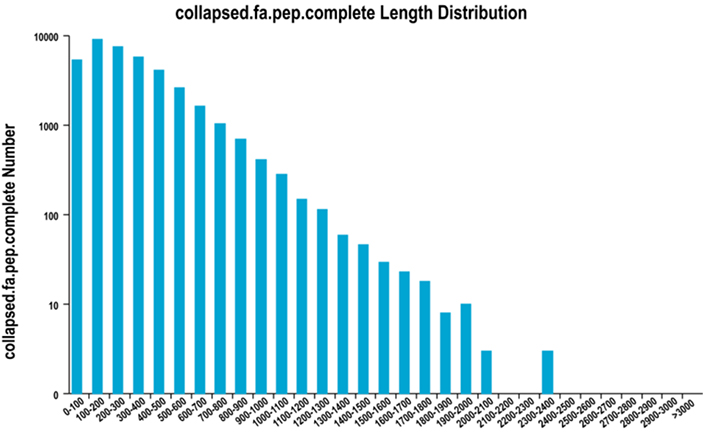
Fullstendig ORF-regionlengdefordeling
3.KEGG pathway anrikningsanalyse
Differensielt uttrykte transkripter (DETs) kan identifiseres ved å justere NGS-baserte RNA-sekvenseringsdata på full-lengde transkripsjonssett generert av PacBio-sekvenseringsdata.Disse DET-ene kan viderebehandles for ulike funksjonelle analyser, f.eks. KEGG-baneanrikningsanalyse.
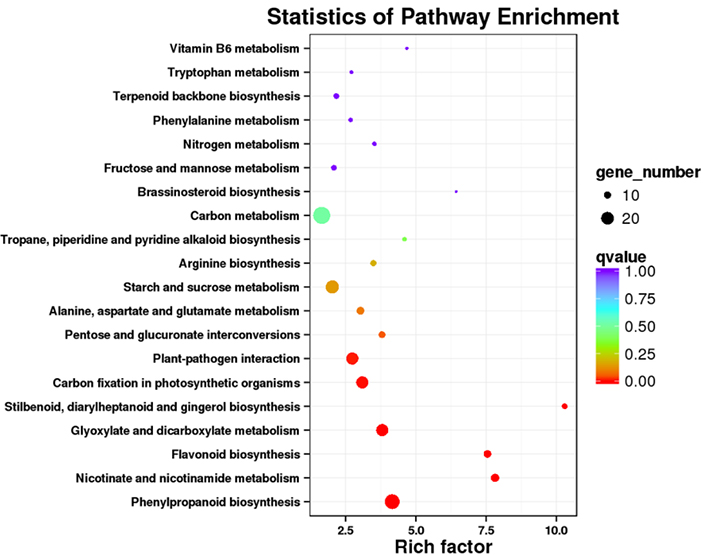
DET KEGG baneberikelse -Prikkplott
BMK sak
Utviklingsdynamikken til Populus stammetranskriptom
Publisert: Plantebioteknologisk tidsskrift, 2019
Sekvenseringsstrategi:
Prøvesamling:stammeregioner: apex, første internode(IN1), andre internode(IN2), tredje internode(IN3), internode(IN4) og internode(IN5) fra Nanlin895
NGS-sekvens:RNA fra 15 individer ble samlet som én biologisk prøve.Tre biologiske replikater av hvert punkt ble behandlet for NGS-sekvens
TGS-sekvens:Stammeregioner ble delt inn i tre regioner, dvs. apex, IN1-IN3 og IN4-IN5.Hver region ble behandlet for PacBio-sekvensering med fire typer biblioteker: 0-1 kb, 1-2 kb, 2-3 kb og 3-10 kb.
Nøkkelresultater
1.Totalt 87150 full-lengde transkripsjoner ble identifisert, der 2081 nye isoformer og 62058 nye alternative spleisede isoformer ble identifisert.
2.1187 lncRNA og 356 fusjonsgener ble identifisert.
3. Fra primær vekst til sekundær vekst ble 15838 differensielt uttrykte transkripsjoner fra 995 differensielt uttrykte gener identifisert.I alle DEG-er var 1216 transkripsjonsfaktorer, hvorav de fleste ennå ikke er rapportert.
4.GO anrikningsanalyse avdekket viktigheten av celledeling og oksidasjonsreduksjonsprosess i primær og sekundær vekst.
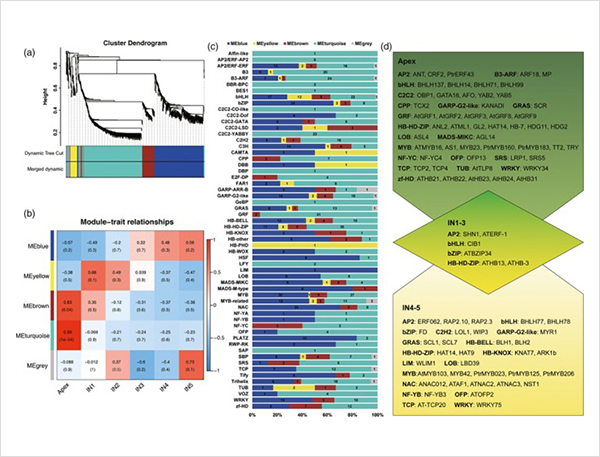
Alternative spleisehendelser og forskjellige isoformer
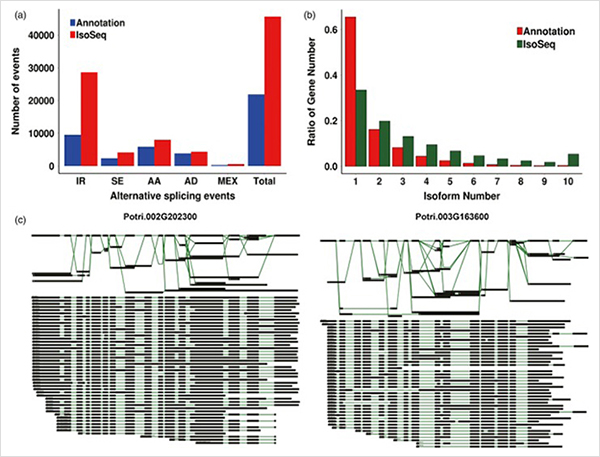
WGCNA-analyse på transkripsjonsfaktorer
Henvisning
Chao Q, Gao ZF, Zhang D, et al.Utviklingsdynamikken til Populus stammetranskriptom.Plant Biotechnol J. 2019;17(1):206-219.doi:10.1111/pbi.12958











