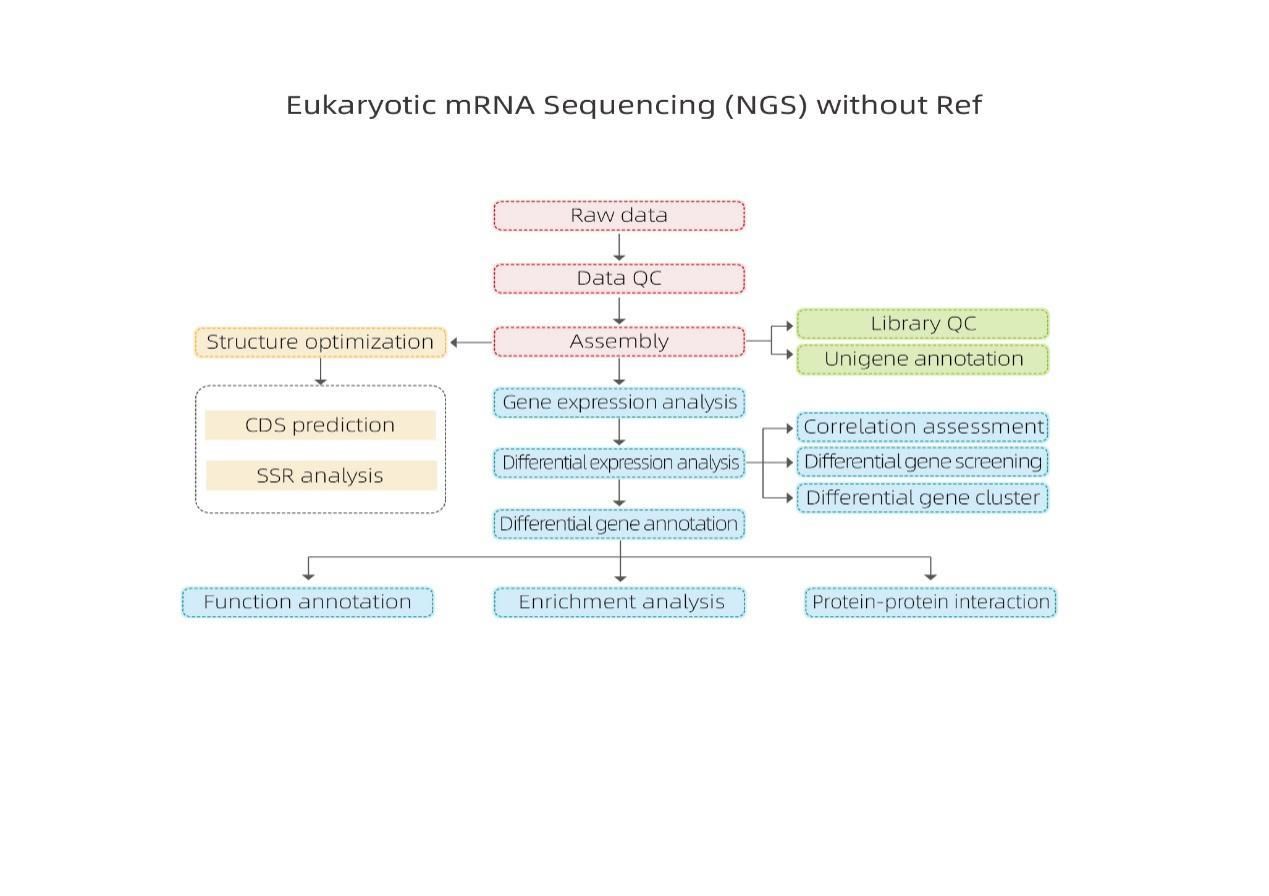
Ikke-referansebasert mRNA-sekvensering-Illumina
Egenskaper
● Uavhengig av ethvert referansegenom,
● Dataene kan brukes til å analysere strukturen og uttrykket til transkripsjoner
● Identifiser variable klippesteder
Tjenestefordeler
● BMKCloud-basert resultatlevering: Resultatene leveres som datafil og interaktiv rapport via BMKCloud-plattformen, som tillater brukervennlig lesing av komplekse analyseresultater og tilpasset datautvinning på grunnlag av standard bioinformatikkanalyse.
● Ettersalgstjenester: Ettersalgstjenester gyldig i 3 måneder etter ferdigstillelse av prosjektet, inkludert prosjektoppfølging, feilsøking, spørsmål og svar på resultater osv.
Prøvekrav og levering
Eksempelkrav:
Nukleotider:
| Kons.(ng/μl) | Mengde (μg) | Renhet | Integritet |
| ≥ 20 | ≥ 0,5 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Begrenset eller ingen protein- eller DNA-kontaminering vist på gel. | For planter: RIN≥6,5; For dyr: RIN≥7,0; 5,0≥28S/18S≥1,0; begrenset eller ingen grunnlinjehøyde |
Vev: Vekt (tørr): ≥1 g
*For vev mindre enn 5 mg anbefaler vi å sende hurtigfrosset (i flytende nitrogen) vevsprøve.
Cellesuspensjon: Celletall = 3×107
*Vi anbefaler å sende frosset cellelysat.I tilfelle den cellen teller mindre enn 5×105, anbefales hurtigfryst i flytende nitrogen.
Blodprøver:
PA×geneBloodRNATube;
6mLTRIzol og 2mL blod(TRIzol:Blod=3:1)
Anbefalt prøvelevering
Container:
2 ml sentrifugerør (tinnfolie anbefales ikke)
Prøvemerking: Gruppe+replikat f.eks. A1, A2, A3;B1, B2, B3... ...
Forsendelse:
1.Tørris: Prøver må pakkes i poser og begraves i tørris.
2.RNAstabile rør: RNA-prøver kan tørkes i RNA-stabiliseringsrør (f.eks. RNAstable®) og sendes i romtemperatur.
Servicearbeidsflyt

Eksperimentdesign

Prøvelevering

RNA-ekstraksjon

Bygging av bibliotek

Sekvensering

Dataanalyse

Ettersalgstjenester
Bioinformatikk
1.mRNA(denovo) Monteringsprinsipp
Ved Trinity blir lesninger fragmentert i mindre biter, kjent som K-mer.Disse K-merene brukes deretter som frø for å bli utvidet til contigs og deretter komponent basert på contig-overlappinger.Til slutt ble De Bruijn brukt her for å gjenkjenne transkripsjoner i komponentene.
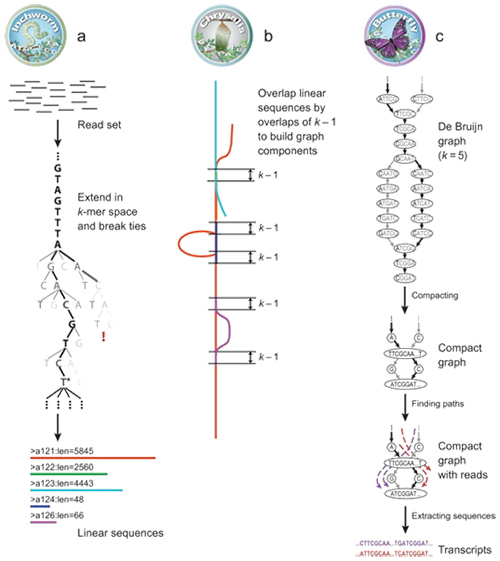
mRNA (De novo) Oversikt over Trinity
2.mRNA (De novo) distribusjon av genekspresjonsnivå
RNA-Seq er i stand til å oppnå et svært sensitivt estimat av genuttrykk.Normalt varierer det detekterbare området for transkripsjonsuttrykk FPKM fra 10^-2 til 10^6
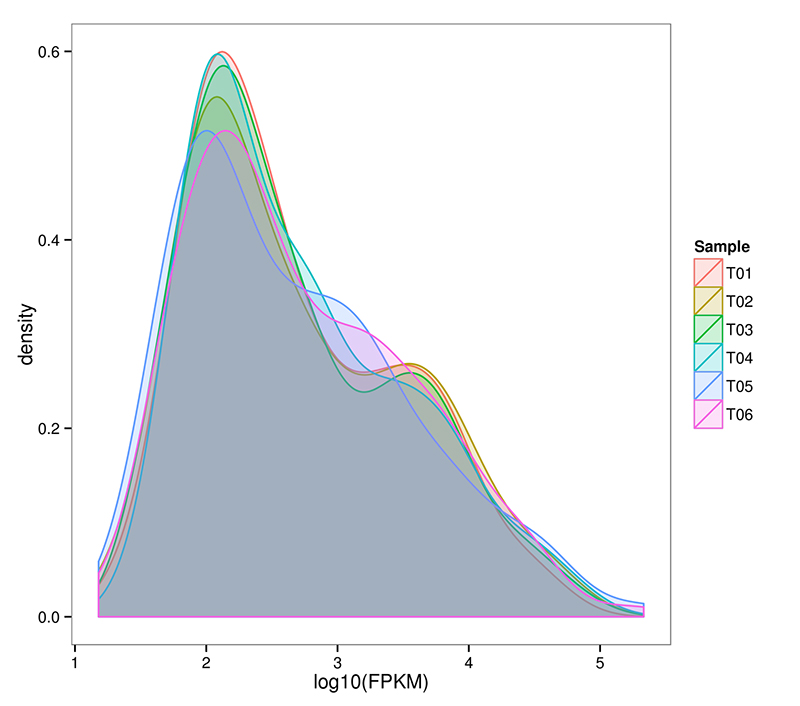
mRNA (De novo) Fordeling av FPKM-tetthet i hver prøve
3.mRNA (De novo) GO anrikningsanalyse av DEG
GO (Gene Ontology) database er et strukturert biologisk merknadssystem som inneholder et standard vokabular over gen- og genproduktfunksjoner.Den inneholder flere nivåer, der jo lavere nivået er, desto mer spesifikke er funksjonene.
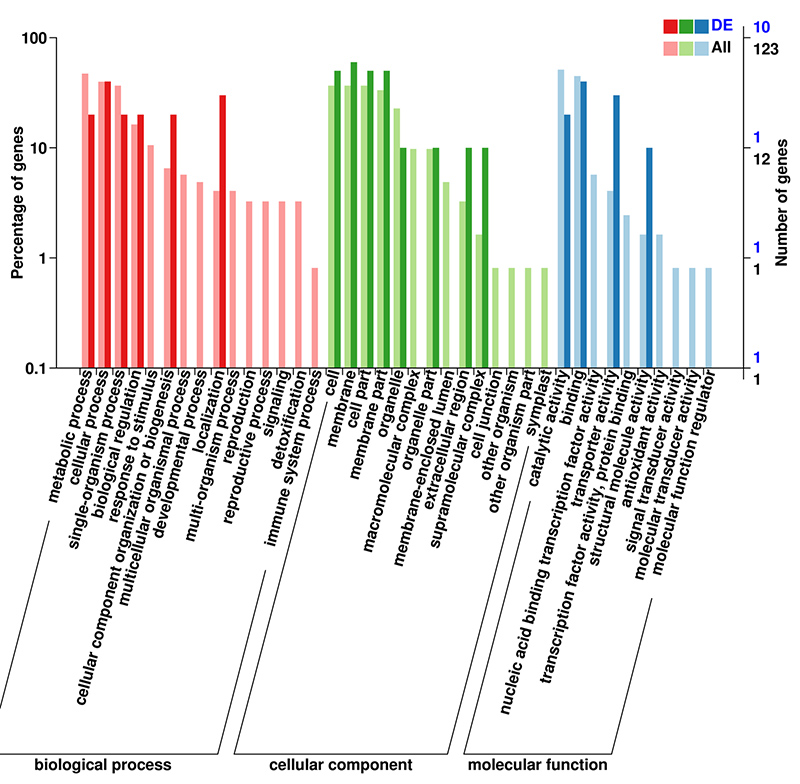
mRNA (De novo) GO klassifisering av DEG på andre nivå
BMK sak
Transkriptomanalyse av sukrosemetabolisme under pærehevelse og utvikling i løk (Allium cepa L.)
Publisert: grenser innen plantevitenskap2016
Sekvenseringsstrategi
Illumina HiSeq2500
Prøvesamling
Utah Yellow Sweet Spain-kultivaren "Y1351" ble brukt i denne studien.Antall prøver samlet var
15. dag etter hevelse (DAS) av pære (2-cm diameter og 3–4 g vekt), 30. DAS (5-cm diameter og 100–110 g vekt), og ~3 på den 40. DAS (7-cm diameter og 260–300 gram).
Nøkkelresultater
1. i Venn-diagrammet ble totalt 146 grader detektert over alle tre parene av utviklingsstadier
2. "Karbohydrattransport og metabolisme" ble representert av bare 585 unigener (dvs. 7 % av den annoterte COG).
3. Unigenes som var vellykket annotert til GO-databasen, ble klassifisert i tre hovedkategorier for de tre forskjellige stadiene av pæreutvikling.Mest representert i hovedkategorien "biologisk prosess" var "metabolsk prosess", etterfulgt av "cellulær prosess".I hovedkategorien "molekylær funksjon" var de to kategoriene mest representert "bindende" og "katalytisk aktivitet".
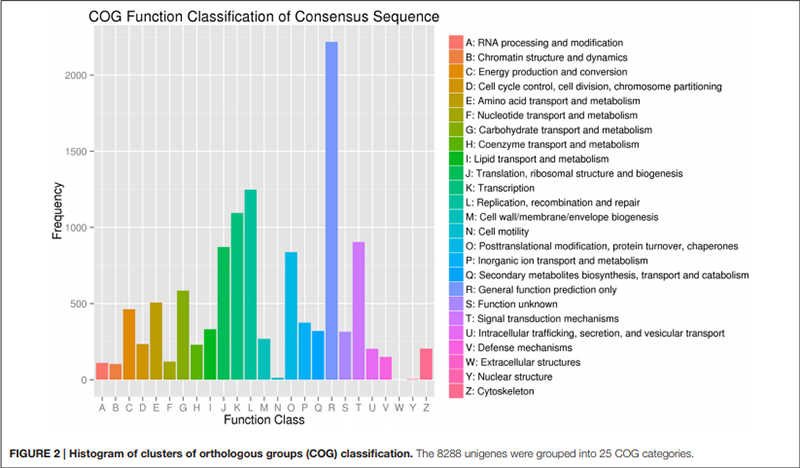 Histogram av klynger av ortologe grupper (COG) klassifisering | 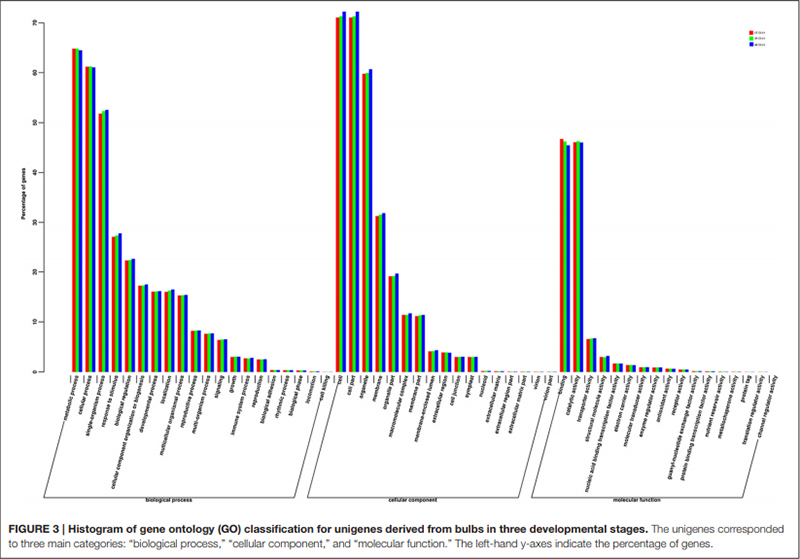 Histogram av genontologi (GO) klassifisering for unigener avledet fra pærer i tre utviklingsstadier |
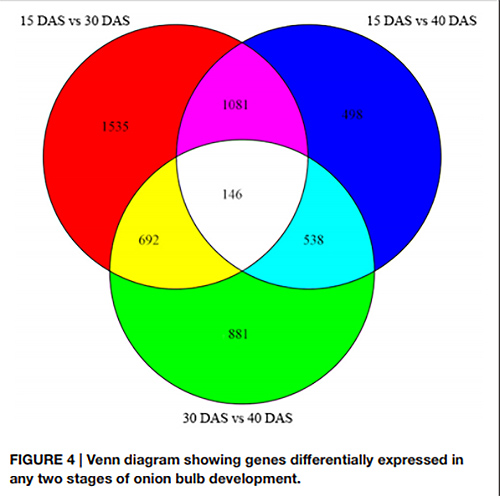 Venn-diagram som viser gener differensielt uttrykt i alle to stadier av løkløkutvikling |
Henvisning
Zhang C, Zhang H, Zhan Z, et al.Transkriptomanalyse av sukrosemetabolisme under pærehevelse og utvikling i løk (Allium cepa L.)[J].Frontiers in Plant Science, 2016, 7:1425-.DOI: 10.3389/fpls.2016.01425