
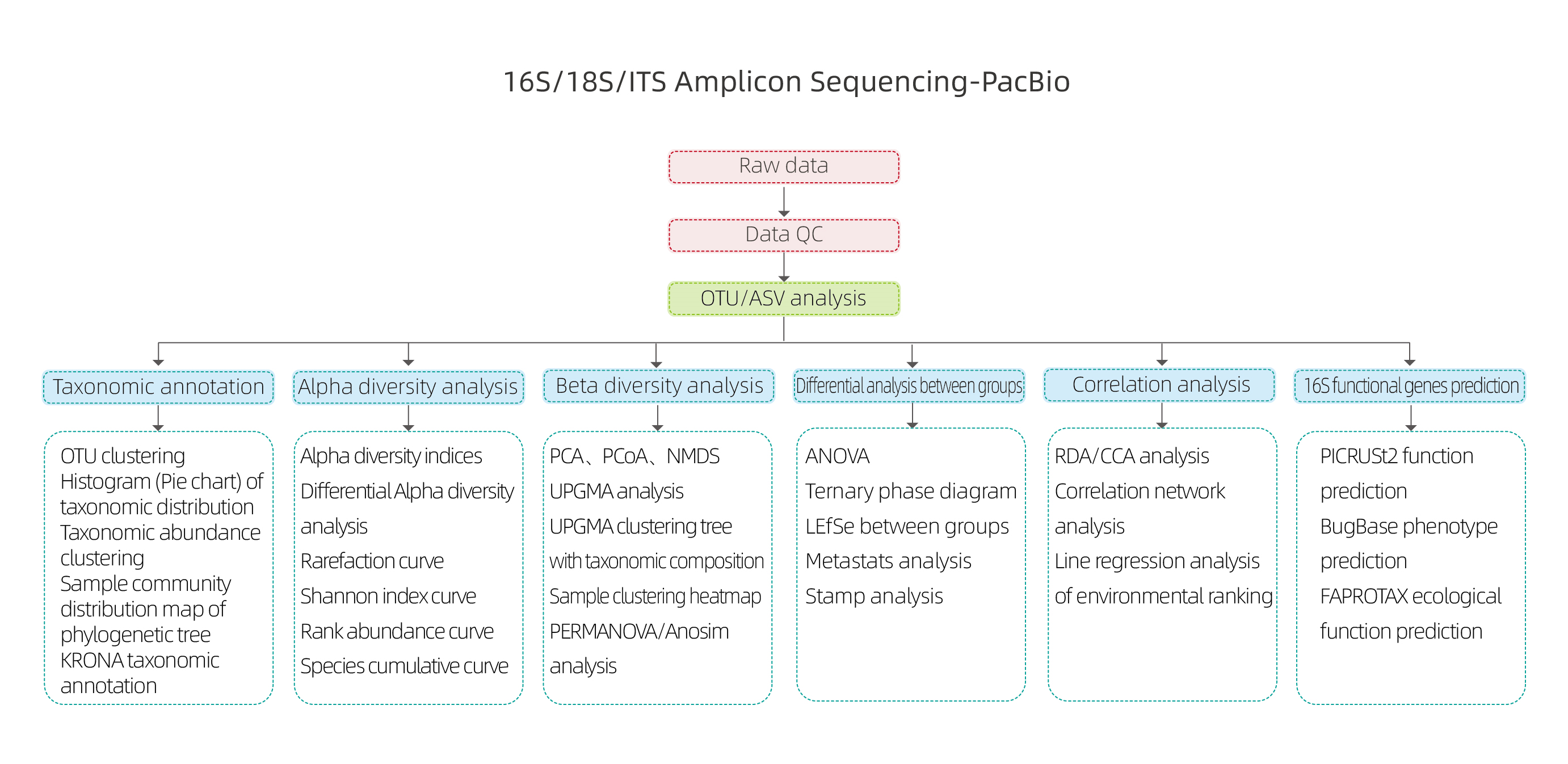
Sekwencjonowanie amplikonu 16S/18S/ITS – PacBio
Zalety serwisu

● Długie odczyty ujawniające pełną sekwencję 16S/18S/ITS
● Bardzo dokładne wywołanie podstawowe dzięki sekwencjonowaniu w trybie PacBio CCS
● Rozdzielczość na poziomie gatunku w adnotacji OTU/ASV
● Najnowsza analiza przepływu QIIME2 z różnorodnymi analizami pod względem bazy danych, adnotacji, OTU/ASV.
● Ma zastosowanie w różnorodnych badaniach społeczności drobnoustrojów
● BMK posiada bogate doświadczenie z ponad 100 000 próbek rocznie, obejmujących glebę, wodę, gaz, osad, kał, jelita, skórę, bulion fermentacyjny, owady, rośliny itp.
● BMKCloud ułatwił interpretację danych, zawierający 45 spersonalizowanych narzędzi analitycznych
Specyfikacje usług
| SekwencjonowaniePlatforma | Biblioteka | Zalecane dane | Czas realizacji |
| Kontynuacja PacBio II | Dzwonek SMRT | Tagi 5 tys./10 tys./20 tys | 44 dni robocze |
Analizy bioinformatyczne
● Kontrola jakości surowych danych
● Klastrowanie/odszumianie OTU (ASV)
● Adnotacja OTU
● Różnorodność alfa
● Różnorodność wersji beta
● Analiza międzygrupowa
● Analiza asocjacyjna względem czynników eksperymentalnych
● Przewidywanie genów funkcyjnych
Przykładowe wymagania i dostawa
Przykładowe wymagania:
DlaEkstrakty DNA:
| Typ próbki | Kwota | Stężenie | Czystość |
| Ekstrakty DNA | > 1 µg | > 20 ng/μl | OD260/280= 1,6-2,5 |
Dla próbek środowiskowych:
| Typ próbki | Zalecana procedura pobierania próbek |
| Gleba | Ilość próbki: ok.5 g;Pozostałą zwiędłą substancję należy usunąć z powierzchni;Zmiel duże kawałki i przepuść przez filtr 2 mm;Próbki w sterylnej probówce EP lub cyrotubie do rezerwacji. |
| Kał | Ilość próbki: ok.5 g;Zbieraj i rozdzielaj próbki do sterylnej probówki EP lub krioprobówki w celu rezerwacji. |
| Treść jelitowa | Próbki należy przetwarzać w warunkach aseptycznych.Przemyć pobraną tkankę PBS;Odwirować PBS i zebrać osad do probówek EP. |
| Osad | Ilość próbki: ok.5 g;Zbierz i podziel na porcje próbkę osadu do sterylnej probówki EP lub krioprobówki w celu rezerwacji |
| Zbiornik wodny | W przypadku próbki zawierającej ograniczoną ilość drobnoustrojów, takiej jak woda z kranu, woda ze studni itp., zebrać co najmniej 1 l wody i przepuścić przez filtr 0,22 μm, aby wzbogacić mikroorganizmy na membranie.Przechowywać membranę w sterylnej probówce. |
| Skóra | Ostrożnie zeskrob powierzchnię skóry sterylnym wacikiem lub ostrzem chirurgicznym i umieść go w sterylnej probówce. |
Zalecana dostawa próbek
Zamrozić próbki w ciekłym azocie na 3-4 godziny i przechowywać w ciekłym azocie lub w -80 stopniach z rezerwacją długoterminową.Wymagana jest wysyłka próbek z suchym lodem.
Przebieg prac serwisowych

Dostawa próbek

Budowa biblioteki

Sekwencjonowanie

Analiza danych

Usługi posprzedażowe
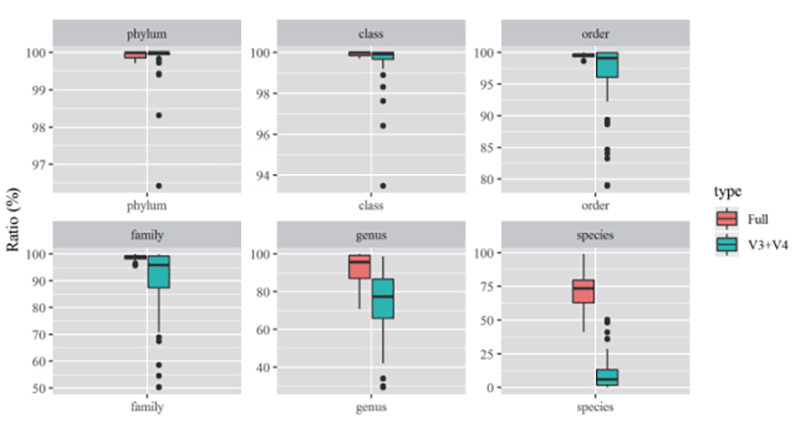
1. Częstotliwość adnotacji w profilowaniu społeczności drobnoustrojów w oparciu o V3+V4(Illumina) w porównaniu z profilowaniem pełnej długości (PacBio).
(W celach statystycznych zastosowano dane dotyczące 30 losowo wybranych projektów)
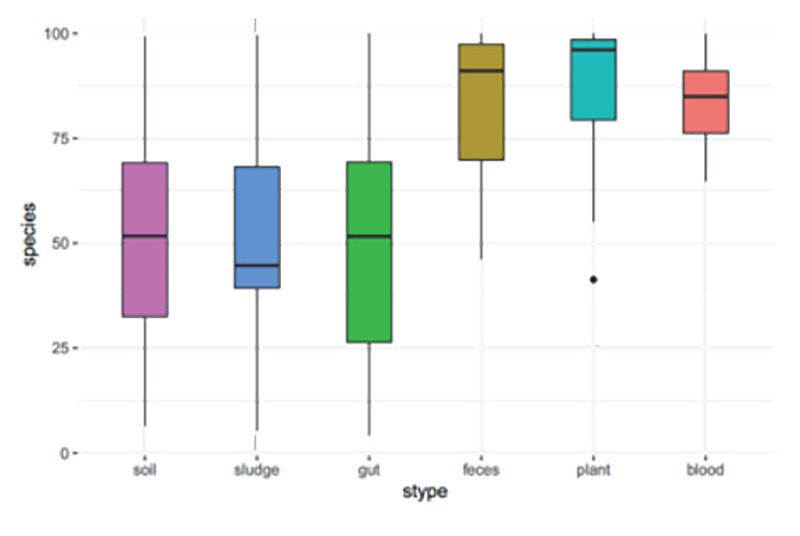
2. Częstotliwość adnotacji w przypadku sekwencjonowania amplikonu pełnej długości na poziomie gatunku w różnych typach próbek
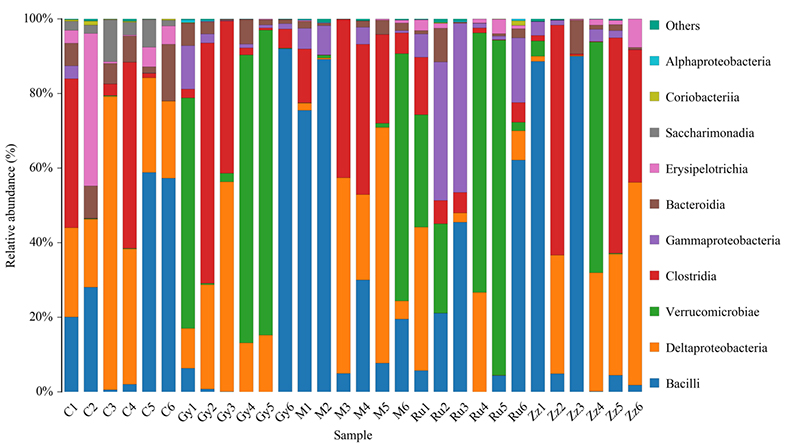
3.Rozmieszczenie gatunków
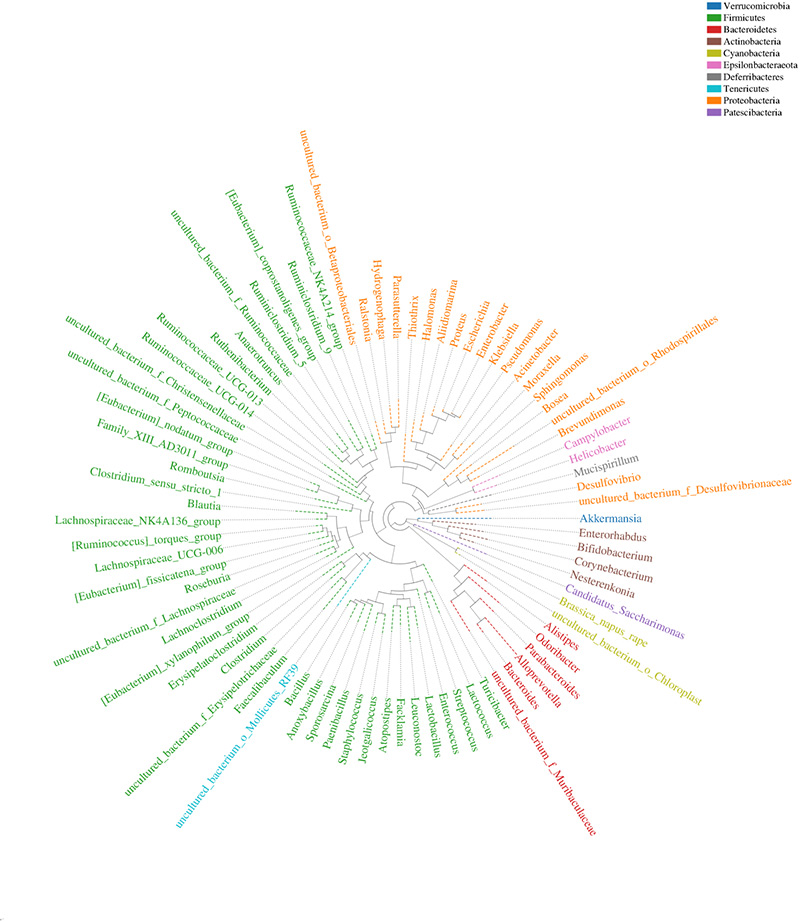
4.Drzewo filogenetyczne
Sprawa BMK
Narażenie na arsen powoduje uszkodzenie bariery jelitowej i w konsekwencji aktywację osi jelitowo-wątrobowej, co prowadzi do zapalenia i piroptozy wątroby u kaczek
Opublikowany:Nauka o Środowisku Całościowym,2021
Strategia sekwencjonowania:
Próbki: Kontrola vs grupa narażona na dawkę 8 mg/kg ATO
Wydajność danych sekwencjonowania: łącznie 102 583 surowych sekwencji CCS
Kontrola: 54 518 ± 747 efektywnych CCS
Narażony na działanie ATO: 45 050 ± 1675 efektywnych CCS
Kluczowe wyniki
Różnorodność alfa:Ekspozycja na ATO znacząco zmieniła bogactwo i różnorodność mikroorganizmów jelitowych u kaczek.
Analiza metastatów:
Na poziomie gromady: 2 gromady bakteryjne wykryte tylko w grupach kontrolnych
Na poziomie rodzaju: Stwierdzono, że 6 rodzajów różni się znacząco pod względem względnej liczebności
Na poziomie gatunku: łącznie zidentyfikowano 36 gatunków, z czego 6 różniło się istotnie liczebnością względną
Odniesienie
Thingholm, LB i in.„Osoby otyłe z cukrzycą typu 2 i bez niej wykazują różną pojemność funkcjonalną i skład drobnoustrojów jelitowych”.Gospodarz komórkowy i mikrob26,2 (2019).











