Analiza asociației la nivelul genomului
1. Avantajele serviciului
● Cazuri de proiecte abundente: de la înființarea sa în 2009, BMKGENE a finalizat sute de proiecte de specii în cercetarea populației GWAS, a ajutat cercetătorii să publice peste 100 de articole, iar factorul de impact cumulat a ajuns la 500.
● Analiști profesioniști.
● Ciclu scurt de analiză.
● Exploatarea precisă a datelor.
2. Specificații de service
| Tip | Scara Populației | Strategia de secvențiere și profunzime |
| SLAF-GWAS | Numărul eșantionului ≥200 | Dimensiunea genomului < 400M, cu genom ref, se recomandă WGS |
| Dimensiunea genomului ≤ 1G, 100K etichete și 10X | ||
| 1G ≤ dimensiunea genomului ≤ 2G, 200K etichete și 10X | ||
| Dimensiunea genomului > 2G, 300K etichete și 10X | ||
| WGS-GWAS | Numărul eșantionului ≥200 | 10X pentru fiecare probă |
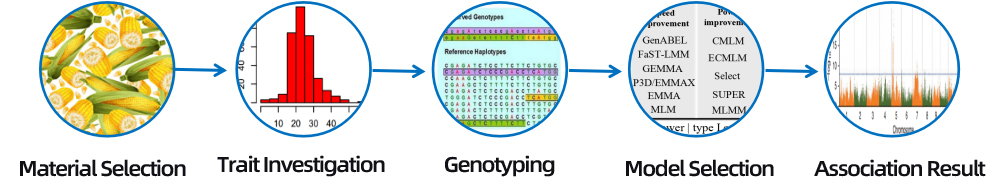
3. Selectarea materialului



Diferite soiuri, subspecii, rase locale/banci de gene/familii mixte/resurse sălbatice
Diferite soiuri, subspecii, rase locale
Familie cu frați jumătate/Familie cu frați întregi/resurse sălbatice
4. Analiza bioinformației
● Analiza asocierii la nivelul genomului
● Analiza și screening-ul SNP semnificativ
● Adnotarea funcțională a genei candidate
5. Fluxul de lucru al serviciului

Design experiment

Livrare mostre

extracția ARN

Construcția bibliotecii

Secvențierea

Analiza datelor

Servicii post-vânzare
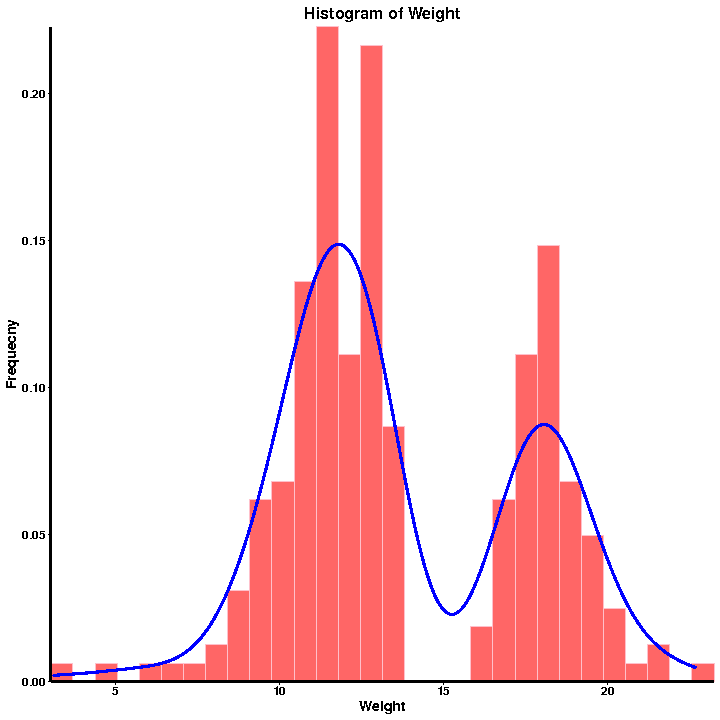
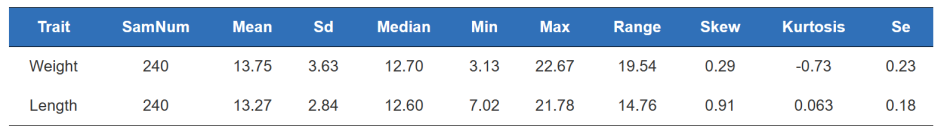
A.Fenotip QC
Histograma distribuției de frecvență
Statistica fenotipului
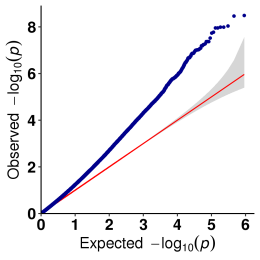
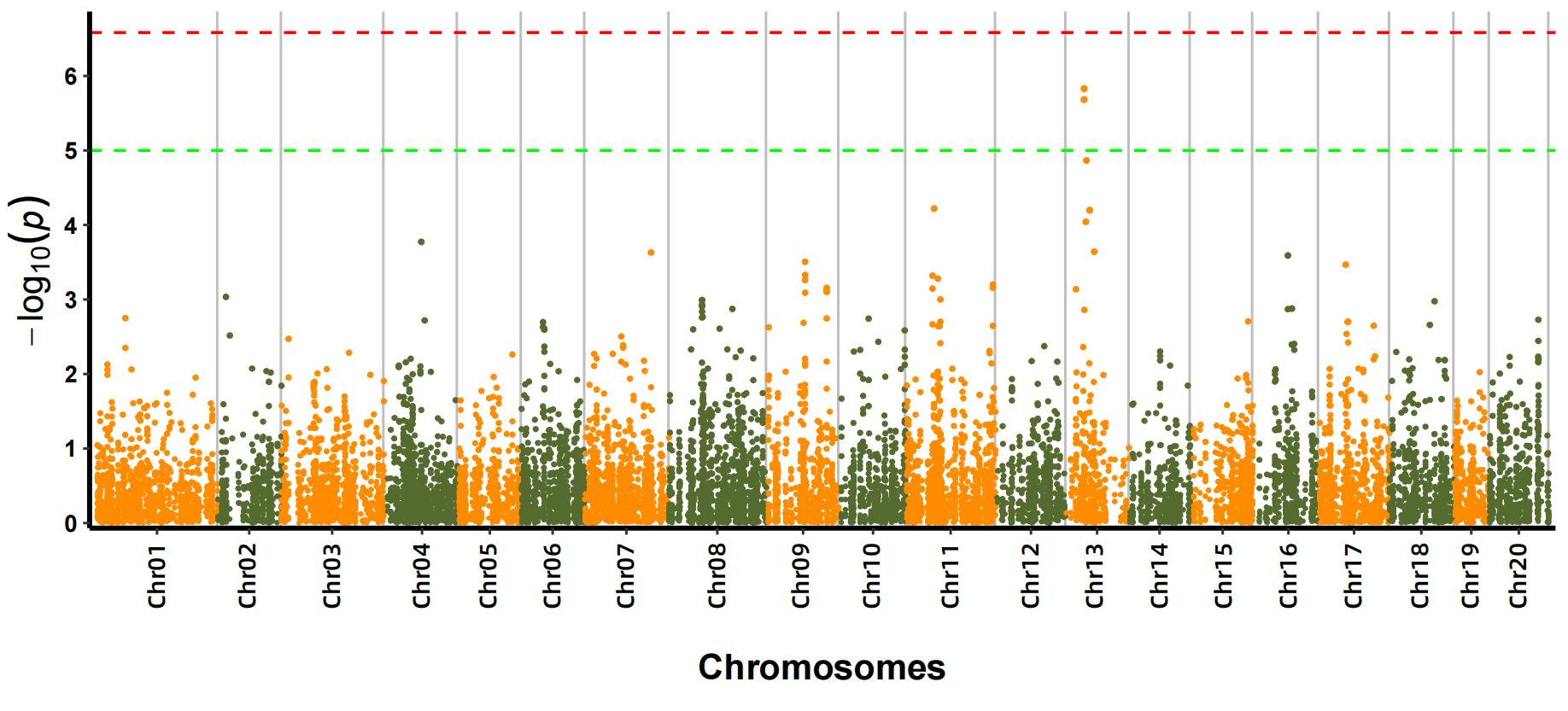
b.Analiza asocierii (Model: GEMMA, FaST-LMM, EMMAX)
Complot QQ
Plot Manhattan
| An | Jurnal | IF | Titlu |
| 2022 | NC | 17.69 | Baza genomică a giga-cromozomilor și giga-genomul bujorului de copac Paeonia ostii |
| 2015 | NP | 7.43 | Amprentele domestice ancorează regiunile genomice de importanță agronomică în boabele de soia |
| 2018 | MP | 9.32 | Resecvențierea întregului genom a unei colecții la nivel mondial de accesări de rapiță dezvăluie baza genetică a divergenței lor de ecotip |
| 2022 | HR | 7.29 | Analiza de asociere la nivelul genomului oferă perspective moleculare asupra variației naturale a mărimii semințelor de pepene verde |