Analýza asociácie celého genómu
1. Výhody služby
● Abundant Project Cases: od svojho založenia v roku 2009 spoločnosť BMKGENE dokončila stovky druhov projektov v oblasti výskumu populácie GWAS, pomohla výskumníkom publikovať viac ako 100 článkov a kumulatívny dopadový faktor dosiahol 500.
● Profesionálni analytici.
● Krátky cyklus analýzy.
● Presné získavanie údajov.
2. Špecifikácie služby
| Typ | Populačná mierka | Stratégia a hĺbka sekvenovania |
| SLAF-GWAS | Číslo vzorky ≥200 | Veľkosť genómu < 400M, s referenčným genómom, odporúča sa WGS |
| Veľkosť genómu ≤ 1G, 100K tagov a 10X | ||
| 1G ≤ Veľkosť genómu ≤ 2G, 200 000 tagov a 10X | ||
| Veľkosť genómu > 2G, 300 000 značiek a 10X | ||
| WGS-GWAS | Číslo vzorky ≥200 | 10X pre každú vzorku |
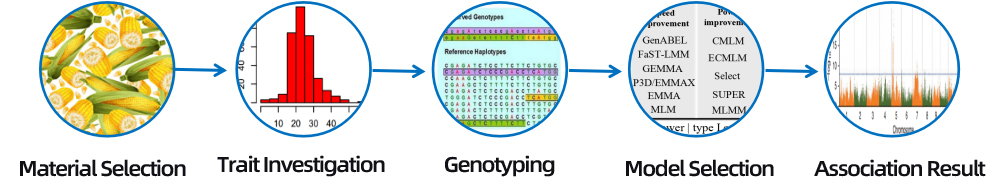
3. Výber materiálu



Rôzne odrody, poddruhy, krajové rasy / génové banky / zmiešané rodiny / divoké zdroje
Rôzne odrody, poddruhy, krajinné rasy
Rodina polovičného súrodenca/rodina úplného súrodenca/divoké zdroje
4. Bioinformačná analýza
● Analýza asociácií v rámci celého genómu
● Analýza a skríning významného SNP
● Funkčná anotácia kandidátskeho génu
5. Tok servisných prác

Dizajn experimentu

Doručenie vzorky

Extrakcia RNA

Výstavba knižnice

Sekvenovanie

Analýza dát

Popredajné služby
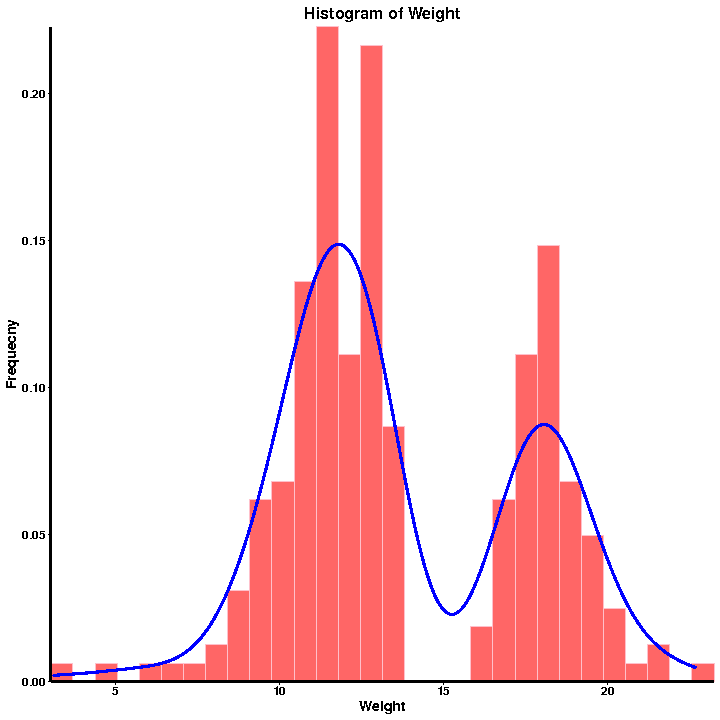
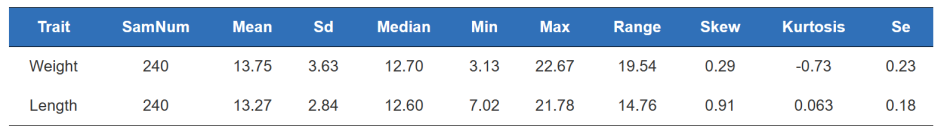
a.Fenotyp QC
Histogram rozdelenia frekvencií
Štatistika fenotypov
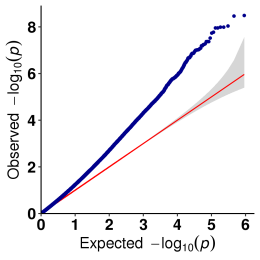
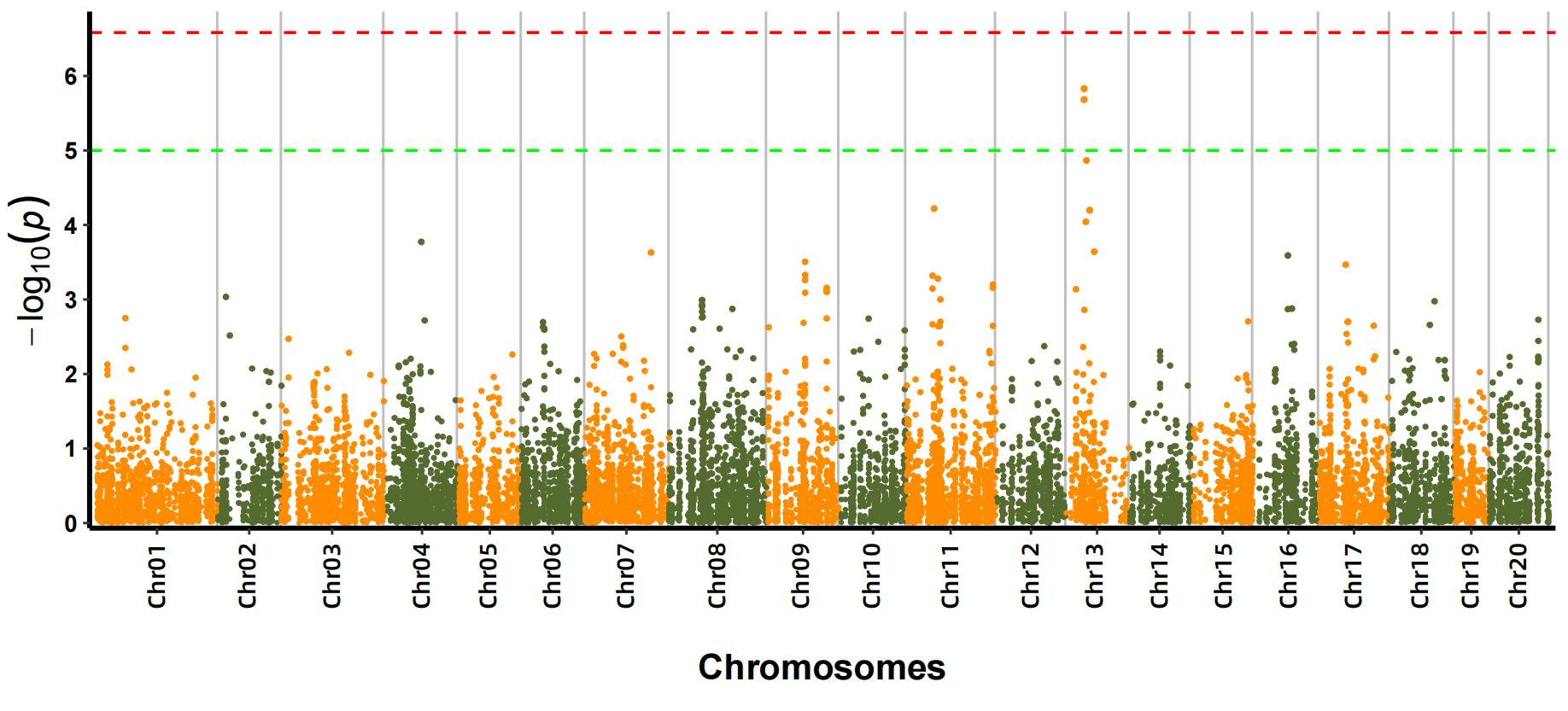
b.Asociačná analýza (Model: GEMMA, FaST-LMM, EMMAX)
Zápletka QQ
Sprisahanie Manhattanu
| rok | Denník | IF | Názov |
| 2022 | NC | 17,69 | Genomický základ giga-chromozómov a giga-genómu stromovej pivonky Paeonia ostii |
| 2015 | NP | 7.43 | Stopy domestikácie ukotvujú genómové oblasti agronomického významu v sójových bôboch |
| 2018 | MP | 9.32 | Resekvenovanie celého genómu celosvetovej zbierky prírastkov repky odhaľuje genetický základ ich ekotypovej divergencie |
| 2022 | HR | 7.29 | Asociačná analýza celého genómu poskytuje molekulárny pohľad na prirodzenú variáciu veľkosti semien vodného melónu |