
Runtuyan mRNA panjangna pinuh -PacBio
Kaunggulan Service
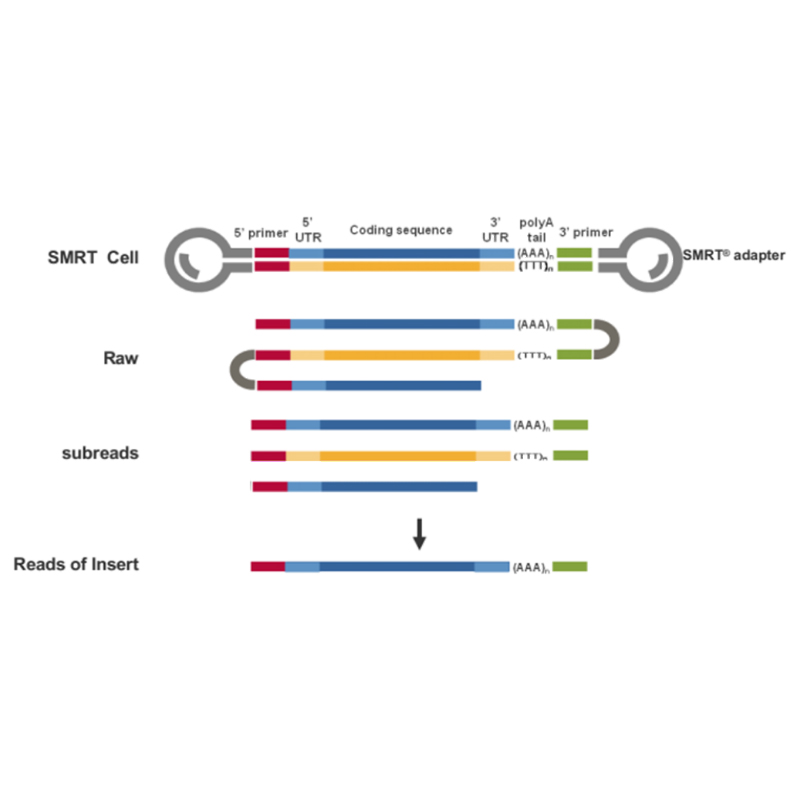
● Langsung maca-kaluar molekul cDNA full-length ti tungtung 3'- nepi ka tungtung 5'-
● resolusi tingkat Iso-formulir dina struktur runtuyan
● Transkrip kalayan akurasi sareng integritas anu luhur
● Kacida cocog jeung spésiés vaiours
● kapasitas sequencing badag kalawan 4 PacBio Sequel II platform sequencing dilengkepan
● Kacida ngalaman kalawan leuwih 700 proyék RNA sequencing basis Pacbio
● pangiriman hasil basis BMKCloud: ngaropéa data-pertambangan sadia on platform.
● jasa saatos-diobral valid pikeun 3 bulan sanggeus proyék parantosan
Spésifikasi Service
Platform: PacBio Sequel II
Perpustakaan sequencing: perpustakaan mRNA poly A- enriched
Hasil data anu disarankeun: 20 Gb/sampel (Gumantung kana spésiés)
FLNC(%): ≥75%
*FLNC: Transcipts non-chimeric panjang pinuh
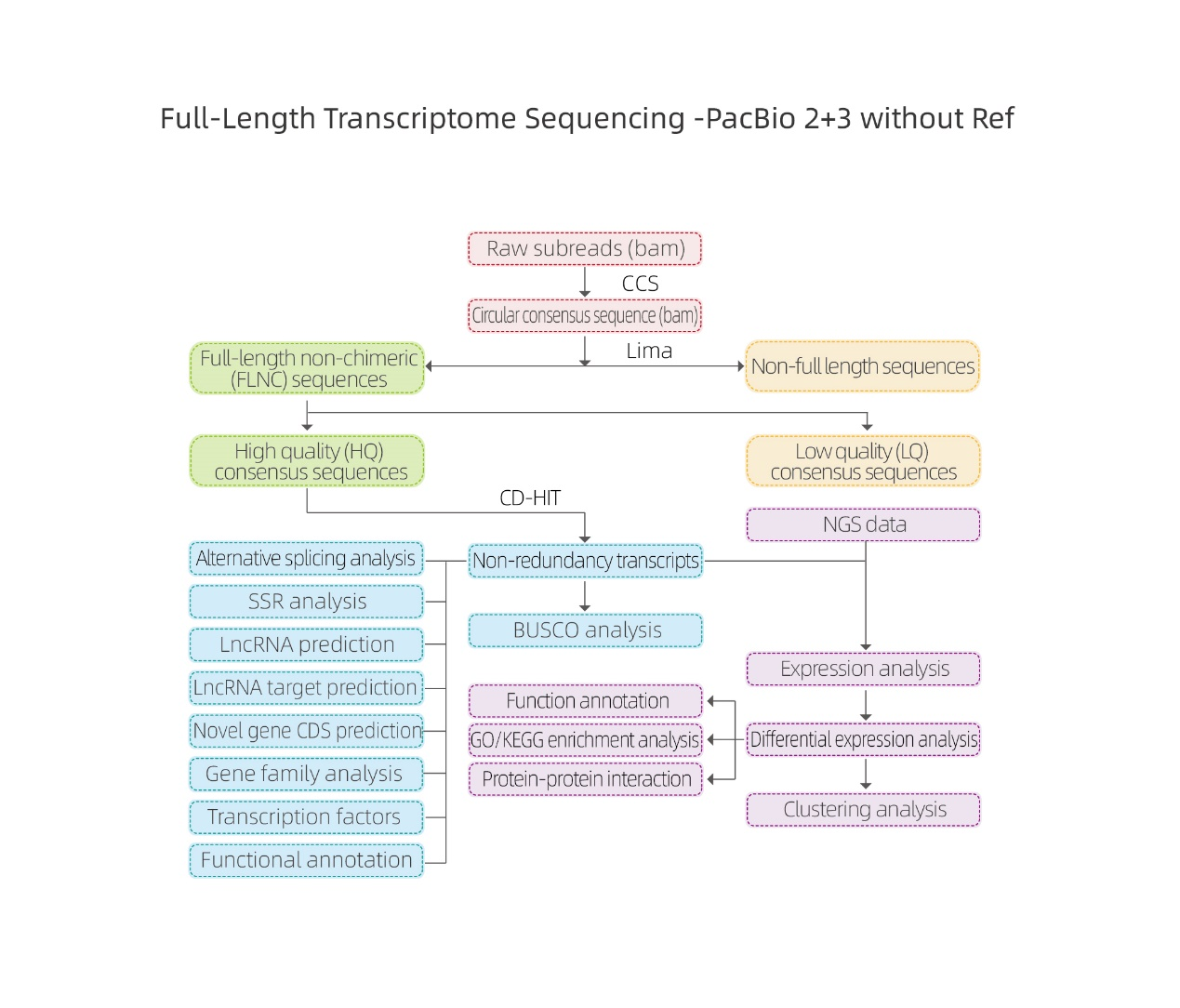
Analisis bioinformatika
● Ngolah data atah
● idéntifikasi Transcript
● Struktur runtuyan
● éksprési Quantification
● Fungsi Anotasi
Syarat Sampel sareng Pangiriman
Syarat Sampel:
Nukléotida:
| Conc.(ng/μl) | Jumlah (μg) | Kasucian | Integritas |
| ≥ 120 | ≥ 0,6 | OD260/280 = 1,7-2,5 OD260 / 230 = 0,5-2,5 Kawates atanapi henteu aya kontaminasi protéin atanapi DNA anu dipidangkeun dina gél. | Pikeun tutuwuhan: RIN≥7.5; Pikeun sato: RIN≥8.0; 5.0≥ 28S/18S≥1.0; kawates atawa euweuh élévasi dasar |
Tisu: Beurat (garing):≥1 g
*Pikeun jaringan anu langkung alit ti 5 mg, kami nyarankeun ngirim sampel jaringan flash beku (dina nitrogén cair).
Suspensi sél:Jumlah sél = 3 × 106- 1 × 107
* Kami nyarankeun pikeun ngirim lysate sél beku.Upami sél éta cacah langkung alit ti 5×105, flash beku dina nitrogén cair disarankeun, nu leuwih hade pikeun ékstraksi mikro.
Sampel getih:Volume≥1 ml
Mikroorganisme:Beurat ≥ 1 g
Disarankeun Pangiriman Sampel
Wadahna:
2 ml centrifuge tube (Timah foil teu dianjurkeun)
Sampel panyiri: Grup + ulangan misalna A1, A2, A3;B1, B2, B3...
Pangiriman:
1. Garing-és: Sampel kudu dipak dina kantong jeung dikubur di garing-és.
2. tabung RNAstable: sampel RNA bisa garing dina tube stabilisasi RNA (misalna RNAstable®) jeung shipped dina suhu kamar.
Aliran Gawé Palayanan

Desain ékspérimén

pangiriman sampel

ékstraksi RNA

Pangwangunan perpustakaan

Sequencing

Analisis data

jasa saatos-diobral
1.FLNC distribusi panjangna
Panjang full-length non-chimeric read(FLNC) nunjukkeun panjang cDNA dina konstruksi perpustakaan.Sebaran panjang FLNC mangrupikeun indikator anu penting dina ngevaluasi kualitas konstruksi perpustakaan.
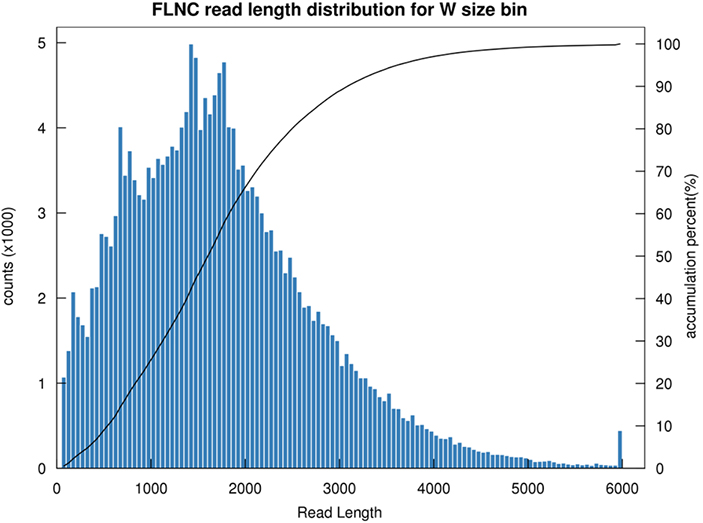
FLNC baca distribusi panjangna
2.Complete ORF distribusi panjang wewengkon
Kami nganggo TransDecoder pikeun ngaramalkeun daérah coding protéin sareng sekuen asam amino anu cocog pikeun ngahasilkeun set unigene, anu ngandung inpormasi transkrip anu henteu kaleuleuwihan dina sadaya conto.
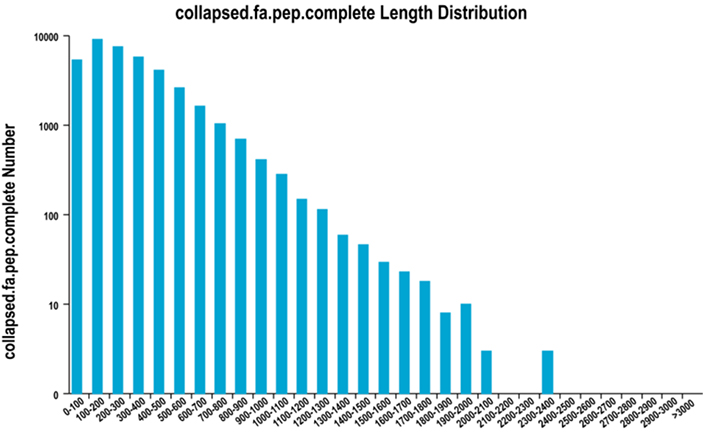
Distribusi panjang wilayah ORF lengkep
3. Analisis pengayaan jalur KEGG
Transkrip anu dikedalkeun sacara béda (DETs) tiasa diidentipikasi ku cara ngajajarkeun data urutan RNA basis NGS dina set transkrip full-length anu dihasilkeun ku data urutan PacBio.DETs ieu tiasa salajengna diolah pikeun sagala rupa analisis fungsional, misalna analisis pengayaan jalur KEGG.
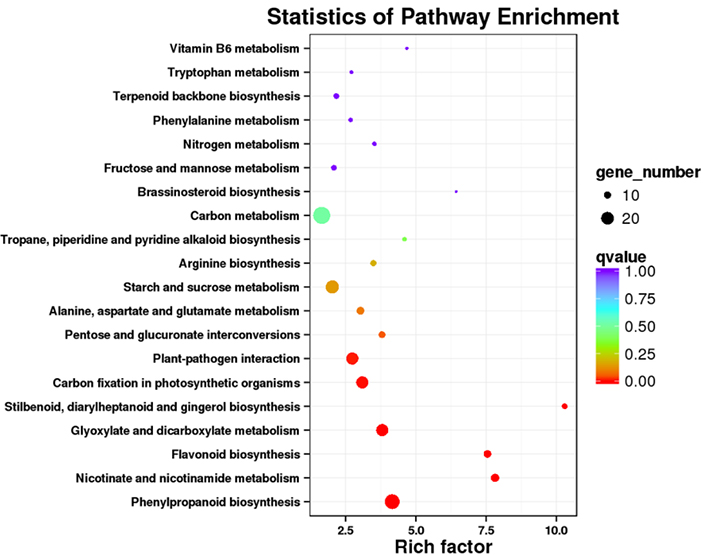
DET KEGG jalur pengayaan -Dot plot
Kasus BMK
Dinamika perkembangan Populus stem transcriptome
Diterbitkeun: Jurnal Biotéhnologi Tutuwuhan, 2019
Strategi urutan:
kumpulan sampel:wewengkon batang: puncak, ruas kahiji (IN1), ruas kadua (IN2), ruas katilu (IN3), ruas (IN4) jeung ruas (IN5) ti Nanlin895
runtuyan NGS:RNA tina 15 individu dikumpulkeun salaku hiji sampel biologis.Tilu ulangan biologis unggal titik diolah pikeun urutan NGS
TGS-runtuyan:Wewengkon batang dibagi jadi tilu wilayah, nyaéta apex, IN1-IN3 sareng IN4-IN5.Unggal daérah diolah pikeun urutan PacBio kalayan opat jinis perpustakaan: 0-1 kb, 1-2 kb, 2-3 kb sareng 3-10 kb.
Hasil konci
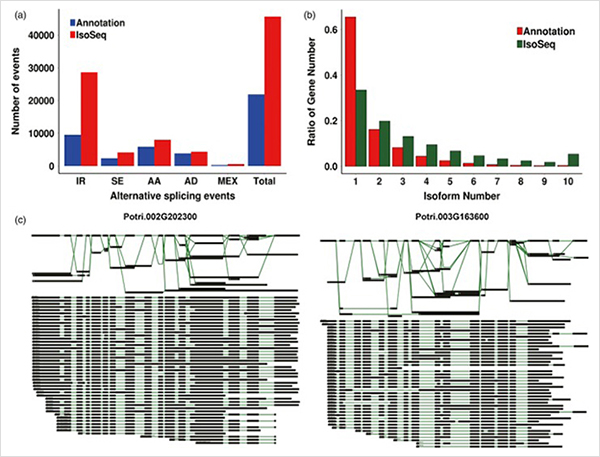
1. Jumlahna aya 87150 transkrip panjang pinuh diidentifikasi, dimana, 2081 isoforms novel sareng 62058 isoforms spliced alternatif novel anu diidentifikasi.
2.1187 lncRNA sareng 356 gén fusi diidentifikasi.
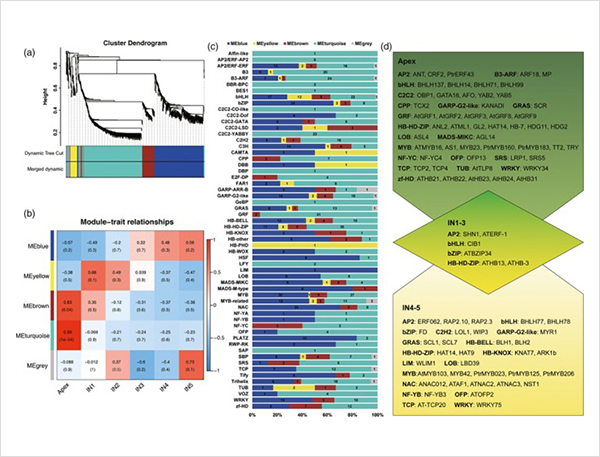
3.From tumuwuhna primér pikeun tumuwuhna sekundér, 15838 differentially dikedalkeun transkrip ti 995 differentially dikedalkeun gén anu dicirikeun.Dina sakabéh DEGs, 1216 éta faktor transkripsi, lolobana nu teu acan dilaporkeun.
4.GO analisis pengayaan wangsit pentingna division sél jeung prosés oksidasi-réduksi dina tumuwuhna primér sarta sekundér.
Acara splicing alternatif sareng isoforms béda
Analisis WGCNA dina faktor transkripsi
Rujukan
Chao Q, Gao ZF, Zhang D, et al.Dinamika perkembangan Populus stem transcriptome.Tutuwuhan Biotéhnologi J. 2019;17 (1): 206-219.doi: 10.1111/pbi.12958











