10x Genomics Visium Spatial Transcriptome
Funktioner
● Upplösning: 100 µM
● Punktdiameter: 55 µM
● Antal platser: 4992
● Fångstområde: 6,5 x 6,5 mm
● Varje streckkodad fläck är laddad med primers som består av 4 sektioner:
- poly(dT)-svans för mRNA-priming och cDNA-syntes
- Unik Molecular Identifier (UMI) för att korrigera amplifieringsbias
- Rumslig streckkod
- Bindningssekvens av partiell läs 1 sekvenseringsprimer
● H&E-färgning av sektioner
Fördelar
●One-stop service: integrerar alla erfarenhets- och färdighetsbaserade steg, inklusive kryosnitt, färgning, vävnadsoptimering, rumslig streckkodning, biblioteksförberedelse, sekvensering och bioinformatik.
● Mycket kompetent tekniskt team: med erfarenhet av över 250 vävnadstyper och 100+ arter inklusive människor, mus, däggdjur, fiskar och växter.
●Realtidsuppdatering av hela projektet: med full kontroll över experimentella framsteg.
●Omfattande standard bioinformatik:paketet innehåller 29 analyser och 100+ högkvalitativa siffror.
●Anpassad dataanalys och visualisering: tillgänglig för olika forskningsförfrågningar.
●Valfri gemensam analys med encellig mRNA-sekvensering
Specifikationer
| Exempel på krav | Bibliotek | Sekvenseringsstrategi | Data rekommenderas | Kvalitetskontroll |
| OCT-inbäddade kryoprover, FFPE-prover (Optimal diameter: ca 6x6x6 mm3) 3 block per prov | 10X Visium cDNA-bibliotek | Illumina PE150 | 50K PE-avläsningar per punkt (60 Gb) | RIN>7 |
För mer information om vägledning för provförberedelser och servicearbetsflöde är du välkommen att prata med aBMKGENE expert
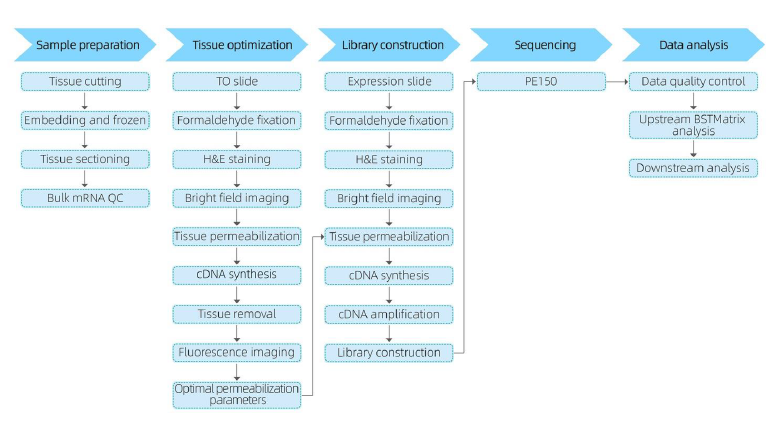
Service arbetsflöde
I provberedningsfasen utförs ett första bulk-RNA-extraktionsförsök för att säkerställa att ett högkvalitativt RNA kan erhållas.I vävnadsoptimeringssteget färgas och visualiseras sektionerna och permeabiliseringsförhållandena för mRNA-frisättning från vävnad optimeras.Det optimerade protokollet tillämpas sedan under bibliotekskonstruktion, följt av sekvensering och dataanalys.
Det kompletta tjänstearbetsflödet innefattar uppdateringar i realtid och klientbekräftelser för att upprätthålla en responsiv återkopplingsslinga, vilket säkerställer smidigt projektgenomförande.
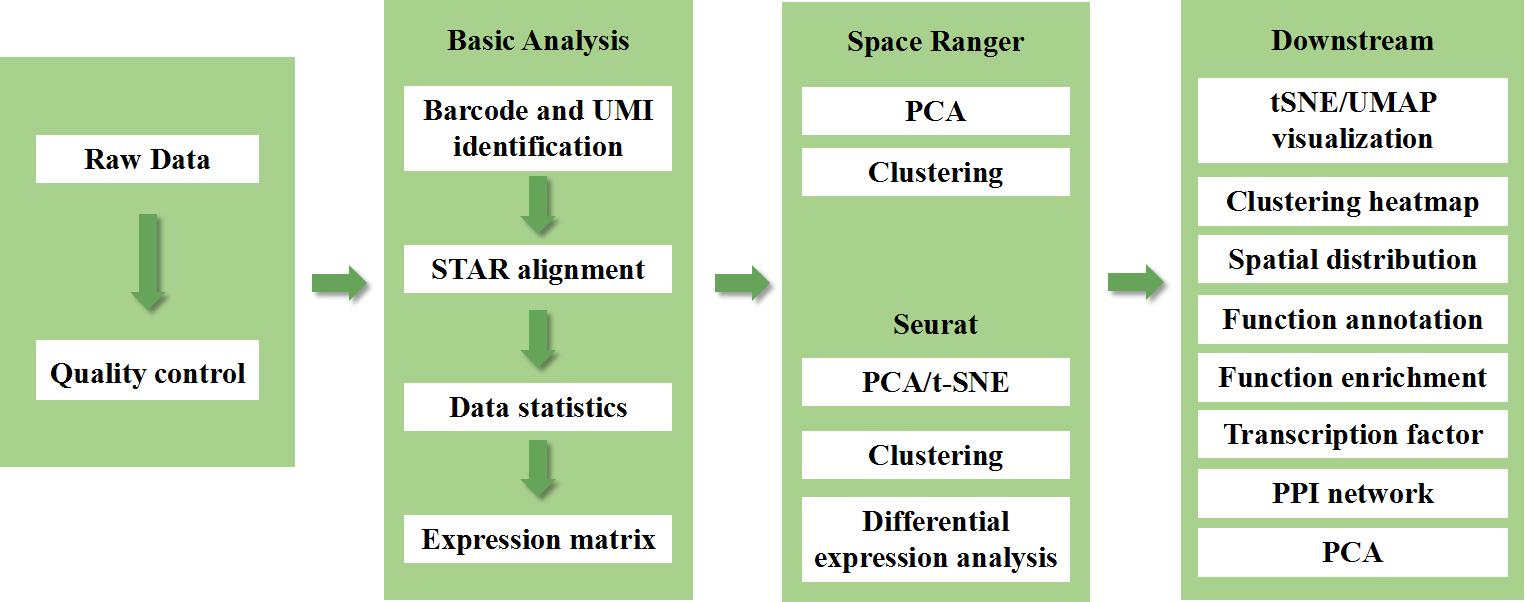
Innehåller följande analys:
Datakvalitetskontroll:
o Datautgång och distribution av kvalitetspoäng
o Gendetektion per punkt
o Vävnadstäckning
Analys av inre prov:
o Genrikedom
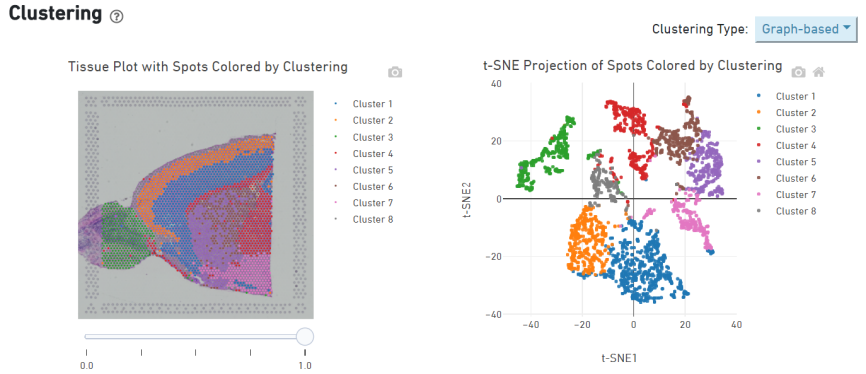
o Punktklustring, inklusive reducerad dimensionsanalys
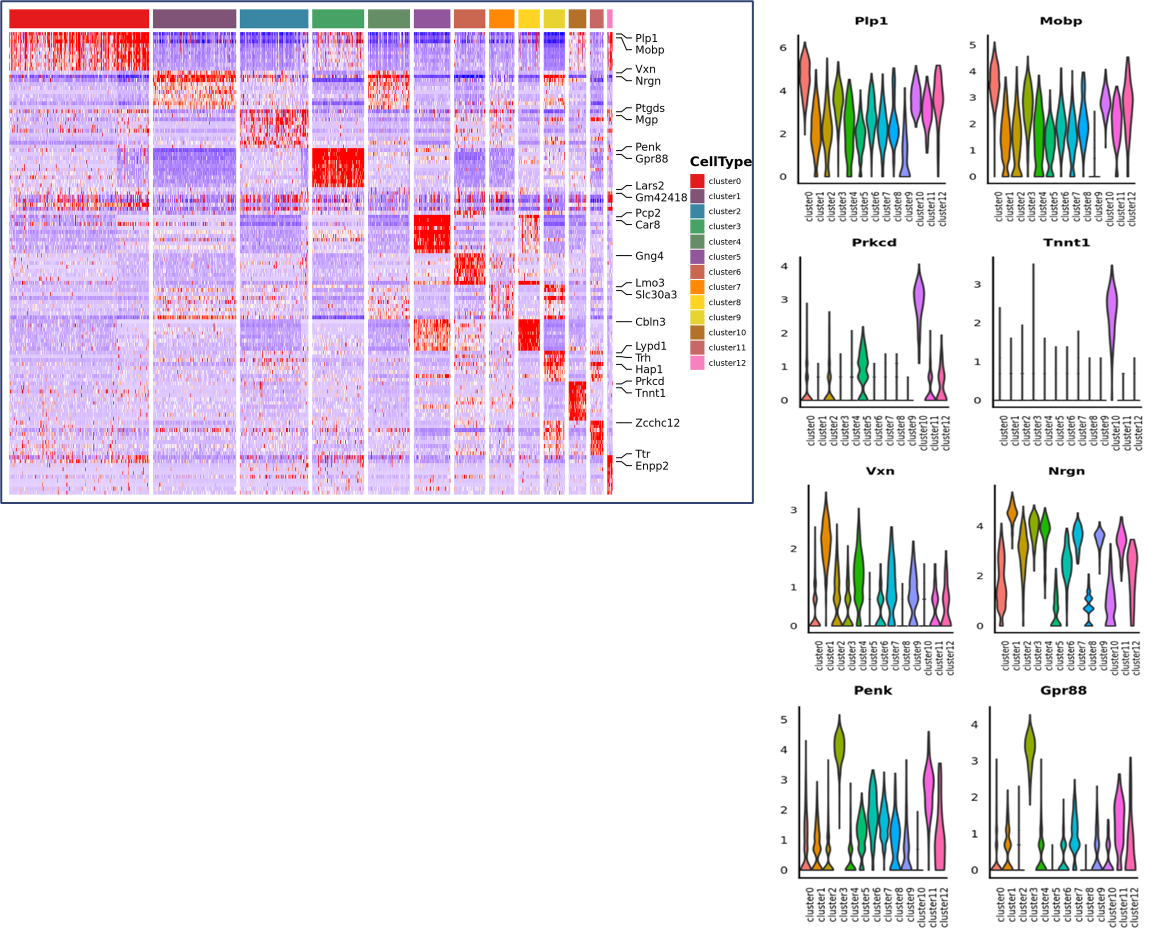
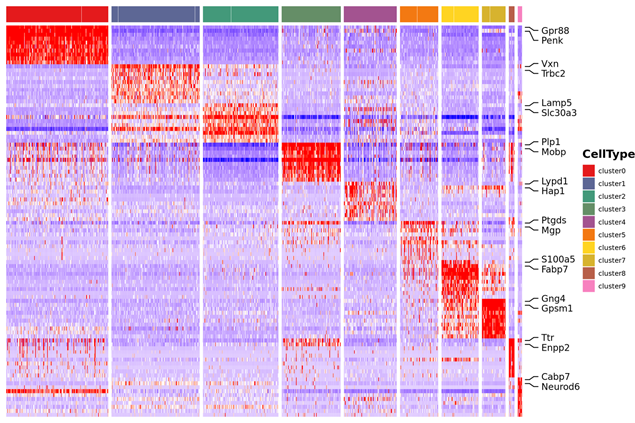
o Differentiell expressionsanalys mellan kluster: identifiering av markörgener
o Funktionell annotering och anrikning av markörgener
Intergruppsanalys
o Återkombination av fläckar från både prover (t.ex. sjuka och kontroll) och re-kluster
o Identifiering av markörgener för varje kluster
o Funktionell annotering och anrikning av markörgener
o Differentiellt uttryck för samma kluster mellan grupper
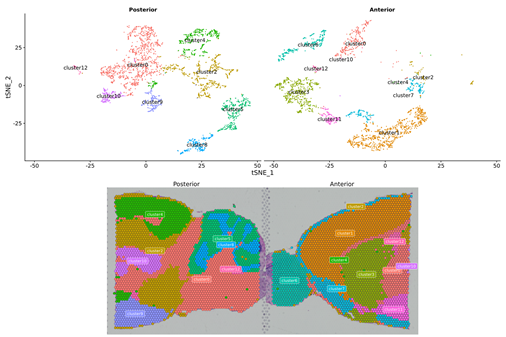
Analys av inre prov
Fläckklustring
Identifiering av markörgener och rumslig fördelning
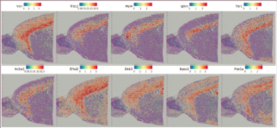
Intergruppsanalys
Datakombination från båda grupperna och re-cluster
Markörgener för nya kluster
Utforska framstegen som underlättas av BMKGenes rumsliga transkriptomiktjänst av 10X Visium I dessa utvalda publikationer:
Chen, D. et al.(2023) "mthl1, en potentiell Drosophila-homolog av däggdjursadhesion GPCRs, är involverad i antitumörreaktioner på injicerade onkogena celler i flugor", Proceedings of the National Academy of Sciences of the United States of America, 120(30), s.e2303462120.doi: /10.1073/pnas.2303462120
Chen, Y. et al.(2023) 'STEEL möjliggör högupplöst avgränsning av spatiotemporala transkriptomiska data', Briefings in Bioinformatics, 24(2), s. 1–10.doi: 10.1093/BIB/BBAD068.
Liu, C. et al.(2022) 'A spatiotemporal atlas of organogenesis in the development of orchid flowers', Nucleic Acids Research, 50(17), s. 9724–9737.doi: 10.1093/NAR/GKAC773.
Wang, J. et al.(2023) "Integrating Spatial Transcriptomics and Single-nucleus RNA Sequencing Reveals the Potential Therapeutic Strategies for Uterine Leiomyoma", International Journal of Biological Sciences, 19(8), s. 2515–2530.doi: 10.7150/IJBS.83510.