
Evolutionär genetik
Servicefördelar
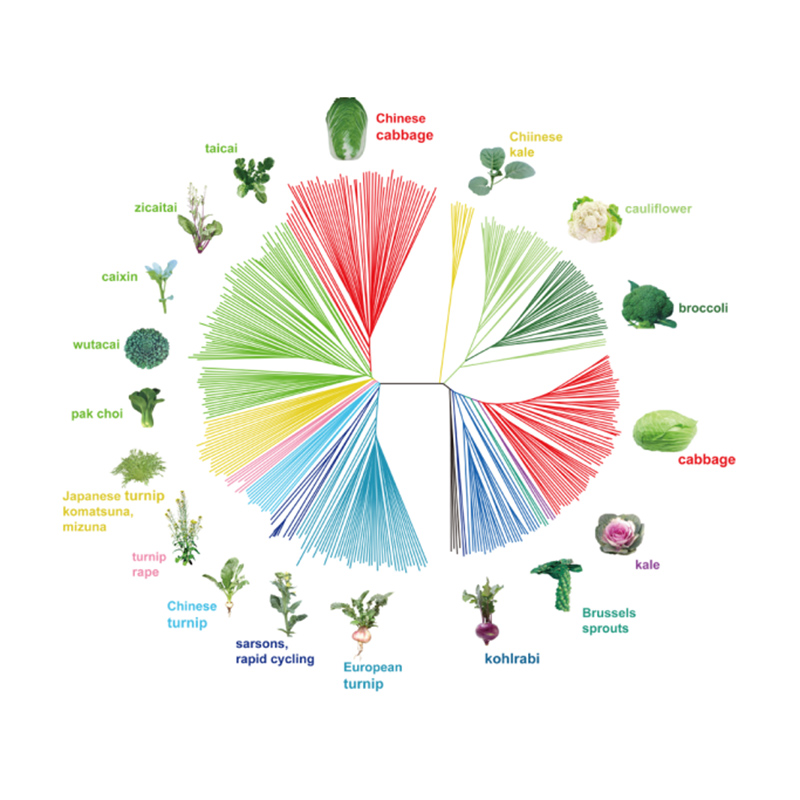
Takagi et al.,Växtjournalen, 2013
● Uppskattning av artens divergenstid och hastighet baserat på variationer på nukleotid- och aminosyranivå
● Avslöjande av mer tillförlitlig fylogenetisk relation mellan arter med minimerad påverkan av konvergent evolution och parallell evolution
● Konstruera kopplingar mellan genetiska förändringar och fenotyper för att avslöja egenskapsrelaterade gener
● Uppskattning av genetisk mångfald, vilket återspeglar arternas evolutionära potential
● Snabbare handläggningstid
● Omfattande erfarenhet: BMK har samlat massiv erfarenhet av befolknings- och evolutionära relaterade projekt i över 12 år, som täcker hundratals arter etc. och bidragit i över 80 högnivåprojekt publicerade i Nature Communications, Molecular Plants, Plant Biotechnology Journal, etc.
Servicespecifikationer
Material:
Normalt rekommenderas minst tre delpopulationer (t.ex. underarter eller stammar).Varje delpopulation bör innehålla inte mindre än 10 individer (växter >15, kan reduceras för sällsynta arter).
Sekvenseringsstrategi:
* WGS kan användas för arter med högkvalitativt referensgenom, medan SLAF-Seq är tillämpbart på arter antingen med eller utan referensgenom, eller referensgenom av dålig kvalitet.
| Tillämplig på genomstorlek | WGS | SLAF-taggar (×10 000) |
| ≤ 500 Mb | 10×/individ | WGS rekommenderas mer |
| 500 Mb - 1 Gb | 10 | |
| 1 Gb - 2 Gb | 20 | |
| ≥2 Gb | 30 |
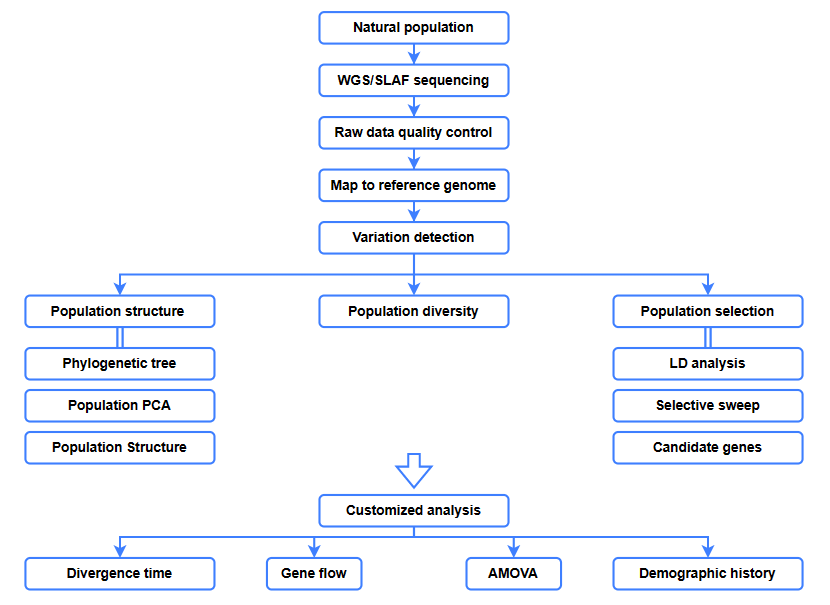
Bioinformatikanalyser
● Evolutionsanalys
● Selektivt svep
● Genflöde
● Demografisk historia
● Divergenstid
Exempel på krav och leverans
Exempelkrav:
| Arter | Vävnad | WGS-NGS | SLAF |
| Djur
| Visceral vävnad |
0,5~1g
|
0,5 g
|
| Muskelvävnad | |||
| Däggdjursblod | 1,5 ml
| 1,5 ml
| |
| Fjäderfä/fiskblod | |||
| Växt
| Färskt blad | 1~2g | 0,5~1g |
| Kronblad/Stjälk | |||
| Rot/frö | |||
| Celler | Odlad cell |
| gDNA | Koncentration | Belopp (ug) | OD260/OD280 |
| SLAF | ≥35 | ≥1,6 | 1,6-2,5 |
| WGS-NGS | ≥1 | ≥0,1 | - |
Service Arbetsflöde

Experimentdesign

Provleverans

Byggande av bibliotek

Sekvensering

Dataanalys

Service efter försäljning
*Demoresultat som visas här är alla från genom publicerade med BMKGENE
1. Evolutionsanalys innehåller konstruktion av fylogenetiskt träd, populationsstruktur och PCA baserat på genetiska variationer.
Fylogenetiska träd representerar taxonomiska och evolutionära relationer mellan arter med gemensam förfader.
PCA syftar till att visualisera närhet mellan delpopulationer.
Populationsstruktur visar närvaron av genetiskt distinkt subpopulation i termer av allelfrekvenser.
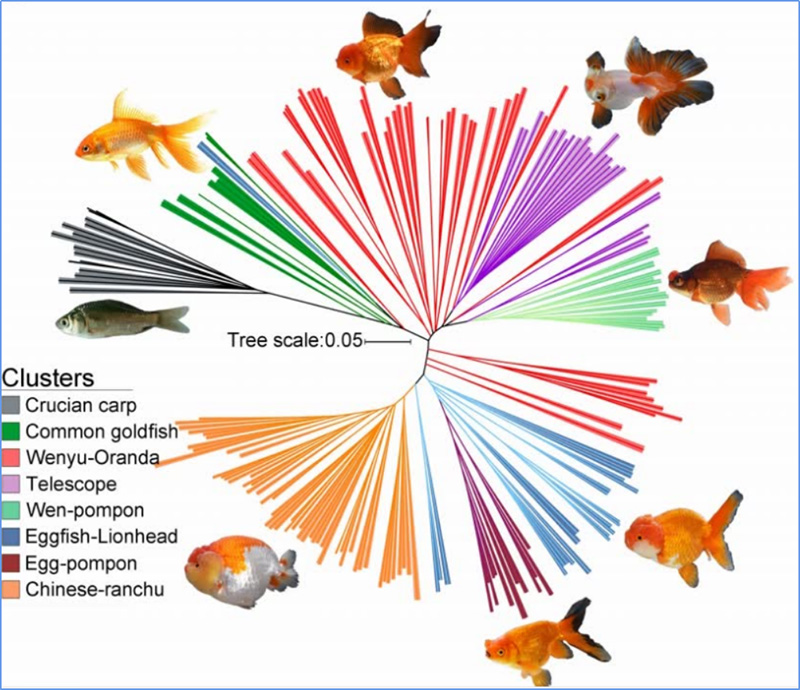
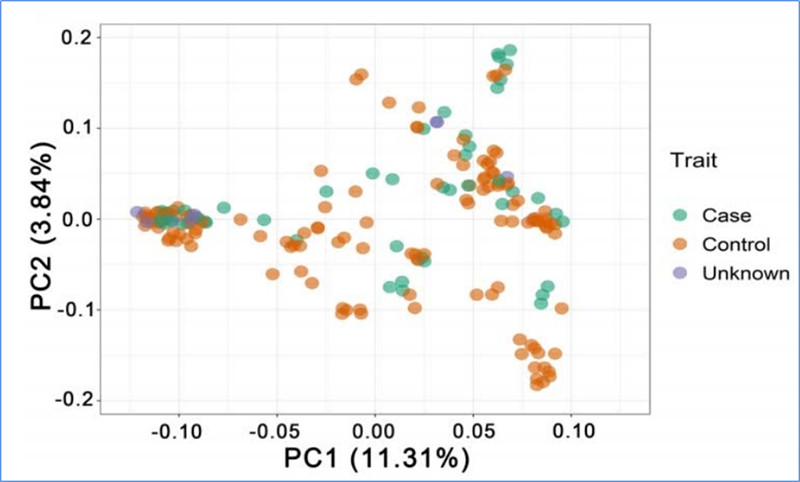
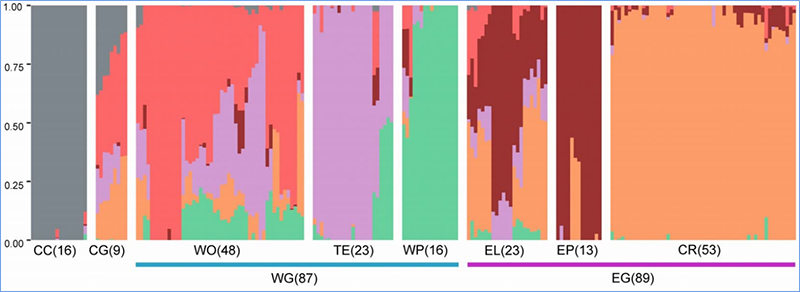
Chen, et.al.,PNAS, 2020
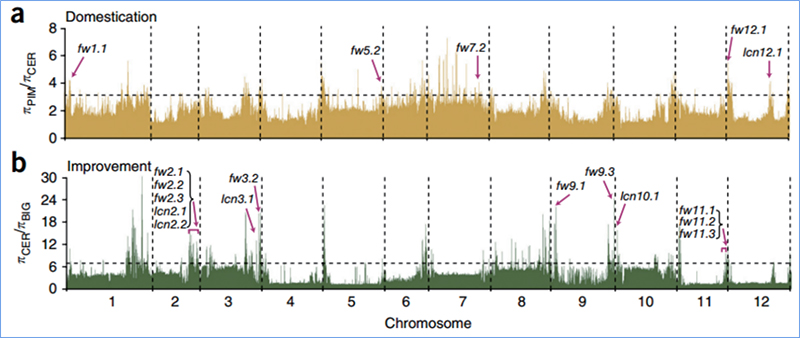
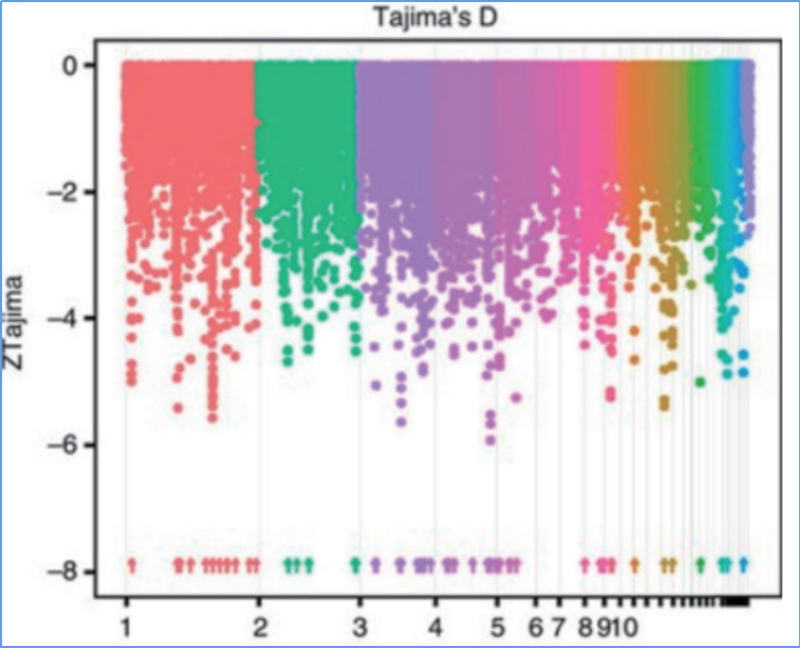
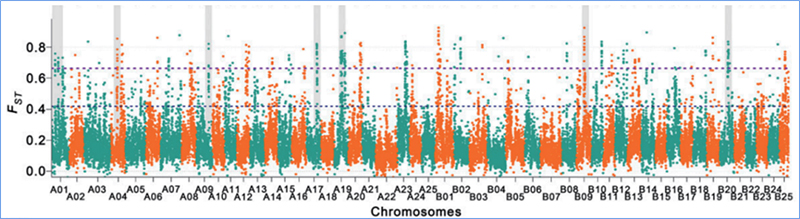
2.Selektivt svep
Selektivt svep hänvisar till en process genom vilken en fördelaktig plats väljs och frekvenser för länkade neutrala platser ökas och de för olänkade webbplatser minskas, vilket resulterar i minskning av regionala.
Genomomfattande detektion på selektiva svepregioner bearbetas genom att beräkna populationsgenetiskt index (π,Fst, Tajimas D) för alla SNP: er inom ett glidande fönster (100 Kb) vid ett visst steg (10 Kb).
Nukleotiddiversitet(π)
Tajimas D
Fixationsindex (Fst)
Wu, et.al.,Molekylär växt, 2018
3.Genflöde
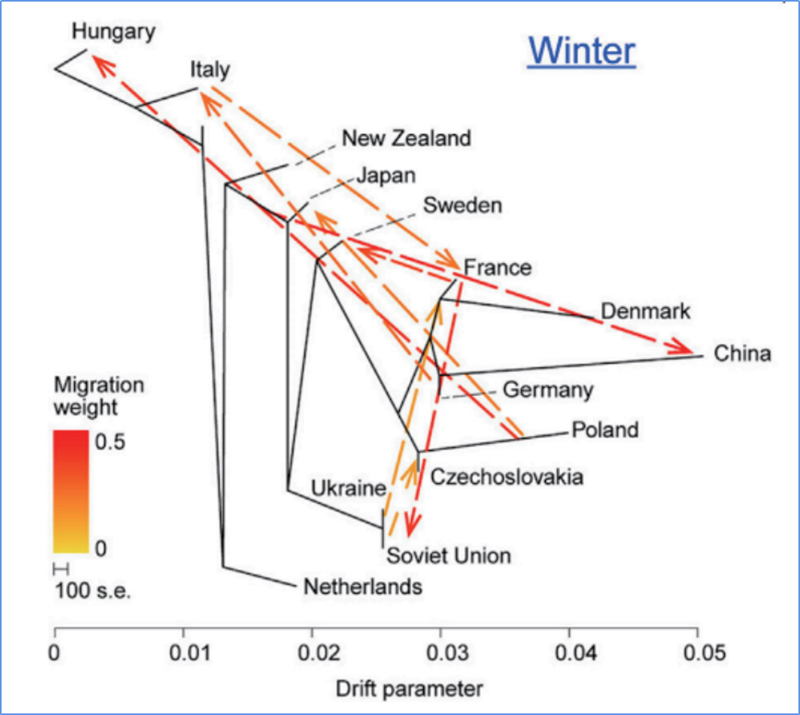
Wu, et.al.,Molekylär växt, 2018
4.Demografisk historia
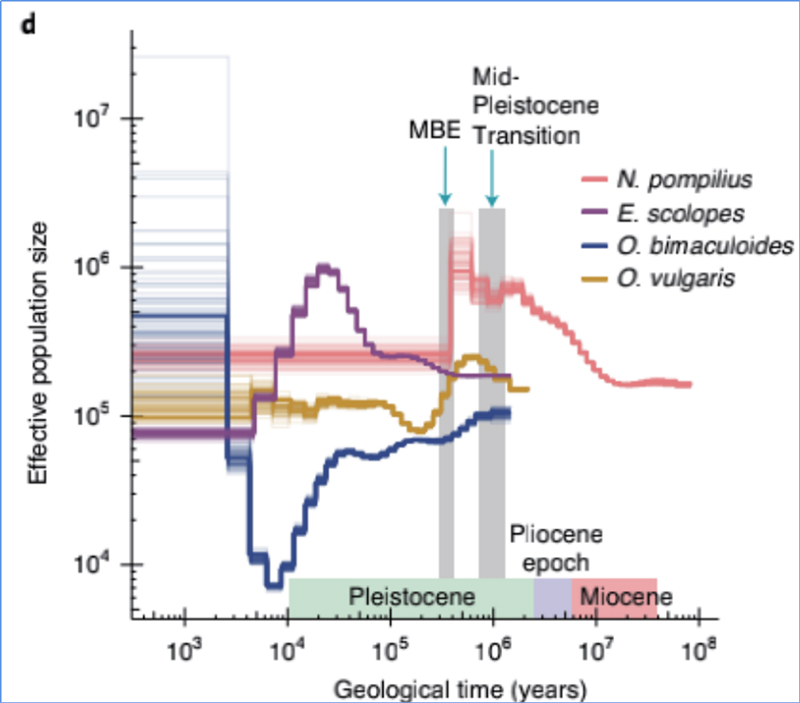
Zhang, et.al.,Naturekologi och evolution, 2021
5.Divergenstid
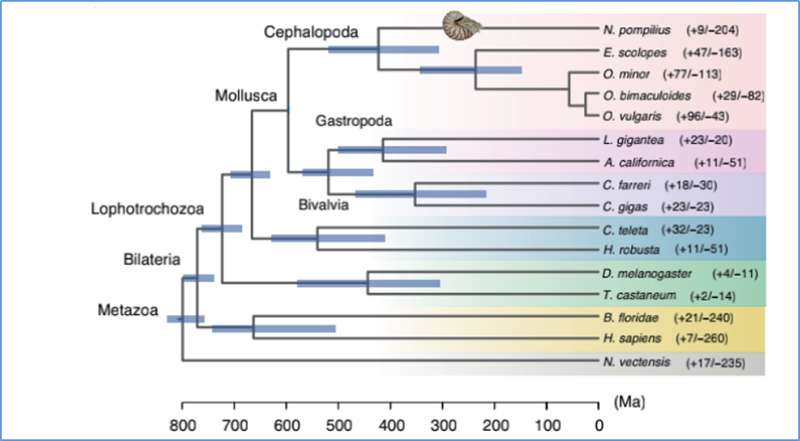
Zhang, et.al.,Naturekologi och evolution, 2021
BMK Fall
En genomisk variationskarta ger insikter i den genetiska grunden för valet av vårkinesisk kål (Brassica rapa ssp. Pekinensis)
Publicerad: Molekylär växt, 2018
Sekvenseringsstrategi:
Återsekvensering: sekvenseringsdjup: 10×
Nyckelresultat
I denna studie bearbetades 194 kinakålar för omsekvensering med ett genomsnittligt djup på 10×, vilket gav 1 208 499 SNP och 416 070 InDels.Filogenetisk analys på dessa 194 linjer visade att dessa linjer kan delas in i tre ekotyper, vår, sommar och höst.Dessutom indikerade befolkningsstruktur och PCA-analys att vårkinakål härstammade från en höstkål i Shandong, Kina.Dessa introducerades sedan till Korea och Japan, korsades med lokala linjer och några sent bultade varianter av dem introducerades tillbaka till Kina och blev till slut vårkineskål.
Genomomfattande skanning på vårkineskål och höstkål vid selektion avslöjade 23 genomiska loci som har genomgått ett starkt urval, varav två överlappades med bultningstidskontrollerande region baserad på QTL-kartläggning.Dessa två regioner visade sig innehålla nyckelgener som reglerar blomningen, BrVIN3.1 och BrFLC1.Dessa två gener bekräftades vidare vara involverade i bultningstiden genom transkriptomstudie och transgena experiment.
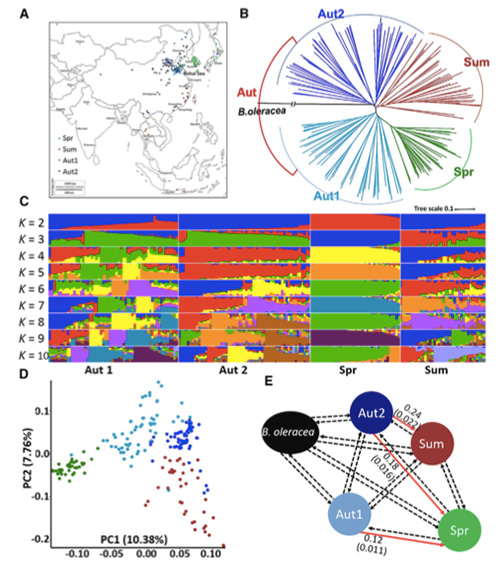 Befolkningsstrukturanalys på kinakål | 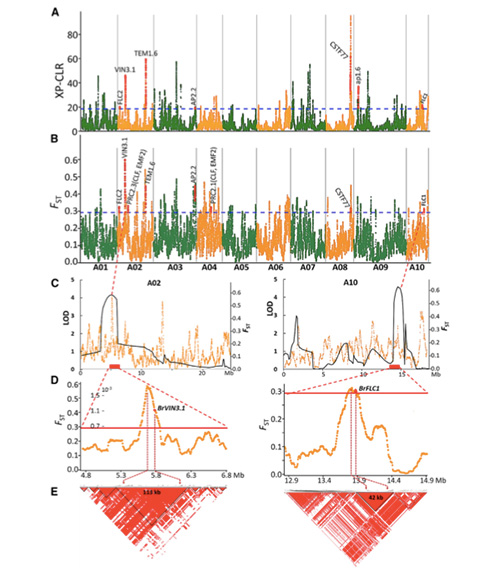 Genetisk information om urval av kinesisk kål |
Tongbing, et al."En genomisk variationskarta ger insikter i den genetiska grunden för vårens kinesiska kål (Brassica rapa ssp.pekinensis) urval."Molekylära växter,11(2018):1360-1376.















