Svampgenom
Servicefördelar
● Flera sekvenseringsstrategier tillgängliga för olika forskningsmål
● Mycket erfaren i svampgenomsättning med över 10 000 pene-kompletta genom sammansatta.
● Professionellt tekniskt supportteam efter försäljning som uppfyller mer specifika forskningsbehov.
Servicespecifikationer
| Service | Sekvenseringsstrategi | Kvalitet garanterad | Beräknad handläggningstid |
| Svampfinkarta | Illumina 50X+Nanopore 100X | Contig N50≥2 Mb | 35 arbetsdagar |
| PacBio HiFi 30X | |||
| Svamppene-komplett karta | Illumina 50X+Nanopore 100X(Pacbio HiFi 30X)+Hi-C 100X | Kromosomförankringsförhållande >90 % | 45 arbetsdagar |
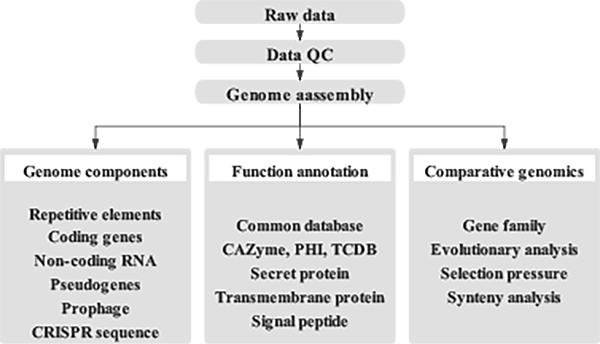
Bioinformatikanalyser
● Kvalitetskontroll av rådata
● Genomsammansättning
● Genomkomponentanalys
● Genfunktionsanteckning
● Jämförande genomisk analys
Exempel på krav och leverans
Exempelkrav:
FörDNA-extrakt:
| Provtyp | Belopp | Koncentration | Renhet |
| DNA-extrakt | > 1,2 μg | > 20 ng/μl | OD260/280= 1,6-2,5 |
För vävnadsprover:
| Provtyp | Rekommenderad provbehandling | Provförvaring och leverans |
| Encellig svamp | Titta på jäst under mikroskop och samla dem i sin exponentiella fas Överför kulturen (innehållande ca 3-4.5e9 celler) till en 1,5 eller 2 ml eppendorf.(Håll på is) Centrifugera röret i 1 min vid 14000 g för att samla upp bakterier och ta bort supernatanten försiktigt Förslut röret och frys bakterierna i flytande kväve i minst 1-3 timmar.Förvara röret i -80 ℃ kyl. | Frys in proverna i flytande kväve i 3-4 timmar och förvara i flytande kväve eller -80 grader till långtidsreservation.Provfrakt med torris krävs. |
| Makrosvamp | Vävnad i aktivt växande fas rekommenderas. Skölj vävnaden med endotoxinfritt vatten, sedan 70 % etonal. Spara provet i kryorör. |
Service Arbetsflöde

Provleverans

Byggande av bibliotek

Sekvensering

Dataanalys

Service efter försäljning
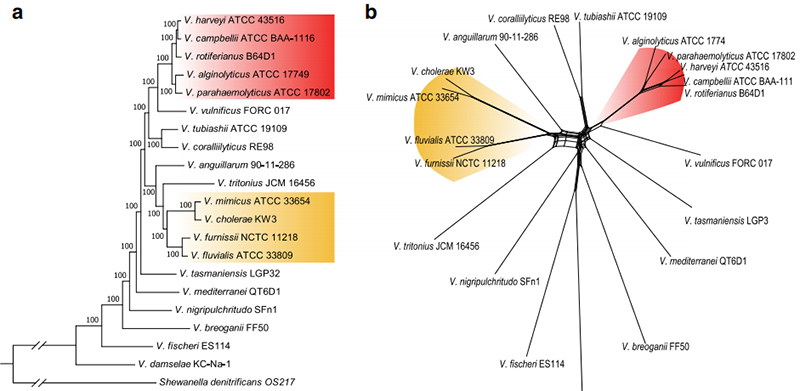
1. Cirkosdiagram över svampgenomiska komponenter
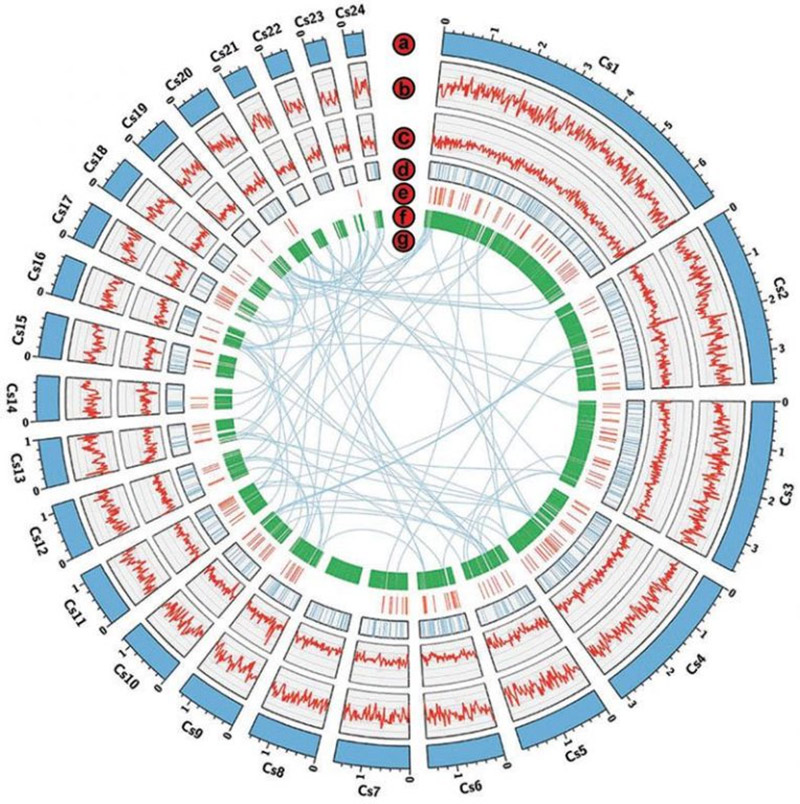
2. Jämförande genomikanalys: Fylogenetiskt träd