Människans hela exomsekvensering
Servicefördelar
● Riktad proteinkodande region: genom att fånga och sekvensera proteinkodande region, används hWES för att avslöja varianter relaterade till proteinstruktur;
● Hög noggrannhet: med högt sekvenseringsdjup underlättar hWES detektering av vanliga varianter och sällsynta varianter med frekvenser lägre än 1 %;
● Kostnadseffektivt: hWES ger cirka 85 % av mänskliga sjukdomsmutationer från 1 % av mänskligt genom;
● Fem strikta QC-procedurer som täcker hela processen med Q30>85% garanterad.
Exempel på specifikationer
| Plattform
| Bibliotek
| Exon Capture Strategy
| Rekommendera sekvenseringsstrategi
|
|
Illumina NovaSeq-plattformen
| PE150 | Agilent SureSelect Human All Exon V6 IDT xGen Exome Hyb Panel V2 | 5 Gb 10 Gb |
Exempel på krav
| Provtyp
| Belopp(Qubit®)
| Volym
| Koncentration
| Renhet (NanoDrop™) |
|
Genomiskt DNA
| ≥ 300 ng | ≥ 15 μL | ≥ 20 ng/μL | OD260/280=1,8-2,0 ingen nedbrytning, ingen kontaminering
|
Rekommenderat sekvenseringsdjup
För mendelska sjukdomar/sällsynta sjukdomar: effektivt sekvenseringsdjup över 50×
För tumörprover: effektivt sekvenseringsdjup över 100×
Bioinformatik
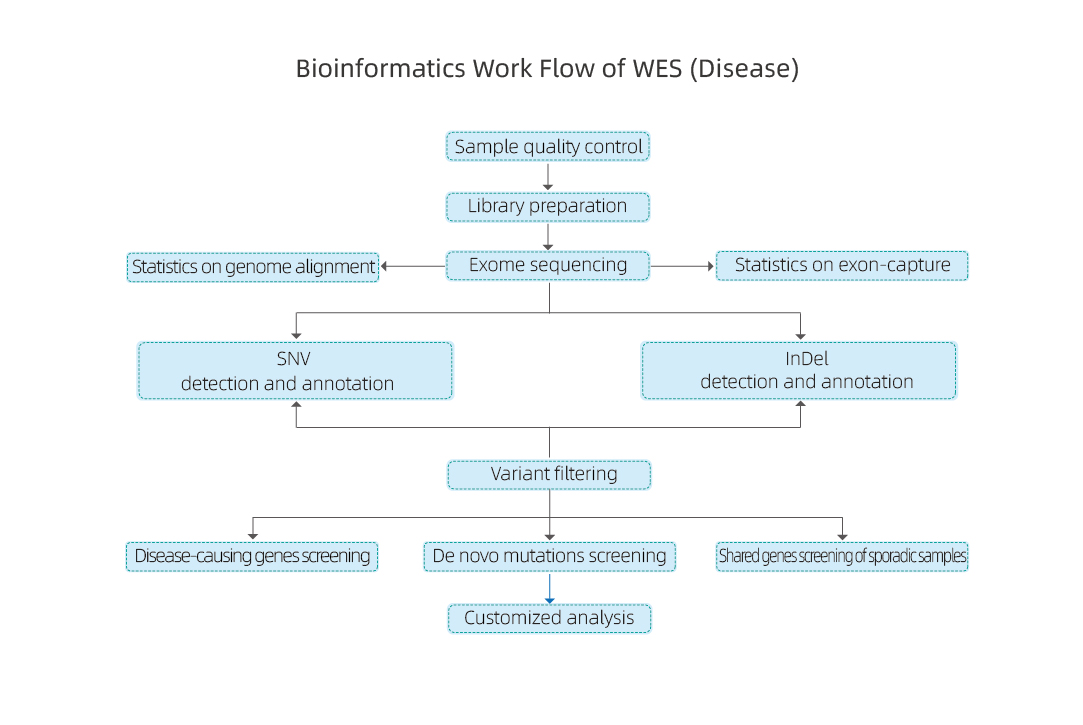
Service arbetsflöde
Provleverans

DNA-extraktion

Byggande av bibliotek

Sekvensering

Dataanalys
Dataleverans

Service efter försäljning
1. Inriktningsstatistik
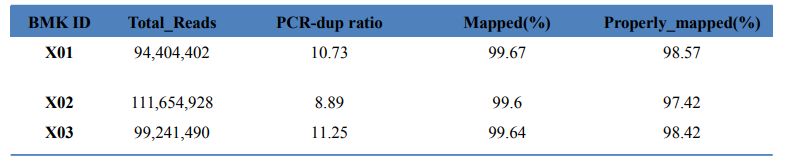
Tabell 1 Statistik över kartresultat
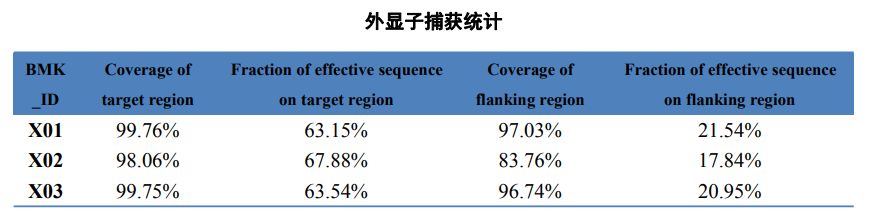
Tabell 2 Statistik över exomefångning
2. Variationsdetektering
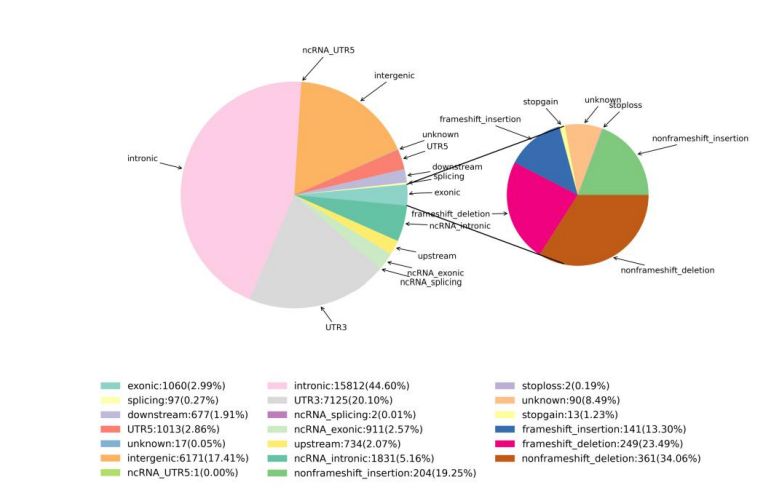
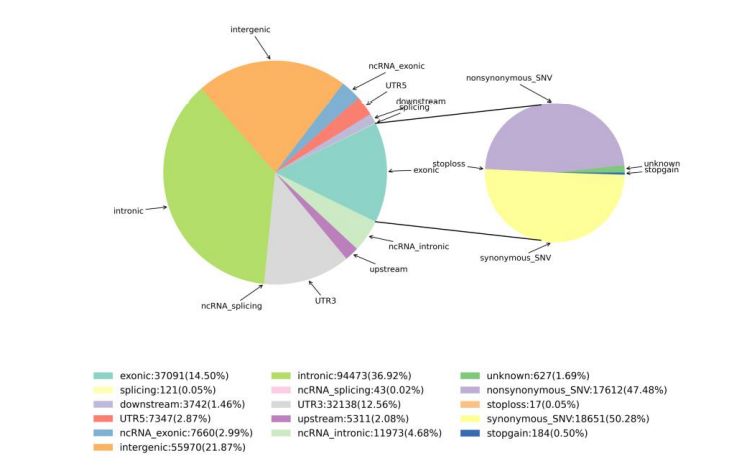
Figur 1 Statistik över SNV och InDel
3. Avancerad analys
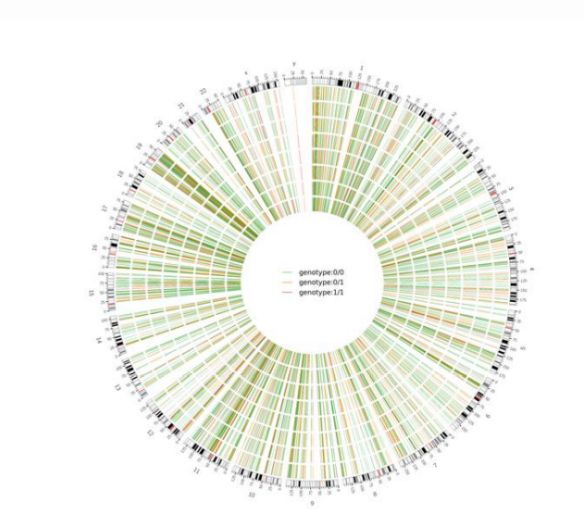
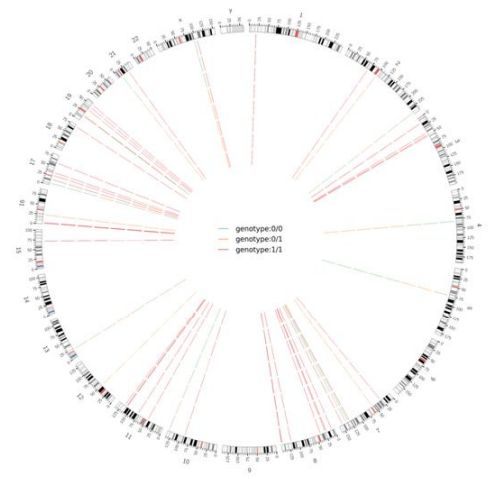
Figur 2 Circos plot av genomomfattande skadliga SNV och InDel
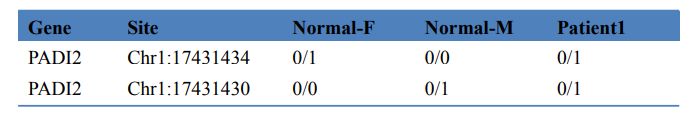
Tabell 3 Screening av sjukdomsalstrande gener