Sekvensering av hela genomet av växter/djur
1. Servicefördelar
Lång erfarenhet av genomsekvensering för över 1000 arter.
Över 800 publicerade fall med en ackumulerad effektfaktor på över 4000.
Omfattande bioinformatikanalys om variationsupprop och funktionsanalys.
2. Servicespecifikationer
| Plattform | Bibliotek | Rekommenderat följddjup | |
| Illumina | PE 150 | För SNP, InDel-anrop ≥ 10x För SV, CNY-samtal ≥ 30x
| |
| Nanopore
| 8 kb | För SV, CNY-samtal ≥ 20x | |
| Pacbio | CCS | 15 kb | För SNP, InDel, SV, CNY-samtal ≥ 10x |
3. Exempel på krav
| Plattform | Konc.(ng/μL)
| Belopp (ng)
| Renhet
| Agaros gel
| ||
| OD260/280 | OD260/230 | 1. Rensa huvudband med ingen eller begränsadnedbrytning observerad på gel. 2. Ingen eller begränsad RNA- eller proteinkontamination
| ||||
| Illumina | ≥1 | ≥30
| - | - | ||
| Nanopore
| ≥30 | Beror på datautbytet 10 μg/cell | 1,7-2,2 | ≥1,5 | ||
| Pacbio | CCS | ≥50 | 1,7-2,2 | 1,8-2,5 | ||
4. Bioinformationsanalys
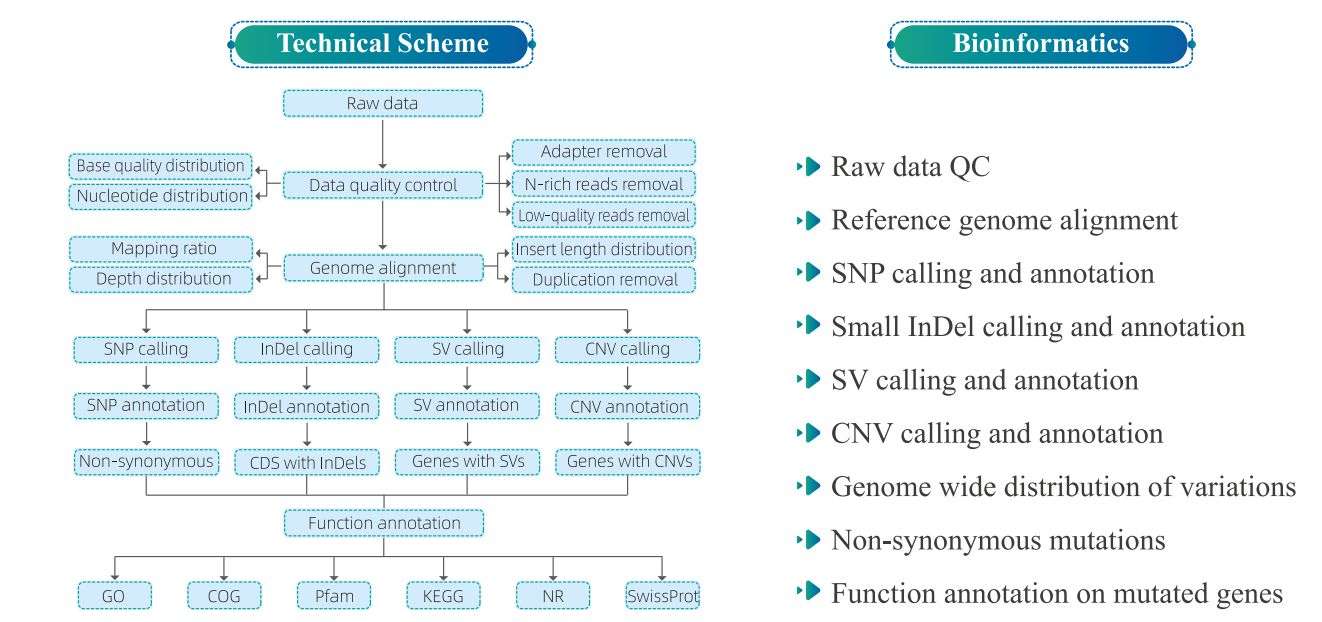
5. Service Arbetsflöde

Provleverans

DNA-extraktion

Byggande av bibliotek

Sekvensering

Dataanalys
Dataleverans
1) Statistik över genomkartläggning
Tabell 1 Statistik över kartläggningsresultat
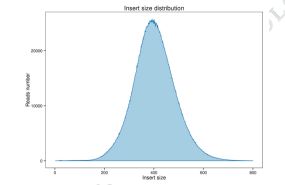
Figur 1 Fördelning av skärstorlek och avläsning av täckning.
2) Variationsdetektering
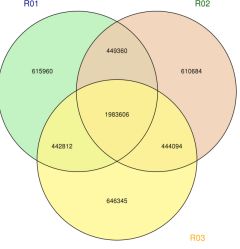
Figur 2 Statistik och anteckning av SNP/INDEL/SV bland prover
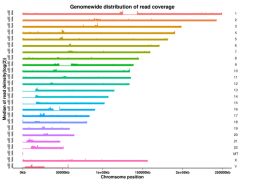
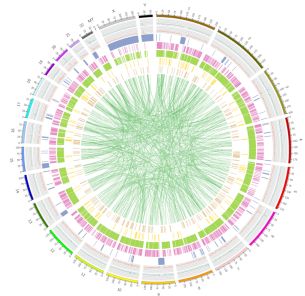
Figur 3 Genom-omfattande fördelning av vatiationer
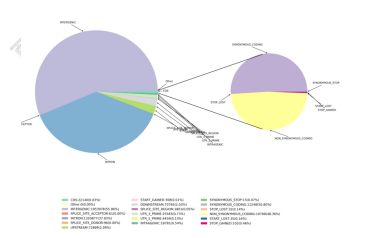
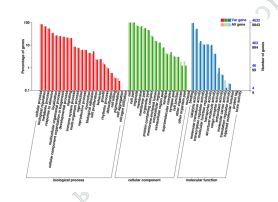
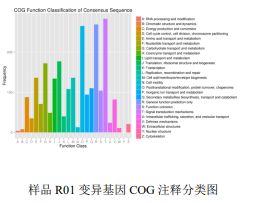
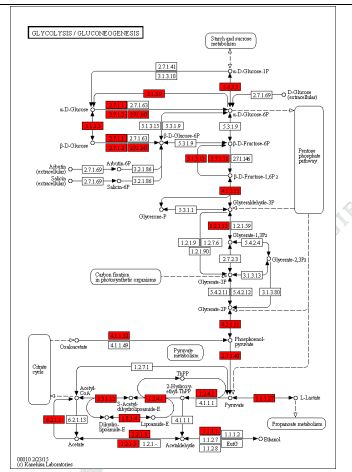
3) Funktionell anteckning av variationer
| 2019 | Naturkommunikation | Helgenomsekvensering avslöjar Brassica napus ursprung och genetiska loci som är involverade i dess förbättring |
| 2020 | PNAS | Guldfiskarnas evolutionära ursprung och domesticeringshistoria (Carassius auratus) |
| 2021 | Plant Biotechnology Journal | Referensgenom för de två odlade jutearterna |
| 2021 | Plant Biotechnology Journal | Genomiska signaturer av vegetabiliskt och oljefrö allopolyploid Brassicajuncea och genetiska loci som kontrollerar ackumuleringen av glukosinolater |
| 2019 | Molekylär växt | Helgenomsekvensering av en världsomspännande samling av rapsaccessioner avslöjar genetisk grund för deras ekotypdivergens |
| 2022 | Trädgårdsbruksforskning | Genomomfattande associationsanalys ger molekylära insikter i den naturliga variationen av vattenmelonfröstorlek |
| 2021 | Journal of Experimental Botany | Genomomfattande associationsstudie identifierar varianter av GhSAD1 som ger köldtolerans i bomull |
| 2021 | Journal of Experimental Botany | Genomomfattande associationsstudie och transkriptomjämförelse avslöjar nya QTL och kandidatgener som kontrollerar kronbladsstorleken i raps |