10x การถอดเสียงเชิงพื้นที่ของ Genomics Visium
คุณสมบัติ
● ความละเอียด: 100 µM
● เส้นผ่านศูนย์กลางสปอต: 55 µM
● จำนวนสปอต: 4992
● พื้นที่จับภาพ: 6.5 x 6.5 มม
● จุดบาร์โค้ดแต่ละจุดจะเต็มไปด้วยไพรเมอร์ที่ประกอบด้วย 4 ส่วน:
- ส่วนท้ายโพลี (dT) สำหรับการเตรียม mRNA และการสังเคราะห์ cDNA
- Unique Molecular Identifier (UMI) เพื่อแก้ไขอคติในการขยาย
- บาร์โค้ดเชิงพื้นที่
- ลำดับการเชื่อมโยงของไพรเมอร์ลำดับการอ่านบางส่วน 1
● การย้อมสี H&E ของส่วนต่างๆ
ข้อดี
●บริการครบวงจร: บูรณาการประสบการณ์และขั้นตอนตามทักษะทั้งหมด รวมถึงการตัดด้วยความเย็นจัด การย้อมสี การปรับเนื้อเยื่อให้เหมาะสม บาร์โค้ดเชิงพื้นที่ การเตรียมห้องสมุด การจัดลำดับ และชีวสารสนเทศศาสตร์
● ทีมงานด้านเทคนิคที่มีทักษะสูง: ด้วยประสบการณ์เกี่ยวกับเนื้อเยื่อมากกว่า 250 ชนิดและมากกว่า 100 สายพันธุ์ รวมถึงมนุษย์ หนู สัตว์เลี้ยงลูกด้วยนม ปลา และพืช
●อัพเดทเรียลไทม์ตลอดทั้งโครงการ: พร้อมควบคุมความคืบหน้าการทดลองเต็มรูปแบบ
●ชีวสารสนเทศศาสตร์มาตรฐานที่ครอบคลุม:แพ็คเกจประกอบด้วยการวิเคราะห์ 29 รายการและตัวเลขคุณภาพสูงมากกว่า 100 รายการ
●การวิเคราะห์ข้อมูลและการแสดงภาพแบบกำหนดเอง: มีให้สำหรับการร้องขอการวิจัยที่แตกต่างกัน
●การวิเคราะห์ข้อต่อทางเลือกพร้อมการจัดลำดับ mRNA เซลล์เดียว
ข้อมูลจำเพาะ
| ข้อกำหนดตัวอย่าง | ห้องสมุด | กลยุทธ์การจัดลำดับ | ข้อมูลที่แนะนำ | ควบคุมคุณภาพ |
| ตัวอย่างไครโอที่ฝังใน OCT, ตัวอย่าง FFPE (เส้นผ่านศูนย์กลางที่เหมาะสมที่สุด: ประมาณ 6x6x6 มม.3) 3 บล็อกต่อตัวอย่าง | ไลบรารี cDNA Visium 10X | อิลลูมิน่า พีอี150 | อ่าน PE 50,000 ต่อจุด ( 60กิกะบิต ) | ริน>7 |
สำหรับรายละเอียดเพิ่มเติมเกี่ยวกับคำแนะนำในการจัดเตรียมตัวอย่างและขั้นตอนการบริการ โปรดอย่าลังเลที่จะพูดคุยกับ กผู้เชี่ยวชาญของ BMKGENE
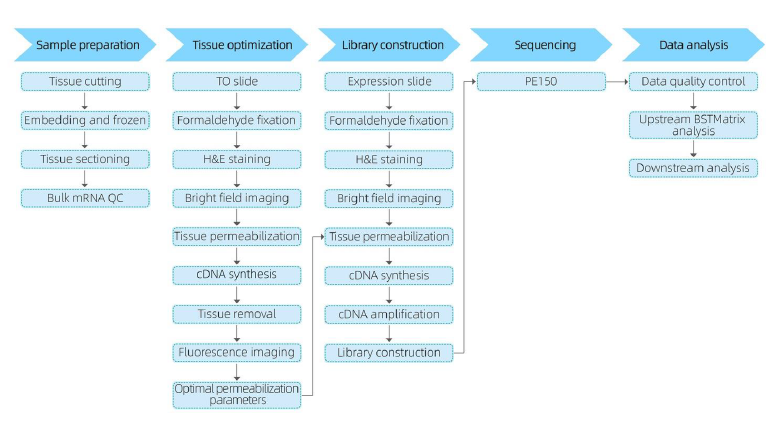
ขั้นตอนการบริการ
ในขั้นตอนการเตรียมตัวอย่าง จะมีการดำเนินการทดลองสกัด RNA จำนวนมากครั้งแรกเพื่อให้แน่ใจว่าจะได้ RNA คุณภาพสูงในขั้นตอนการปรับเนื้อเยื่อให้เหมาะสม ส่วนต่างๆ จะถูกย้อมสีและมองเห็นได้ และเงื่อนไขการซึมผ่านของการปล่อย mRNA จากเนื้อเยื่อได้รับการปรับปรุงให้เหมาะสมจากนั้นจะใช้โปรโตคอลที่ได้รับการปรับปรุงให้เหมาะสมในระหว่างการก่อสร้างห้องสมุด ตามด้วยลำดับและการวิเคราะห์ข้อมูล
ขั้นตอนการบริการที่สมบูรณ์เกี่ยวข้องกับการอัพเดตแบบเรียลไทม์และการยืนยันจากลูกค้าเพื่อรักษาวงจรตอบรับที่ตอบสนอง เพื่อให้มั่นใจว่าการดำเนินโครงการเป็นไปอย่างราบรื่น
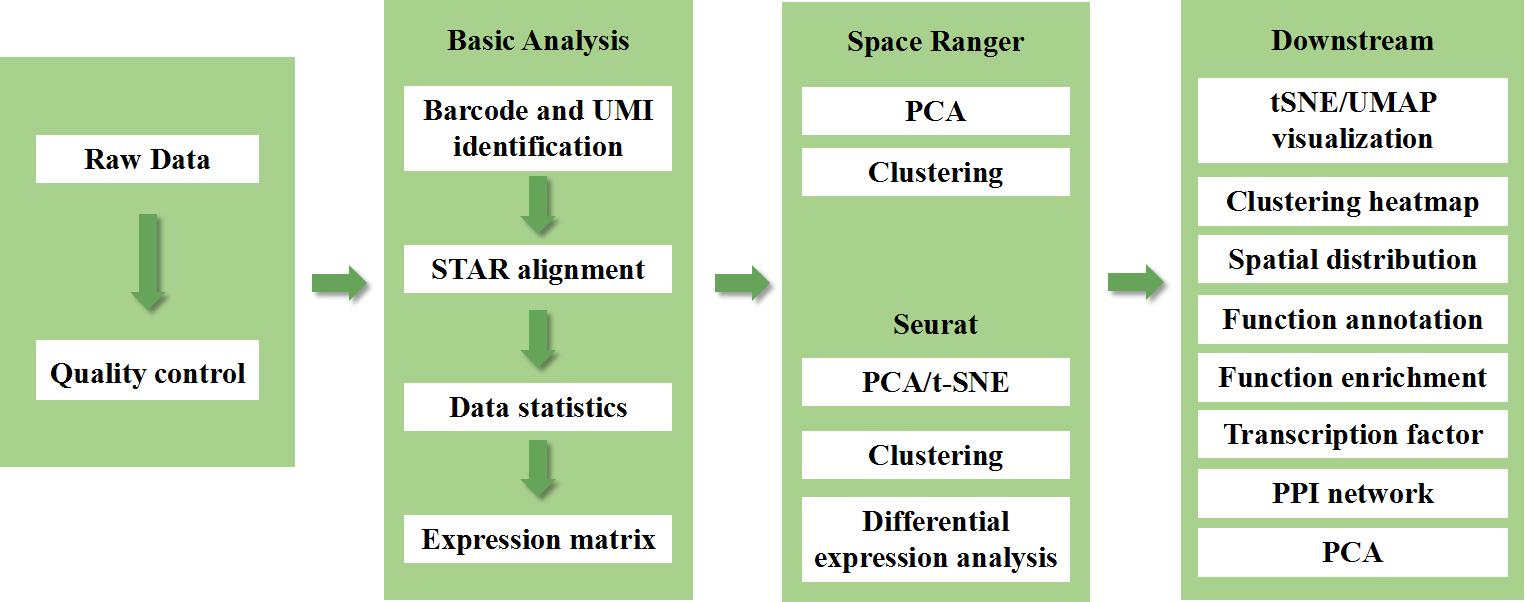
รวมถึงการวิเคราะห์ต่อไปนี้:
การควบคุมคุณภาพข้อมูล:
o การส่งออกข้อมูลและการกระจายคะแนนคุณภาพ
o การตรวจจับยีนต่อจุด
o การครอบคลุมของเนื้อเยื่อ
การวิเคราะห์ตัวอย่างภายใน:
o ความสมบูรณ์ของยีน
o การจัดกลุ่มเฉพาะจุด รวมถึงการวิเคราะห์มิติที่ลดลง
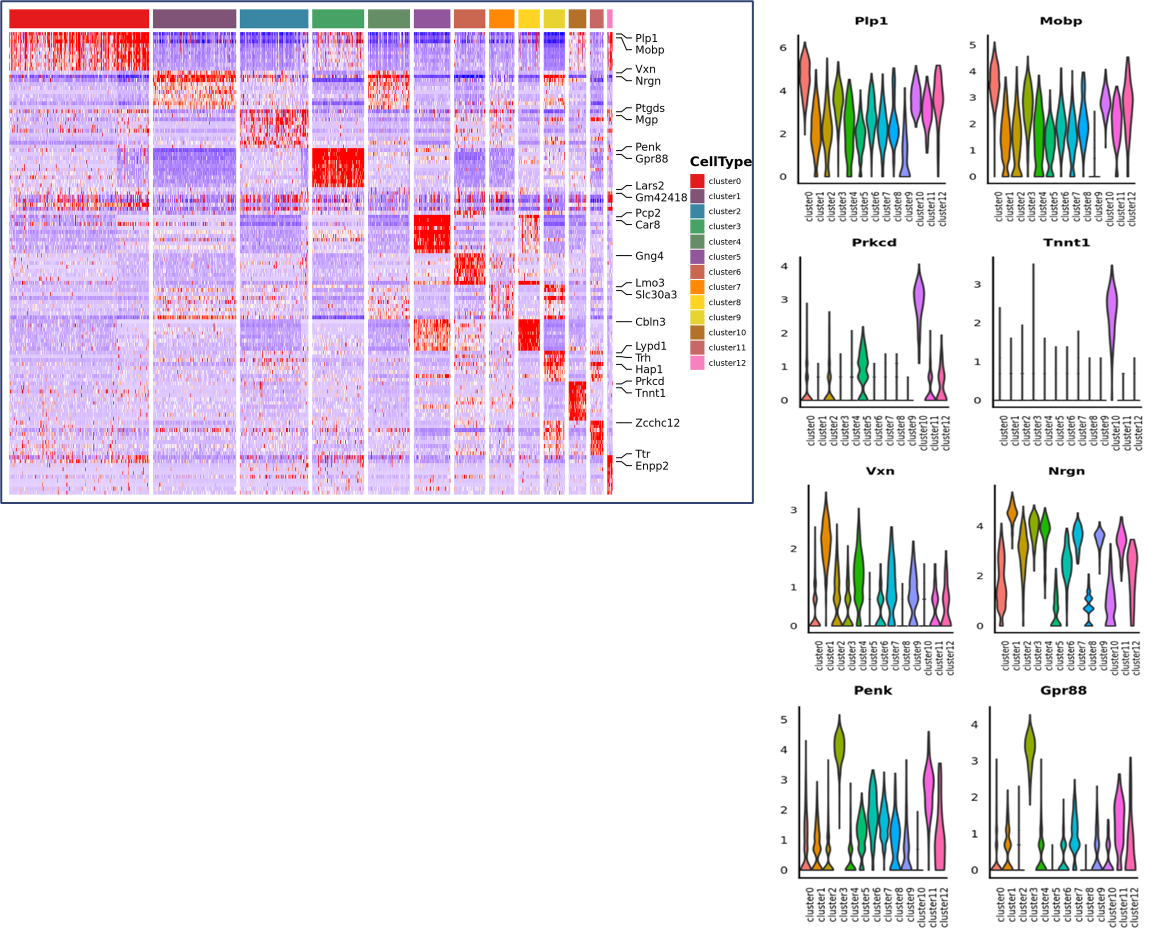
การวิเคราะห์การแสดงออกที่แตกต่างกันระหว่างกลุ่ม: การจำแนกยีนมาร์กเกอร์
คำอธิบายประกอบการทำงานและการเสริมคุณค่าของยีนมาร์กเกอร์
การวิเคราะห์ระหว่างกลุ่ม
o การรวมจุดใหม่จากทั้งสองตัวอย่าง (เช่น ที่เป็นโรคและกลุ่มควบคุม) และรวมกลุ่มใหม่
o การจำแนกยีนมาร์กเกอร์สำหรับแต่ละคลัสเตอร์
คำอธิบายประกอบการทำงานและการเสริมคุณค่าของยีนมาร์กเกอร์
o การแสดงออกที่แตกต่างกันของกลุ่มเดียวกันระหว่างกลุ่ม
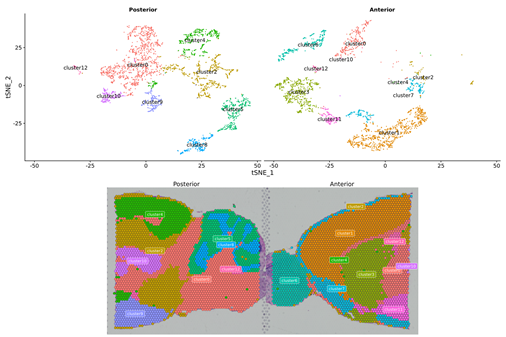
การวิเคราะห์ตัวอย่างภายใน
การจัดกลุ่มเฉพาะจุด
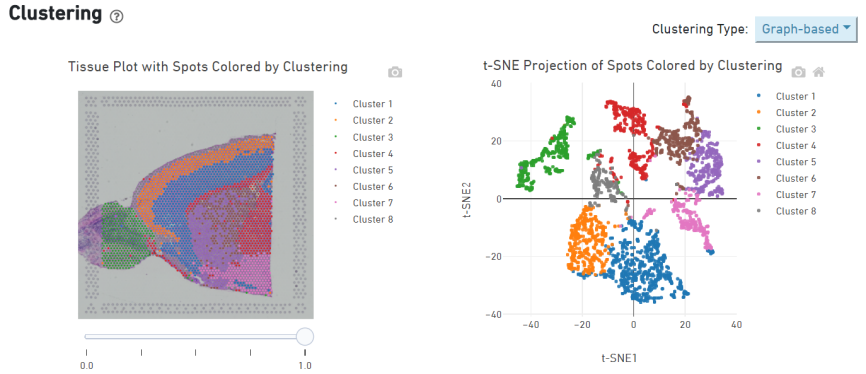
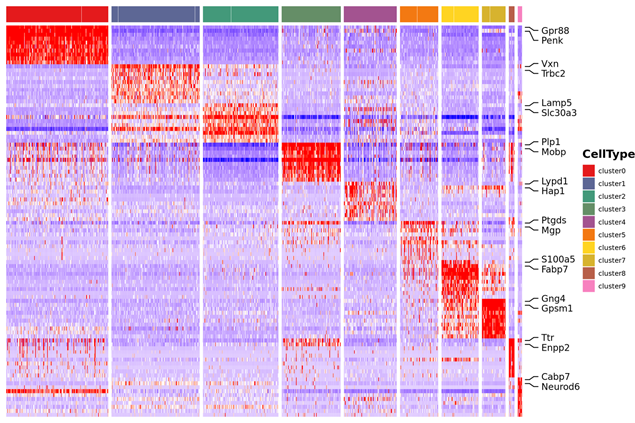
การจำแนกยีนของเครื่องหมายและการกระจายเชิงพื้นที่
การวิเคราะห์ระหว่างกลุ่ม
การรวมข้อมูลจากทั้งสองกลุ่มและการจัดกลุ่มใหม่
ยีนเครื่องหมายของกลุ่มใหม่
สำรวจความก้าวหน้าที่อำนวยความสะดวกโดยบริการถอดเสียงเชิงพื้นที่ของ BMKGene โดย 10X Visium ในสิ่งพิมพ์เด่นเหล่านี้:
เฉิน ดี. และคณะ(2023) 'mthl1 ซึ่งเป็นสิ่งที่คล้ายคลึงกันของดรอสโซฟิล่าของการยึดเกาะของสัตว์เลี้ยงลูกด้วยนม GPCR เกี่ยวข้องกับปฏิกิริยาต่อต้านเซลล์มะเร็งที่ฉีดเข้าไปในแมลงวัน', Proceedings of the National Academy of Sciences of the United States of America, 120(30), p.e2303462120.ดอย: /10.1073/pnas.2303462120
เฉิน วาย และคณะ(2023) 'STEEL ช่วยให้สามารถแยกแยะข้อมูลการถอดรหัส spatiotemporal ที่มีความละเอียดสูง', Briefings in Bioinformatics, 24(2), pp. 1–10ดอย: 10.1093/BIB/BBAD068.
หลิวซีและคณะ(2022) 'แผนที่ spatiotemporal ของการสร้างอวัยวะในการพัฒนาดอกกล้วยไม้', การวิจัยกรดนิวคลีอิก, 50(17), หน้า 9724–9737ดอย: 10.1093/NAR/GKAC773.
วังเจและคณะ(2023) 'การบูรณาการการถอดเสียงเชิงพื้นที่และการจัดลำดับอาร์เอ็นเอของนิวเคลียสเดี่ยวเผยให้เห็นกลยุทธ์การรักษาที่มีศักยภาพสำหรับมะเร็งเนื้องอกในมดลูก', วารสารวิทยาศาสตร์ชีวภาพนานาชาติ, 19(8), หน้า 2515–2530ดอย: 10.7150/IJBS.83510.