
จีโนมิกส์เปรียบเทียบ
ข้อดีของการบริการ
● แพ็คเกจการวิเคราะห์ที่ครอบคลุม ประกอบด้วยการวิเคราะห์ที่จำเป็นที่สุดแปดรายการ
● ความน่าเชื่อถือสูงในการวิเคราะห์พร้อมการตีความผลลัพธ์ที่ละเอียดและเข้าใจง่าย
● ตัวเลขที่ออกแบบอย่างดีพร้อมเผยแพร่
● ทีมชีวสารสนเทศที่มีทักษะสูงตอบสนองความต้องการในการวิเคราะห์ส่วนบุคคลที่หลากหลาย
● ระยะเวลาดำเนินการสั้นลงพร้อมการวิเคราะห์ที่แม่นยำยิ่งขึ้น
● ประสบการณ์มากมายกับเคสที่ประสบความสำเร็จมากกว่า 90 เคส โดยมีปัจจัยผลกระทบที่เผยแพร่สะสมมากกว่า 900 เคส
ข้อมูลจำเพาะของบริการ
| ระยะเวลาดำเนินการโดยประมาณ | จำนวนชนิด | วิเคราะห์ |
| 30 วันทำการ | 6 - 12 | การรวมกลุ่มตระกูลยีน การขยายตัวและการหดตัวของตระกูลยีน การสร้างต้นไม้สายวิวัฒนาการ การประมาณเวลาความแตกต่าง (ต้องมีการสอบเทียบฟอสซิล) ระยะเวลาการใส่ LTR (สำหรับพืช) การทำสำเนาจีโนมทั้งหมด (สำหรับพืช) แรงกดดันแบบเลือกสรร การวิเคราะห์ซินเทนี |
การวิเคราะห์ทางชีวสารสนเทศ
● ตระกูลยีน
● สายวิวัฒนาการ
● เวลาที่แตกต่าง
● แรงกดดันแบบเลือก
● การวิเคราะห์แบบซินเทนี
ข้อกำหนดตัวอย่างและการจัดส่ง
ข้อกำหนดตัวอย่าง:
เนื้อเยื่อหรือ DNA สำหรับการจัดลำดับและการประกอบจีโนม
สำหรับทิชชู่
| สายพันธุ์ | เนื้อเยื่อ | สำรวจ | แพคไบโอ ซีซีเอส |
| สัตว์ | เนื้อเยื่ออวัยวะภายใน | 0.5 ~ 1ก | ≥ 3.5ก |
| เนื้อเยื่อกล้ามเนื้อ | |||
| ≥ 5.0ก | |||
| ≥ 5.0 มล | |||
| เลือดของสัตว์เลี้ยงลูกด้วยนม | |||
| ≥ 0.5 มล | |||
| เลือดสัตว์ปีก/ปลา | |||
| ปลูก | ใบสด | 1 ~ 2ก | ≥ 5.0ก |
| กลีบดอกไม้/ก้าน | 1 ~ 2ก | ≥ 10.0ก | |
| ราก/เมล็ด | 1 ~ 2ก | ≥ 20.0ก | |
| เซลล์ | เซลล์เพาะเลี้ยง | - | ≥ 1 x 108 |
ข้อมูล
ไฟล์ลำดับจีโนม (.fasta) และไฟล์คำอธิบายประกอบ (.gff3) ของสปีชีส์ที่เกี่ยวข้องอย่างใกล้ชิด
ขั้นตอนการทำงานบริการ

การออกแบบการทดลอง

การจัดส่งตัวอย่าง

การก่อสร้างห้องสมุด

การเรียงลำดับ

การวิเคราะห์ข้อมูล

บริการหลังการขาย
*ผลลัพธ์การสาธิตที่แสดงไว้ที่นี่ทั้งหมดมาจากจีโนมที่เผยแพร่โดย Biomarker Technologies
1.การประมาณเวลาแทรก LTR: รูปภาพแสดงการกระจายแบบไบโมดัลที่ไม่ซ้ำกันในระยะเวลาการแทรก LTR-RT ในจีโนมไรย์ของ Weining เมื่อเปรียบเทียบกับสายพันธุ์อื่นยอดเขาล่าสุดปรากฏขึ้นเมื่อประมาณ 0.5 ล้านปีก่อน
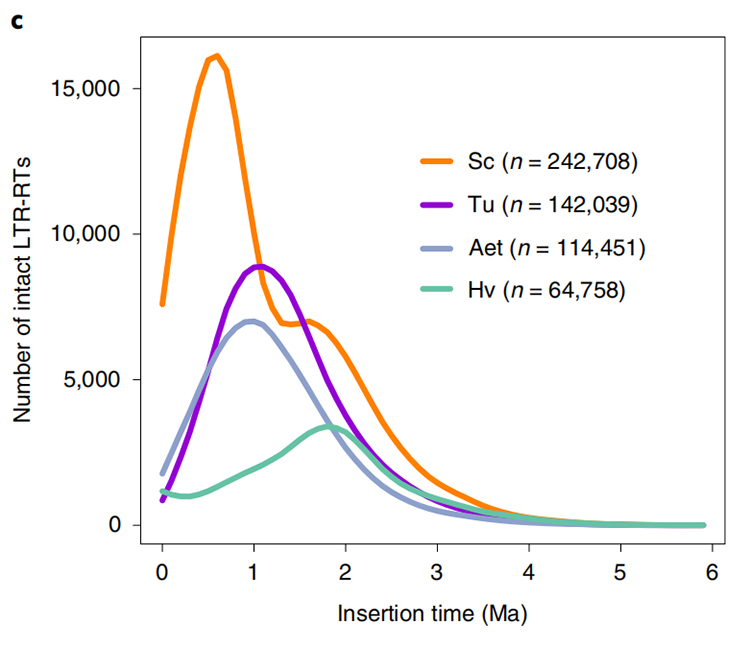
หลี่กวง และคณะพันธุศาสตร์ธรรมชาติ, 2021
2.การวิเคราะห์สายวิวัฒนาการและตระกูลยีนของ Chayote (Sechium edule) : จากการวิเคราะห์ Chayote และอีก 13 ชนิดที่เกี่ยวข้องในตระกูลยีน พบว่า Chayote มีความสัมพันธ์ใกล้ชิดกับมะระงู (Trichosanthes anguina) มากที่สุดChayote ที่ได้มาจากมะระงูในช่วงประมาณ 27-45 Mya และการทำซ้ำจีโนมทั้งหมด (WGD) ถูกพบใน Chayote ในช่วง 25 ± 4 Mya ซึ่งเป็นเหตุการณ์ WGD ครั้งที่สามในพืชตระกูลแตงกวา
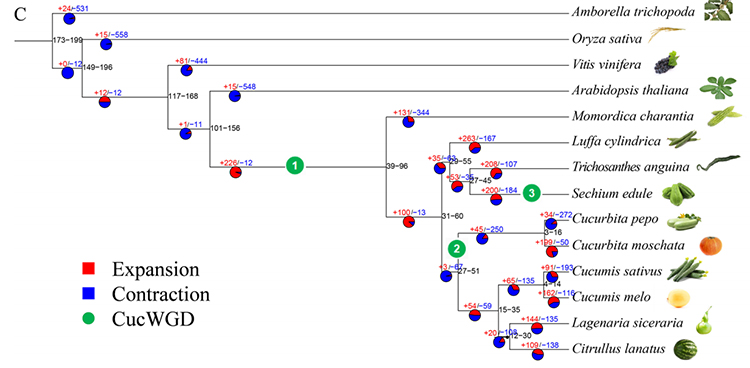
ฟูเอ และคณะการวิจัยพืชสวน, 2021
3.การวิเคราะห์แบบซินเทนี: ยีนบางชนิดที่เกี่ยวข้องกับไฟโตฮอร์โมนในการพัฒนาผลไม้พบได้ในชโยต บวบงู และสควอชความสัมพันธ์ระหว่าง Chayote และสควอชจะสูงกว่าความสัมพันธ์ระหว่าง Chayote กับมะระงูเล็กน้อย
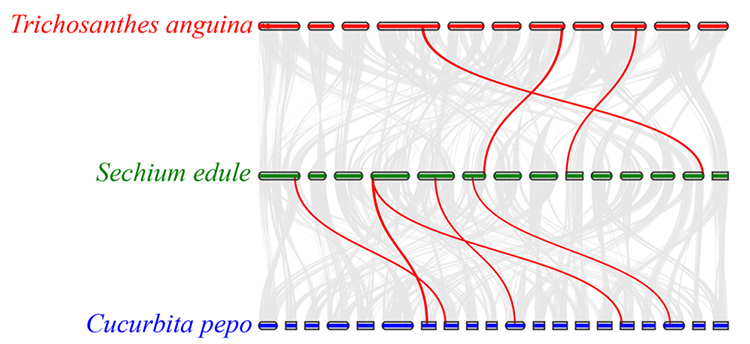
ฟูเอ และคณะการวิจัยพืชสวน, 2021
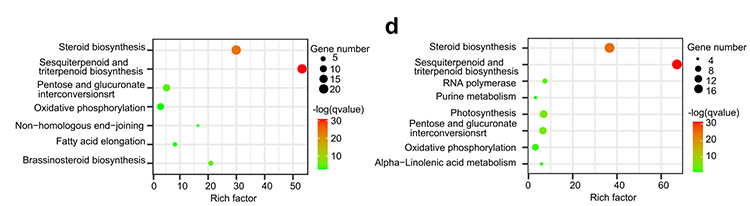
4. การวิเคราะห์ตระกูลยีน: การเพิ่มประสิทธิภาพของ KEGG ในการขยายและการหดตัวของตระกูลยีนในจีโนม G.thurberi และ G.davidsonii แสดงให้เห็นว่าการสังเคราะห์สเตียรอยด์และการสังเคราะห์ทางชีวภาพของบราสซิโนสเตอรอยด์ที่เกี่ยวข้องกับยีนได้รับการขยาย
หยาง ซี และคณะบีเอ็มซี ชีววิทยา, 2021
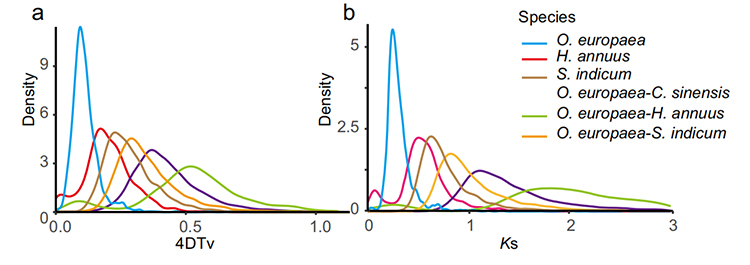
5. การวิเคราะห์การทำซ้ำจีโนมทั้งหมด: การวิเคราะห์การกระจายของ 4DTV และ Ks แสดงเหตุการณ์การทำซ้ำจีโนมทั้งหมดจุดสูงสุดของ intraspecies แสดงเหตุการณ์การทำซ้ำจุดสูงสุดของสปีชีส์ต่าง ๆ แสดงเหตุการณ์การสปีชีส์การวิเคราะห์ชี้ให้เห็นว่าเมื่อเปรียบเทียบกับอีกสามสายพันธุ์ที่เกี่ยวข้องกันอย่างใกล้ชิด O. europaea ได้ผ่านการทำซ้ำของยีนในวงกว้างเมื่อไม่นานมานี้
เราจี และคณะการวิจัยพืชสวน, 2021
คดีบีเอ็มเค
ดอกกุหลาบไร้หนาม: ข้อมูลเชิงลึกด้านจีโนมที่เชื่อมโยงกับการปรับความชื้น
ที่ตีพิมพ์: ทบทวนวิทยาศาสตร์แห่งชาติ, 2021
กลยุทธ์การจัดลำดับ:
'บาส'ไม่มีหนาม' (ร.วิชุไรนันท์) จีโนม:
ประมาณ93 X PacBio + ประมาณ90 X นาโนพอร์ + 267 X อิลลูมินา
ผลลัพธ์ที่สำคัญ
1. จีโนม R.wichuraiana คุณภาพสูงถูกสร้างขึ้นโดยใช้เทคนิคการจัดลำดับแบบอ่านยาว ซึ่งให้ผลการประกอบ 530.07 Mb (ขนาดจีโนมโดยประมาณคือประมาณ 525.9 Mb โดย flow cytometry และ 525.5 โดยการสำรวจจีโนม; Heterozygosity อยู่ที่ประมาณ 1.03%)คะแนนโดยประมาณของ BUSCO อยู่ที่ 93.9%เมื่อเปรียบเทียบกับ “หน้าแดงแบบเก่า” (haploOB) คุณภาพและความสมบูรณ์ของจีโนมนี้ได้รับการยืนยันโดยความแม่นยำเบสฐานเดี่ยวและดัชนีการประกอบ LTR (LAI=20.03)จีโนม R.wichuraiana มียีนเข้ารหัสโปรตีน 32,674 ยีน
2. การวิเคราะห์ข้อต่อแบบ Multi-omics ซึ่งประกอบด้วยจีโนมิกเชิงเปรียบเทียบ การถอดเสียง การวิเคราะห์ QTL ของประชากรทางพันธุกรรม เผยให้เห็นถึงลักษณะเฉพาะที่สำคัญระหว่าง R. wichuraiana และ Rosa chinensisนอกจากนี้การเปลี่ยนแปลงการแสดงออกของยีนที่เกี่ยวข้องใน QTL น่าจะสัมพันธ์กับลวดลายหนามของลำต้น

การวิเคราะห์จีโนมเชิงเปรียบเทียบระหว่าง Basye;s Thornless และ Rosa chinensis รวมถึงการวิเคราะห์ซินเทนี กลุ่มตระกูลยีน การวิเคราะห์การขยายตัวและการหดตัว เผยให้เห็นการเปลี่ยนแปลงจำนวนมาก ซึ่งเกี่ยวข้องกับลักษณะที่สำคัญในดอกกุหลาบการขยายตัวที่ไม่เหมือนใครในตระกูลยีน NAC และ FAR1/FRS มีแนวโน้มที่จะสัมพันธ์กับการต้านทานจุดดำอย่างมาก
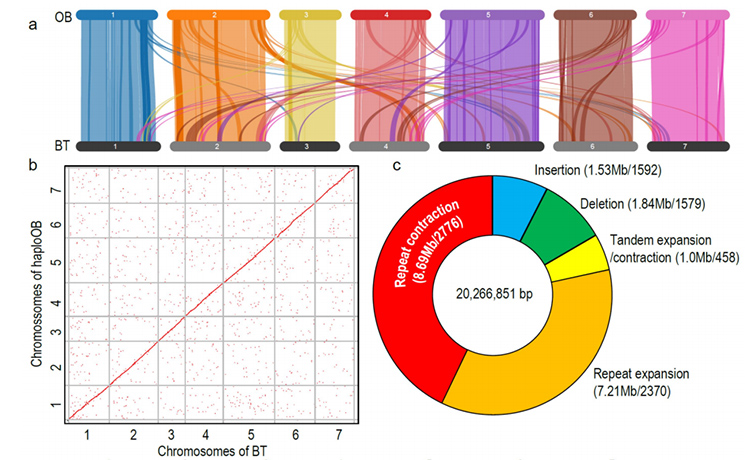

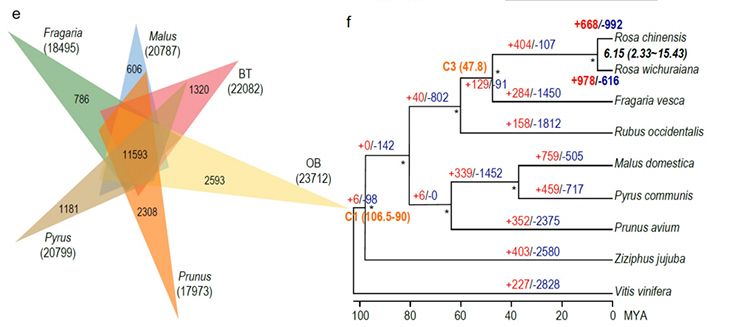
การวิเคราะห์จีโนมเชิงเปรียบเทียบระหว่างจีโนม BT และ haploOB
จง, เอ็ม, และคณะ.“กุหลาบไร้หนาม: ความเข้าใจเชิงจีโนมที่เชื่อมโยงกับการปรับตัวของความชื้น”ทบทวนวิทยาศาสตร์แห่งชาติ, 2021;, nwab092.













