อิลลูมินาและบีจีไอ
คุณสมบัติ
●แพลตฟอร์ม:Illumina NovaSeq 6000, NovaSeq , HiSeq X สิบ และ BGI-DNB-T7
●โหมดการเรียงลำดับ:PE50, PE100, PE150, PE250
●การควบคุมคุณภาพของห้องสมุดก่อนการจัดลำดับ
●การจัดลำดับการส่งข้อมูลและการควบคุมคุณภาพ:การจัดส่งรายงาน QC และข้อมูลดิบในรูปแบบ fastq หลังจากดีมัลติเพล็กซ์และการกรองการอ่าน Q30
ข้อดีของการบริการ
●ความคล่องตัวของบริการการจัดลำดับ:ลูกค้าอาจเลือกที่จะเรียงลำดับตามช่องทาง โฟลว์เซลล์ หรือจำนวนข้อมูล
●ความคล่องตัวของแพลตฟอร์ม:ไลบรารี DNB สามารถถ่ายโอนไปยังแพลตฟอร์มของ Illumina ได้
●ประสบการณ์ที่กว้างขวางบนแพลตฟอร์มการจัดลำดับของอิลลูมินา:ด้วยโครงการปิดหลายพันโครงการที่มีหลากหลายสายพันธุ์
●การส่งมอบรายงานการควบคุมคุณภาพตามลำดับ:ด้วยตัวชี้วัดคุณภาพ ความถูกต้องของข้อมูล และประสิทธิภาพโดยรวมของโปรเจ็กต์การจัดลำดับ
●กระบวนการจัดลำดับที่สมบูรณ์:ด้วยระยะเวลาการหมุนที่สั้น
●การควบคุมคุณภาพอย่างเข้มงวด: เราใช้ข้อกำหนด QC ที่เข้มงวดเพื่อรับประกันการส่งมอบผลลัพธ์คุณภาพสูงอย่างสม่ำเสมอ
ข้อกำหนดตัวอย่าง*
การจัดลำดับเลนบางส่วน
| ปริมาณข้อมูล (X) | ความเข้มข้น (qPCR/นาโนโมลาร์) | ปริมาณ |
| X ≤ 50 กิกะไบต์ | ≥ 2 นาโนโมลาร์ | ≥ 20 ไมโครลิตร |
| 50 Gb ≤ X < 100 Gb | ≥ 3 นาโนโมลาร์ | ≥ 20 ไมโครลิตร |
| X ≥ 100 กิกะไบต์ | ≥ 4 นาโนโมลาร์ | ≥ 20 ไมโครลิตร |
เลนเดียว (อิลลูมินา)
| แพลตฟอร์ม | ความเข้มข้น (qPCR/นาโนโมลาร์) | ปริมาณ |
| HiSeq X สิบ | ≥ 2 นาโนโมลาร์ | ≥ 20 ไมโครลิตร |
| NovaSeq 6000 SP | ≥ 1 นาโนโมลาร์ | ≥ 25 ไมโครลิตร |
| โนวาซีค 6000 เอส4 | ≥ 1.5 นาโนโมลาร์ | ≥ 25 ไมโครลิตร |
| NovaSeq X | ≥ 1.5 นาโนโมลาร์ | ≥ 25 ไมโครลิตร |
| BGI-DNBSEQ-T7 | ≥ 1.5 นาโนโมลาร์ | ≥ 25 ไมโครลิตร |
นอกจากความเข้มข้นและปริมาณทั้งหมดแล้ว ยังจำเป็นต้องมีรูปแบบพีคที่เหมาะสมอีกด้วย
โปรดติดต่อเราหากตัวอย่างของคุณไม่ตรงตามข้อกำหนดวัสดุเริ่มต้น
ขั้นตอนการบริการ
การควบคุมคุณภาพห้องสมุด

การเรียงลำดับ

การควบคุมคุณภาพข้อมูล

การส่งมอบโครงการ
รายงานการควบคุมคุณภาพห้องสมุด
มีการรายงานคุณภาพของห้องสมุดก่อนการจัดลำดับ การประเมินจำนวนห้องสมุด และการกระจายตัวของห้องสมุด
รายงานการควบคุมคุณภาพตามลำดับ
ตารางที่ 1. สถิติเกี่ยวกับข้อมูลลำดับ.
| รหัสตัวอย่าง | บีเอ็มคิด | อ่านดิบ | ข้อมูลดิบ (bp) | อ่านสะอาด (%) | ไตรมาสที่ 20(%) | ไตรมาสที่ 30(%) | GC(%) |
| C_01 | บีเอ็มเค_01 | 22,870,120 | 6,861,036,000 | 96.48 | 99.14 | 94.85 | 36.67 |
| C_02 | บีเอ็มเค_02 | 14,717,867 | 4,415,360,100 | 96.00 น | 98.95 | 93.89 | 37.08 |
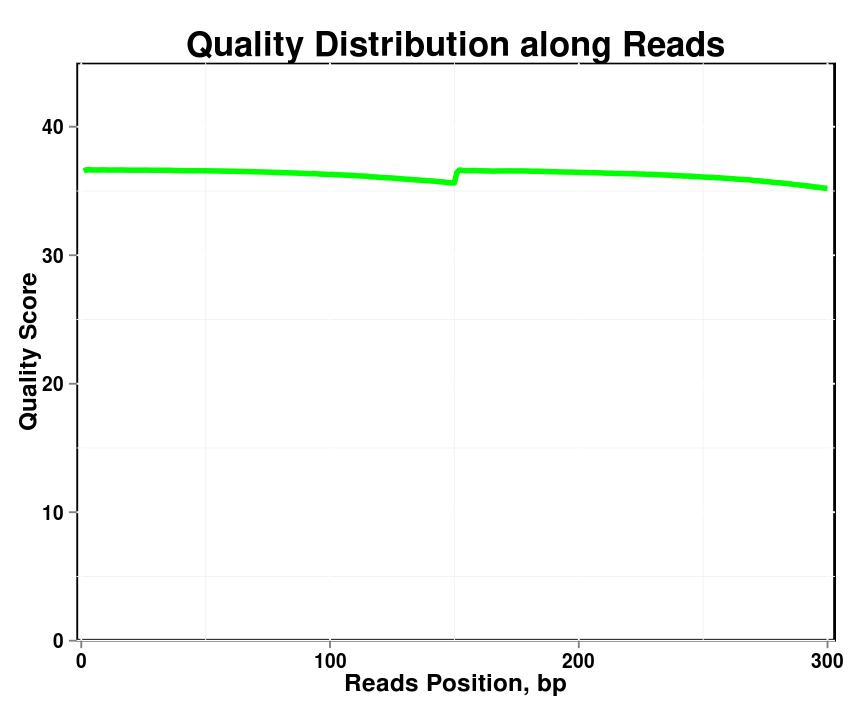
รูปที่ 1 การกระจายคุณภาพตามการอ่านในแต่ละตัวอย่าง
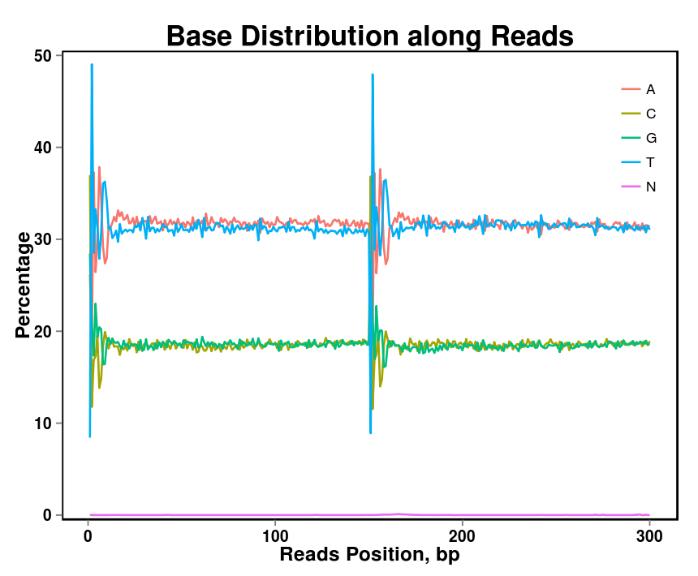
รูปที่ 2 การกระจายเนื้อหาฐาน
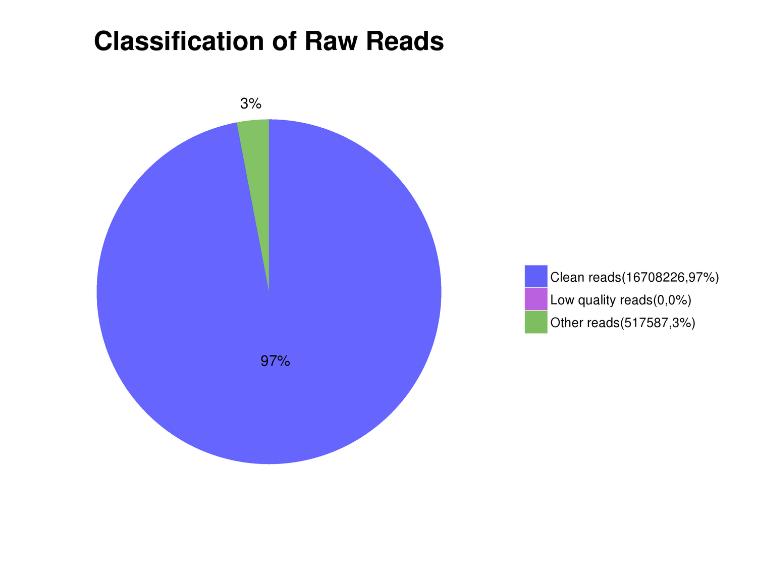
รูปที่ 3 การกระจายเนื้อหาที่อ่านในข้อมูลลำดับ