ลำดับแบบไม่เข้ารหัสแบบยาว - อิลลูมินา
ข้อดีของการบริการ
● ข้อดีของบริการ
● เฉพาะเซลล์และเนื้อเยื่อ
● ขั้นตอนเฉพาะเป็นการแสดงออกและนำเสนอการเปลี่ยนแปลงการแสดงออกแบบไดนามิก
● รูปแบบการแสดงออกของเวลาและพื้นที่ที่แม่นยำ
● การวิเคราะห์ร่วมกับข้อมูล mRNA
● การส่งมอบผลลัพธ์ตาม BMKCloud: การทำเหมืองข้อมูลแบบกำหนดเองพร้อมใช้งานบนแพลตฟอร์ม
● บริการหลังการขายจะมีอายุการใช้งาน 3 เดือนเมื่อโครงการเสร็จสิ้น
ข้อกำหนดตัวอย่างและการจัดส่ง
| ห้องสมุด | แพลตฟอร์ม | ข้อมูลที่แนะนำ | การควบคุมคุณภาพข้อมูล |
| การสูญเสีย rRNA | อิลลูมิน่า พีอี150 | 10 กิกะไบต์ | Q30≥85% |
| ความเข้มข้น(ng/μl) | ปริมาณ (ไมโครกรัม) | ความบริสุทธิ์ | ความซื่อสัตย์ |
| ≥ 100 | ≥ 0.5 | OD260/280=1.7-2.5 โอดี260/230=0.5-2.5 มีการปนเปื้อนของโปรตีนหรือ DNA อย่างจำกัดหรือไม่มีเลยบนเจล | สำหรับพืช: RIN≥6.5; สำหรับสัตว์: RIN≥7.0; 5.0≥28S/18S≥1.0; ระดับความสูงพื้นฐานที่จำกัดหรือไม่มีเลย |
นิวคลีโอไทด์:
เนื้อเยื่อ: น้ำหนัก(แห้ง): ≥1 g
*สำหรับเนื้อเยื่อที่มีขนาดเล็กกว่า 5 มก. เราแนะนำให้ส่งตัวอย่างเนื้อเยื่อแช่แข็งแบบแฟลช (ในไนโตรเจนเหลว)
การระงับเซลล์: จำนวนเซลล์ = 3 × 107
*เราแนะนำให้จัดส่งไลเซทเซลล์แช่แข็งในกรณีที่เซลล์นั้นนับน้อยกว่า 5×105แนะนำให้ใช้แฟลชแช่แข็งในไนโตรเจนเหลว
ตัวอย่างเลือด:
PA ×ยีนBloodRNATube;
เลือด 6 มล.ไตรโซล และ 2 มล.(ไตรโซล:เลือด=3:1)
การจัดส่งตัวอย่างที่แนะนำ
ภาชนะบรรจุ: หลอดหมุนเหวี่ยงขนาด 2 มล. (ไม่แนะนำให้ใช้ฟอยล์ดีบุก)
การติดฉลากตัวอย่าง: กลุ่ม+ทำซ้ำ เช่น A1, A2, A3;บี1 บี2 บี3......
การจัดส่ง:
1.น้ำแข็งแห้ง: ตัวอย่างจะต้องบรรจุในถุงและฝังในน้ำแข็งแห้ง
2.หลอด RNAstable: ตัวอย่าง RNA สามารถทำให้แห้งในหลอดรักษาเสถียรภาพ RNA (เช่น RNAstable®) และจัดส่งในอุณหภูมิห้อง
ขั้นตอนการทำงานบริการ

การออกแบบการทดลอง

การจัดส่งตัวอย่าง

การสกัดอาร์เอ็นเอ

การก่อสร้างห้องสมุด

การเรียงลำดับ

การวิเคราะห์ข้อมูล

บริการหลังการขาย
ชีวสารสนเทศศาสตร์
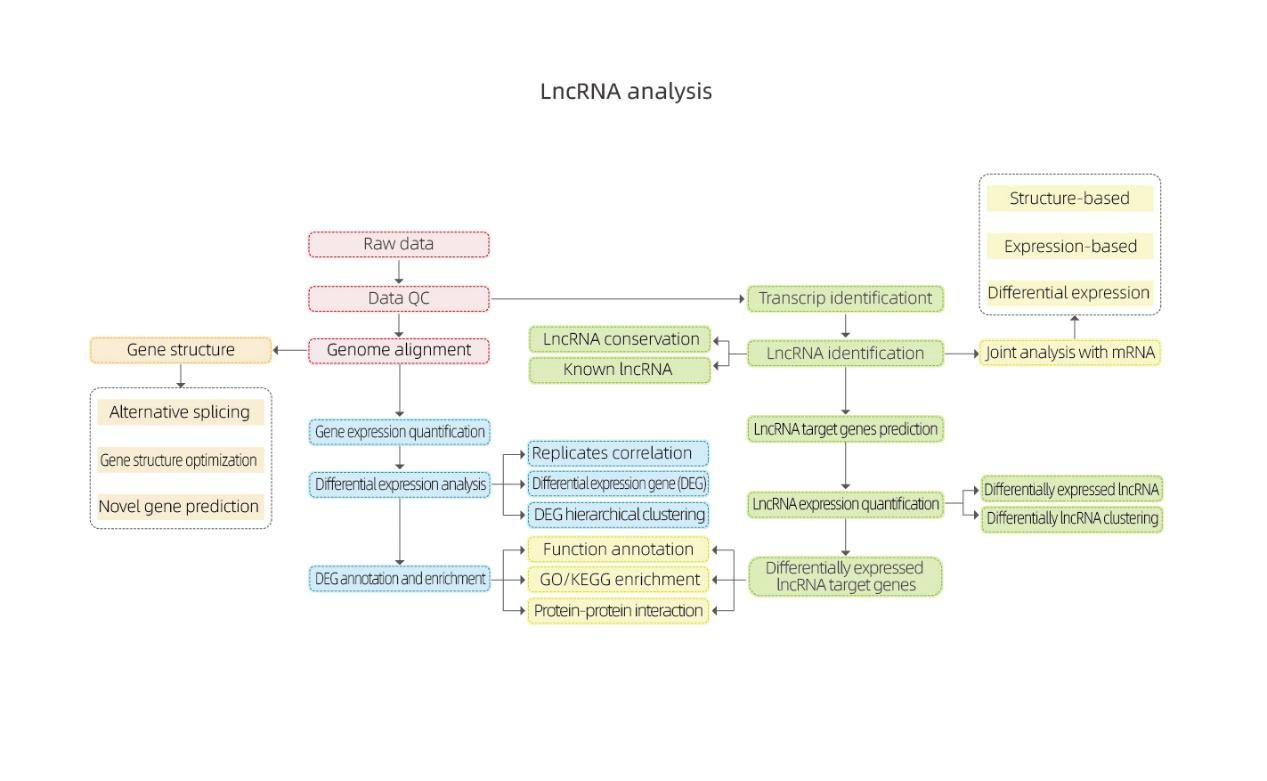
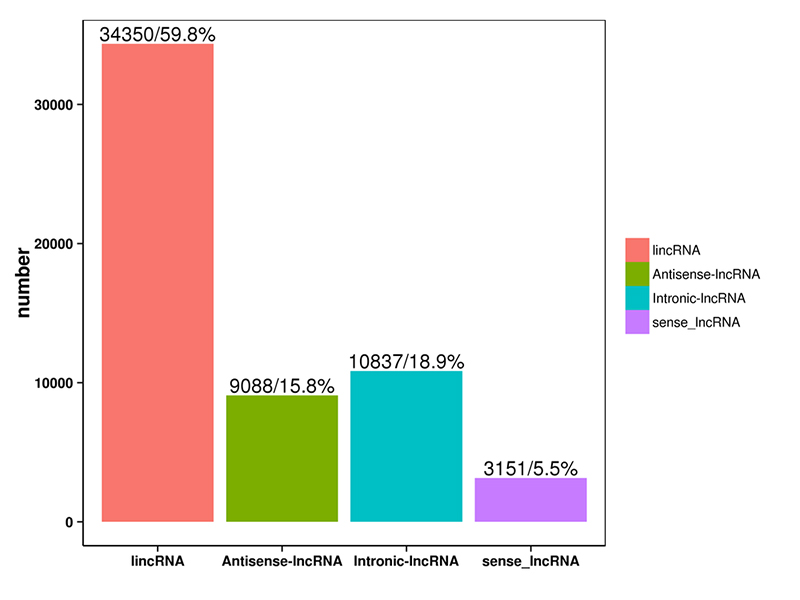
1.การจำแนกประเภท LncRNA
LncRNA ที่ทำนายโดยซอฟต์แวร์ทั้งสี่ด้านบนนั้นแบ่งออกเป็น 4 ประเภท: lincRNA, anti-sense-LncRNA, intronic-LncRNA;ความรู้สึก-LncRNAการจำแนกประเภท LncRNA แสดงอยู่ในฮิสโตแกรมด้านล่าง
การจำแนกประเภท LncRNA
2. ยีนเป้าหมาย Cis ของการวิเคราะห์การเพิ่มคุณค่า DE-lncRNA
ClusterProfiler ถูกนำมาใช้ในการวิเคราะห์การเพิ่มคุณค่า GO บนยีนเป้าหมายที่ถูกต้องของ lncRNA (DE-lncRNA) ที่แสดงออกแตกต่างกัน ในแง่ของกระบวนการทางชีววิทยา หน้าที่ของโมเลกุล และส่วนประกอบของเซลล์การวิเคราะห์การเพิ่มคุณค่า GO เป็นกระบวนการในการระบุคำศัพท์ GO ที่ได้รับการเสริมสมรรถนะอย่างมีนัยสำคัญซึ่งกำกับโดย DEG เมื่อเปรียบเทียบกับจีโนมทั้งหมดคำศัพท์ที่ได้รับการเสริมสมรรถนะถูกนำเสนอในฮิสโตแกรม แผนภูมิฟอง ฯลฯ ดังที่แสดงด้านล่าง
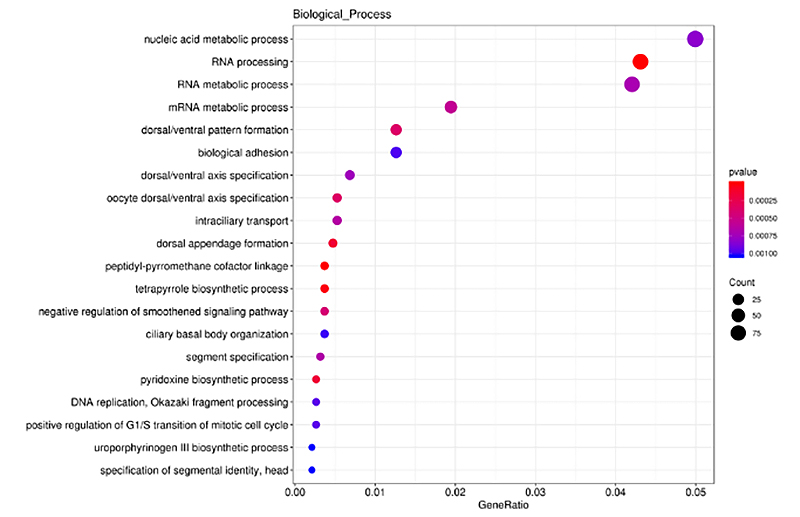 ยีนที่กำหนดเป้าหมาย Cis ของการวิเคราะห์การเพิ่มคุณค่า DE-lncRNA - แผนภูมิบับเบิ้ล
ยีนที่กำหนดเป้าหมาย Cis ของการวิเคราะห์การเพิ่มคุณค่า DE-lncRNA - แผนภูมิบับเบิ้ล
3. ด้วยการเปรียบเทียบความยาว หมายเลขเอ็กซอน ORF และจำนวนการแสดงออกของ mRNA และ lncRNA เราสามารถเข้าใจความแตกต่างในโครงสร้าง ลำดับ และอื่นๆ ระหว่างสิ่งเหล่านั้น และยังตรวจสอบว่า lncRNA นวนิยายที่เราทำนายไว้นั้นสอดคล้องกับลักษณะทั่วไปหรือไม่
คดีบีเอ็มเค
โปรไฟล์การแสดงออก lncRNA ที่ไม่ได้รับการควบคุมใน adenocarcinomas ของหนูเมาส์ด้วยการกลายพันธุ์ KRAS-G12D และการทำให้ล้มลง P53
ที่ตีพิมพ์:วารสารการแพทย์ระดับเซลล์และโมเลกุล,2019
กลยุทธ์การจัดลำดับ
อิลลูมินา
การเก็บตัวอย่าง
ได้รับเซลล์ NONMMUT015812-knockdown KP (shRNA-2) และเซลล์ควบคุมเชิงลบ (sh-Scr) ในวันที่ 6 ของการติดเชื้อไวรัสโดยเฉพาะ
ผลลัพธ์ที่สำคัญ
การศึกษานี้ตรวจสอบ lncRNAs ที่แสดงออกอย่างผิดปกติในมะเร็งของต่อมในปอดของหนูโดยมีค่า P53 ที่น่าพิศวงและการกลายพันธุ์ของ KrasG12D
1.6424 lncRNAs มีการแสดงออกที่แตกต่างกัน (≥ การเปลี่ยนแปลง 2 เท่า, P <0.05)
2. ในบรรดาทั้งหมด 210 lncRNAs (FC≥8) การแสดงออกของ 11 lncRNAs ถูกควบคุมโดย P53, 33 lncRNAs โดย KRAS และ 13 lncRNAs โดยภาวะขาดออกซิเจนในเซลล์ KP หลักตามลำดับ
3.NOMMUT015812 ซึ่งได้รับการควบคุมอย่างน่าทึ่งในมะเร็งของต่อมในปอดของหนู และควบคุมเชิงลบโดยการแสดงออกใหม่ของ P53 ถูกตรวจพบเพื่อวิเคราะห์การทำงานของเซลล์
4. การล้มลงของ NONMMUT015812 โดย shRNAs ลดการแพร่กระจายและความสามารถในการย้ายของเซลล์ KPNONMMUT015812 เป็นยีนที่มีศักยภาพ
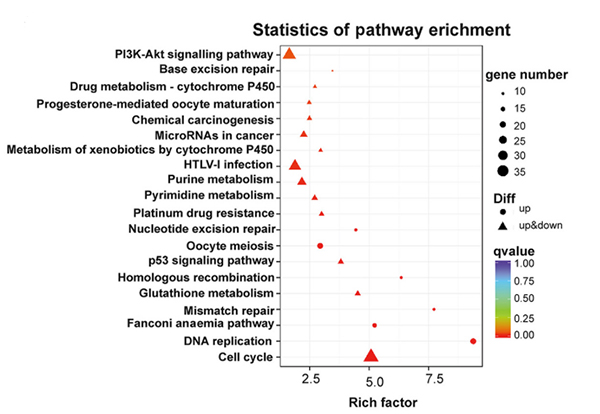 การวิเคราะห์วิถี KEGG ของยีนที่แสดงออกแตกต่างกันในเซลล์ KP NONMMUT015812-knockdown | 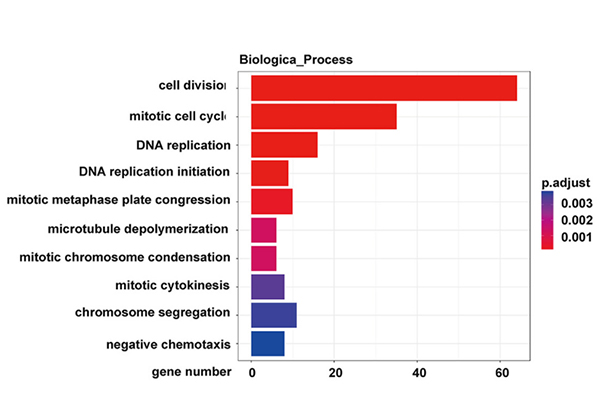 การวิเคราะห์ยีนอภิปรัชญาของยีนที่แสดงออกแตกต่างกันในเซลล์ KP NONMMUT015812-knockdown |
อ้างอิง
โปรไฟล์การแสดงออก lncRNA ที่ยกเลิกการควบคุมใน adenocarcinomas ของหนูเมาส์ด้วยการกลายพันธุ์ KRAS-G12D และการทำให้ล้มลง P53 [J]วารสารการแพทย์ระดับเซลล์และโมเลกุล, 2019, 23(10)ดอย: 10.1111/jcmm.14584