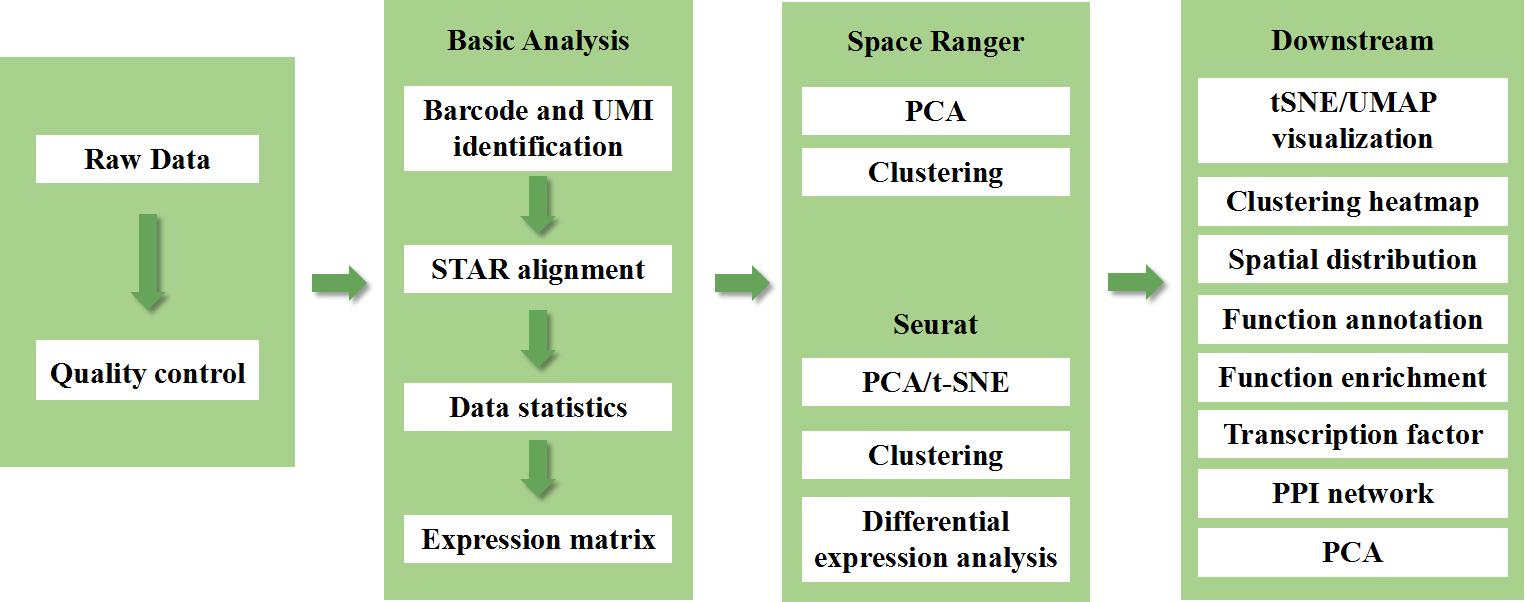
10x Genomics Visium Spatial Transcriptome
Mga Kalamangan sa Serbisyo
1) Pinagsasama ng one-stop service ang lahat ng mga hakbang na nakabatay sa karanasan at kasanayan, kabilang ang cryo-sectioning,HE paglamlam, tissue optimization, spatial barcoding, paghahanda sa library, sequencing at bioinformatics
2) Highly skilled technical group na may karanasan sa mahigit 250 na uri ng tissue, 50+ species kabilang ang tao, mouse, mammal, isda at halaman
3) Real-time na pag-update sa buong proyekto na may ganap na kontrol sa pang-eksperimentong pag-unlad
4) Comprehensive standard bioinformatics package na may 29 na pagsusuri, 100+ mataas na kalidad na mga numero
5) Available ang customized na pagsusuri at visualization ng data para sa iba't ibang kahilingan sa pananaliksiks
Mga Detalye ng Serbisyo
| Aklatan | Diskarte sa pagkakasunud-sunod | Inirerekomenda ang data | Mga Sample na Kinakailangan |
| 10X Visium cDNA library | 10x Visium-Illumina PE150 | 60 Gb/sample | OCT na naka-embed na mga sample ng cryo; Mga sample ng FFPE (Optimal na diameter: humigit-kumulang 6x6x6 mm3) |
Para sa higit pang mga detalye sa gabay sa paghahanda ng sample at daloy ng trabaho sa serbisyo, mangyaring huwag mag-atubiling makipag-usap sa aDalubhasa sa BMKGENE
Daloy ng Trabaho ng Serbisyo

Eksperimento na disenyo

Paghahatid ng sample

Paunang eksperimento
Spatial barcoding

Paggawa ng aklatan

Pagsusunod-sunod

Pagsusuri sa datos

Mga serbisyo pagkatapos ng pagbebenta
1)Kontrol sa Kalidad ng Data
Output ng data at pamamahagi ng marka ng kalidad
Pag-detect ng gene bawat lugar
Saklaw ng tissue
2)Panloob na sample na Pagsusuri
Pagtuklas ng gene
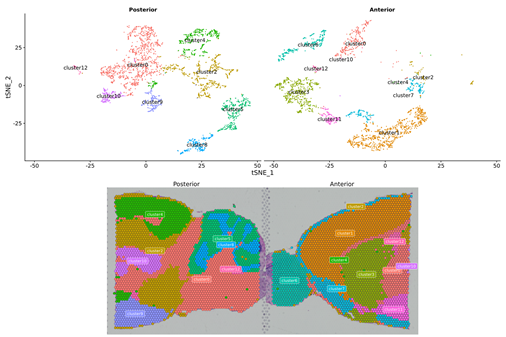
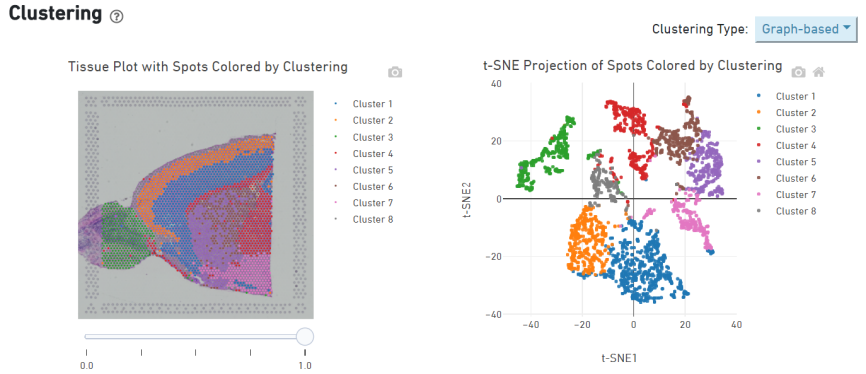
Spot clustering
Differential analysis sa mga cluster
3)Pagsusuri sa pagitan ng pangkat
Kumbinasyon ng data
Spot clustering ng pinagsamang data
Differential analysis sa pagitan ng mga grupo
1.Spot clustering
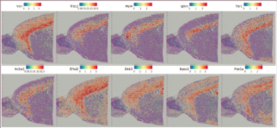
 2.Spatial na pamamahaging mga marker genes
2.Spatial na pamamahaging mga marker genes
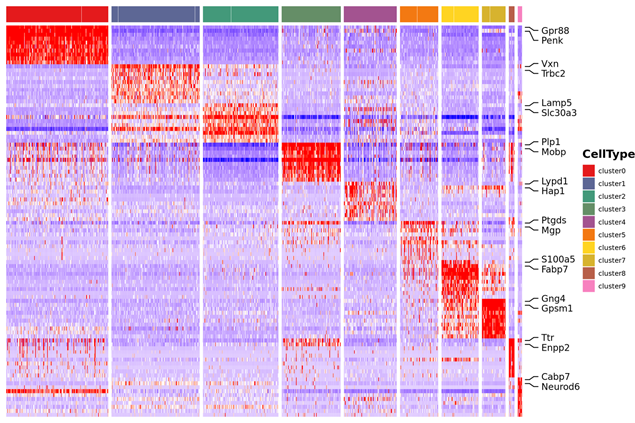
 3.Heatmap ng clustering ng clustering ng kasaganaan ng expression ng marker
3.Heatmap ng clustering ng clustering ng kasaganaan ng expression ng marker
 4. Inter-sample na pagsusuri ng data
4. Inter-sample na pagsusuri ng data