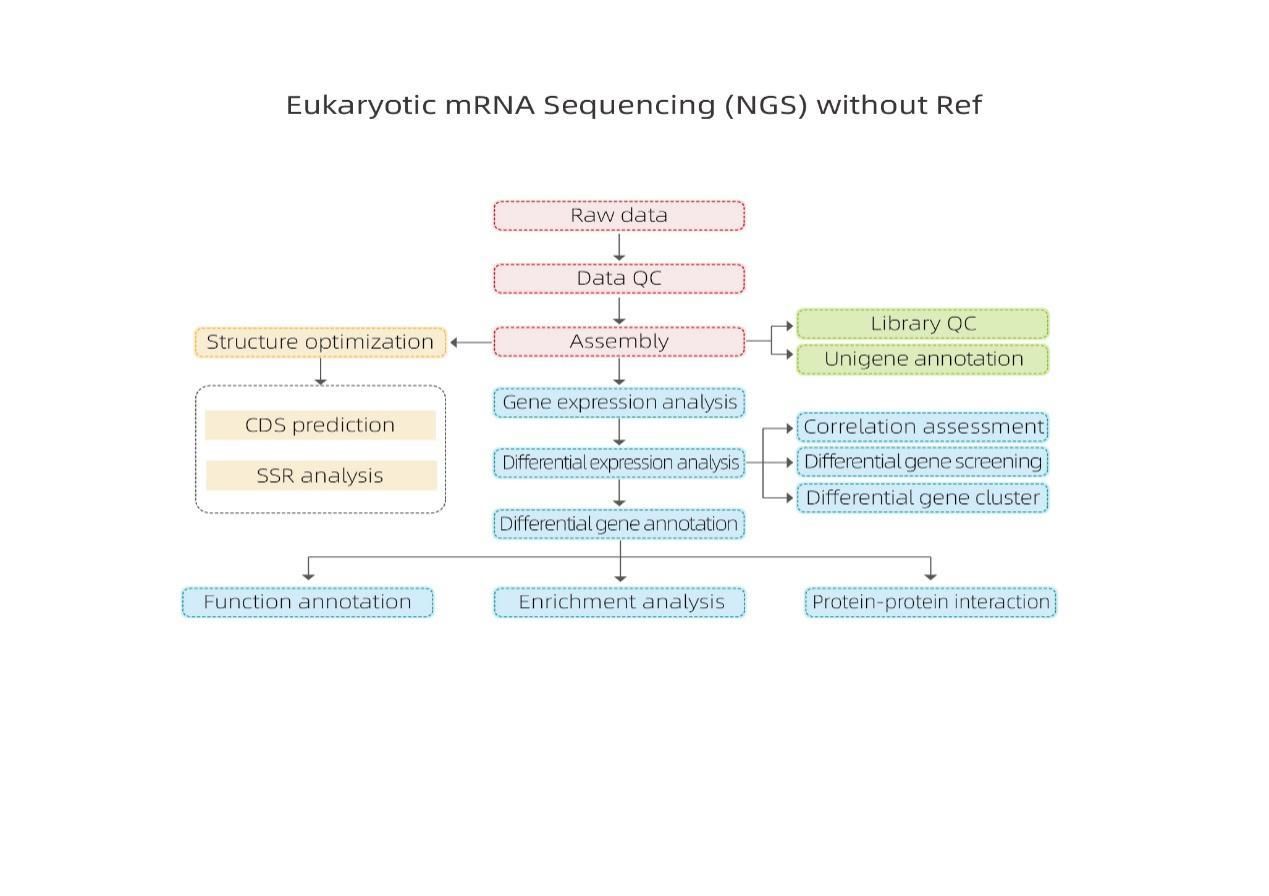
Non-Reference based mRNA Sequencing-Illumina
Mga tampok
● Independent sa anumang reference na genome,
● Maaaring gamitin ang data upang suriin ang istruktura at pagpapahayag ng mga transcript
● Tukuyin ang mga variable na clipping site
Mga Kalamangan sa Serbisyo
● Paghahatid ng resulta na nakabatay sa BMKCloud: Ang mga resulta ay inihahatid bilang data file at interactive na ulat sa pamamagitan ng BMKCloud platform, na nagbibigay-daan sa user-friendly na pagbabasa ng mga kumplikadong output ng pagsusuri at naka-customize na data mining batay sa karaniwang pagsusuri ng bioinformatics.
● Mga serbisyo pagkatapos ng pagbebenta: Mga serbisyo pagkatapos ng pagbebenta na may bisa sa loob ng 3 buwan pagkatapos makumpleto ang proyekto, kabilang ang pag-follow-up ng mga proyekto, pag-troubleshoot, mga resulta ng Q&A, atbp.
Mga Sample na Kinakailangan at Paghahatid
Mga Sample na Kinakailangan:
Nucleotides:
| Conc.(ng/μl) | Halaga (μg) | Kadalisayan | Integridad |
| ≥ 20 | ≥ 0.5 | OD260/280=1.7-2.5 OD260/230=0.5-2.5 Limitado o walang protina o kontaminasyon ng DNA na ipinapakita sa gel. | Para sa mga halaman: RIN≥6.5; Para sa mga hayop: RIN≥7.0; 5.0≥28S/18S≥1.0; limitado o walang baseline elevation |
Tissue: Timbang(tuyo): ≥1 g
*Para sa tissue na mas maliit sa 5 mg, inirerekomenda naming magpadala ng flash frozen(sa liquid nitrogen) sample ng tissue.
Pagsuspinde ng cell: Bilang ng cell = 3×107
*Inirerekomenda naming ipadala ang frozen cell lysate.Kung sakaling mas maliit ang cell na iyon sa 5×105, inirerekomenda ang flash frozen sa likidong nitrogen.
Sampol ng dugo:
PA×geneBloodRNATube;
6mLTRIzol at 2mL na dugo(TRIzol:Blood=3:1)
Inirerekomendang Paghahatid ng Sample
Lalagyan:
2 ml centrifuge tube (Hindi inirerekomenda ang tin foil)
Sample na pag-label: Pangkat+kopya hal. A1, A2, A3;B1, B2, B3... ...
Pagpapadala:
1. Dry-ice: Ang mga sample ay kailangang ilagay sa mga bag at ibaon sa dry-ice.
2.RNAstable tubes: Ang mga sample ng RNA ay maaaring patuyuin sa RNA stabilization tube(eg RNAstable®) at ipadala sa room temperature.
Daloy ng Trabaho ng Serbisyo

Eksperimento na disenyo

Paghahatid ng sample

Pagkuha ng RNA

Paggawa ng aklatan

Pagsusunod-sunod

Pagsusuri sa datos

Mga serbisyo pagkatapos ng pagbebenta
Bioinformatics
1.mRNA(denovo) Prinsipyo ng Pagpupulong
Sa pamamagitan ng Trinity, ang mga nabasa ay nahahati sa mas maliliit na piraso, na kilala bilang K-mer.Ang mga K-mer na ito ay gagamitin bilang mga buto na ipapalawak sa contigs at pagkatapos ay bahagi na batay sa contig overlappings.Sa wakas, inilapat si De Bruijn dito upang makilala ang mga transcript sa mga bahagi.
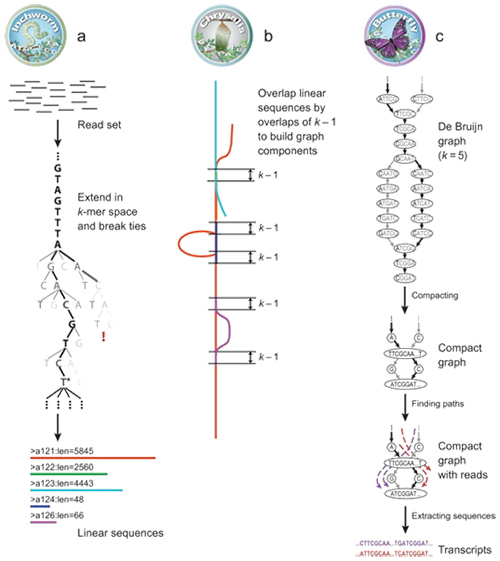
mRNA (De novo) Pangkalahatang-ideya ng Trinity
2.mRNA (De novo) Distribusyon ng Gene Expression Level
Nagagawa ng RNA-Seq na makamit ang isang napaka-sensitibong pagtatantya ng pagpapahayag ng gene.Karaniwan, ang nakikitang hanay ng mga transcript expression na FPKM ay mula 10^-2 hanggang 10^6
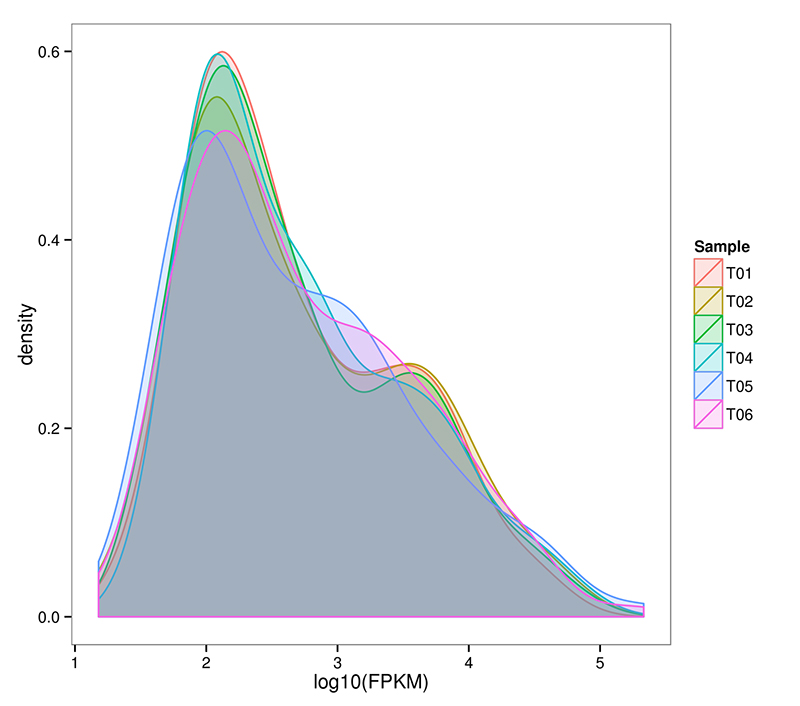
mRNA (De novo) Pamamahagi ng density ng FPKM sa bawat sample
3.mRNA (De novo) GO Enrichment Analysis ng mga DEG
Ang database ng GO (Gene Ontology) ay isang structured na biological annotation system na naglalaman ng karaniwang bokabularyo ng mga function ng gene at gene products.Naglalaman ito ng maraming antas, kung saan mas mababa ang antas, mas tiyak ang mga pag-andar.
mRNA (De novo) GO na pag-uuri ng mga DEG sa ikalawang antas
Kaso ng BMK
Transcriptome Analysis ng Sucrose Metabolism sa panahon ng Bulb Pamamaga at Pag-unlad sa Sibuyas (Allium cepa L.)
Nai-publish: mga hangganan sa agham ng halaman,2016
Diskarte sa pagkakasunud-sunod
Illumina HiSeq2500
Sample ng koleksyon
Ang Utah Yellow Sweet Spain cultivar na "Y1351" ay ginamit sa pag-aaral na ito.Ang bilang ng mga sample na nakolekta ay
Ika-15 araw pagkatapos ng pamamaga (DAS) ng bombilya (2-cm diameter at 3-4 g weight), ika-30 DAS (5-cm diameter at 100-110 g weight), at ∼3 sa ika-40 DAS (7-cm diameter at 260–300 gramo).
Mga pangunahing resulta
1. sa Venn diagram, kabuuang 146 DEG ang nakita sa lahat ng tatlong pares ng mga yugto ng pag-unlad
2. Ang "carbohydrate transport at metabolism" ay kinakatawan ng 585 unigenes lamang (ibig sabihin, 7% ng annotated na COG).
3. Ang mga Unigenes na matagumpay na na-annotate sa GO database ay inuri sa tatlong pangunahing kategorya para sa tatlong magkakaibang yugto ng pagbuo ng bombilya.Karamihan sa mga kinakatawan sa pangunahing kategorya ng "biological process" ay "metabolic process", na sinusundan ng "cellular process".Sa pangunahing kategorya ng "molecular function" ang dalawang kategorya na pinakakinatawan ay "binding" at "catalytic activity".
 Histogram ng mga kumpol ng orthologous groups (COG) na pag-uuri |  Histogram ng gene ontology (GO) na pag-uuri para sa mga unigenes na nagmula sa mga bombilya sa tatlong yugto ng pag-unlad |
 Venn diagram na nagpapakita ng mga gene na naiibang ipinahayag sa alinmang dalawang yugto ng pagbuo ng bombilya ng sibuyas |
Sanggunian
Zhang C, Zhang H , Zhan Z , et al.Transcriptome Analysis ng Sucrose Metabolism sa panahon ng Bulb Pamamaga at Pag-unlad sa Sibuyas (Allium cepa L.)[J].Frontiers sa Plant Science, 2016, 7:1425-.DOI: 10.3389/fpls.2016.01425