
Секвенування генома рослин/тварин De Novo
Переваги сервісу
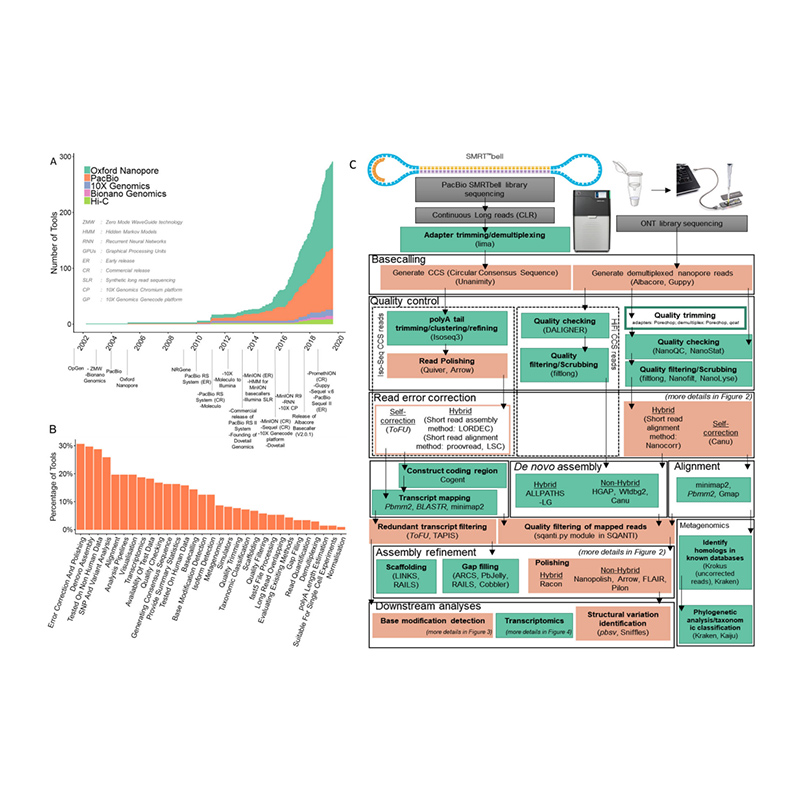
Розробка платформ секвенування та біоінформатики вde novoзбірка геному
(Amarasinghe SL та ін.,Біологія геному, 2020)
● Створення нових геномів і вдосконалення існуючих еталонних геномів для цікавих видів.
● Вища точність, безперервність і повнота складання
● Створення фундаментального ресурсу для досліджень поліморфізму послідовностей, QTL, редагування генів, селекції тощо.
● Оснащено повним спектром платформ секвенування третього покоління: універсальне рішення для збирання геному
● Гнучкі стратегії секвенування та складання, що відповідають різноманітним геномам із різними характеристиками
● Висококваліфікована команда біоінформатиків із великим досвідом роботи зі складними геномами, включаючи поліплоїди, гігантські геноми тощо.
● Понад 100 успішних кейсів із сукупним опублікованим імпакт-фактором понад 900
● Час виконання всього 3 місяці для складання генома на рівні хромосоми.
● Надійна технічна підтримка з низкою патентів і авторських прав на програмне забезпечення як в експериментальній частині, так і в біоінформатиці.
Специфікації послуги
|
Зміст
|
Платформа
|
Прочитати довжину
|
Покриття
|
| Обстеження геному
| Illumina NovaSeq
| PE150
| ≥ 50X
|
| Секвенування геному
| PacBio Revio
| 15 кб HiFi Reads
| ≥ 30X
|
| Привіт-C
| Illumina NovaSeq
| PE150
| ≥100X
|
Потік роботи

Вимоги до зразків і доставка
Вимоги до зразків:
| види | Тканина | Для PacBio | Для нанопор |
| Тварини | Вісцеральні органи (печінка, селезінка та ін.) | ≥ 1,0 г | ≥ 3,5 г |
| м'язи | ≥ 1,5 г | ≥ 5,0 г | |
| Кров ссавців | ≥ 1,5 мл | ≥ 5,0 мл | |
| Кров риб або птахів | ≥ 0,2 мл | ≥ 0,5 мл | |
| Рослини | Свіже листя | ≥ 1,5 г | ≥ 5,0 г |
| Пелюстка або стебло | ≥ 3,5 г | ≥ 10,0 г | |
| Коріння або насіння | ≥ 7,0 г | ≥ 20,0 г | |
| Клітини | Культура клітин | ≥ 3×107 | ≥ 1×108 |
Рекомендована доставка зразків
Контейнер: центрифужна пробірка на 2 мл (фольга не рекомендована)
Для більшості зразків ми рекомендуємо не зберігати в етанолі.
Маркування зразків: зразки повинні бути чітко марковані та ідентичні поданій інформаційній формі зразка.
Відвантаження: сухий лід: зразки спочатку потрібно запакувати в мішки та закопати в сухий лід.
Потік роботи служби

Дизайн експерименту

Доставка зразків

екстракція ДНК

Будівництво бібліотеки

Секвенування

Аналіз даних

Післяпродажне обслуговування
*Наведені тут демонстраційні результати взято з геномів, опублікованих за допомогою Biomarker Technologies
1. Circos на складанні генома на рівні хромосомиG. rotundifoliumплатформою секвенування Nanopore
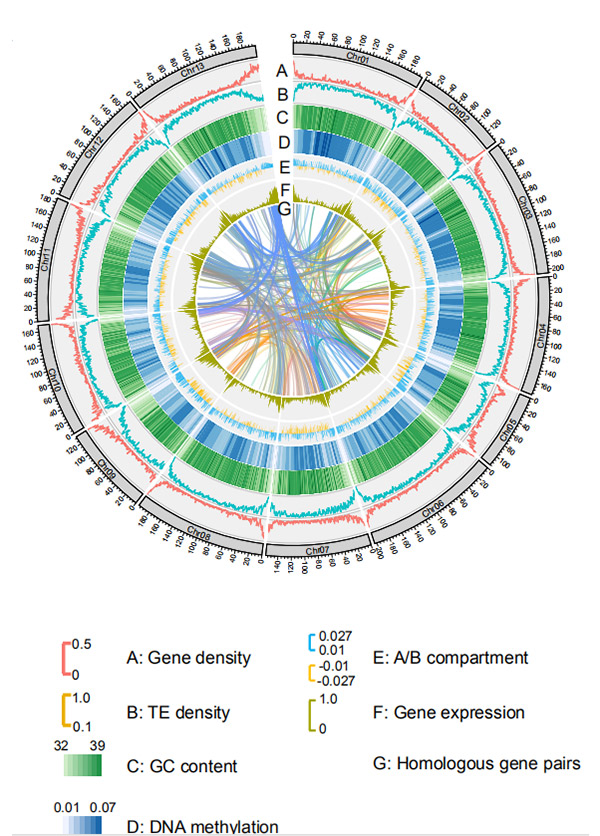
Wang M та ін.,Молекулярна біологія та еволюція, 2021 рік
2. Статистика складання та анотація геному жита Вейнінга
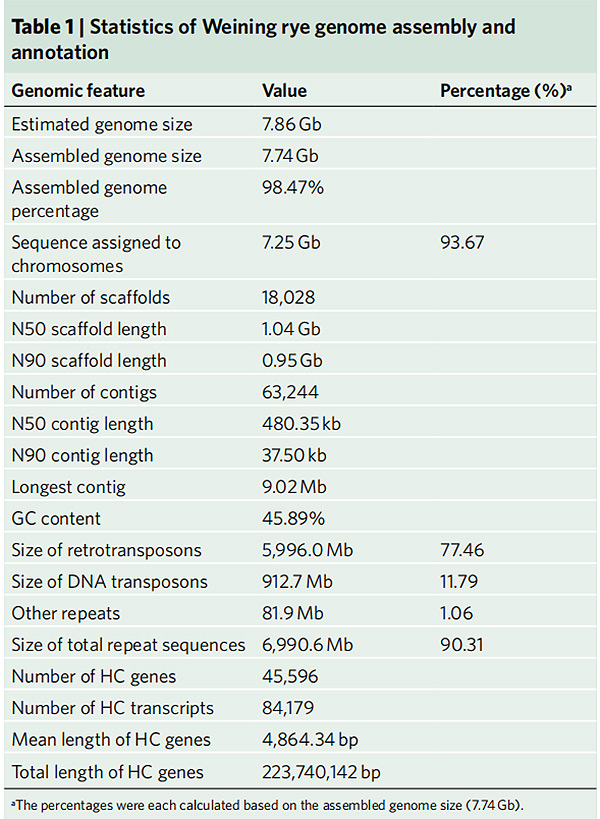
Li G та ін.,Генетика природи, 2021 рік
3. Генне передбаченняСехіум eduleгеному, отриманого за допомогою трьох методів прогнозування:De novoпрогнозування, прогнозування на основі гомології та прогнозування на основі даних RNA-Seq
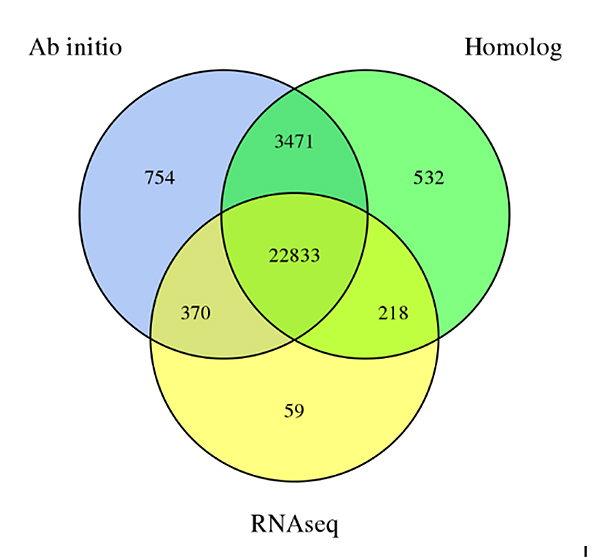
Фу А та ін.,Дослідження садівництва, 2021 рік
4. Ідентифікація інтактних довгих кінцевих повторів у трьох геномах бавовни
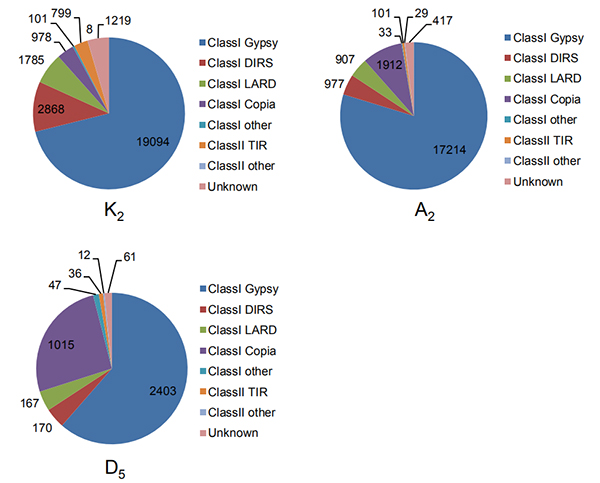
Wang M та ін.,Молекулярна біологія та еволюція, 2021 рік
5. Теплова карта Hi-CC. acuminataгеном, що показує взаємодію всіх на всіх у всьому геномі.Інтенсивність взаємодії Hi-C пропорційна лінійній відстані між контигами.Чітка пряма лінія на цій тепловій карті вказує на дуже точне закріплення контигів на хромосомах.(Коефіцієнт закріплення Contig: 96,03%)
kang M та ін.,Комунікації природи,2021 рік
Корпус БМК
Високоякісна збірка геному висвітлює геномні характеристики жита та агрономічно важливі гени
Опубліковано: Генетика природи, 2021 рік
Стратегія послідовності:
Збірка геному: режим PacBio CLR з бібліотекою 20 Кб (497 Гб, прибл. 63×)
Корекція послідовності: NGS з бібліотекою ДНК 270 bp (430 Гб, прибл. 54 ×) на платформі Illumina
Прив’язка контиґів: бібліотека Hi-C (560 Гб, прибл. 71 ×) на платформі Illumina
Оптична карта: (779,55 Гб, прибл. 99×) на Bionano Irys
Ключові результати
1. Було опубліковано збірку геному жита Вейнінга із загальним розміром геному 7,74 Гб (98,74% від оціненого розміру геному за допомогою проточної цитометрії).Scaffold N50 цієї збірки досяг 1,04 Гб.93,67% контигів були успішно закріплені на 7 псевдохромосомах.Цю збірку було оцінено за допомогою карти зв’язків, LAI і BUSCO, що призвело до високих балів у всіх оцінках.
2. Подальші дослідження з порівняльної геноміки, карти генетичного зчеплення, дослідження транскриптомії були проведені на основі цього геному.Було виявлено низку ознак, пов’язаних з геномними особливостями, включаючи подвоєння генів у всьому геномі та їхній вплив на гени біосинтезу крохмалю;фізична організація складних проламінових локусів, ознаки експресії генів, що лежать в основі ознаки раннього заголовка, і передбачуваних хромосомних областей і локусів, пов’язаних з одомашненням, у жита.
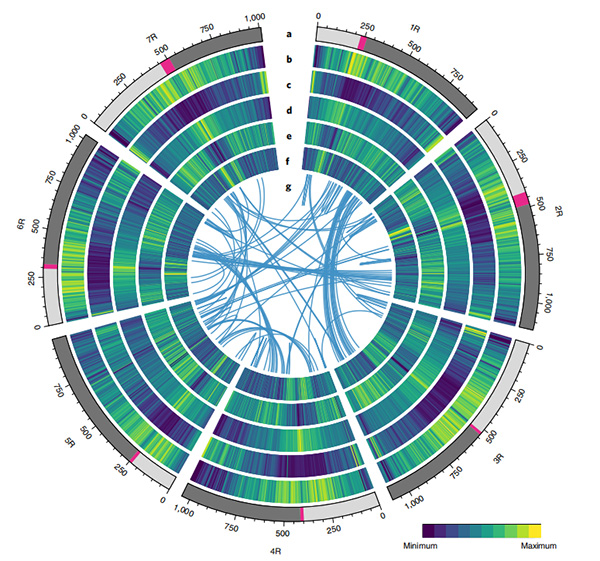 Діаграма Circos щодо геномних особливостей геному жита Вейнінга | 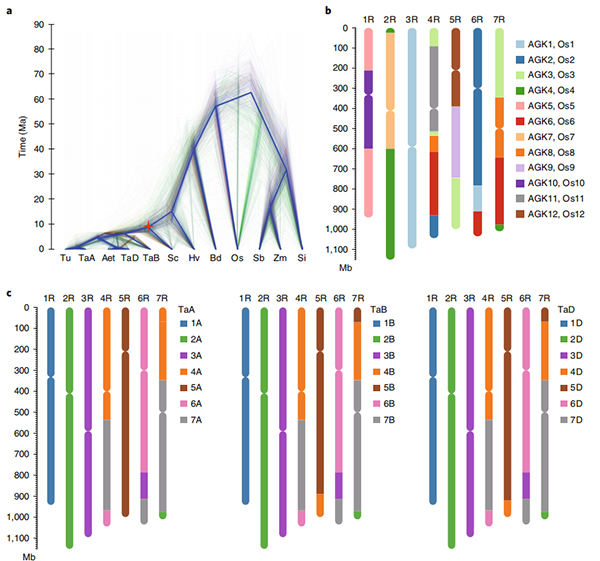 Еволюційний та хромосомно-синтетичний аналіз геному жита |
Лі Г., Ван Л., Ян Дж.та ін.Високоякісна збірка геному висвітлює геномні характеристики жита та агрономічно важливі гени.Нат Генет 53,574–584 (2021).
https://doi.org/10.1038/s41588-021-00808-z










