Metagenomics (NGS)
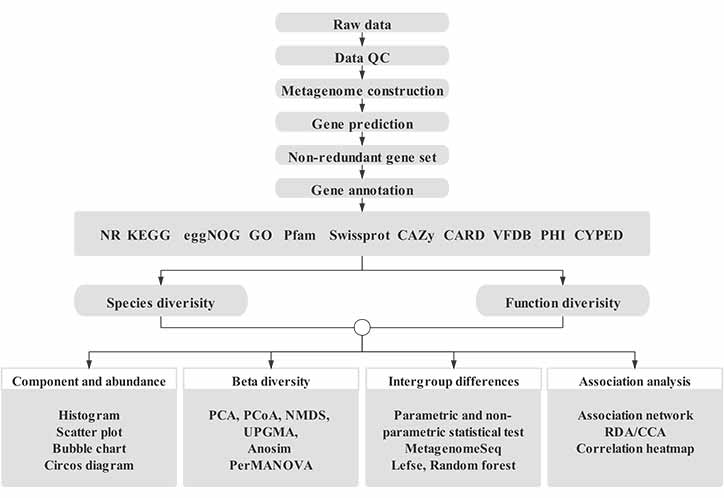
Denne analyseplatform er designet til metagenomisk dataanalyse af haglgevær på basis af mange års erfaring.Den består af en integreret arbejdsgang, der indeholder forskellige almindeligt nødvendige metagenomiske analyser, herunder databehandling, undersøgelser på artsniveau, undersøgelser på genfunktionsniveau, metagenombinning osv. Derudover er tilpassede dataminingværktøjer tilgængelige på standardanalysearbejdsgange, herunder gen- og artsforespørgsler , parameterindstilling, personlig figurgenerering osv.
Transcipit identifikation
Bioinformatik arbejdsflow