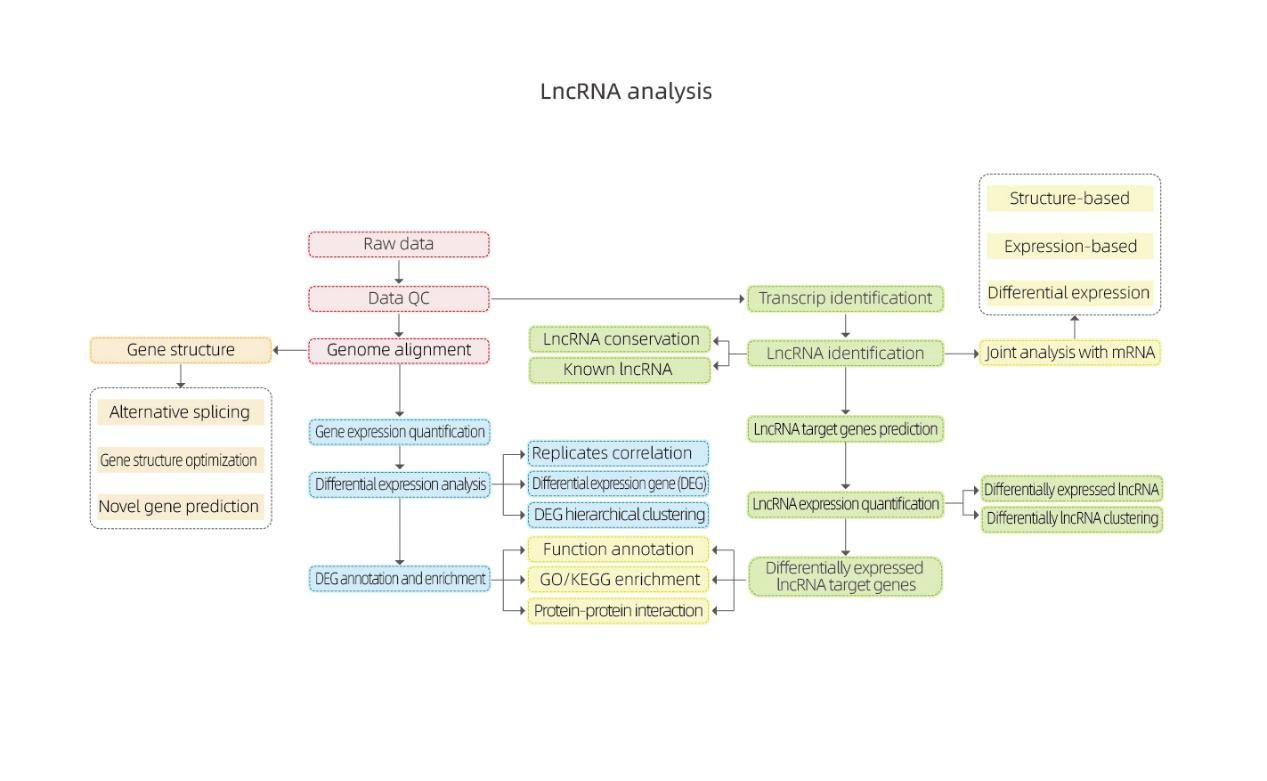
Lang ikke-kodende sekventering-Illumina
Service fordele
● Servicefordele
● Cellulær og vævsspecifik
● Specifik fase udtrykker og præsenterer dynamisk udtryksændring
● Præcise mønstre af tids- og rumudtryk
● Fællesanalyse med mRNA-data.
● BMKCloud-baseret resultatlevering: Tilpasset data-mining tilgængelig på platformen.
● Eftersalgsservice gælder i 3 måneder efter projektets afslutning
Prøvekrav og levering
| Bibliotek | Platform | Anbefalede data | Data QC |
| rRNA udtømning | Illumina PE150 | 10 Gb | Q30≥85 % |
| Konc.(ng/μl) | Mængde (μg) | Renhed | Integritet |
| ≥ 100 | ≥ 0,5 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Begrænset eller ingen protein- eller DNA-kontamination vist på gel. | For planter: RIN≥6,5; For dyr: RIN≥7,0; 5,0≥28S/18S≥1,0; begrænset eller ingen basislinjestigning |
Nukleotider:
Væv: Vægt (tør): ≥1 g
*For væv, der er mindre end 5 mg, anbefaler vi at sende lynfrosset (i flydende nitrogen) vævsprøve.
Cellesuspension: Celletal = 3×107
*Vi anbefaler at sende frosset cellelysat.I tilfælde af at cellen tæller mindre end 5×105, flash frosset i flydende nitrogen anbefales.
Blodprøver:
PA×geneBloodRNATube;
6mLTRIzol og 2mL blod(TRIzol:Blod=3:1)
Anbefalet prøvelevering
Beholder: 2 ml centrifugerør (stanniol anbefales ikke)
Prøvemærkning: Gruppe+replikat f.eks. A1, A2, A3;B1, B2, B3... ...
Forsendelse:
1.Tøris: Prøver skal pakkes i poser og begraves i tøris.
2.RNAstabile rør: RNA-prøver kan tørres i RNA-stabiliseringsrør (f.eks. RNAstable®) og sendes i stuetemperatur.
Service Work Flow

Eksperimentdesign

Prøve levering

RNA-ekstraktion

Biblioteksbyggeri

Sekvensering

Dataanalyse

Eftersalgsservice
Bioinformatik
1.LncRNA klassificering
LncRNA forudsagt af de fire ovenstående software blev klassificeret i 4 kategorier: lincRNA, anti-sense-LncRNA, intronic-LncRNA;sense-LncRNA.LncRNA-klassificering blev vist i histogrammet nedenfor.
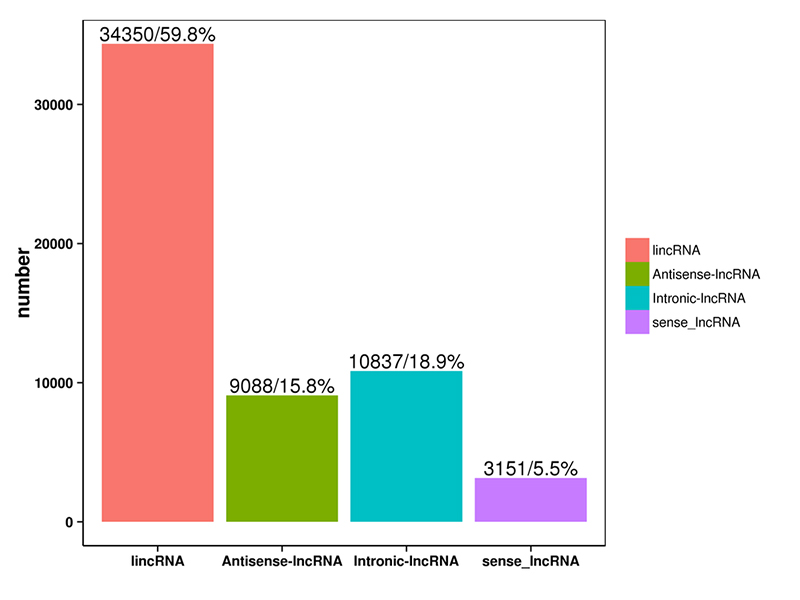
LncRNA klassificering
2. Cis-målrettede gener af DE-lncRNA-berigelsesanalyse
ClusterProfiler blev brugt i GO-berigelsesanalyse på cis-målrettede gener af differentielt udtrykt lncRNA (DE-lncRNA), hvad angår biologiske processer, molekylære funktioner og cellulære komponenter.GO-berigelsesanalyse er en proces til at identificere DEG-rettede signifikant berigede GO-termer sammenlignet med hele genomet.De berigede udtryk blev præsenteret i histogram, boblediagram osv. som vist nedenfor.
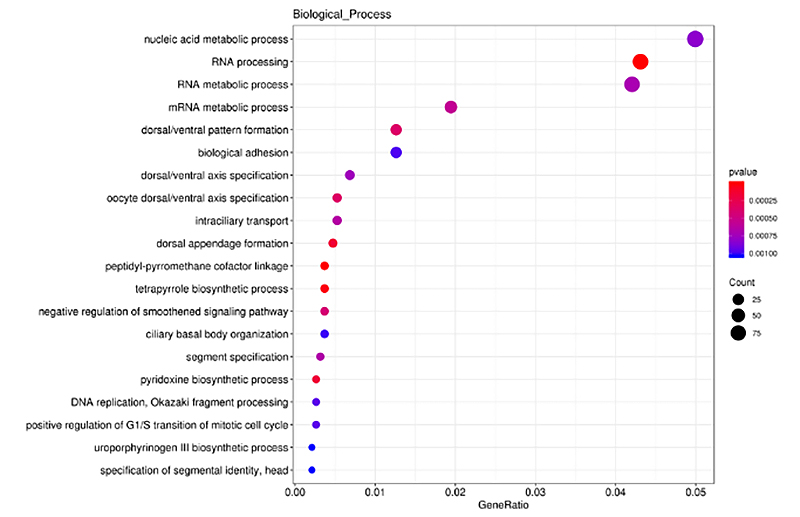 Cis-målrettede gener af DE-lncRNA berigelsesanalyse - Boblediagram
Cis-målrettede gener af DE-lncRNA berigelsesanalyse - Boblediagram
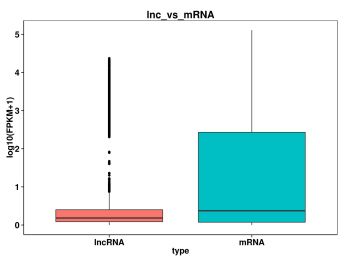
3. Ved at sammenligne længden, exonnummeret, ORF og ekspressionsmængden af mRNA og lncRNA, kan vi forstå forskellene i struktur, sekvens og så videre mellem dem, og også verificere om det nye lncRNA forudsagt af os stemmer overens med de generelle karakteristika.
BMK sag
Dereguleret lncRNA-ekspressionsprofil i muselungeadenokarcinomer med KRAS-G12D-mutation og P53-knockout
Udgivet:Journal of Cellular and Molecular Medicine,2019
Sekvenseringsstrategi
Illumina
Samling af prøver
NONMMUT015812-knockdown KP (shRNA-2) celler og negative kontrol (sh-Scr) celler blev opnået på dag 6 af en specifik virusinfektion.
Nøgleresultater
Denne undersøgelse undersøger de afvigende udtrykte lncRNA'er i musens lungeadenokarcinom med P53-knockout og KrasG12D-mutationen.
1,6424 lncRNA'er blev differentielt udtrykt (≥ 2-fold ændring, P < 0,05).
2. Blandt alle 210 lncRNA'er (FC≥8) blev 11 lncRNA's ekspression reguleret af henholdsvis P53, 33 lncRNA'er af KRAS og 13 lncRNA'er af hypoxi i de primære KP-celler.
3.NONMMUT015812, som var bemærkelsesværdigt opreguleret i muselungeadenokarcinomet og negativt reguleret af P53-re-ekspressionen, blev detekteret for at analysere dets cellulære funktion.
4.Knockdown af NONMMUT015812 af shRNA'er reducerede proliferation og migrationsevner af KP-celler.NONMMUT015812 var et potentielt onkogen.
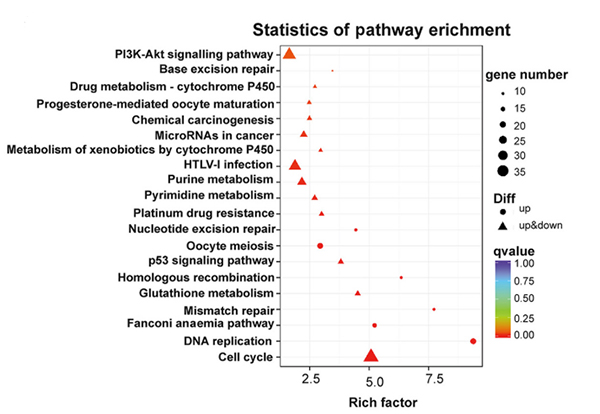 KEGG pathway-analyse af de differentielt udtrykte gener i NONMMUT015812-knockdown KP-cellerne | 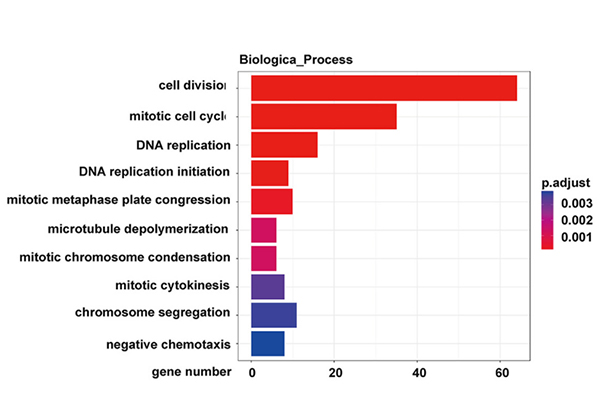 Genontologianalyse af de differentielt udtrykte gener i NONMMUT015812-knockdown KP-cellerne |
Reference
Dereguleret lncRNA-ekspressionsprofil i muselungeadenokarcinomer med KRAS-G12D-mutation og P53-knockout [J].Journal of Cellular and Molecular Medicine, 2019, 23(10).DOI: 10.1111/jcmm.14584