Genom-dækkende associationsanalyse
1. Servicefordele
● Rigelige projekttilfælde: Siden etableringen i 2009 har BMKGENE gennemført hundredvis af artsprojekter i populations-GWAS-forskning, hjulpet forskere med at publicere mere end 100 artikler, og den kumulative effektfaktor nåede 500.
● Professionelle analytikere.
● Kort analysecyklus.
● Nøjagtig datamining.
2. Servicespecifikationer
| Type | Befolkningsskala | Sekvenseringsstrategi og dybde |
| SLAF-GWAS | Prøvenummer ≥200 | Genomstørrelse < 400M, med ref-genom, WGS anbefales |
| Genomstørrelse ≤ 1G, 100K tags og 10X | ||
| 1G ≤ Genomstørrelse ≤ 2G, 200K Tags og 10X | ||
| Genomstørrelse > 2G, 300K Tags og 10X | ||
| WGS-GWAS | Prøvenummer ≥200 | 10X for hver prøve |
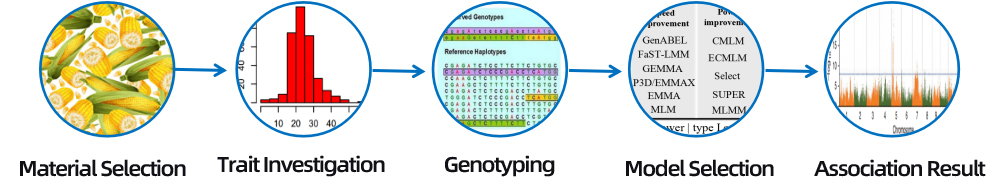
3. Materialevalg



Forskellige sorter, underarter, landracer/genbanker/blandede familier/vilde ressourcer
Forskellige sorter, underarter, landracer
Halvsøskendefamilie/helsøskendefamilie/vilde ressourcer
4. Bioinformationsanalyse
● Genom-dækkende associationsanalyse
● Analyse og screening af signifikant SNP
● Funktionel annotering af kandidatgen
5. Service Work Flow

Eksperimentdesign

Prøve levering

RNA-ekstraktion

Biblioteksbyggeri

Sekvensering

Dataanalyse

Eftersalgsservice
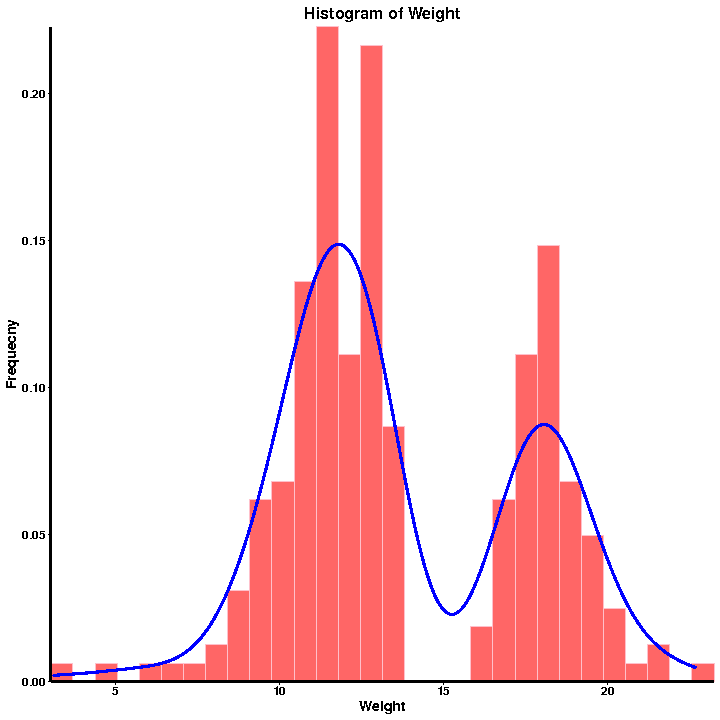
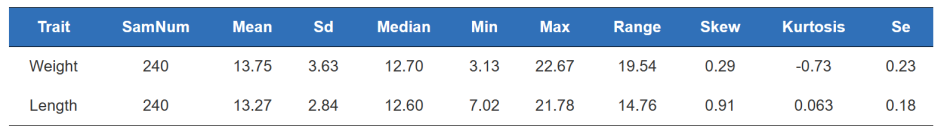
en.Fænotype QC
Frekvensfordelingshistogram
Fænotype statistik
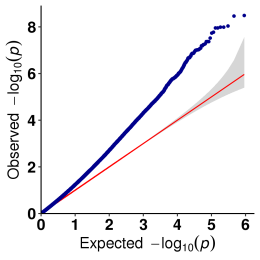
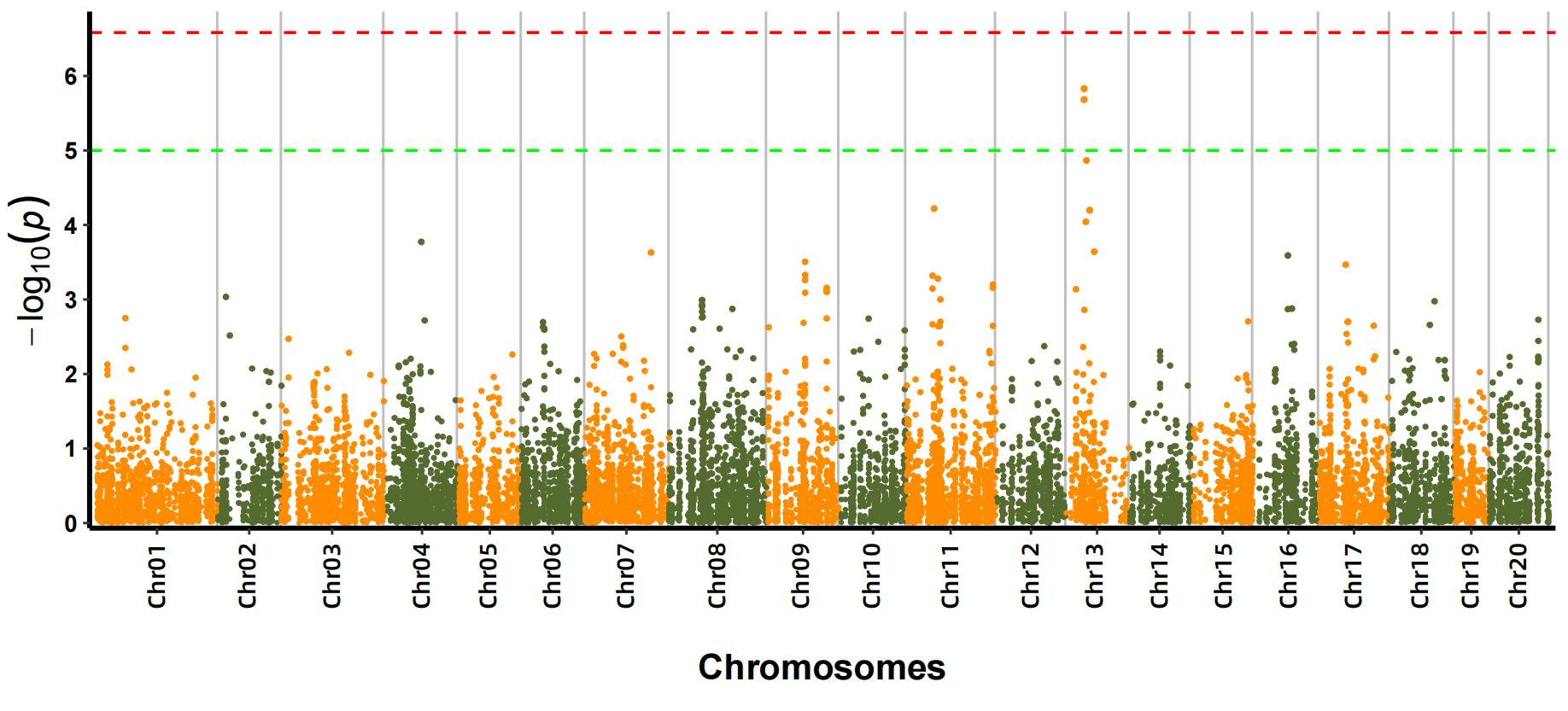
b.Associationsanalyse (model: GEMMA, FaST-LMM, EMMAX)
QQ plot
Manhattan plot
| År | Tidsskrift | IF | Titel |
| 2022 | NC | 17,69 | Genomisk grundlag for giga-kromosomerne og giga-genomet af træpæonen Paeonia ostii |
| 2015 | NP | 7,43 | Domesticeringsfodspor forankrer genomiske regioner af agronomisk betydning i sojabønner |
| 2018 | MP | 9,32 | Helgenom-resekventering af en verdensomspændende samling af rapsfrø afslører genetisk grundlag for deres økotypedivergens |
| 2022 | HR | 7,29 | Genom-dækkende associationsanalyse giver molekylær indsigt i den naturlige variation af vandmelonfrøstørrelse |