Metagenomika (NGS)
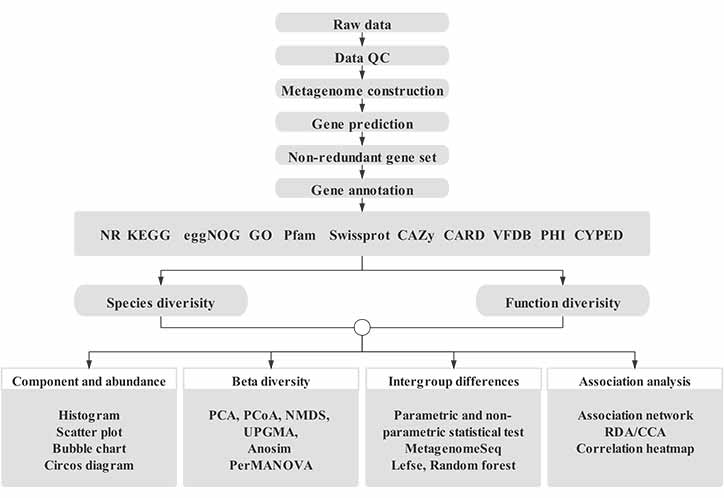
Ta platforma analityczna jest przeznaczona do analizy danych metagenomicznych typu shotgun w oparciu o wieloletnie doświadczenie.Składa się ze zintegrowanego przepływu pracy zawierającego różne powszechnie potrzebne analizy metagenomiczne, w tym przetwarzanie danych, badania na poziomie gatunku, badania na poziomie funkcji genów, kategoryzacja metagenomów itp. Ponadto w ramach standardowego przepływu pracy dostępne są dostosowane narzędzia do eksploracji danych, w tym zapytania dotyczące genów i gatunków , ustawianie parametrów, generowanie spersonalizowanych figur itp.
Identyfikacja tranzytu
Przepływ pracy w bioinformatyce