Ensayo de cromatina accesible a transposasa con secuenciación de alto rendimiento (ATAC-seq)
Ventajas del servicio
● Análisis integral: canal de análisis profesional para satisfacer una variedad de necesidades de análisis personalizadas;
● Amplia experiencia: Cientos de proyectos completados con éxito hasta el momento, incluidas muestras de animales y plantas.
Especificaciones de servicio
Plataforma: plataforma Illumina NovaSeq
Tipo de biblioteca: ATAC-seq
Salida de datos recomendada: ≥20M lecturas
Requisitos de muestra
Tipo de muestra: tejidos, células vivas o células congeladas, etc.
Número de celda: ≥ 5×105células, un número de celda exacto es clave para el éxito del experimento;
Peso del tejido: ≥ 200 mg de tejido fresco;
Sangre: ≥ 2 ml
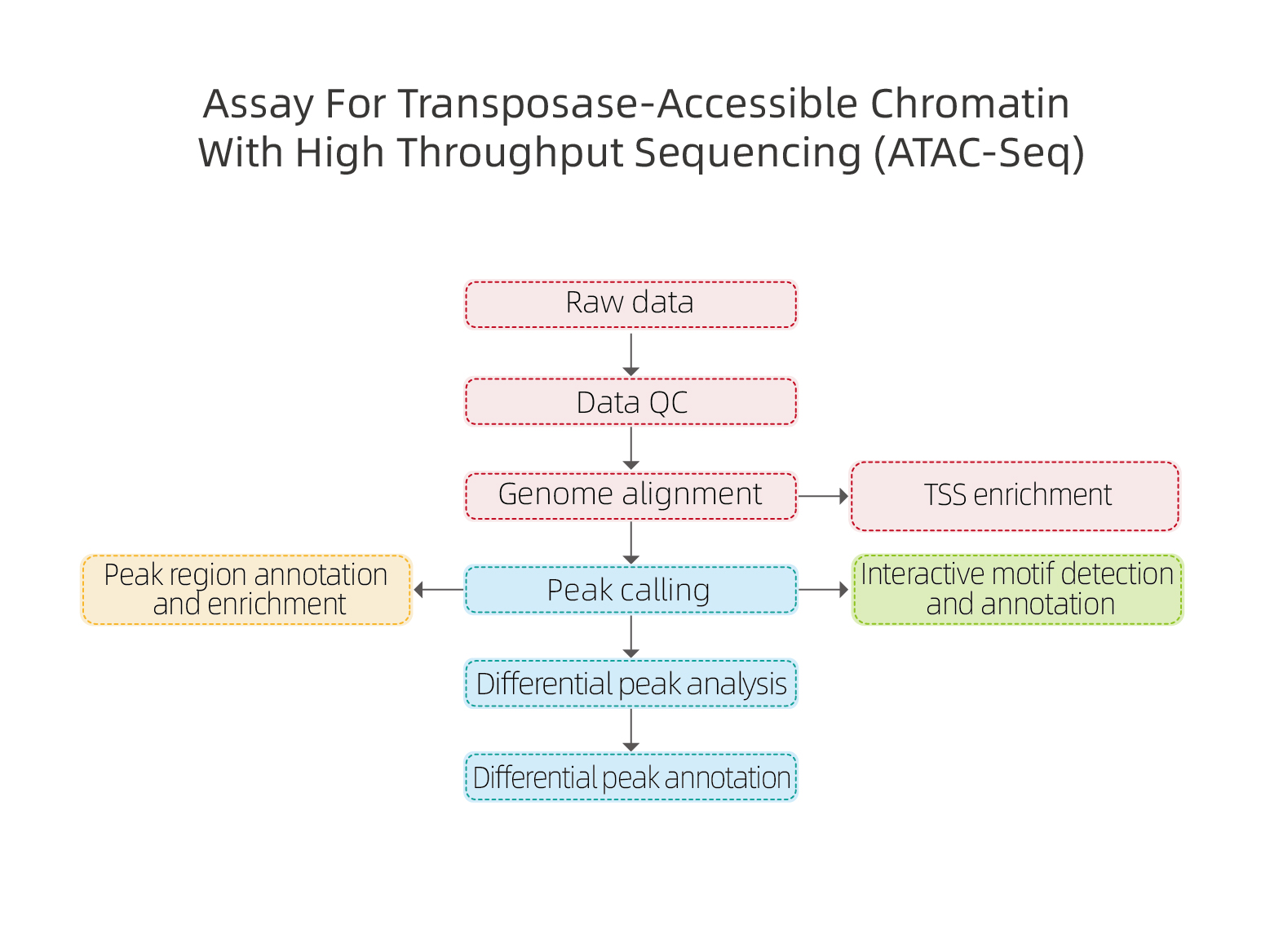
Flujo de trabajo del servicio

Diseño de experimentos

Entrega de muestra

Extracción de ADN

construcción de biblioteca

Secuenciación

Análisis de los datos

Servicios postventa
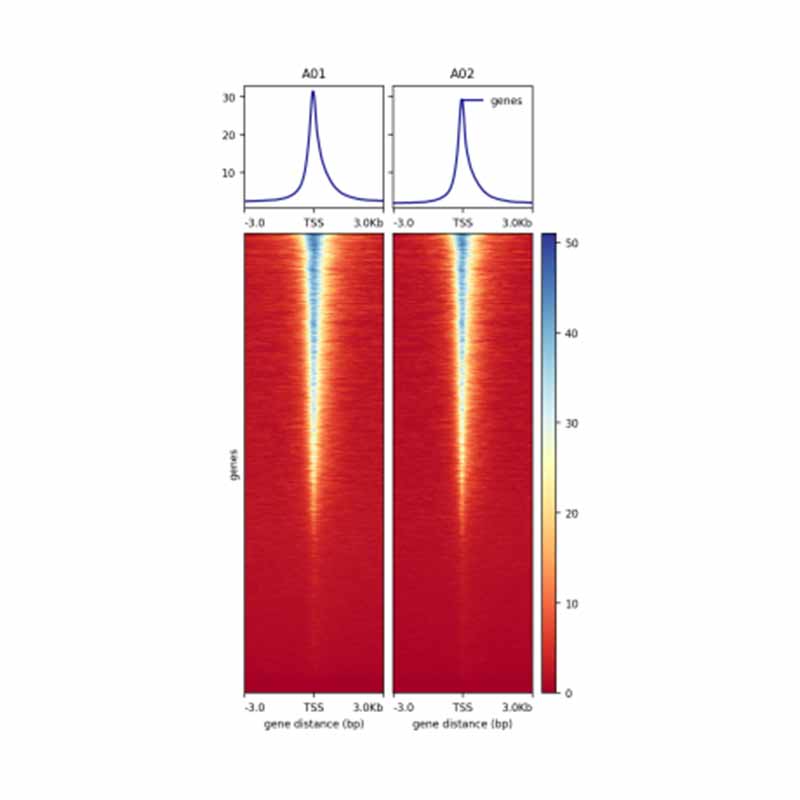
1.Mapa de calor en la distribución de lecturas ATAC en TSS y regiones adyacentes (±3 kb)
1.jpg) 2.Distribución de la región de cromatina abierta en diferentes componentes del genoma.
2.Distribución de la región de cromatina abierta en diferentes componentes del genoma.
3.Llamada pico diferencial entre grupos





.jpg)
.jpg)