Transcriptoma espacial 10x Genomics Visium
Características
● Resolución: 100 µM
● Diámetro del punto: 55 µM
● Número de plazas: 4992
● Área de captura: 6,5 x 6,5 mm
● Cada punto con código de barras está cargado con cebadores compuestos de 4 secciones:
- cola poli(dT) para cebado de ARNm y síntesis de ADNc
- Identificador molecular único (UMI) para corregir el sesgo de amplificación
- Código de barras espacial
- Secuencia de unión del cebador de secuenciación de lectura parcial 1
● Tinción H&E de secciones
Ventajas
●Servicio de una parada: integra todos los pasos basados en la experiencia y las habilidades, incluida la criosección, la tinción, la optimización de tejidos, los códigos de barras espaciales, la preparación de bibliotecas, la secuenciación y la bioinformática.
● Equipo técnico altamente cualificado: con experiencia en más de 250 tipos de tejidos y más de 100 especies, incluidos humanos, ratones, mamíferos, peces y plantas.
●Actualización en tiempo real de todo el proyecto.: con control total del progreso experimental.
●Bioinformática estándar integral:El paquete incluye 29 análisis y más de 100 cifras de alta calidad.
●Análisis y visualización de datos personalizados: disponible para diferentes solicitudes de investigación.
●Análisis conjunto opcional con secuenciación de ARNm unicelular
Especificaciones
| Requisitos de muestra | Biblioteca | Estrategia de secuenciación | Datos recomendados | Control de calidad |
| Muestras criogénicas integradas en OCT, muestras FFPE (Diámetro óptimo: aprox. 6x6x6 mm3) 3 bloques por muestra | Biblioteca de ADNc de Visium 10X | Iluminación PE150 | 50.000 lecturas de PE por lugar (60 GB) | RIN>7 |
Para obtener más detalles sobre la guía de preparación de muestras y el flujo de trabajo del servicio, no dude en hablar con unExperto en BMKGENE
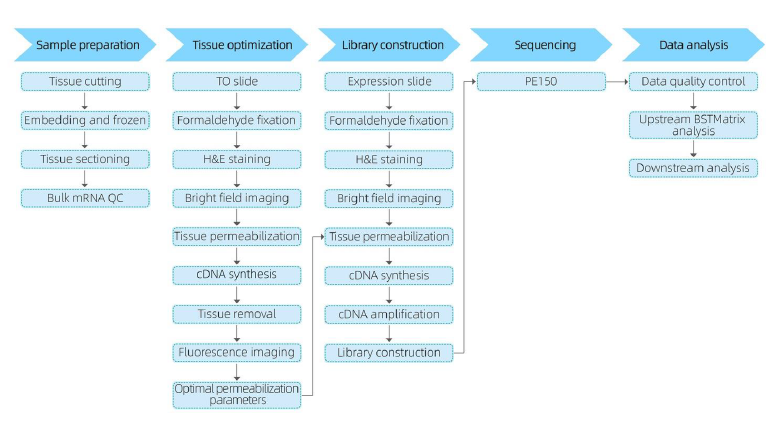
Flujo de trabajo del servicio
En la fase de preparación de la muestra, se realiza una prueba inicial de extracción de ARN en masa para garantizar que se pueda obtener ARN de alta calidad.En la etapa de optimización del tejido, las secciones se tiñen y visualizan y se optimizan las condiciones de permeabilización para la liberación de ARNm del tejido.Luego, el protocolo optimizado se aplica durante la construcción de la biblioteca, seguido de la secuenciación y el análisis de datos.
El flujo de trabajo completo del servicio implica actualizaciones en tiempo real y confirmaciones del cliente para mantener un ciclo de retroalimentación receptivo, lo que garantiza una ejecución fluida del proyecto.
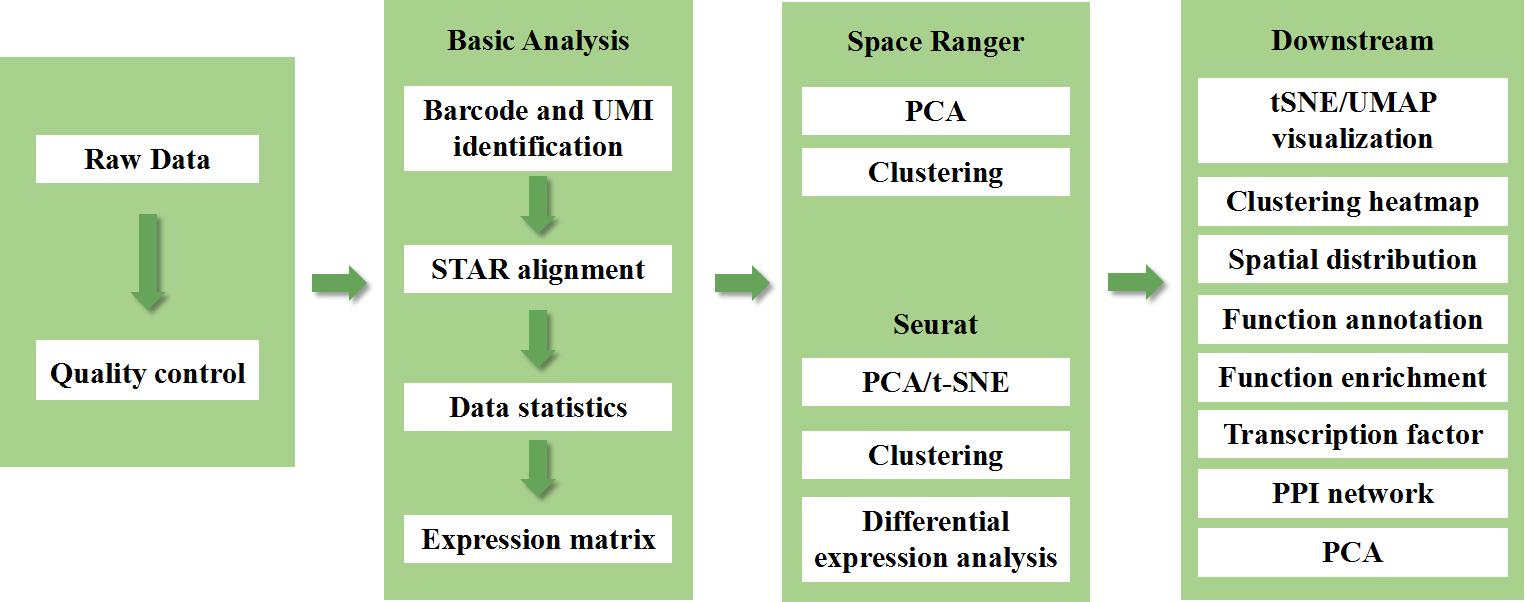
Incluye el siguiente análisis:
Control de calidad de datos:
o Salida de datos y distribución de puntuación de calidad.
o Detección de genes por punto
o Cobertura de tejido
Análisis de muestra interna:
o Riqueza genética
o Agrupación puntual, incluido el análisis de dimensiones reducidas.
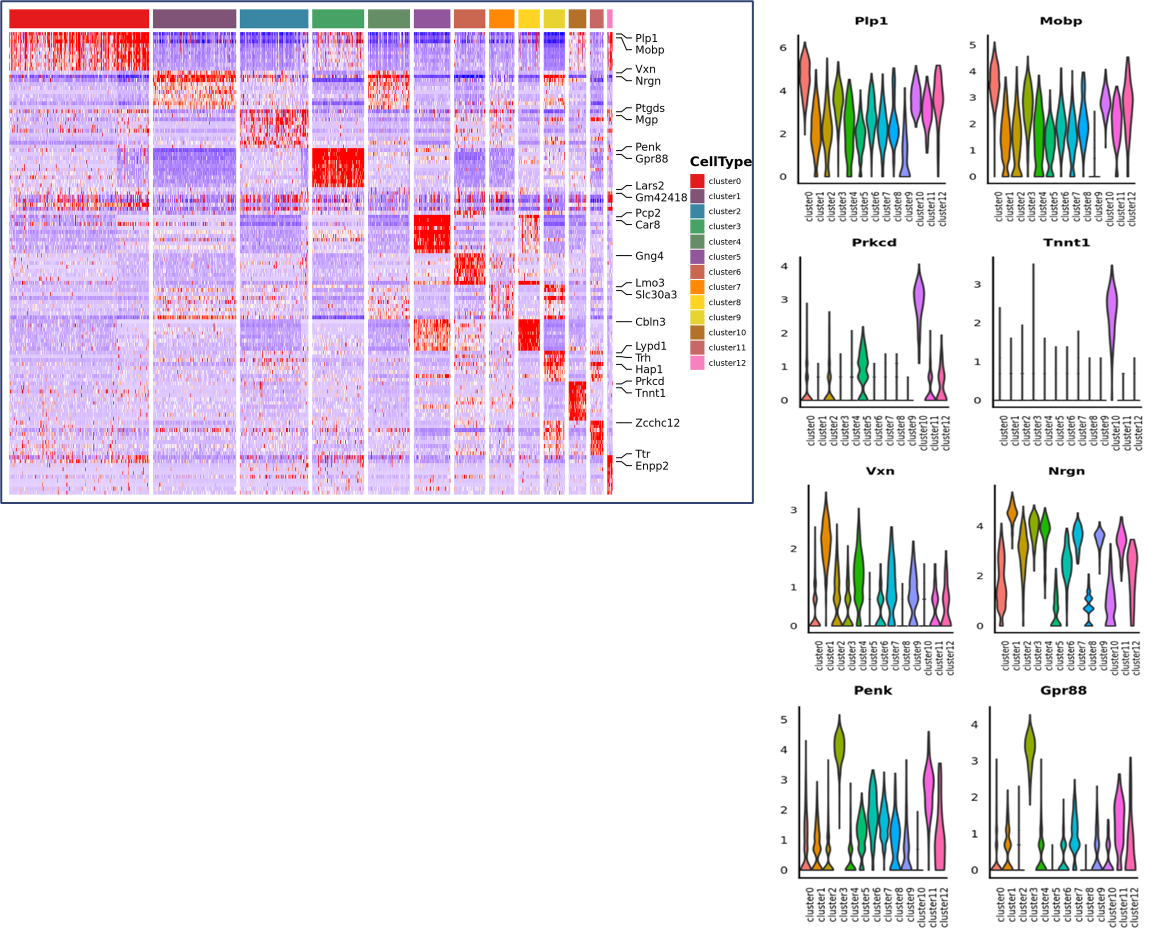
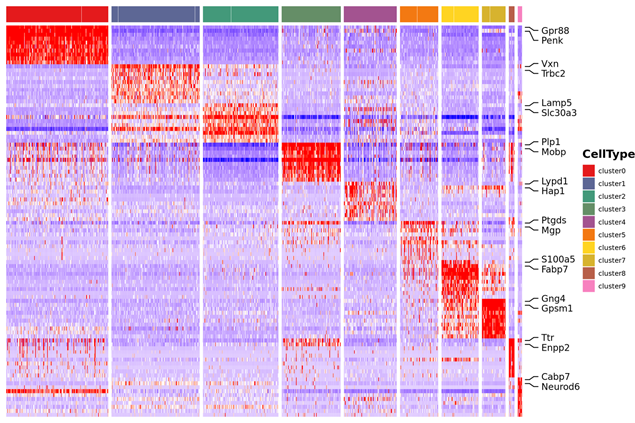
o Análisis de expresión diferencial entre clusters: identificación de genes marcadores
o Anotación funcional y enriquecimiento de genes marcadores.
Análisis intergrupal
o Recombinación de manchas de ambas muestras (p. ej., enferma y control) y reagrupación
o Identificación de genes marcadores para cada grupo.
o Anotación funcional y enriquecimiento de genes marcadores.
o Expresión diferencial de un mismo cluster entre grupos
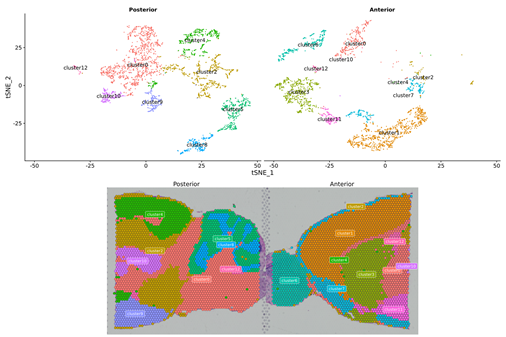
Análisis de muestra interna
Agrupación puntual
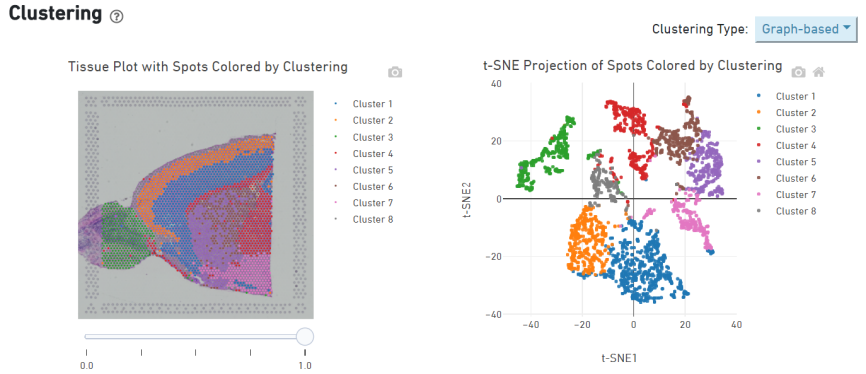
Identificación de genes marcadores y distribución espacial.
Análisis intergrupal
Combinación de datos de ambos grupos y reagrupación.
Genes marcadores de nuevos grupos.
Explore los avances facilitados por el servicio de transcriptómica espacial de BMKGene por 10X Visium en estas publicaciones destacadas:
Chen, D. y col.(2023) 'mthl1, un potencial homólogo de Drosophila de los GPCR de adhesión de mamíferos, participa en reacciones antitumorales a células oncogénicas inyectadas en moscas', Actas de la Academia Nacional de Ciencias de los Estados Unidos de América, 120 (30), pág.e2303462120.doi: /10.1073/pnas.2303462120
Chen, Y. et al.(2023) 'STEEL permite la delimitación de alta resolución de datos transcriptómicos espaciotemporales', Briefings in Bioinformatics, 24 (2), págs.doi: 10.1093/BIB/BBAD068.
Liu, C. y col.(2022) 'Un atlas espaciotemporal de organogénesis en el desarrollo de flores de orquídeas', Nucleic Acids Research, 50 (17), págs.doi: 10.1093/NAR/GKAC773.
Wang, J. y col.(2023) 'La integración de la transcriptómica espacial y la secuenciación de ARN de un solo núcleo revela las posibles estrategias terapéuticas para el leiomioma uterino', Revista Internacional de Ciencias Biológicas, 19 (8), págs.doi: 10.7150/IJBS.83510.