NGS-ARNm (referință)
Transcriptomul este legătura dintre informațiile genetice genomice și proteomul funcției biologice.Reglarea nivelului transcripțional este cel mai important și cel mai larg studiat mod de reglare al organismelor.Secvențierea transcriptomului poate secvenționa transcriptomul în orice moment sau în orice condiție, cu o rezoluție precisă la o singură nucleotidă. Poate reflecta dinamic nivelul transcripției genelor, poate identifica și cuantifica simultan transcriptele rare și normale și poate oferi informații structurale ale probă de transcrieri specifice.
În prezent, tehnologia de secvențiere a transcriptomului a fost utilizată pe scară largă în agronomie, medicină și alte domenii de cercetare, inclusiv reglementarea dezvoltării animalelor și plantelor, adaptarea mediului, interacțiunea imună, localizarea genelor, evoluția genetică a speciilor și detectarea bolilor genetice și a tumorilor.
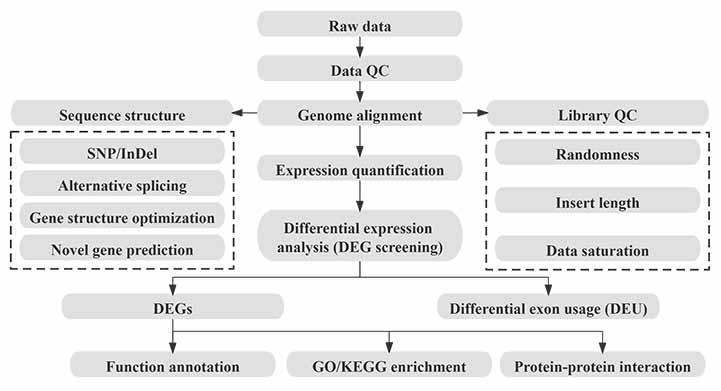
Bioinformatica
Fluxul de lucru în bioinformatică