NGS-mRNA (referens)
Transkriptom är länken mellan genomisk genetisk information och proteomet för biologisk funktion.Transkriptionsnivåreglering är det viktigaste och mest studerade regleringssättet för organismer.Transkriptomsekvensering kan sekvensera transkriptomet vid vilken tidpunkt som helst eller under alla förhållanden, med en upplösning som är exakt för en enskild nukleotid. Den kan dynamiskt återspegla nivån av gentranskription, samtidigt identifiera och kvantifiera sällsynta och normala transkript, och tillhandahålla den strukturella informationen om provspecifika avskrifter.
För närvarande har transkriptomsekvenseringsteknologi använts i stor utsträckning inom agronomi, medicin och andra forskningsområden, inklusive reglering av djur- och växtutveckling, miljöanpassning, immuninteraktion, genlokalisering, genetisk utveckling av arter och upptäckt av tumörer och genetiska sjukdomar.
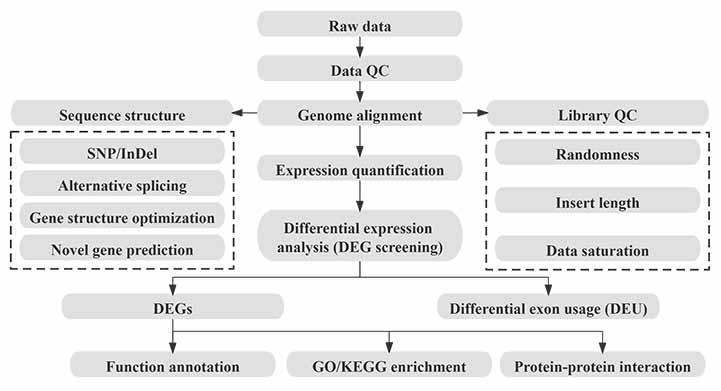
Bioinformatik
Arbetsflöde för bioinformatik