NGS-mRNA (referenční)
Transkriptom je spojením mezi genomickou genetickou informací a proteomem biologické funkce.Regulace na úrovni transkripce je nejdůležitějším a nejvíce studovaným způsobem regulace organismů.Sekvenování transkriptomu může sekvenovat transkriptom v libovolném okamžiku nebo za jakýchkoli podmínek s rozlišením přesným na jeden nukleotid. Dokáže dynamicky odrážet úroveň genové transkripce, současně identifikovat a kvantifikovat vzácné a normální transkripty a poskytnout strukturní informace ukázkové specifické přepisy.
V současné době je technologie transkriptomového sekvenování široce používána v agronomii, medicíně a dalších oblastech výzkumu, včetně regulace vývoje zvířat a rostlin, adaptace prostředí, imunitní interakce, lokalizace genů, genetické evoluce druhů a detekce nádorů a genetických chorob.
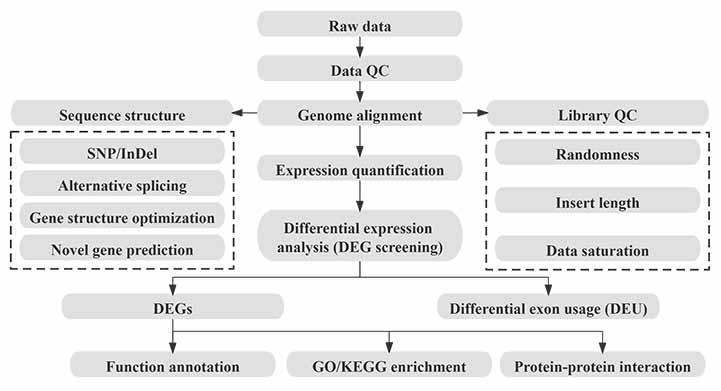
Bioinformatika
Pracovní tok bioinformatiky